peptides
spectra
0.007 | 0.028
0.000 | 0.000
0.694 | 0.720
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.263 | 0.278
0.000 | 0.005
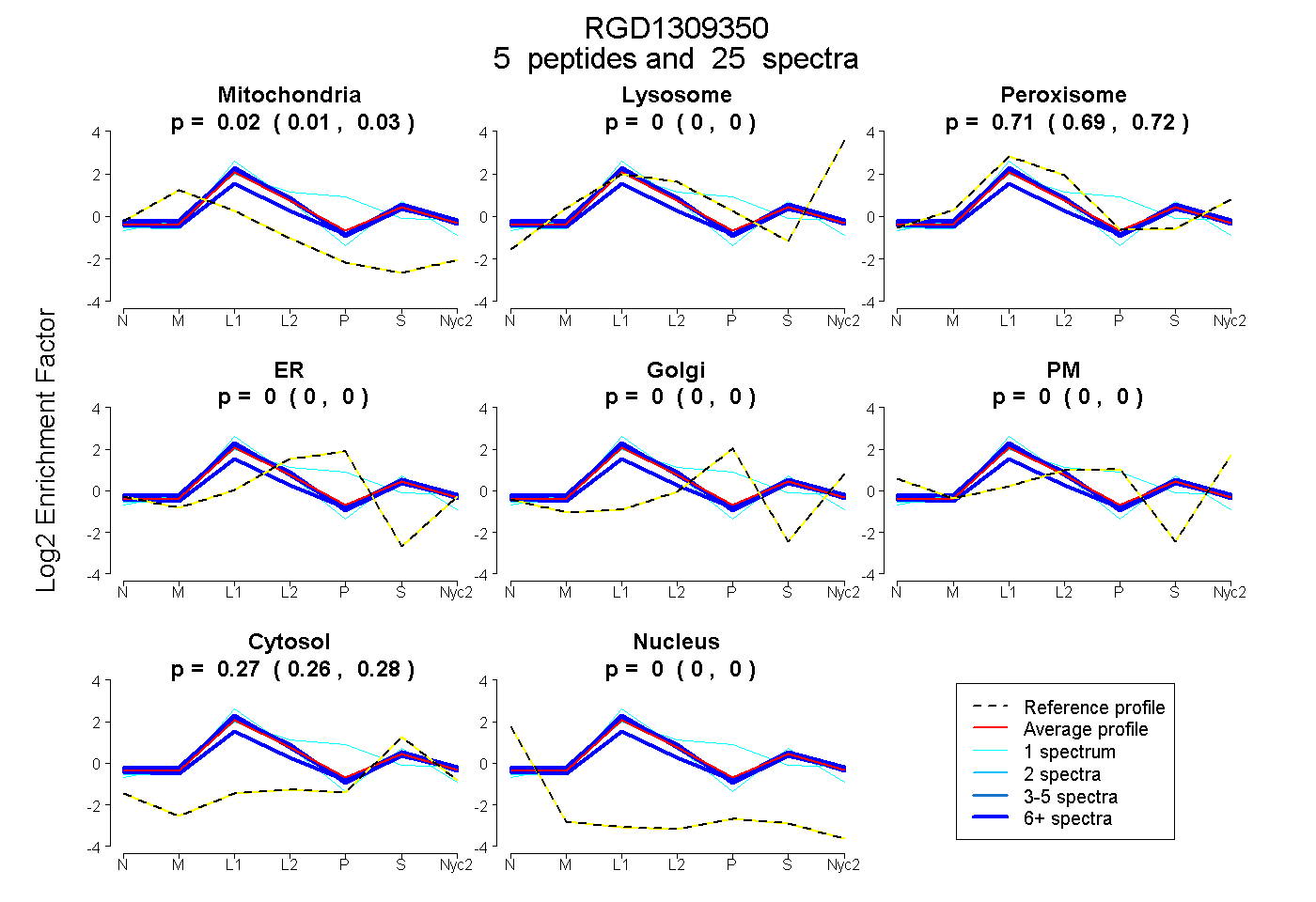
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.021 0.007 | 0.028 |
0.000 0.000 | 0.000 |
0.707 0.694 | 0.720 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.272 0.263 | 0.278 |
0.000 0.000 | 0.005 |
| 1 spectrum, LMTLQR | 0.000 | 0.000 | 0.609 | 0.259 | 0.000 | 0.000 | 0.132 | 0.000 | ||
| 8 spectra, LEAPSQQWMELR | 0.017 | 0.000 | 0.725 | 0.000 | 0.000 | 0.000 | 0.257 | 0.000 | ||
| 8 spectra, LSFDTER | 0.047 | 0.000 | 0.726 | 0.000 | 0.000 | 0.000 | 0.221 | 0.006 | ||
| 1 spectrum, CPGLLTQSQMKPGTYK | 0.038 | 0.000 | 0.687 | 0.000 | 0.000 | 0.000 | 0.275 | 0.000 | ||
| 7 spectra, TSYTNLDGR | 0.037 | 0.000 | 0.596 | 0.000 | 0.000 | 0.000 | 0.367 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
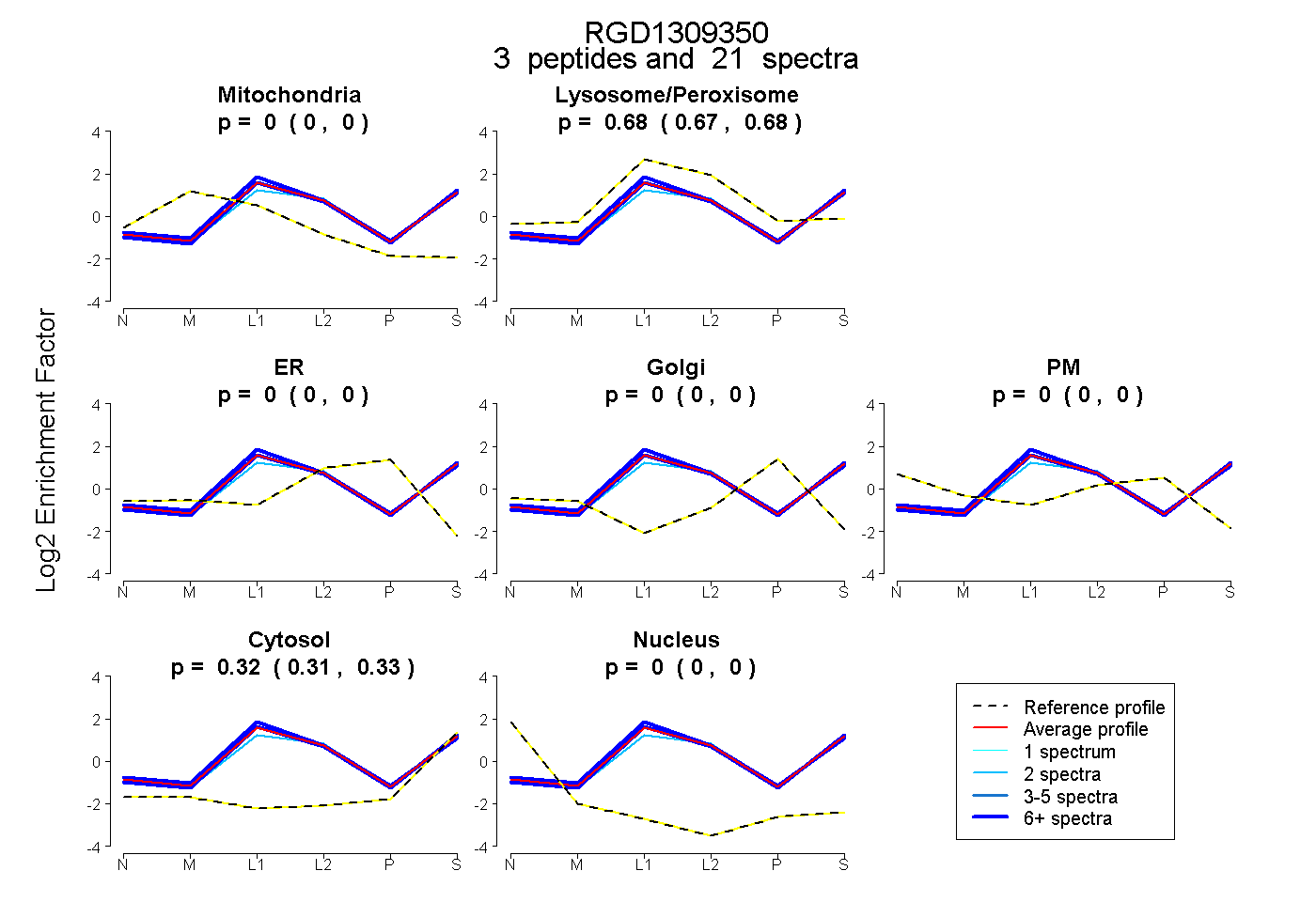 |
0.000 0.000 | 0.000 |
0.679 0.672 | 0.684 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.321 0.314 | 0.327 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
263 spectra |
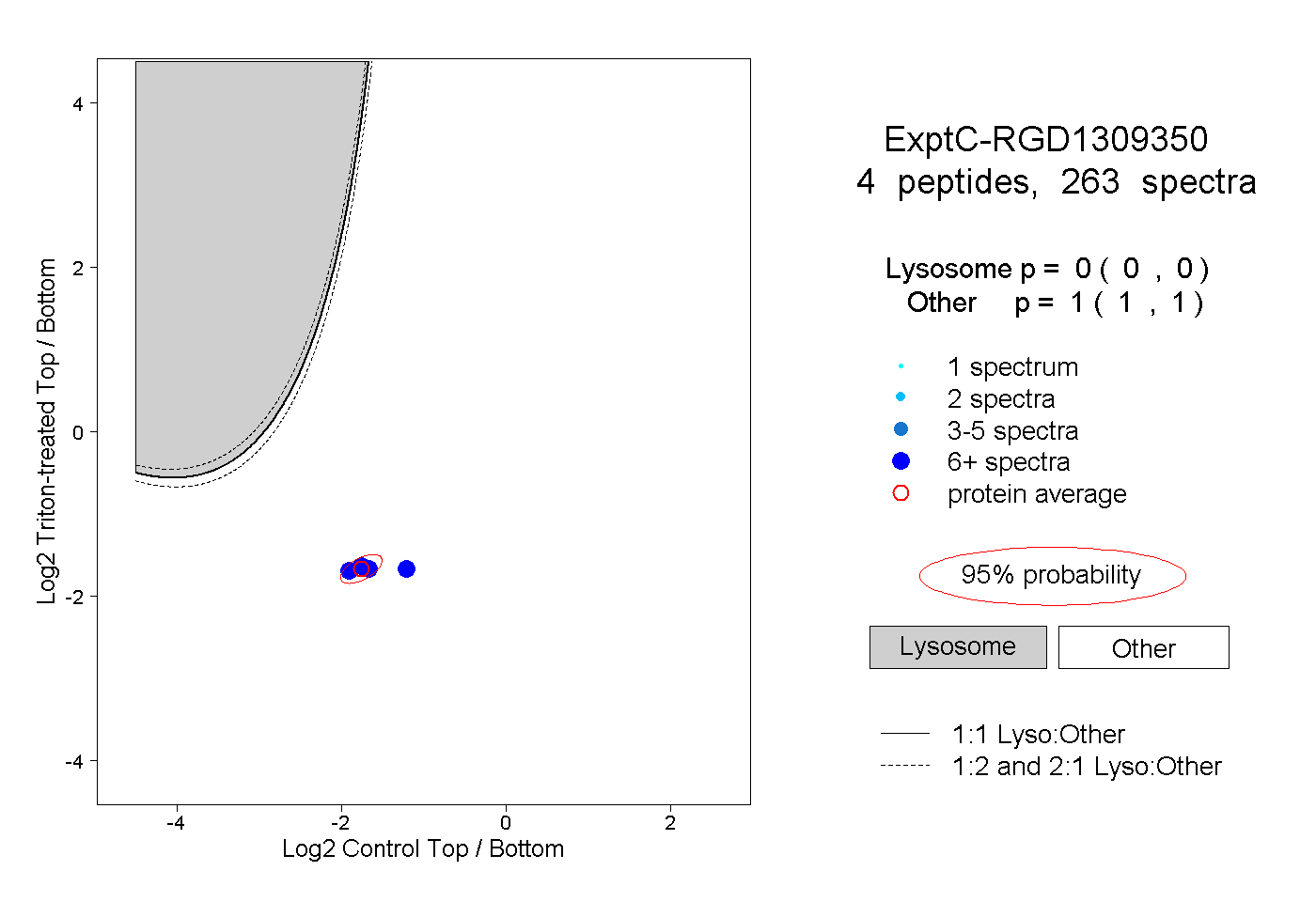 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
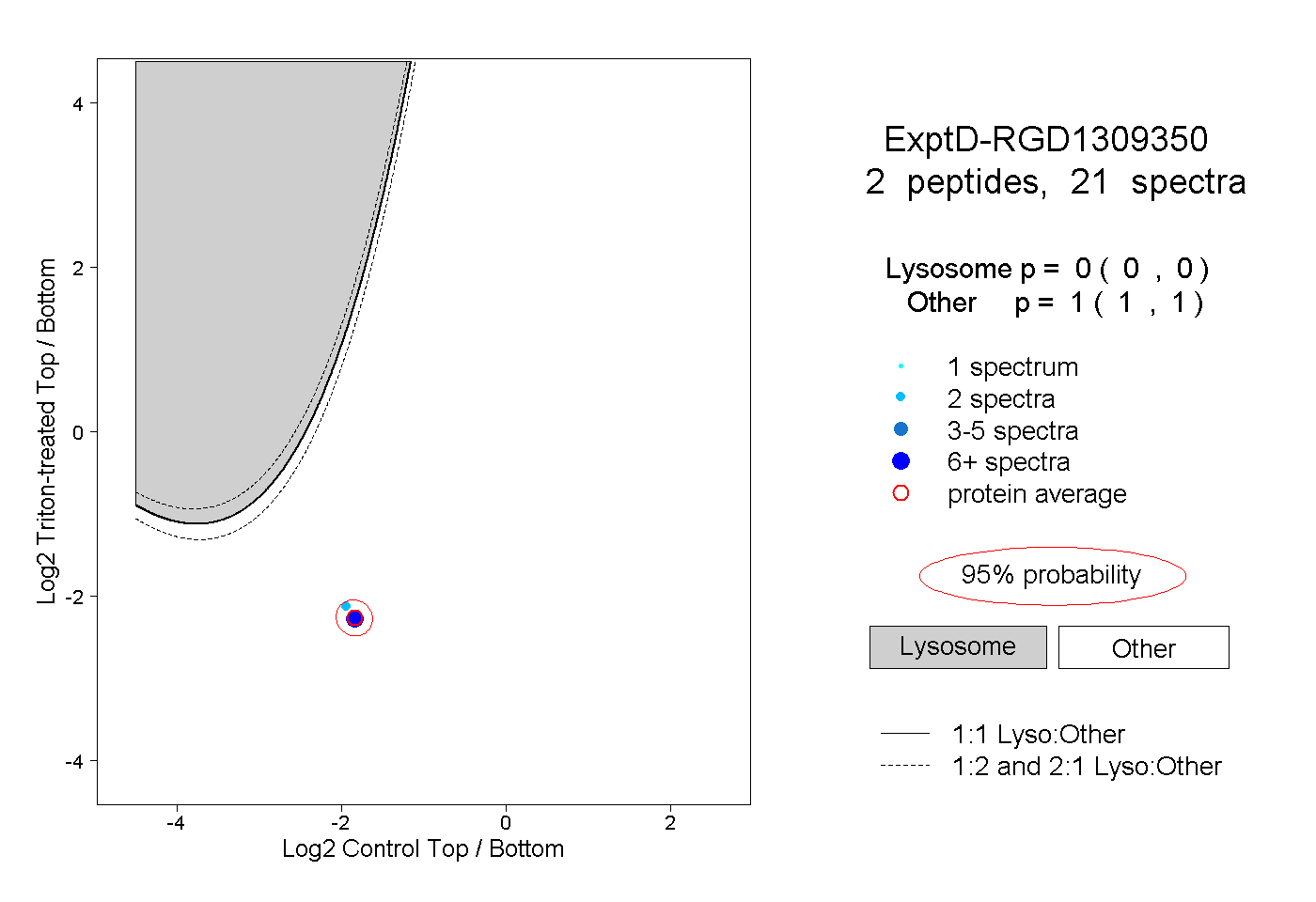 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |