peptides
spectra
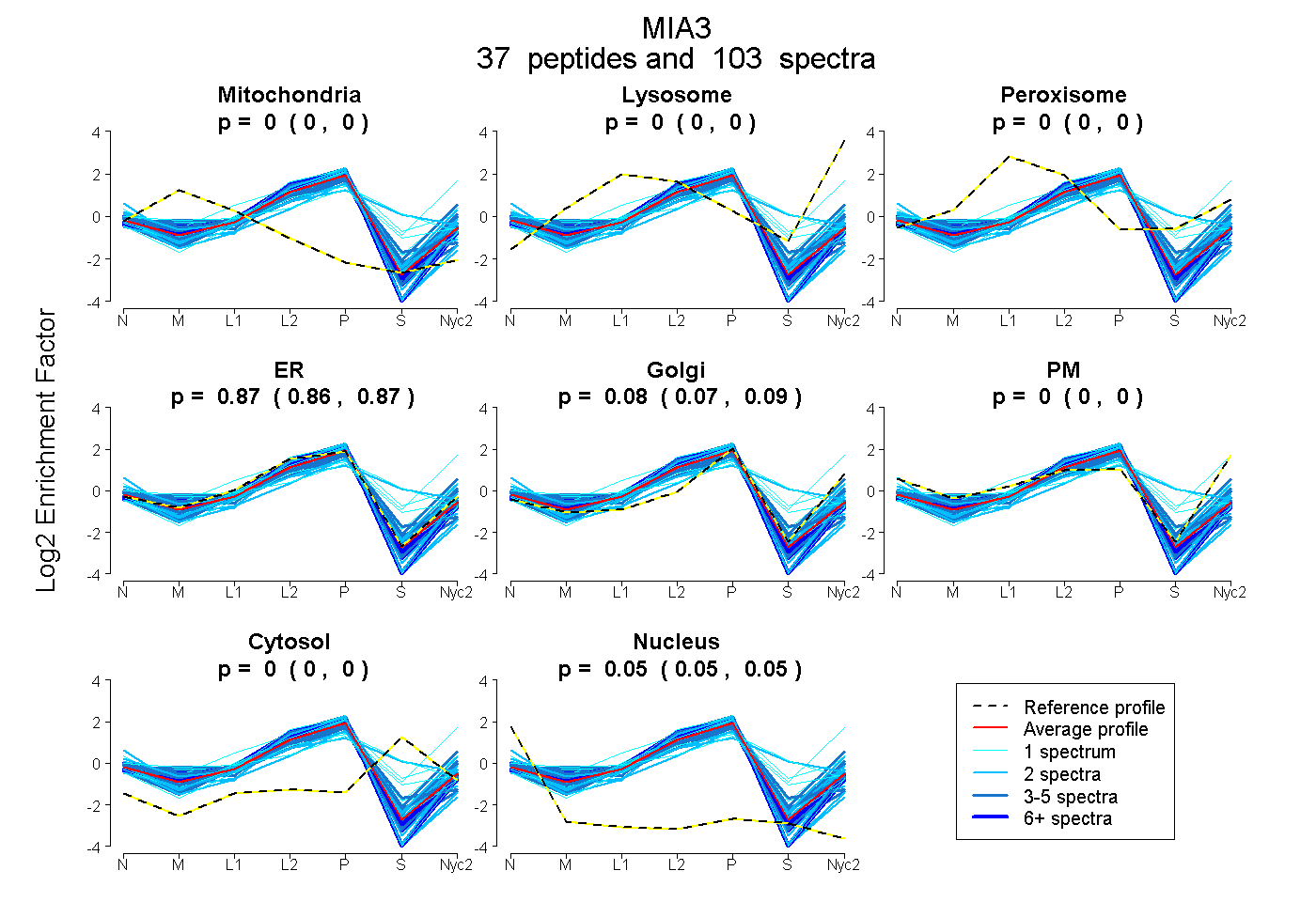
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.864 | 0.874
0.073 | 0.086
0.000 | 0.000
0.000 | 0.000
0.049 | 0.052
peptides
spectra
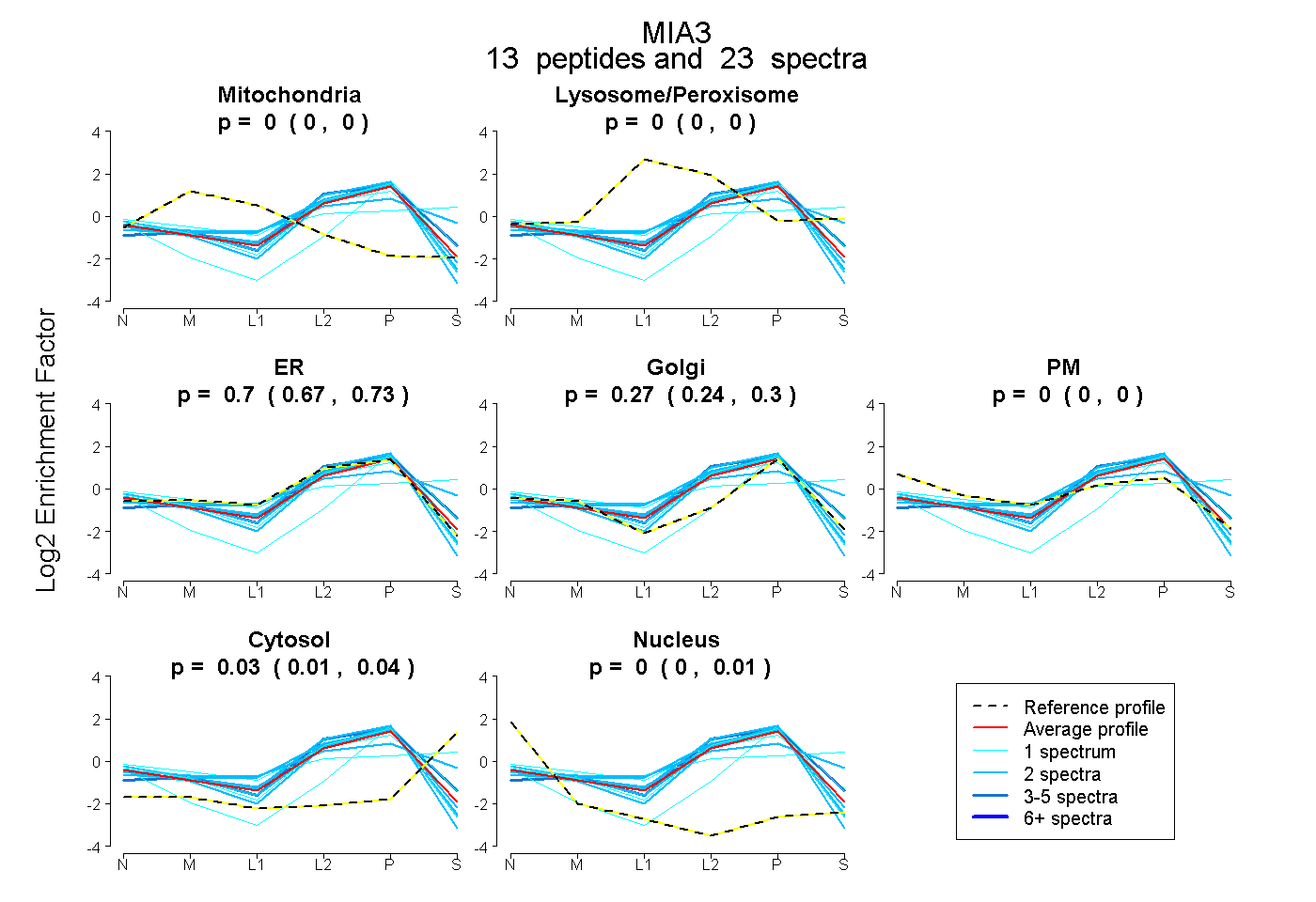
0.000 | 0.000
0.000 | 0.000
0.675 | 0.728
0.235 | 0.299
0.000 | 0.000
0.008 | 0.041
0.000 | 0.008
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
103 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.869 0.864 | 0.874 |
0.080 0.073 | 0.086 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.051 0.049 | 0.052 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.702 0.675 | 0.728 |
0.271 0.235 | 0.299 |
0.000 0.000 | 0.000 |
0.027 0.008 | 0.041 |
0.000 0.000 | 0.008 |
| 2 spectra, ATPEIPDIVLK | 0.000 | 0.000 | 0.824 | 0.176 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VVLAAEEVK | 0.000 | 0.000 | 0.925 | 0.075 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SHAELTEQIR | 0.000 | 0.280 | 0.239 | 0.310 | 0.000 | 0.171 | 0.000 | |||
| 1 spectrum, VQEENAR | 0.000 | 0.000 | 0.657 | 0.343 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CNLEDQIK | 0.000 | 0.127 | 0.431 | 0.249 | 0.164 | 0.029 | 0.000 | |||
| 4 spectra, ELEGLLQDMSIK | 0.000 | 0.000 | 0.826 | 0.081 | 0.000 | 0.092 | 0.000 | |||
| 2 spectra, AGLEDECK | 0.000 | 0.000 | 0.798 | 0.173 | 0.000 | 0.000 | 0.029 | |||
| 1 spectrum, DDQQSLYR | 0.000 | 0.000 | 0.860 | 0.126 | 0.000 | 0.014 | 0.000 | |||
| 1 spectrum, SEFGSLDR | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 | 0.089 | 0.012 | |||
| 1 spectrum, ENPSDLQK | 0.000 | 0.331 | 0.000 | 0.216 | 0.144 | 0.309 | 0.000 | |||
| 2 spectra, LSQEEYER | 0.000 | 0.000 | 0.601 | 0.399 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LSSYEQK | 0.000 | 0.000 | 0.710 | 0.281 | 0.000 | 0.000 | 0.010 | |||
| 2 spectra, VILGTLNLNTEK | 0.000 | 0.000 | 0.936 | 0.062 | 0.000 | 0.003 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
112 spectra |
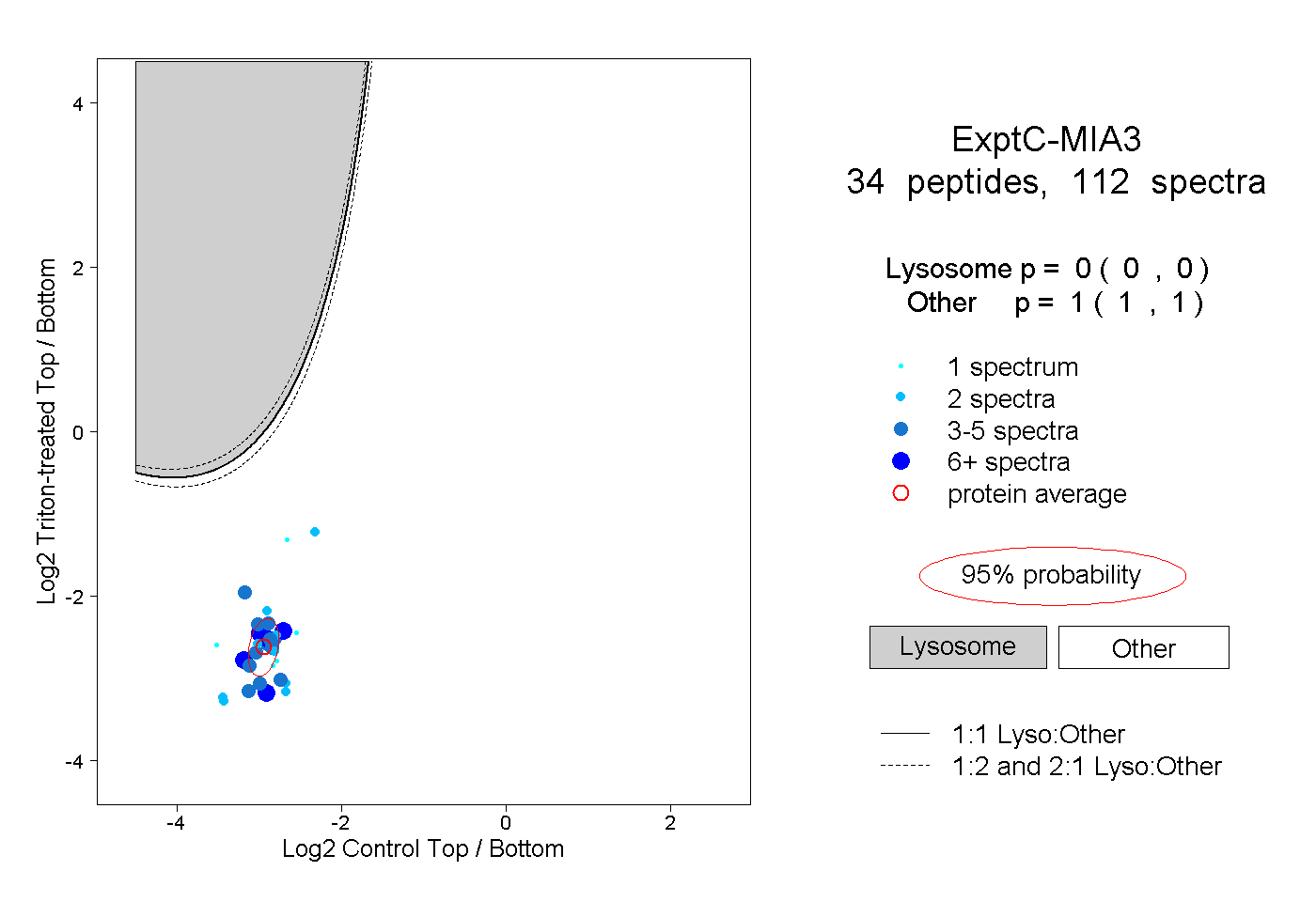 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
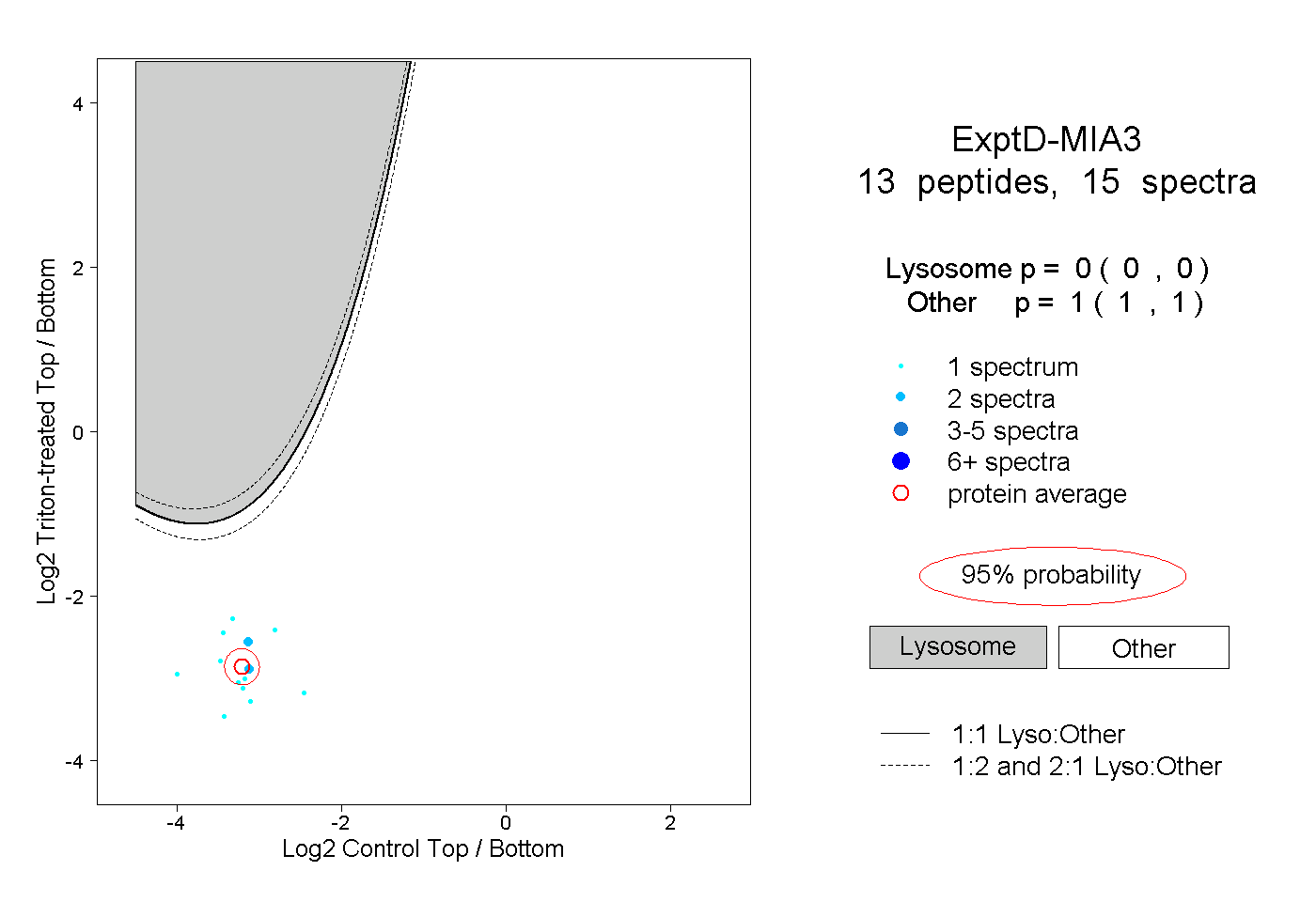 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |