peptides
spectra
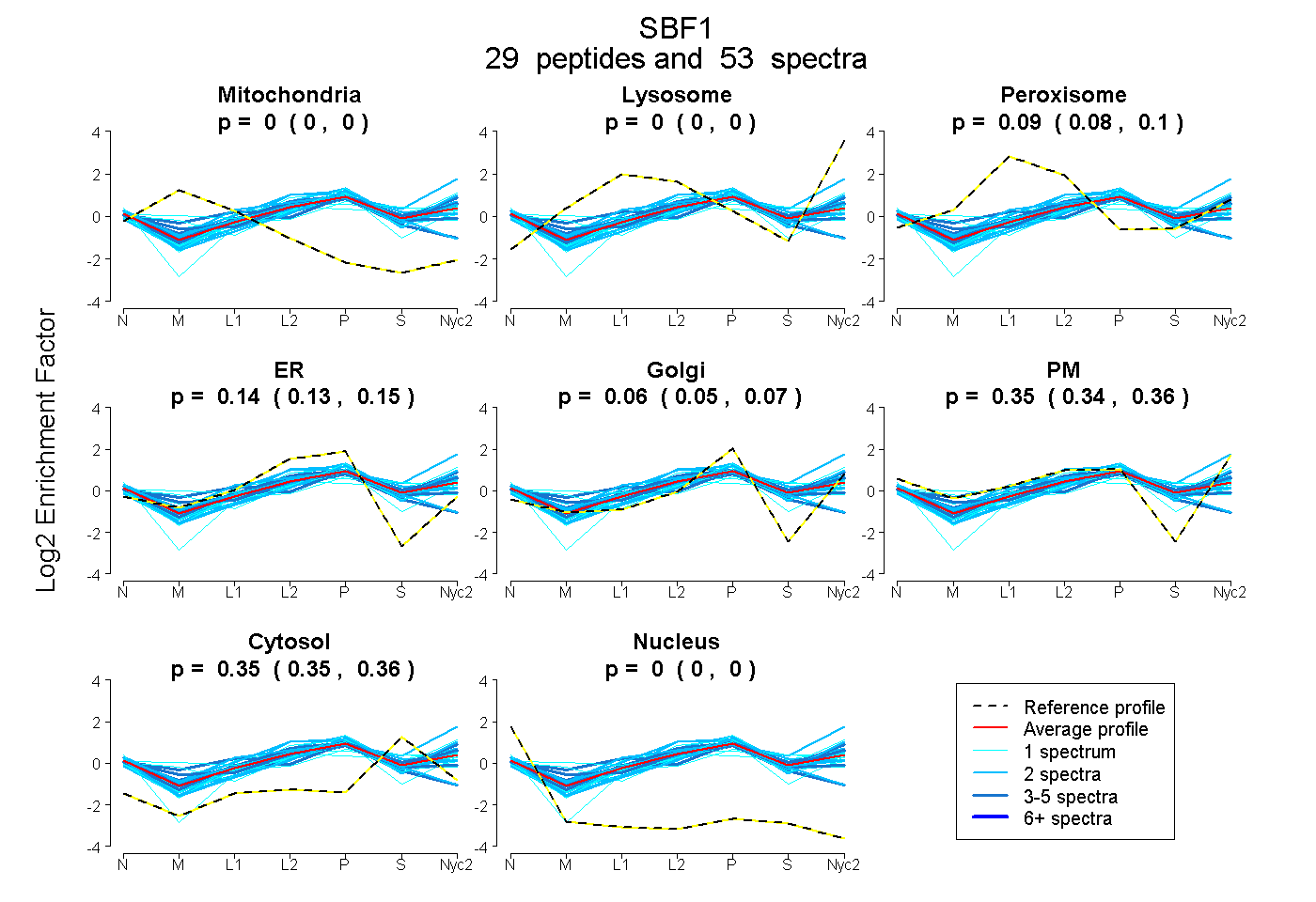
0.000 | 0.000
0.000 | 0.000
0.084 | 0.096
0.128 | 0.155
0.049 | 0.075
0.342 | 0.360
0.348 | 0.356
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
53 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.090 0.084 | 0.096 |
0.142 0.128 | 0.155 |
0.064 0.049 | 0.075 |
0.352 0.342 | 0.360 |
0.352 0.348 | 0.356 |
0.000 0.000 | 0.000 |
| 3 spectra, FPVVCWR | 0.119 | 0.000 | 0.152 | 0.445 | 0.000 | 0.000 | 0.285 | 0.000 | ||
| 2 spectra, SALDVASEQR | 0.000 | 0.219 | 0.000 | 0.000 | 0.169 | 0.229 | 0.383 | 0.000 | ||
| 2 spectra, LDHADVFR | 0.000 | 0.000 | 0.090 | 0.148 | 0.187 | 0.154 | 0.421 | 0.000 | ||
| 2 spectra, LETELGRPSER | 0.000 | 0.071 | 0.000 | 0.165 | 0.000 | 0.514 | 0.250 | 0.000 | ||
| 1 spectrum, LDEGTVQWIVDQAAAK | 0.000 | 0.000 | 0.054 | 0.139 | 0.000 | 0.380 | 0.428 | 0.000 | ||
| 2 spectra, WCLHIVR | 0.000 | 0.000 | 0.131 | 0.496 | 0.000 | 0.000 | 0.339 | 0.033 | ||
| 1 spectrum, SFPVAALTK | 0.000 | 0.000 | 0.066 | 0.371 | 0.000 | 0.185 | 0.378 | 0.000 | ||
| 1 spectrum, LLPAVLR | 0.000 | 0.080 | 0.000 | 0.091 | 0.008 | 0.493 | 0.329 | 0.000 | ||
| 1 spectrum, VTTLSNPLAASASR | 0.000 | 0.000 | 0.000 | 0.132 | 0.251 | 0.223 | 0.394 | 0.000 | ||
| 2 spectra, THRPFPR | 0.000 | 0.065 | 0.109 | 0.110 | 0.000 | 0.471 | 0.246 | 0.000 | ||
| 1 spectrum, QVIQTPLVDSLPVSR | 0.000 | 0.000 | 0.054 | 0.154 | 0.000 | 0.410 | 0.381 | 0.000 | ||
| 2 spectra, IHPEPVIR | 0.000 | 0.000 | 0.081 | 0.206 | 0.056 | 0.265 | 0.392 | 0.000 | ||
| 4 spectra, VVWPCYDSRPR | 0.000 | 0.000 | 0.082 | 0.297 | 0.000 | 0.258 | 0.363 | 0.000 | ||
| 3 spectra, SSGLGADVGSR | 0.000 | 0.000 | 0.138 | 0.000 | 0.248 | 0.262 | 0.352 | 0.000 | ||
| 2 spectra, VQRPGEASHLR | 0.000 | 0.000 | 0.189 | 0.122 | 0.045 | 0.382 | 0.262 | 0.000 | ||
| 1 spectrum, VLEGMAFAGFVSER | 0.071 | 0.000 | 0.223 | 0.027 | 0.427 | 0.146 | 0.106 | 0.000 | ||
| 2 spectra, GVVGLFK | 0.000 | 0.000 | 0.015 | 0.055 | 0.000 | 0.520 | 0.410 | 0.000 | ||
| 1 spectrum, IQSCISDA | 0.000 | 0.000 | 0.205 | 0.000 | 0.000 | 0.423 | 0.371 | 0.000 | ||
| 2 spectra, SCTFQLLK | 0.000 | 0.000 | 0.059 | 0.363 | 0.000 | 0.222 | 0.355 | 0.000 | ||
| 2 spectra, GLVEDDFLMK | 0.000 | 0.119 | 0.000 | 0.177 | 0.110 | 0.278 | 0.316 | 0.000 | ||
| 4 spectra, TFLLDSDYER | 0.000 | 0.008 | 0.085 | 0.040 | 0.000 | 0.545 | 0.321 | 0.000 | ||
| 1 spectrum, STDLFDELVAHEVAR | 0.000 | 0.000 | 0.128 | 0.073 | 0.108 | 0.372 | 0.320 | 0.000 | ||
| 1 spectrum, VLFLSR | 0.045 | 0.000 | 0.035 | 0.146 | 0.162 | 0.300 | 0.312 | 0.000 | ||
| 1 spectrum, HVQELAEQLYK | 0.000 | 0.000 | 0.047 | 0.016 | 0.036 | 0.533 | 0.368 | 0.000 | ||
| 2 spectra, AAFLGQR | 0.000 | 0.000 | 0.077 | 0.062 | 0.000 | 0.493 | 0.368 | 0.000 | ||
| 3 spectra, TLVLVSR | 0.000 | 0.000 | 0.162 | 0.087 | 0.118 | 0.347 | 0.288 | 0.000 | ||
| 2 spectra, WFVLDK | 0.000 | 0.000 | 0.000 | 0.191 | 0.214 | 0.201 | 0.394 | 0.000 | ||
| 1 spectrum, MAFDEEVGSDSAELFR | 0.000 | 0.000 | 0.220 | 0.109 | 0.000 | 0.270 | 0.401 | 0.000 | ||
| 1 spectrum, SLEDSEWLIQIHK | 0.000 | 0.000 | 0.128 | 0.000 | 0.200 | 0.205 | 0.467 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
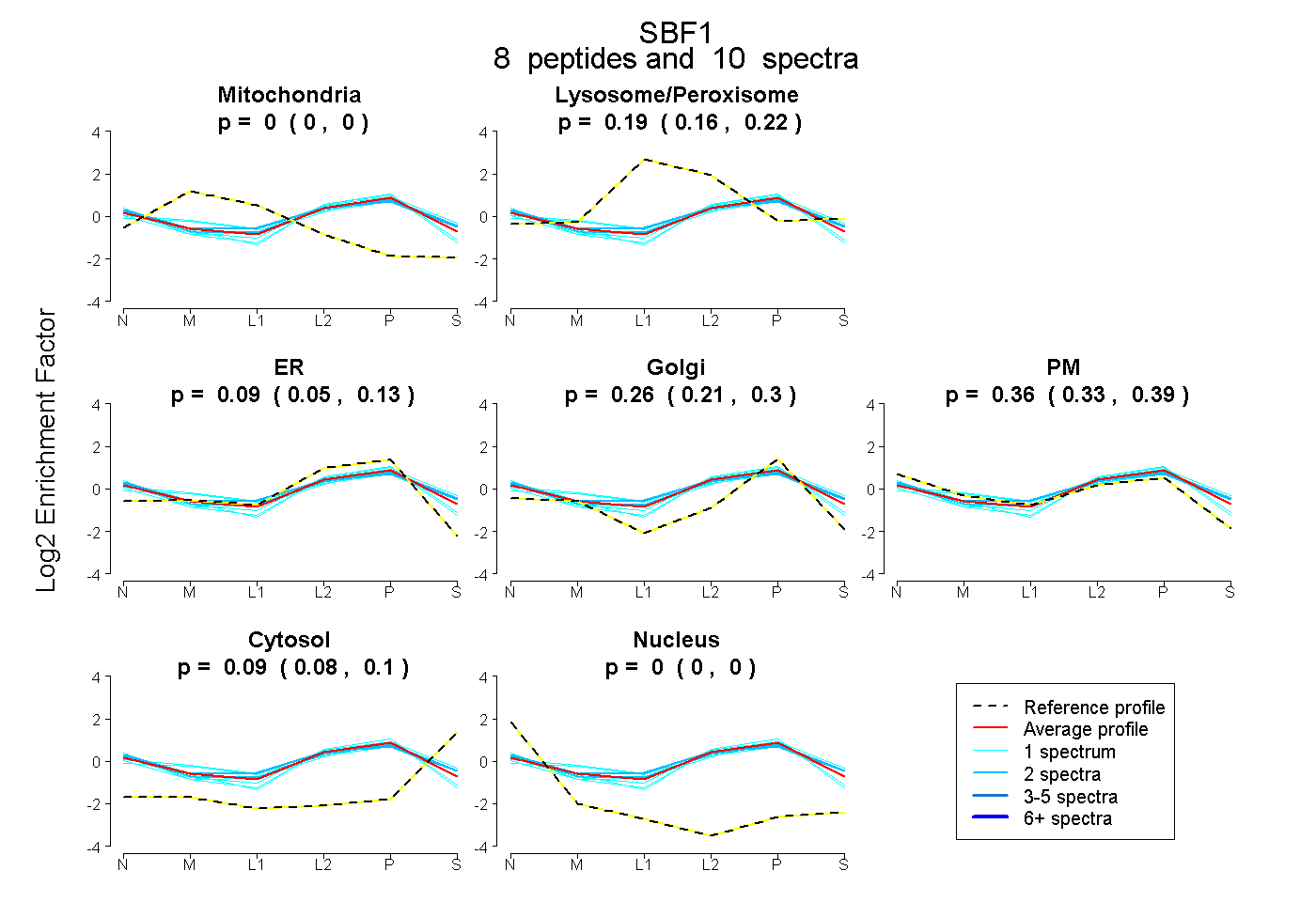 |
0.000 0.000 | 0.000 |
0.192 0.164 | 0.215 |
0.091 0.045 | 0.131 |
0.264 0.215 | 0.304 |
0.362 0.332 | 0.388 |
0.091 0.076 | 0.103 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
43 spectra |
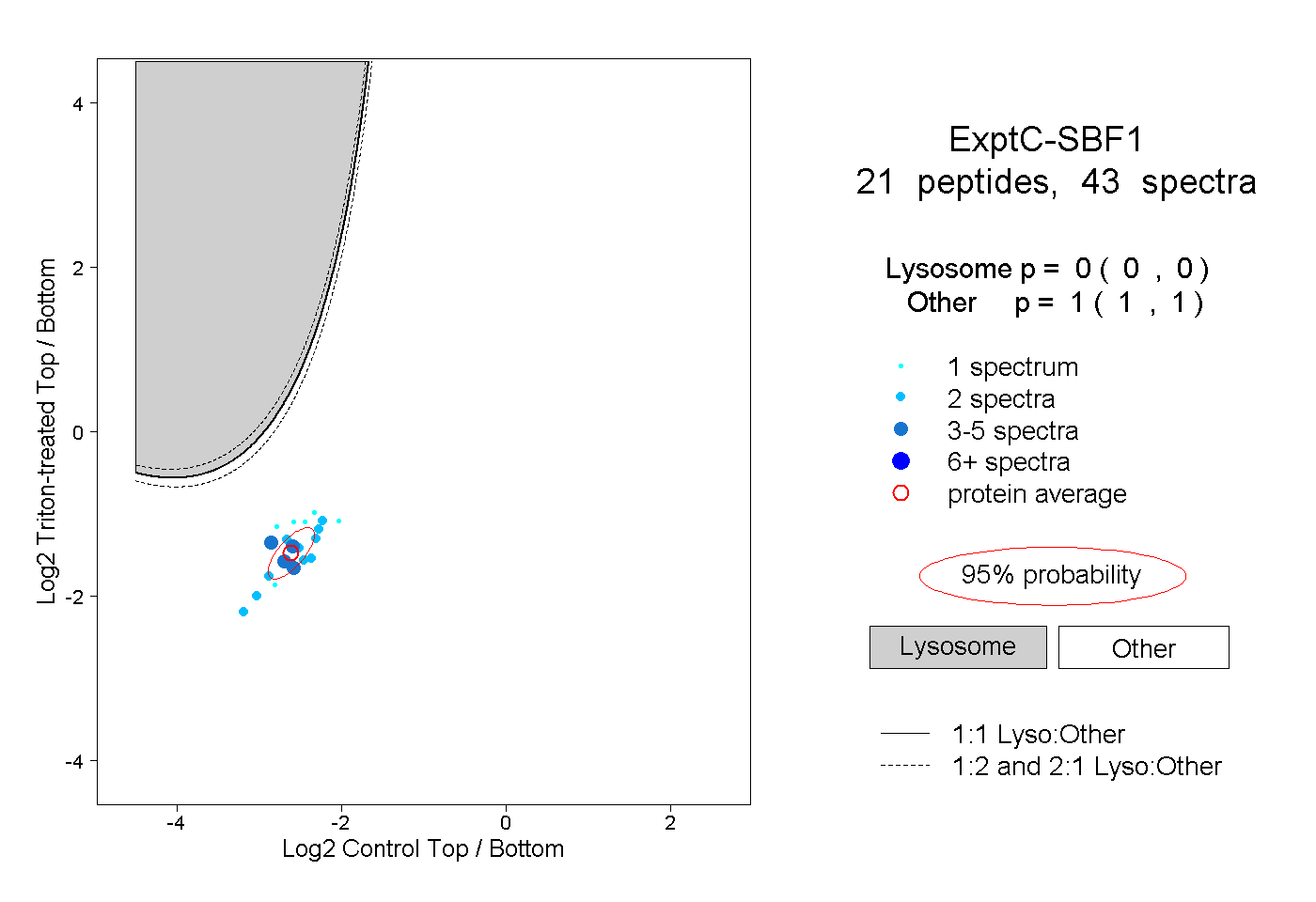 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
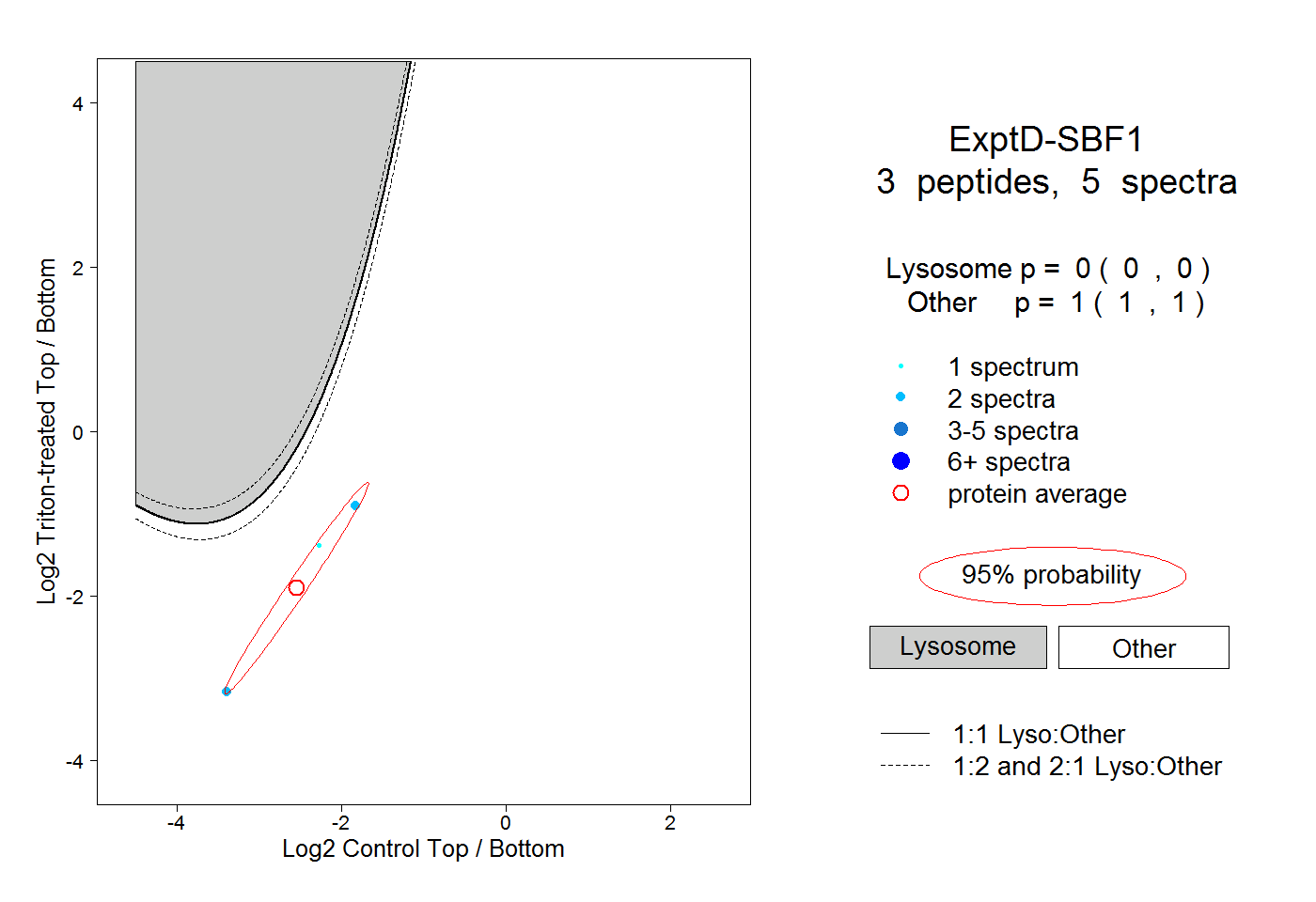 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |