peptides
spectra
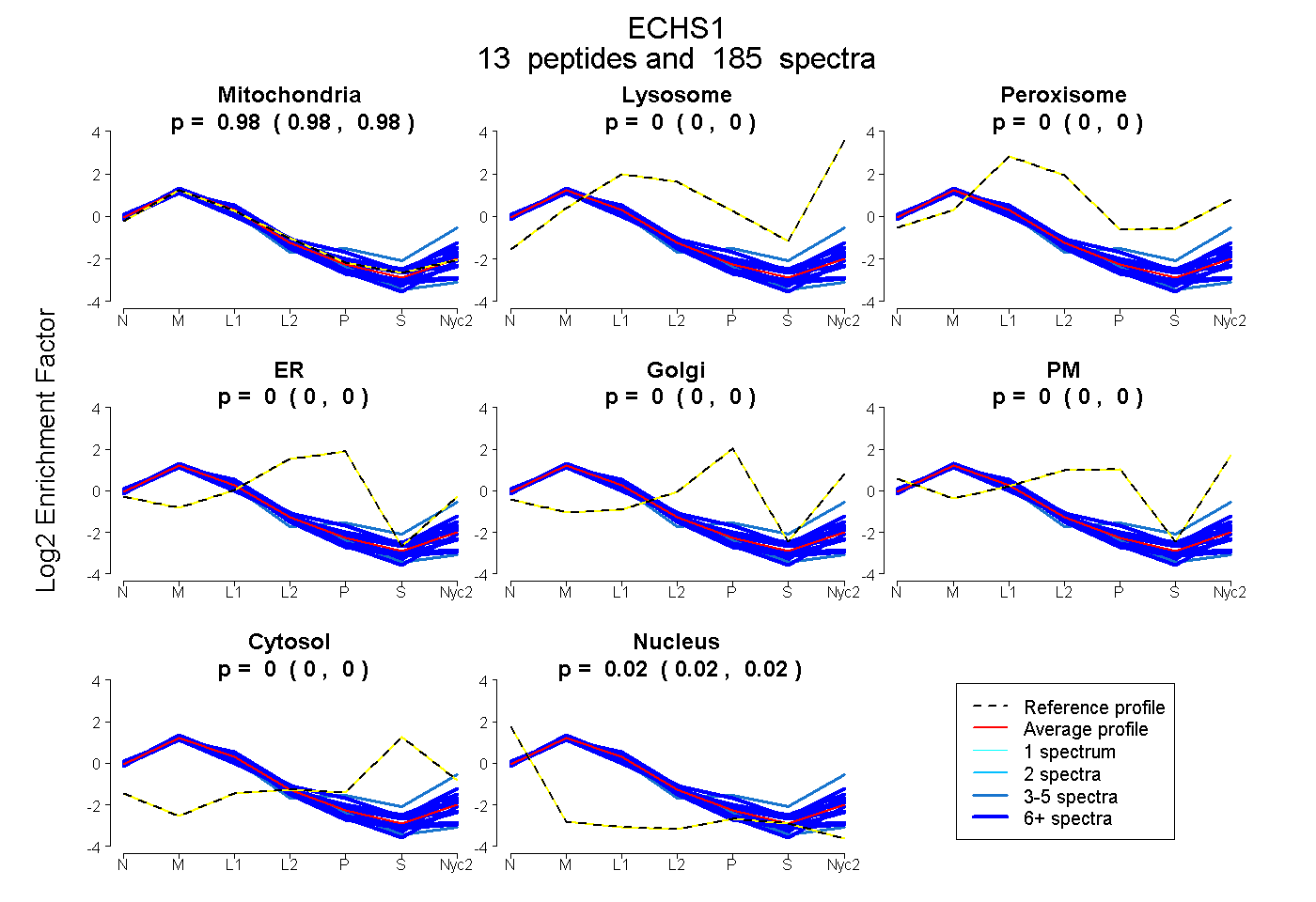
0.977 | 0.980
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.020 | 0.023
peptides
spectra
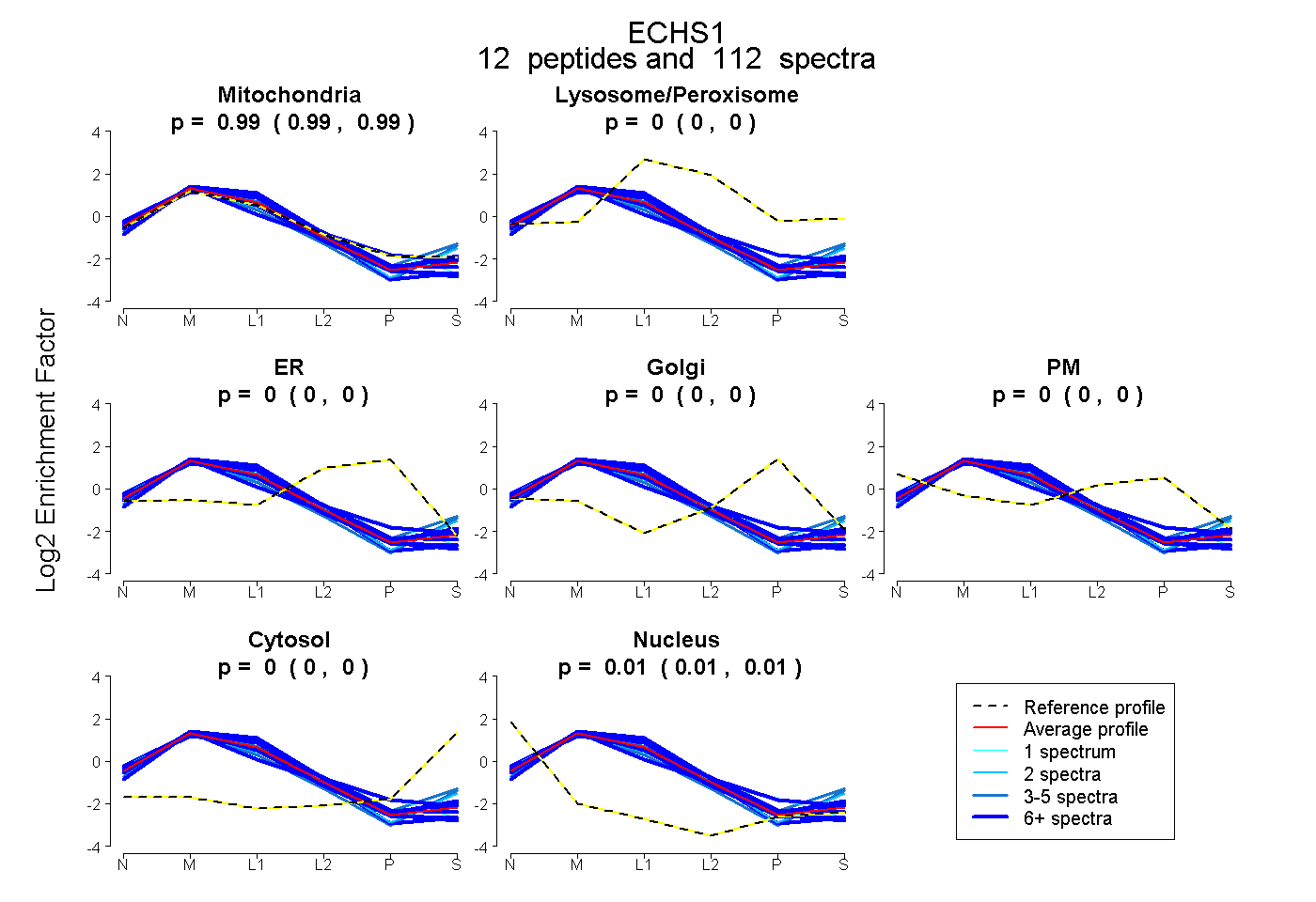
0.986 | 0.989
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.010 | 0.014
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
185 spectra |
 |
0.978 0.977 | 0.980 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.022 0.020 | 0.023 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
112 spectra |
 |
0.988 0.986 | 0.989 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.012 0.010 | 0.014 |
| 6 spectra, NSSVGLIQLNRPK | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | |||
| 7 spectra, QAGLVSK | 0.963 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 | |||
| 10 spectra, AFAAGADIK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 25 spectra, SLAMEMVLTGDR | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.048 | 0.008 | |||
| 3 spectra, IANNSK | 0.937 | 0.004 | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 | |||
| 6 spectra, TFQDCYSGK | 0.942 | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, IFPVETLVEEAIQCAEK | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.005 | |||
| 2 spectra, LFYSTFATDDR | 0.943 | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | 0.032 | |||
| 3 spectra, EGMSAFVEK | 0.903 | 0.000 | 0.000 | 0.000 | 0.000 | 0.097 | 0.001 | |||
| 19 spectra, FLSHWDHITR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, IIVAMAK | 0.983 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 | |||
| 1 spectrum, ISAQDAK | 0.963 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1028 spectra |
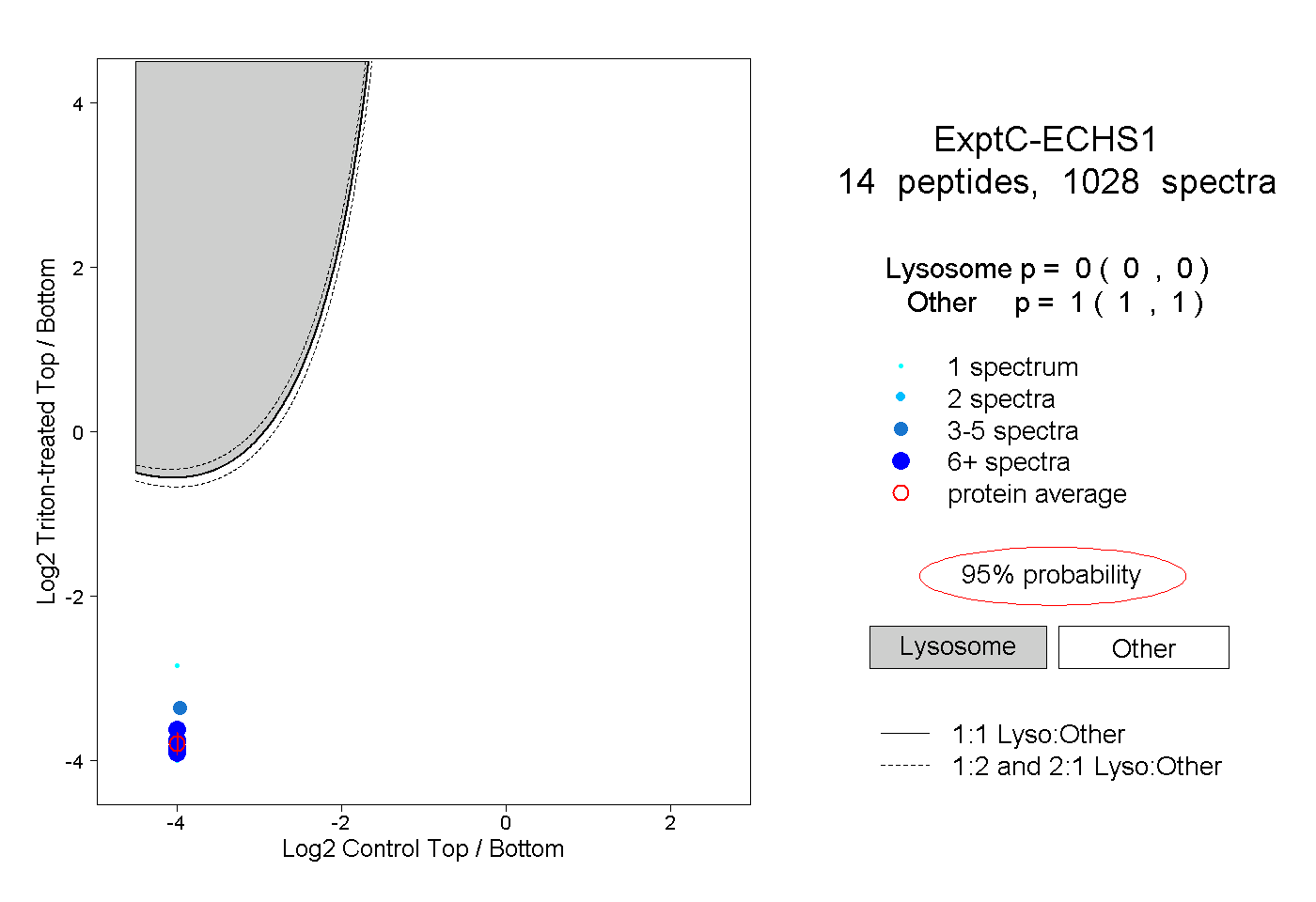 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
63 spectra |
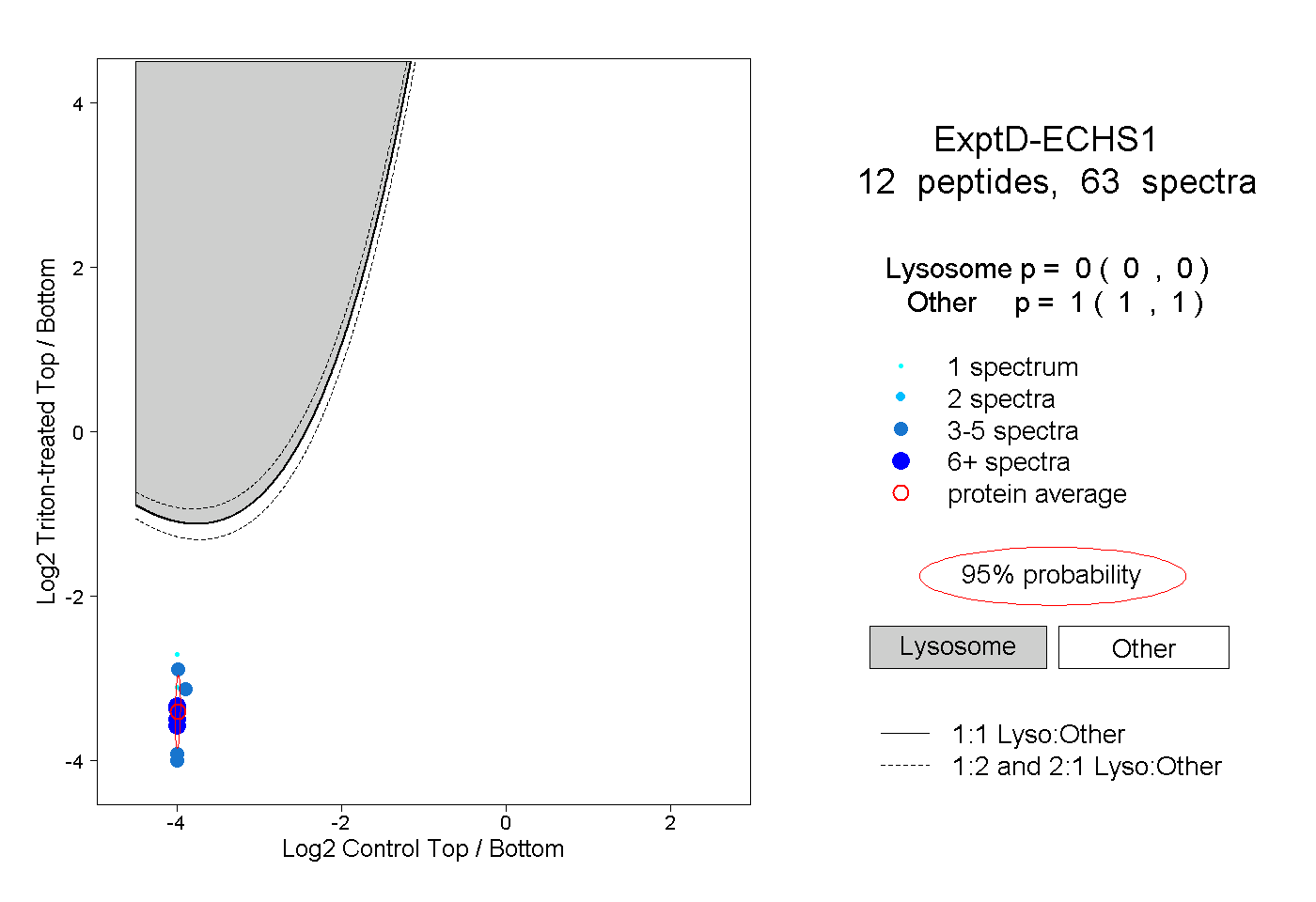 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |