peptides
spectra
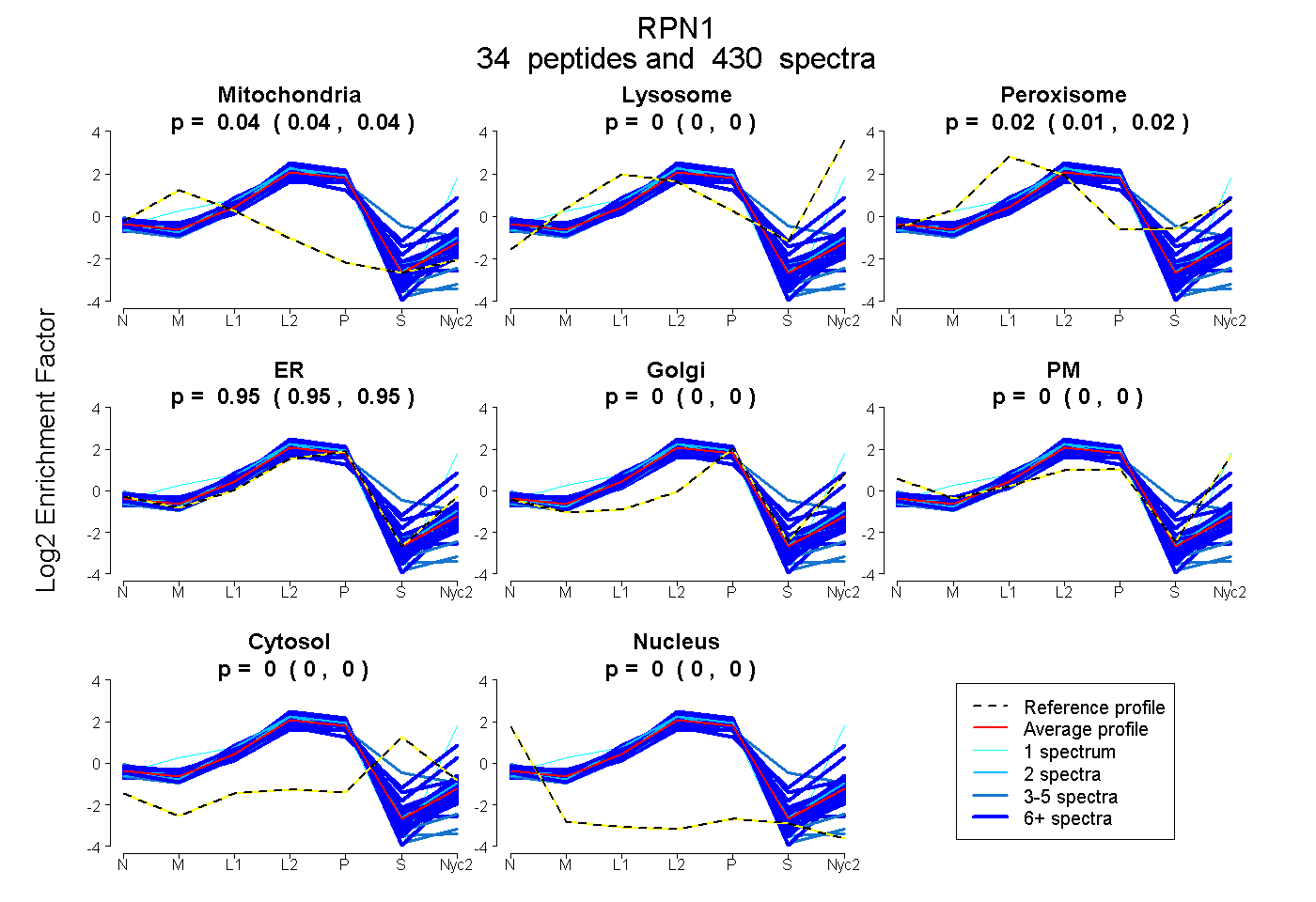
0.035 | 0.038
0.000 | 0.000
0.014 | 0.017
0.947 | 0.949
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
430 spectra |
 |
0.036 0.035 | 0.038 |
0.000 0.000 | 0.000 |
0.016 0.014 | 0.017 |
0.948 0.947 | 0.949 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 6 spectra, LPVALDPGSK | 0.120 | 0.000 | 0.000 | 0.870 | 0.000 | 0.000 | 0.000 | 0.010 | ||
| 3 spectra, QELVTK | 0.000 | 0.000 | 0.154 | 0.644 | 0.000 | 0.000 | 0.202 | 0.000 | ||
| 29 spectra, QPDSGISSIR | 0.000 | 0.000 | 0.040 | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, LDFSITK | 0.005 | 0.000 | 0.000 | 0.995 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, NVESHTK | 0.038 | 0.000 | 0.000 | 0.962 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, DIPAYSQDTFK | 0.064 | 0.000 | 0.014 | 0.922 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VACITEQVLTLVNK | 0.079 | 0.000 | 0.047 | 0.874 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, VHYENNSPFLTITSMTR | 0.000 | 0.198 | 0.136 | 0.487 | 0.000 | 0.110 | 0.070 | 0.000 | ||
| 16 spectra, VTAEVVLAHPGGGSTAR | 0.000 | 0.048 | 0.207 | 0.670 | 0.038 | 0.036 | 0.000 | 0.000 | ||
| 4 spectra, FVDHVFDEQVIDSLTVK | 0.079 | 0.000 | 0.000 | 0.865 | 0.000 | 0.000 | 0.000 | 0.056 | ||
| 6 spectra, TILPAAAQDVYYR | 0.009 | 0.000 | 0.004 | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, TEGSDLCDR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 19 spectra, DTYIENEK | 0.006 | 0.000 | 0.048 | 0.914 | 0.000 | 0.000 | 0.000 | 0.032 | ||
| 12 spectra, ASSFVLALEPELESR | 0.086 | 0.000 | 0.000 | 0.914 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 26 spectra, FPLFGGWK | 0.035 | 0.000 | 0.000 | 0.965 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 24 spectra, LAHLGVQVK | 0.089 | 0.000 | 0.047 | 0.865 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, TVDLSSHLAK | 0.000 | 0.000 | 0.140 | 0.776 | 0.000 | 0.000 | 0.085 | 0.000 | ||
| 8 spectra, LDAQVK | 0.000 | 0.000 | 0.031 | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, NIQVDSPYDISR | 0.000 | 0.000 | 0.023 | 0.977 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 22 spectra, LGNPSR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, NLVEQHIQDIVVHYTFNK | 0.085 | 0.000 | 0.000 | 0.915 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, QFVVFEGNHYFYSPYPTK | 0.000 | 0.000 | 0.079 | 0.921 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, VIEVSHWGNIAVEENVDLK | 0.000 | 0.000 | 0.070 | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, SLETEHK | 0.045 | 0.000 | 0.000 | 0.955 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, DPAAEAR | 0.010 | 0.000 | 0.000 | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 28 spectra, HTGAVLK | 0.000 | 0.000 | 0.024 | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, ISSGK | 0.000 | 0.237 | 0.000 | 0.441 | 0.000 | 0.322 | 0.000 | 0.000 | ||
| 13 spectra, SAVEAER | 0.000 | 0.000 | 0.048 | 0.952 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 24 spectra, VSEMQK | 0.042 | 0.000 | 0.000 | 0.938 | 0.000 | 0.000 | 0.000 | 0.020 | ||
| 3 spectra, IILPEGAK | 0.039 | 0.000 | 0.000 | 0.920 | 0.000 | 0.000 | 0.000 | 0.041 | ||
| 19 spectra, HFDETVNR | 0.071 | 0.000 | 0.048 | 0.881 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, DISTLNSGK | 0.085 | 0.000 | 0.026 | 0.867 | 0.000 | 0.000 | 0.022 | 0.000 | ||
| 14 spectra, SEDILDYGPFK | 0.066 | 0.000 | 0.000 | 0.934 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, AVTSEIAVLQSR | 0.040 | 0.000 | 0.032 | 0.901 | 0.000 | 0.000 | 0.000 | 0.026 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
182 spectra |
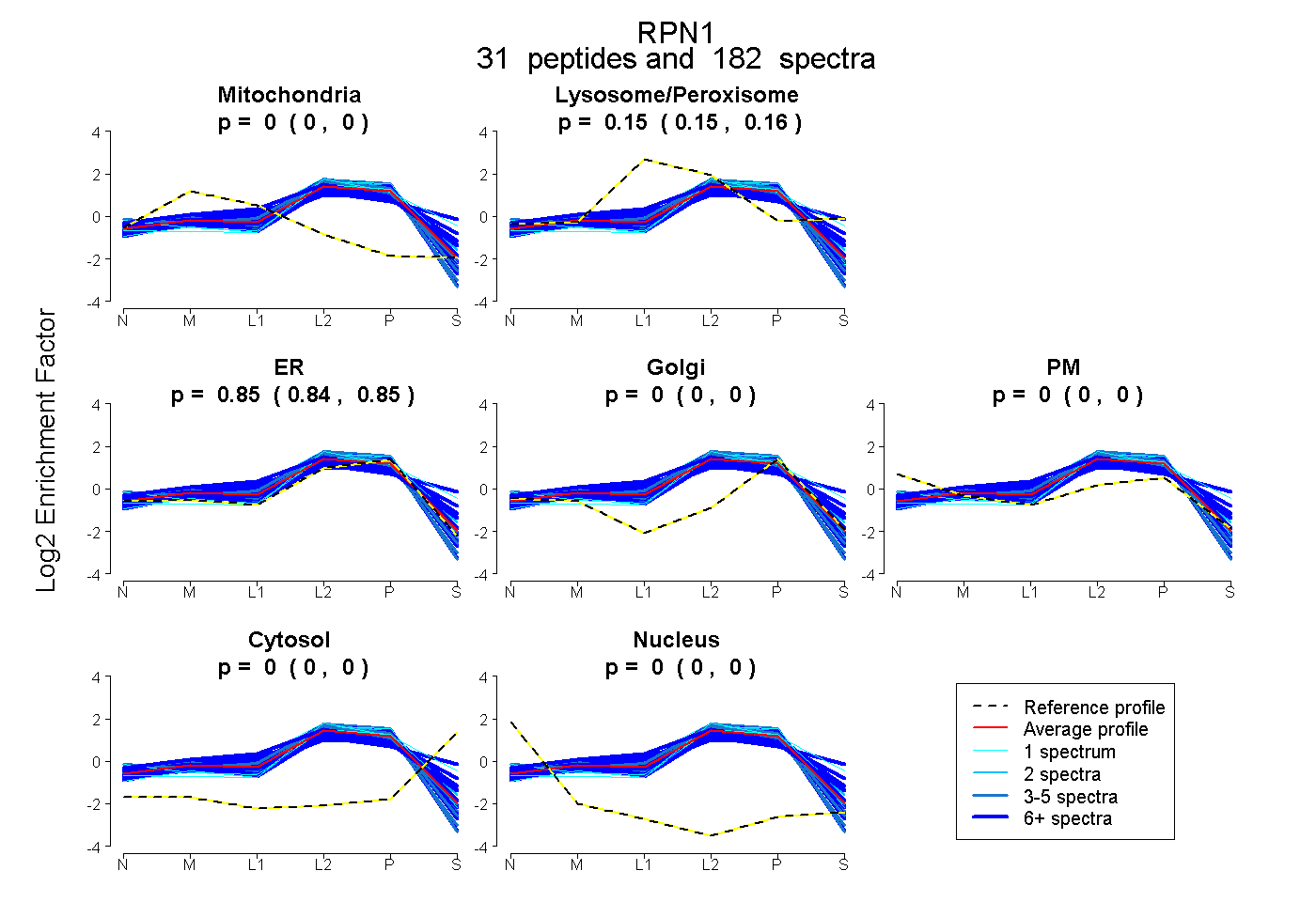 |
0.000 0.000 | 0.000 |
0.154 0.151 | 0.156 |
0.846 0.843 | 0.848 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
684 spectra |
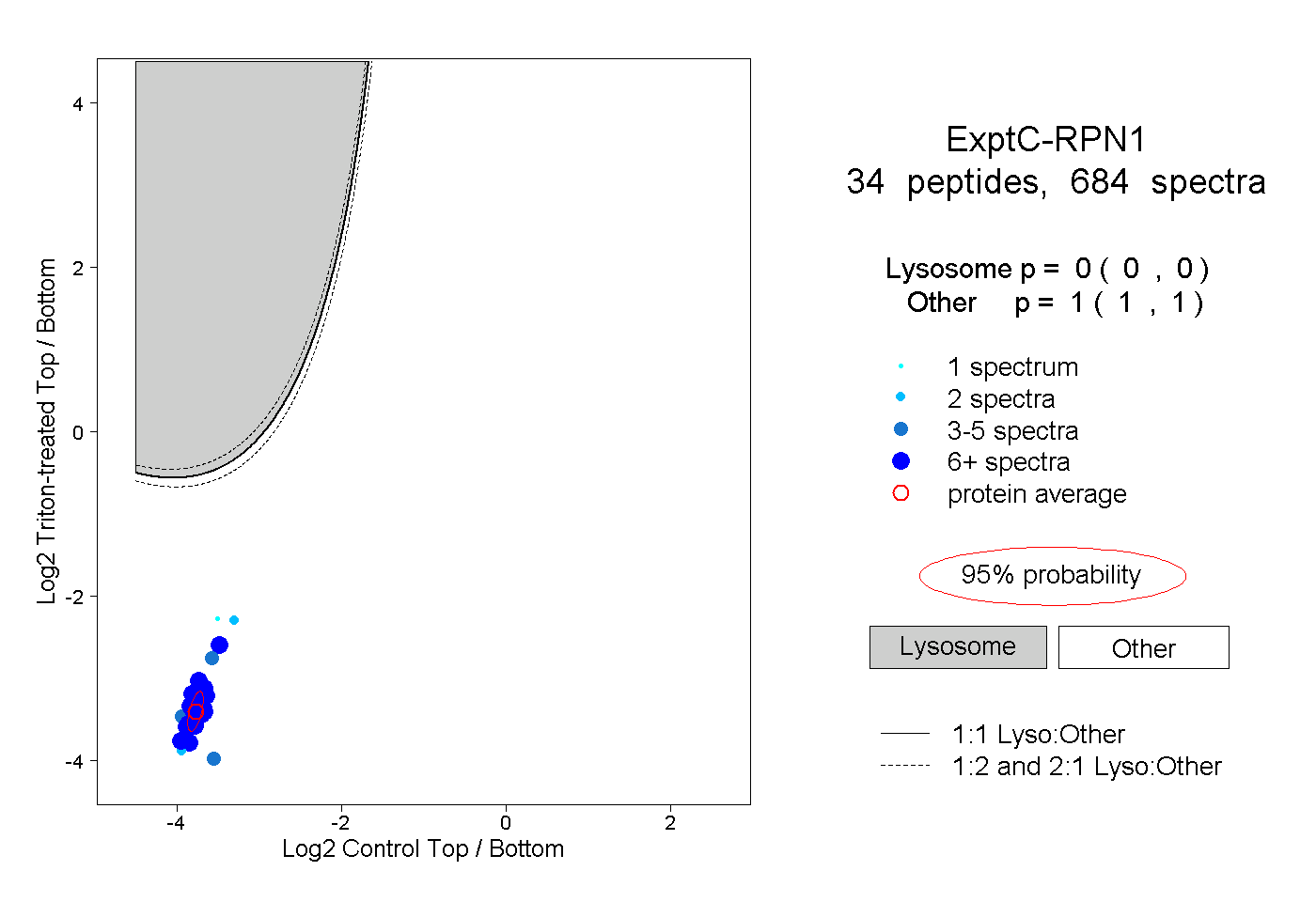 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
80 spectra |
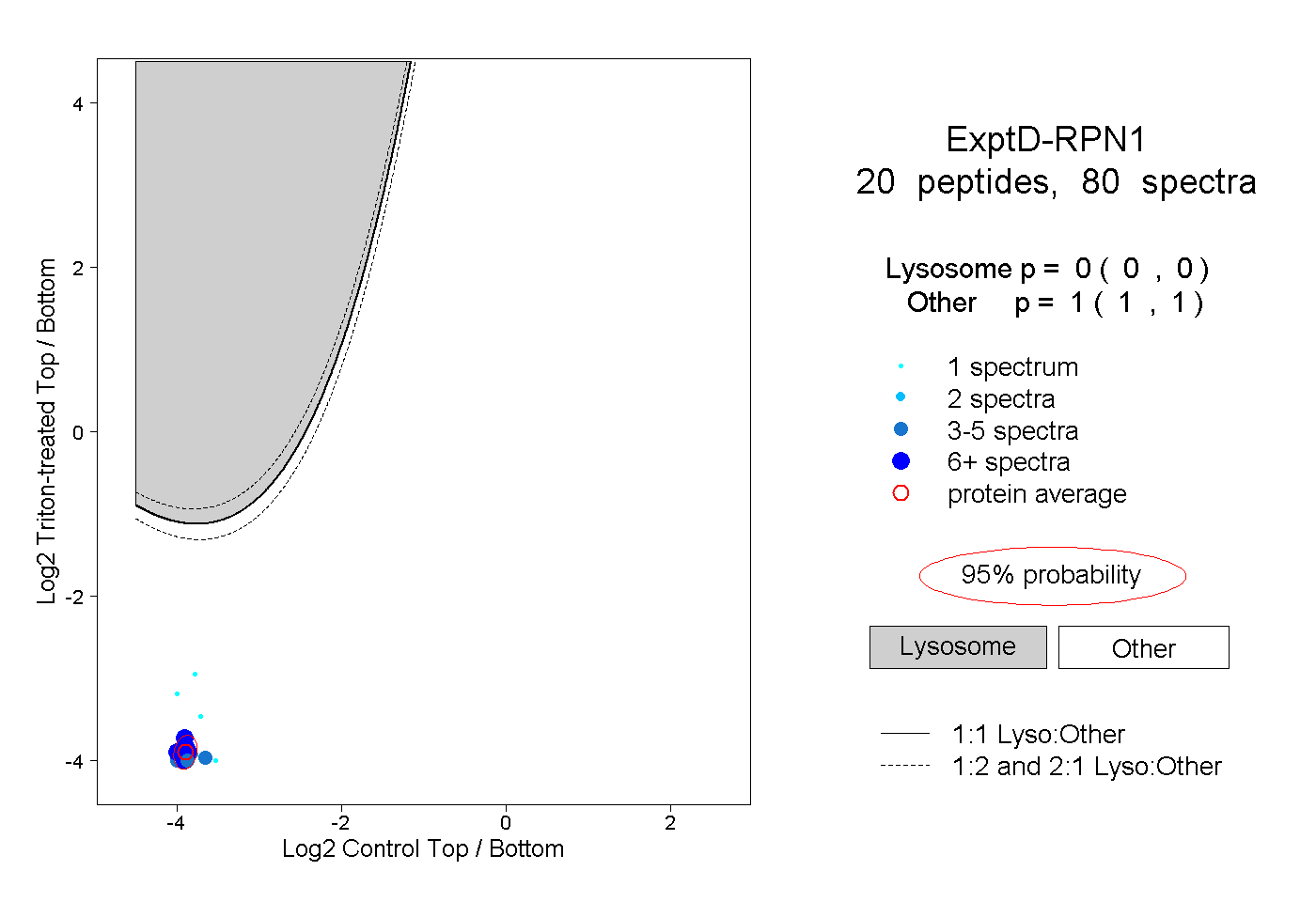 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |