peptides
spectra
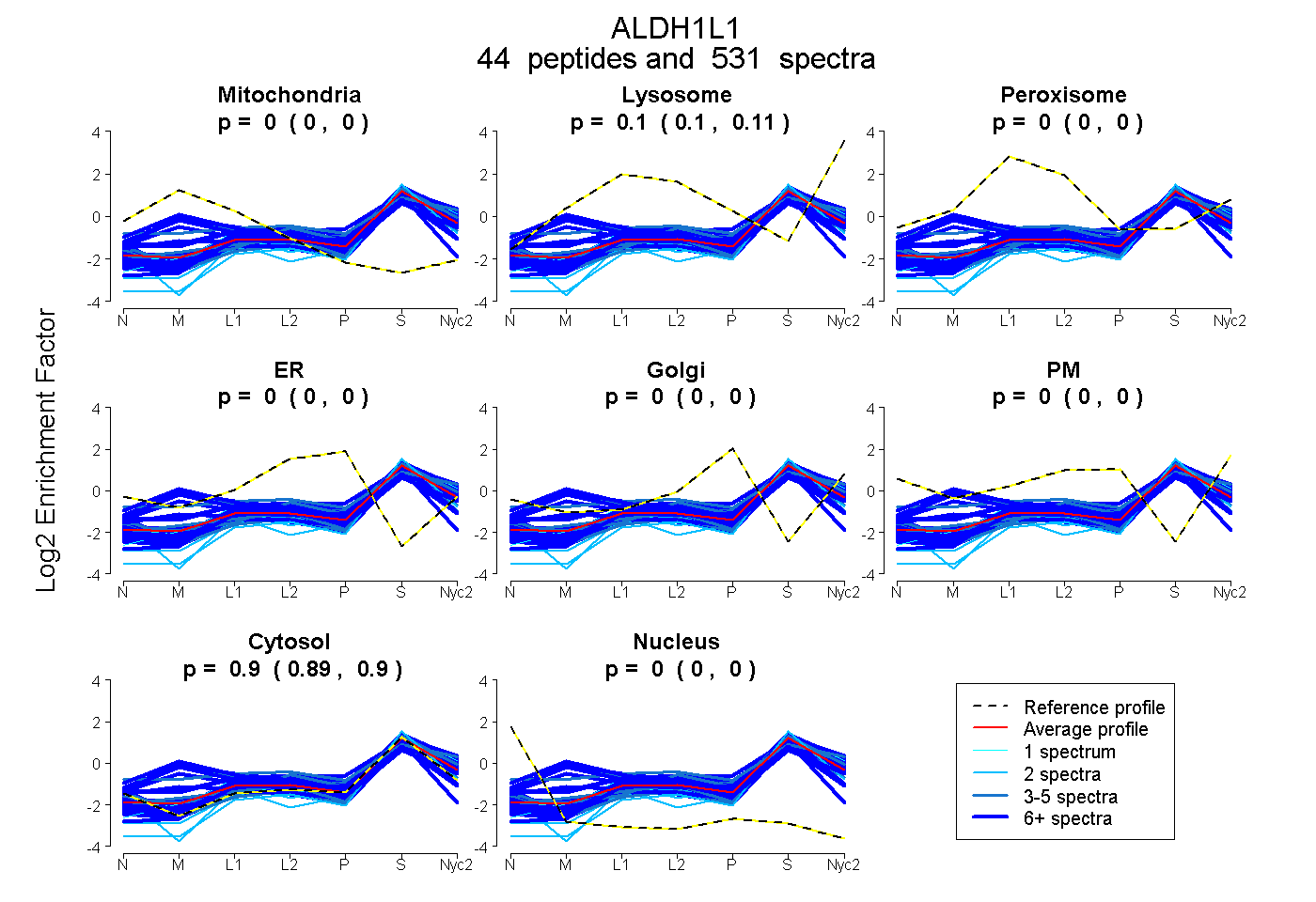
0.000 | 0.000
0.104 | 0.105
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.894 | 0.896
0.000 | 0.000
peptides
spectra
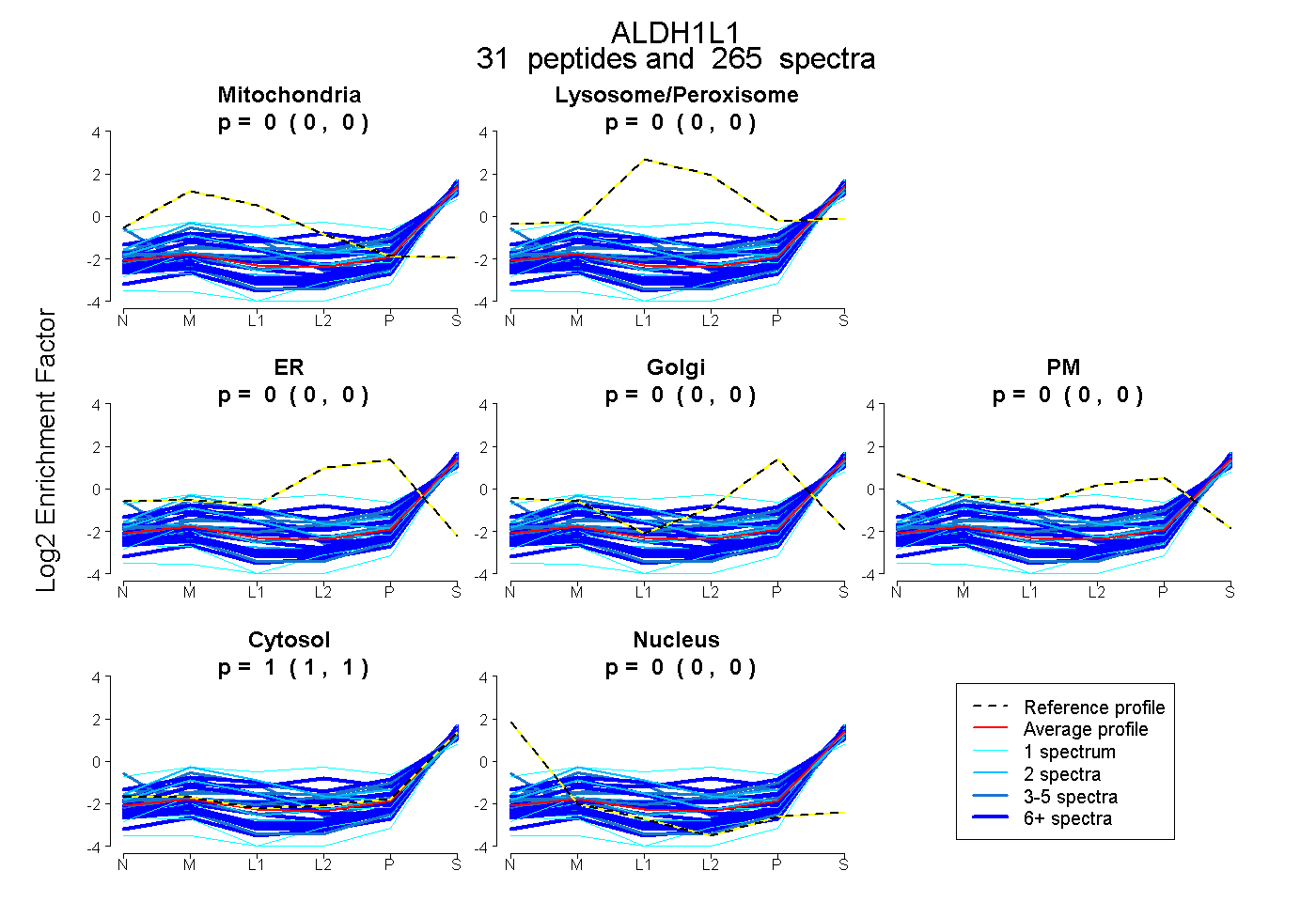
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
531 spectra |
 |
0.000 0.000 | 0.000 |
0.105 0.104 | 0.105 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.895 0.894 | 0.896 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
265 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 4 spectra, AVQMGMSSVFFNK | 0.000 | 0.108 | 0.000 | 0.000 | 0.000 | 0.892 | 0.000 | |||
| 3 spectra, CPQSEEGATYEGIQK | 0.000 | 0.199 | 0.000 | 0.008 | 0.000 | 0.793 | 0.000 | |||
| 9 spectra, EESFGPIMIISR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 19 spectra, FADGDVDAVLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, GQALPEVVAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 29 spectra, IQGATIPINQARPNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 36 spectra, LIAEGTAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 8 spectra, ILPNVPEVEDSTDFFK | 0.051 | 0.060 | 0.000 | 0.000 | 0.000 | 0.889 | 0.000 | |||
| 2 spectra, DGVPVFK | 0.000 | 0.072 | 0.000 | 0.029 | 0.000 | 0.898 | 0.000 | |||
| 13 spectra, GMVQAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LEAGTVFINTYNK | 0.003 | 0.354 | 0.000 | 0.039 | 0.122 | 0.482 | 0.000 | |||
| 6 spectra, GVVNILPGSGSLVGQR | 0.000 | 0.235 | 0.035 | 0.000 | 0.000 | 0.729 | 0.000 | |||
| 5 spectra, LSDHPDVR | 0.000 | 0.040 | 0.005 | 0.000 | 0.000 | 0.955 | 0.000 | |||
| 3 spectra, IGFTGSTEVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.762 | 0.238 | |||
| 4 spectra, FAELTLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, MMPASQFFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, FLFPEGIK | 0.216 | 0.000 | 0.000 | 0.000 | 0.000 | 0.784 | 0.000 | |||
| 28 spectra, GFIQLLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 15 spectra, SPLIIFADCDLNK | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.962 | 0.000 | |||
| 1 spectrum, ECEVLPDDTVSTLYNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 7 spectra, THVGMSIQTFR | 0.028 | 0.205 | 0.000 | 0.085 | 0.000 | 0.682 | 0.000 | |||
| 11 spectra, GENCIAAGR | 0.121 | 0.000 | 0.000 | 0.000 | 0.000 | 0.879 | 0.000 | |||
| 2 spectra, VSLELGGK | 0.221 | 0.086 | 0.000 | 0.000 | 0.000 | 0.692 | 0.000 | |||
| 1 spectrum, GSASSDLELTEAELATAEAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, ADPLGLEAEK | 0.000 | 0.000 | 0.065 | 0.000 | 0.000 | 0.935 | 0.000 | |||
| 5 spectra, TDVAAPFGGFK | 0.000 | 0.000 | 0.111 | 0.000 | 0.000 | 0.889 | 0.000 | |||
| 2 spectra, GASAINWTLIHGDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 15 spectra, INWDQPAEAIHNWIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 20 spectra, AGLILFGNDDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, YFAGWCDK | 0.135 | 0.000 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | |||
| 6 spectra, ANATEFGLASGVFTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
567 spectra |
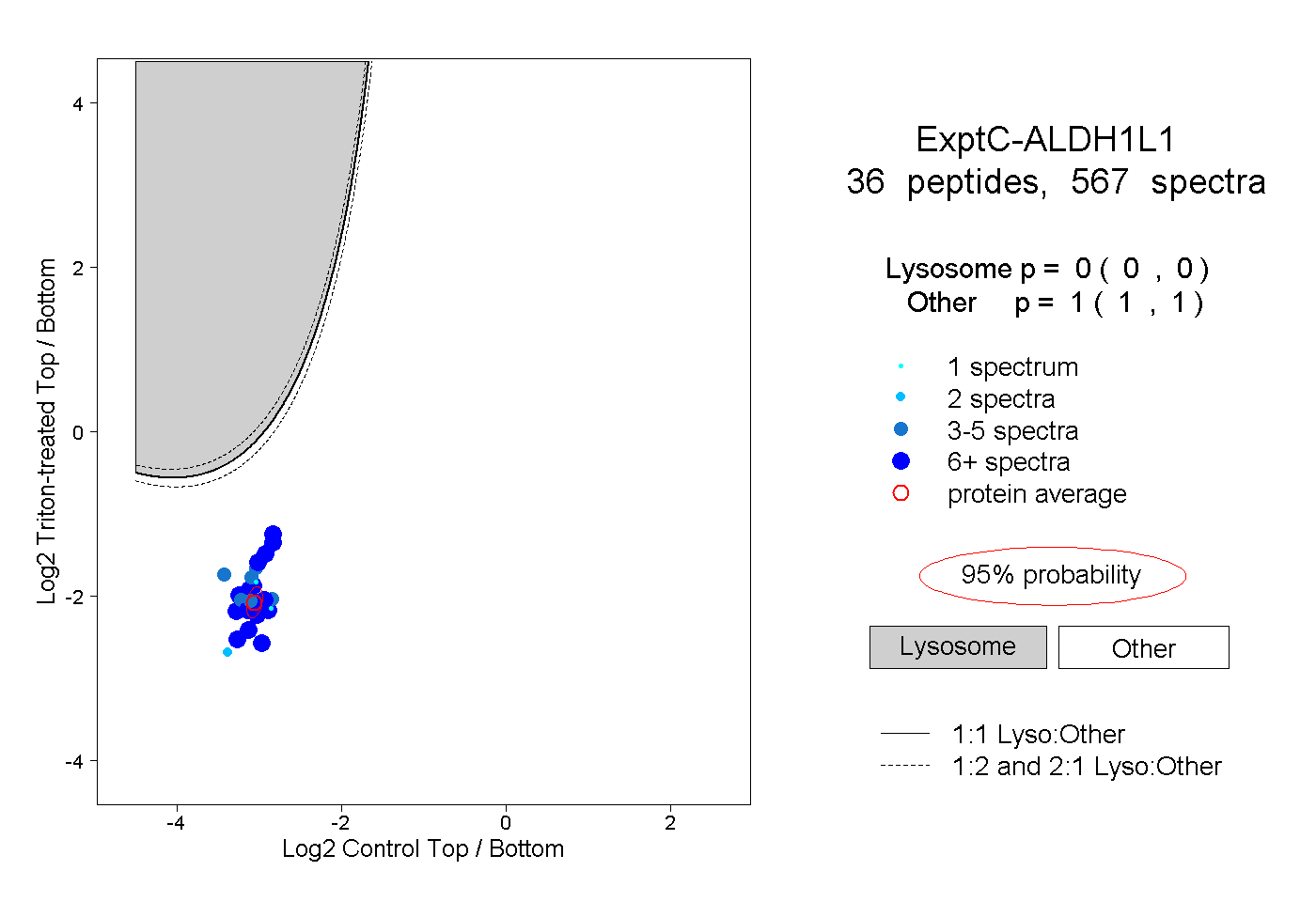 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
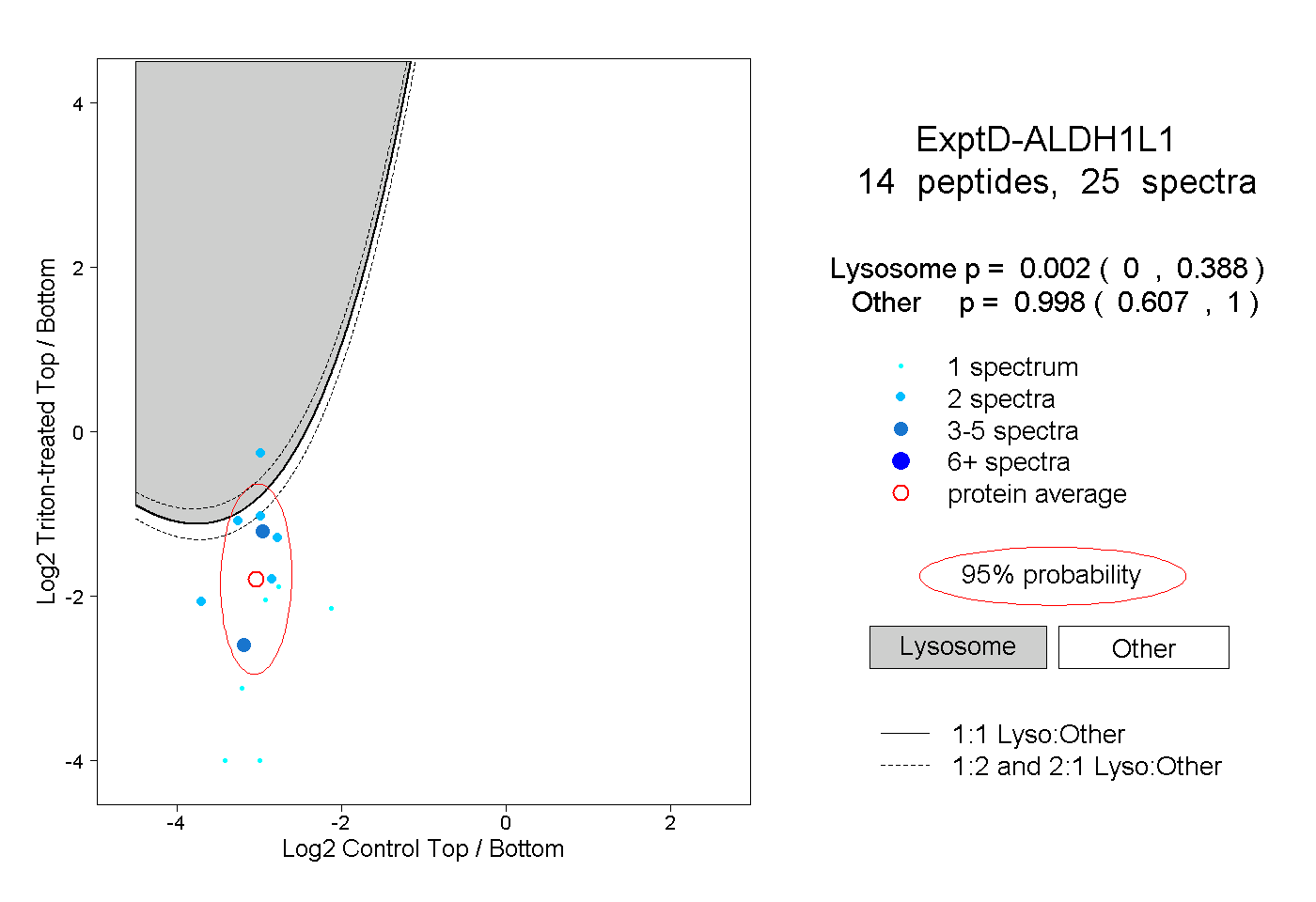 |
0.002 0.000 | 0.388 |
0.998 0.607 | 1.000 |