peptides
spectra
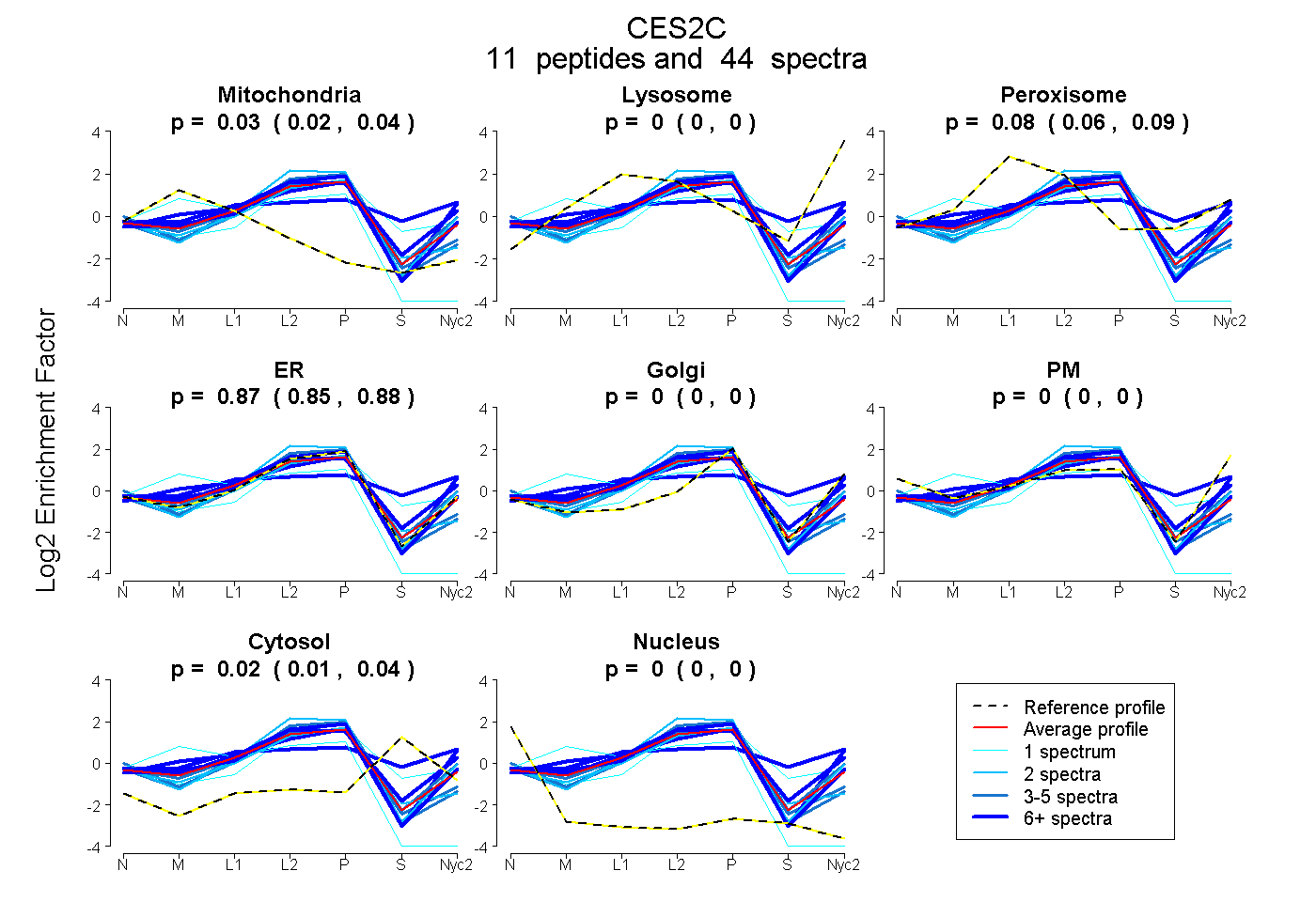
0.016 | 0.044
0.000 | 0.000
0.063 | 0.089
0.852 | 0.877
0.000 | 0.000
0.000 | 0.000
0.013 | 0.036
0.000 | 0.000
peptides
spectra
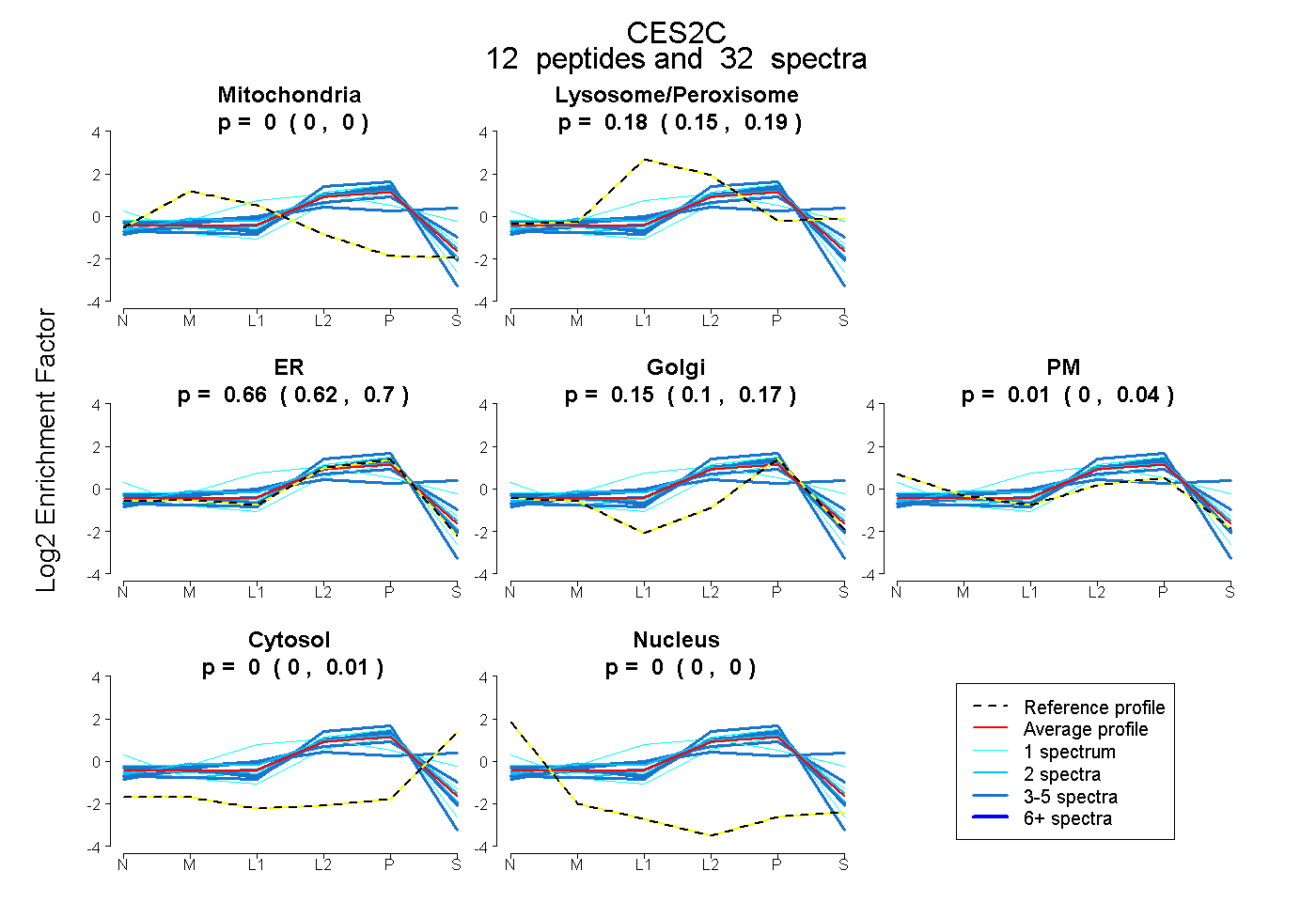
0.000 | 0.000
0.150 | 0.194
0.622 | 0.699
0.100 | 0.173
0.000 | 0.042
0.000 | 0.013
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.031 0.016 | 0.044 |
0.000 0.000 | 0.000 |
0.078 0.063 | 0.089 |
0.866 0.852 | 0.877 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.013 | 0.036 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
 |
0.000 0.000 | 0.000 |
0.178 0.150 | 0.194 |
0.657 0.622 | 0.699 |
0.151 0.100 | 0.173 |
0.013 0.000 | 0.042 |
0.002 0.000 | 0.013 |
0.000 0.000 | 0.000 |
| 1 spectrum, ENLQAVLK | 0.000 | 0.056 | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LGVLGFFSTGDEHAR | 0.000 | 0.479 | 0.000 | 0.267 | 0.000 | 0.254 | 0.000 | |||
| 4 spectra, VDFTEEEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, AGVHTFLGIPFAK | 0.000 | 0.084 | 0.791 | 0.000 | 0.125 | 0.000 | 0.000 | |||
| 2 spectra, WVQQNIAHFGGNPNR | 0.000 | 0.229 | 0.628 | 0.143 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, NVRPPHVK | 0.000 | 0.413 | 0.139 | 0.437 | 0.010 | 0.000 | 0.000 | |||
| 1 spectrum, TTHTGQVR | 0.000 | 0.626 | 0.000 | 0.300 | 0.041 | 0.033 | 0.000 | |||
| 3 spectra, SGAEILVINK | 0.000 | 0.029 | 0.792 | 0.000 | 0.179 | 0.000 | 0.000 | |||
| 1 spectrum, APVGPLR | 0.000 | 0.019 | 0.402 | 0.048 | 0.462 | 0.068 | 0.000 | |||
| 1 spectrum, LSGCEATDSETLVR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FAPPEDPEPWSGVR | 0.000 | 0.098 | 0.861 | 0.000 | 0.000 | 0.018 | 0.023 | |||
| 5 spectra, LQFWTK | 0.000 | 0.024 | 0.965 | 0.012 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
99 spectra |
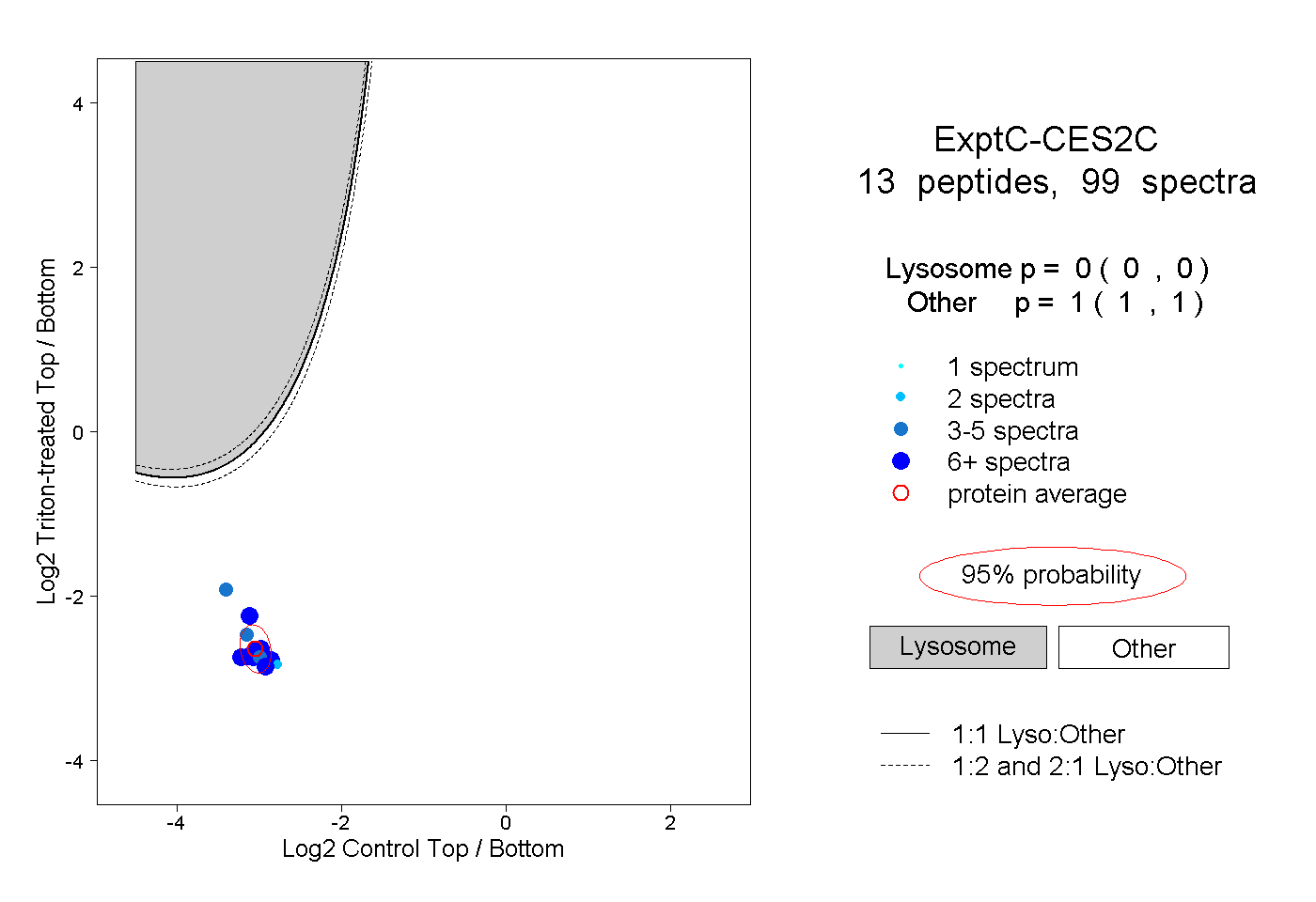 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
8 spectra |
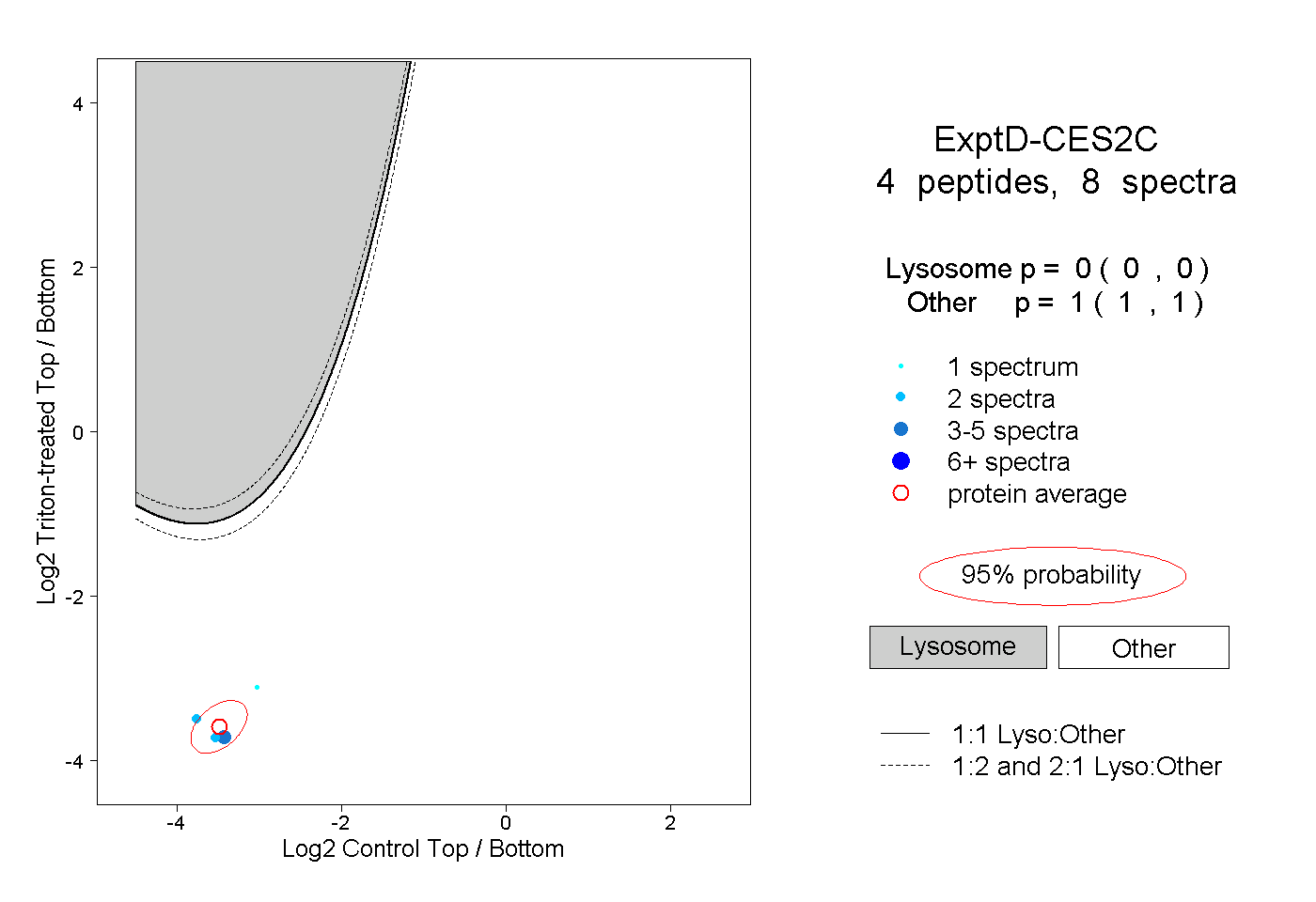 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |