peptides
spectra
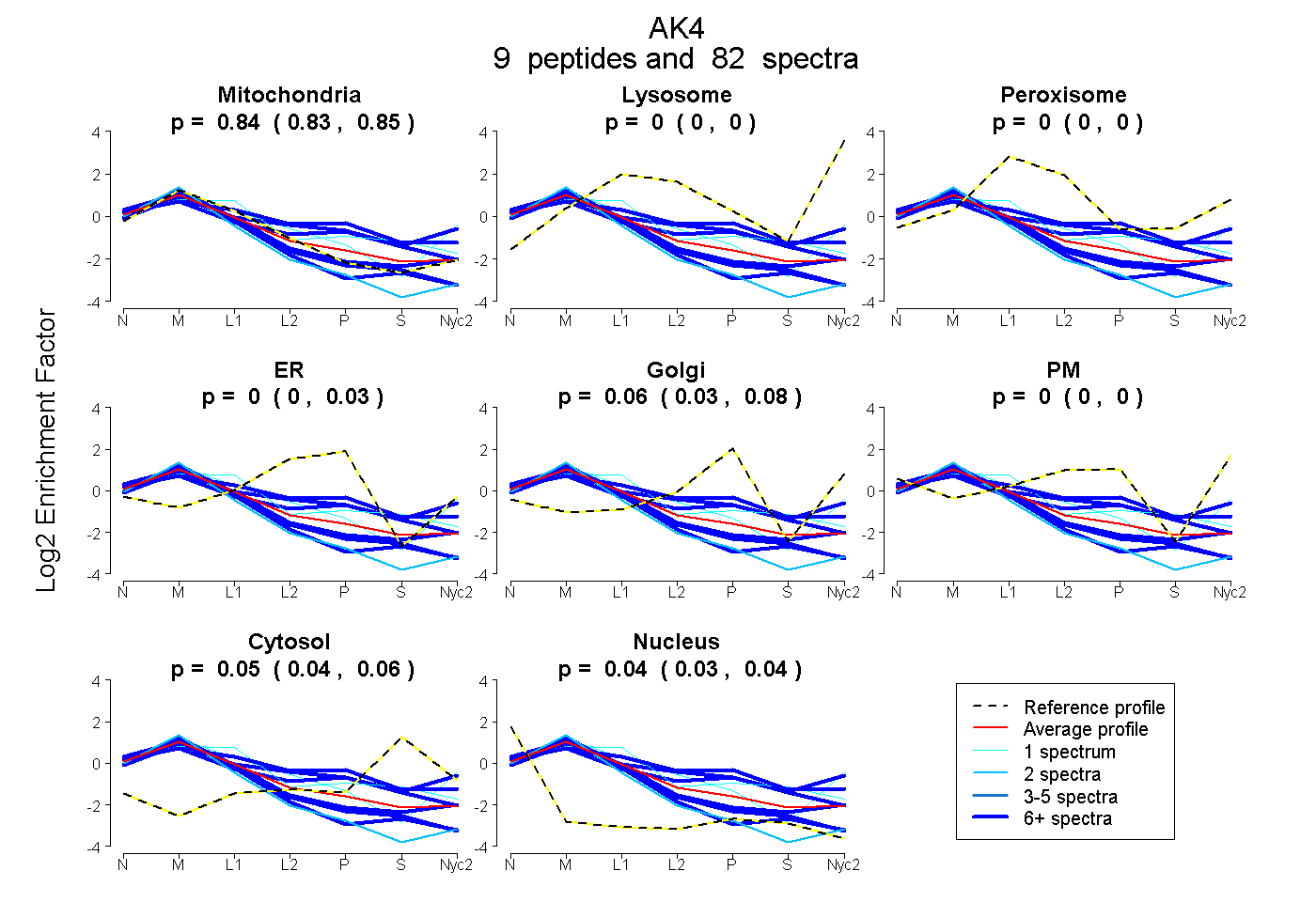
0.835 | 0.851
0.000 | 0.000
0.000 | 0.000
0.000 | 0.028
0.034 | 0.080
0.000 | 0.000
0.037 | 0.059
0.030 | 0.045
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.845 0.835 | 0.851 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.028 |
0.065 0.034 | 0.080 |
0.000 0.000 | 0.000 |
0.048 0.037 | 0.059 |
0.038 0.030 | 0.045 |
| 8 spectra, WIHPSSGR | 0.502 | 0.000 | 0.151 | 0.111 | 0.135 | 0.000 | 0.100 | 0.000 | ||
| 10 spectra, TLVQAEALDR | 0.848 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.152 | ||
| 1 spectrum, IAQNFGLQHLSSGHLLR | 0.648 | 0.000 | 0.166 | 0.000 | 0.041 | 0.000 | 0.132 | 0.012 | ||
| 1 spectrum, AVILGPPGSGK | 0.684 | 0.046 | 0.000 | 0.000 | 0.000 | 0.270 | 0.000 | 0.000 | ||
| 7 spectra, GVLHQFSGTETNR | 0.516 | 0.042 | 0.070 | 0.000 | 0.073 | 0.177 | 0.122 | 0.000 | ||
| 33 spectra, LMMSELETR | 0.918 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | 0.055 | ||
| 2 spectra, TNTEVGDVAK | 0.822 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.178 | ||
| 14 spectra, GLLVPDHVITR | 0.625 | 0.000 | 0.000 | 0.191 | 0.000 | 0.000 | 0.145 | 0.039 | ||
| 6 spectra, SAQHWLLDGFPR | 0.835 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.165 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
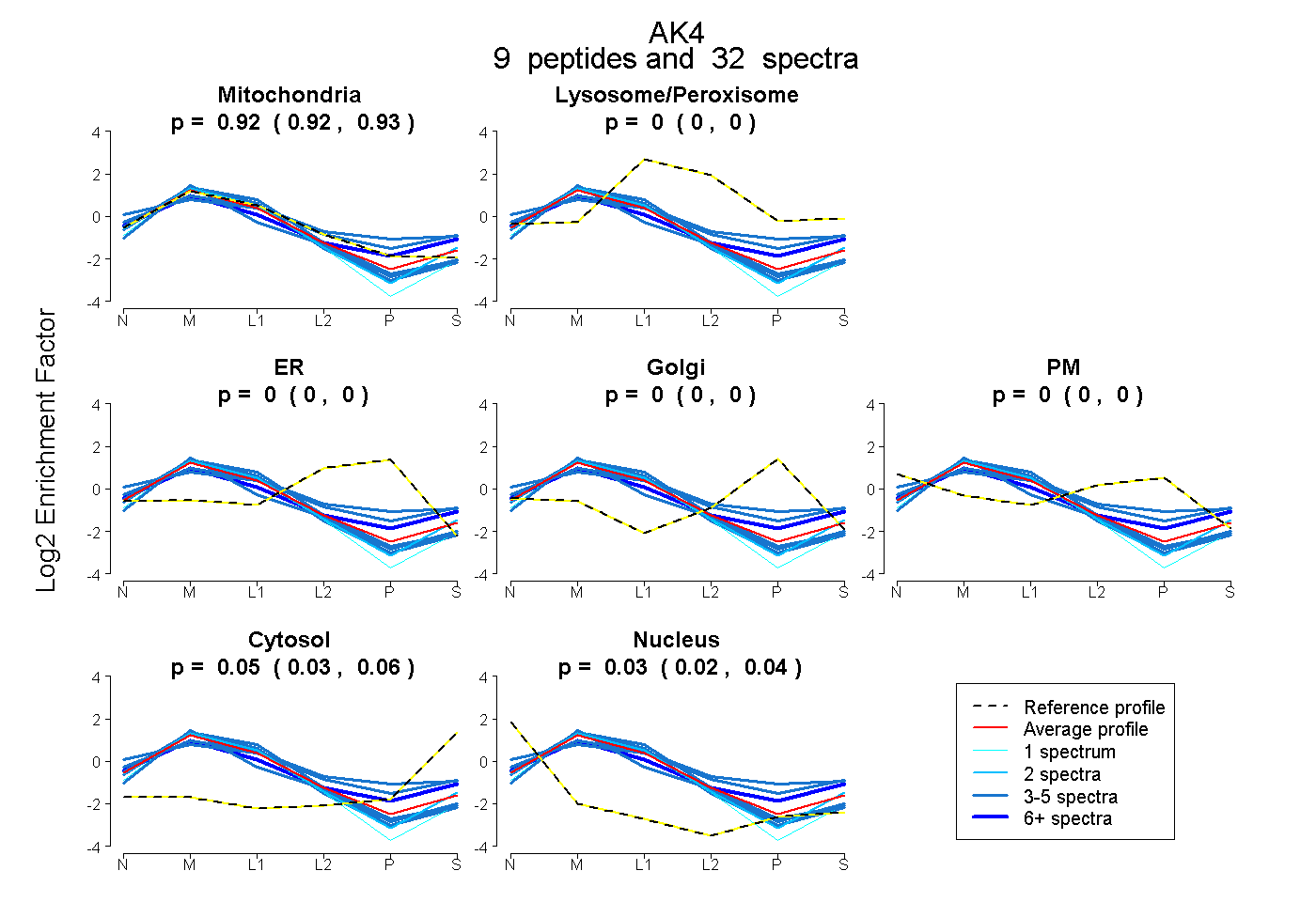 |
0.923 0.915 | 0.930 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.047 0.035 | 0.057 |
0.030 0.021 | 0.037 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
239 spectra |
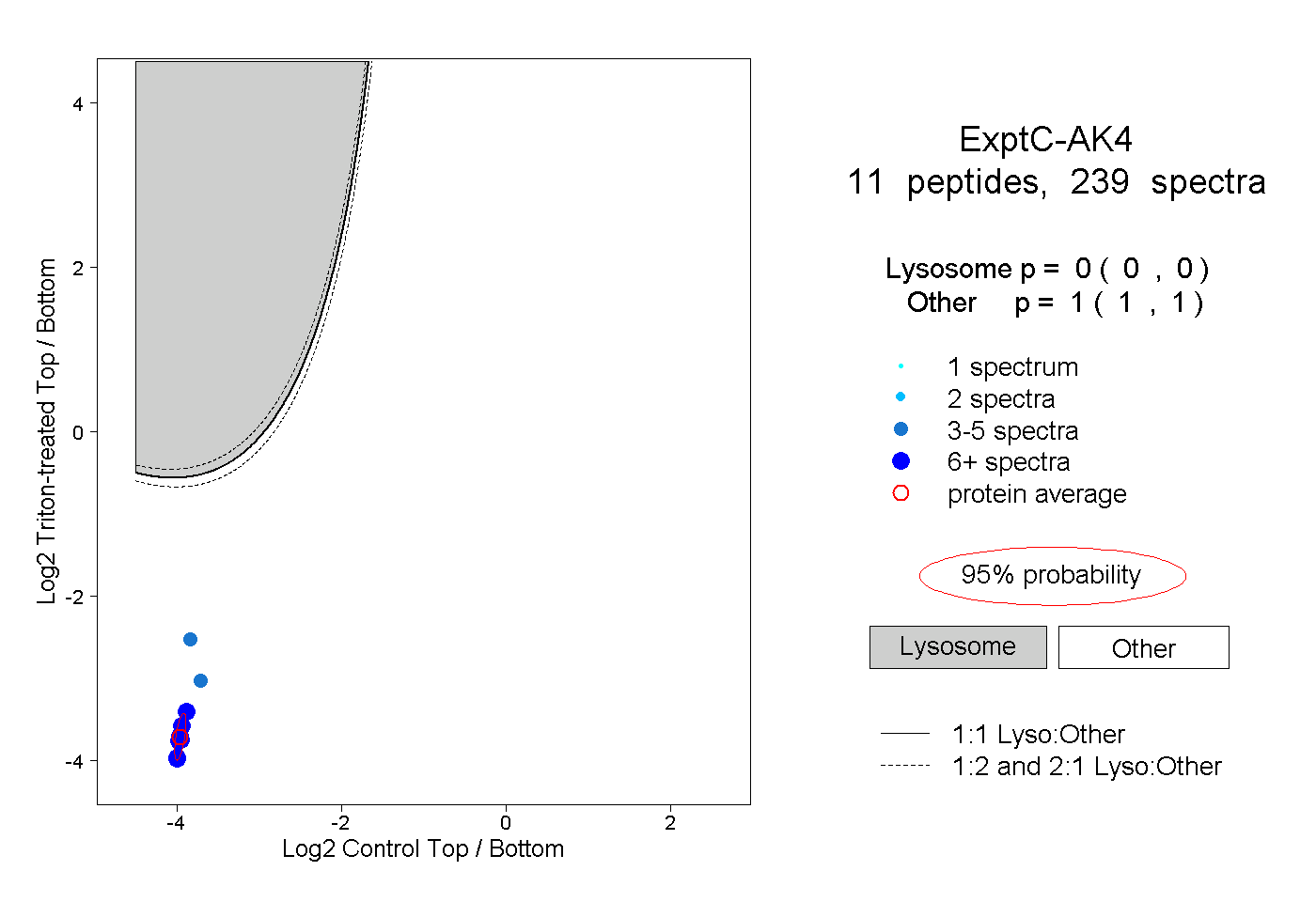 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
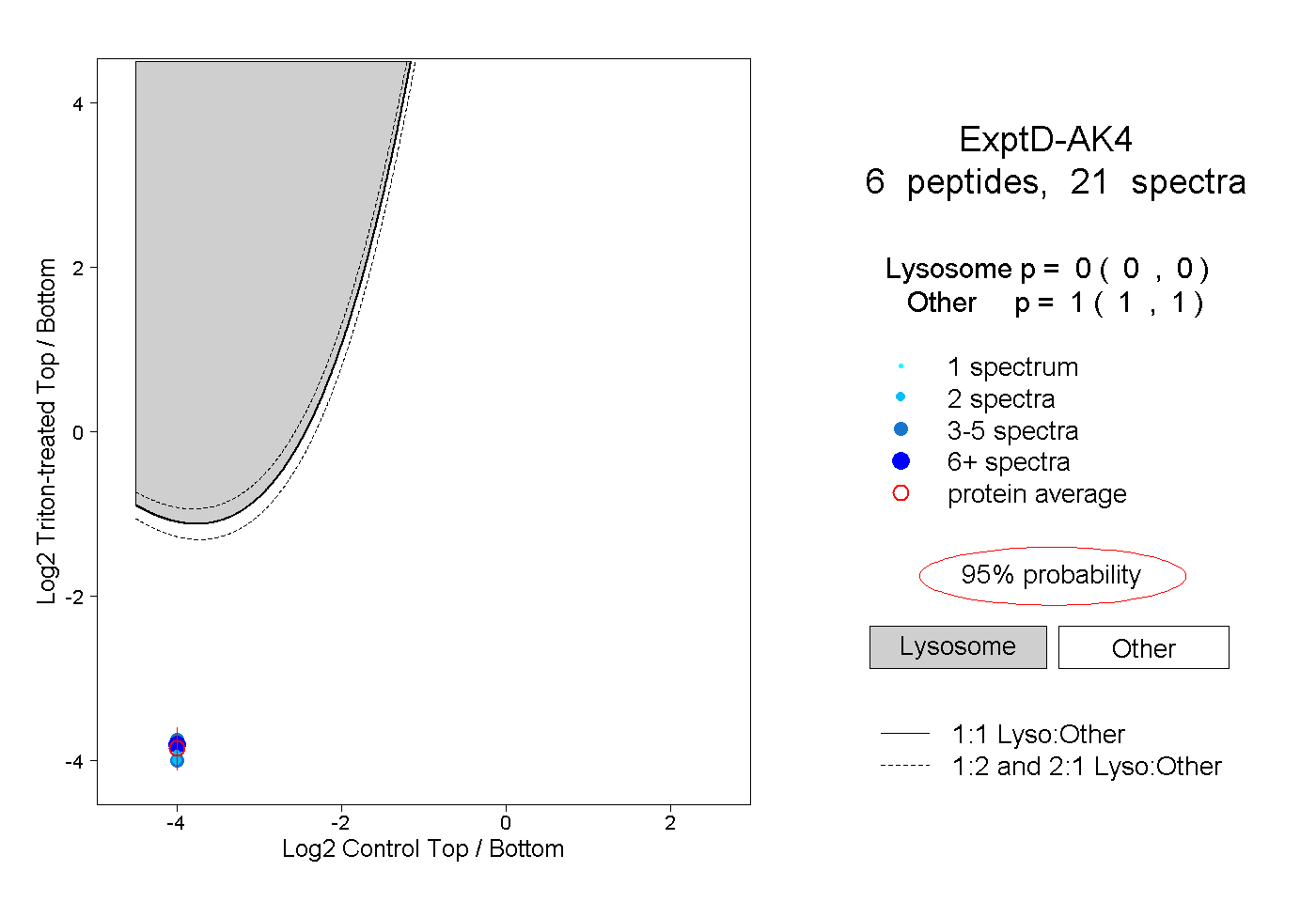 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |