SLC25A51
[ENSRNOP00000065025]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 4
4
peptides |
8
spectra |
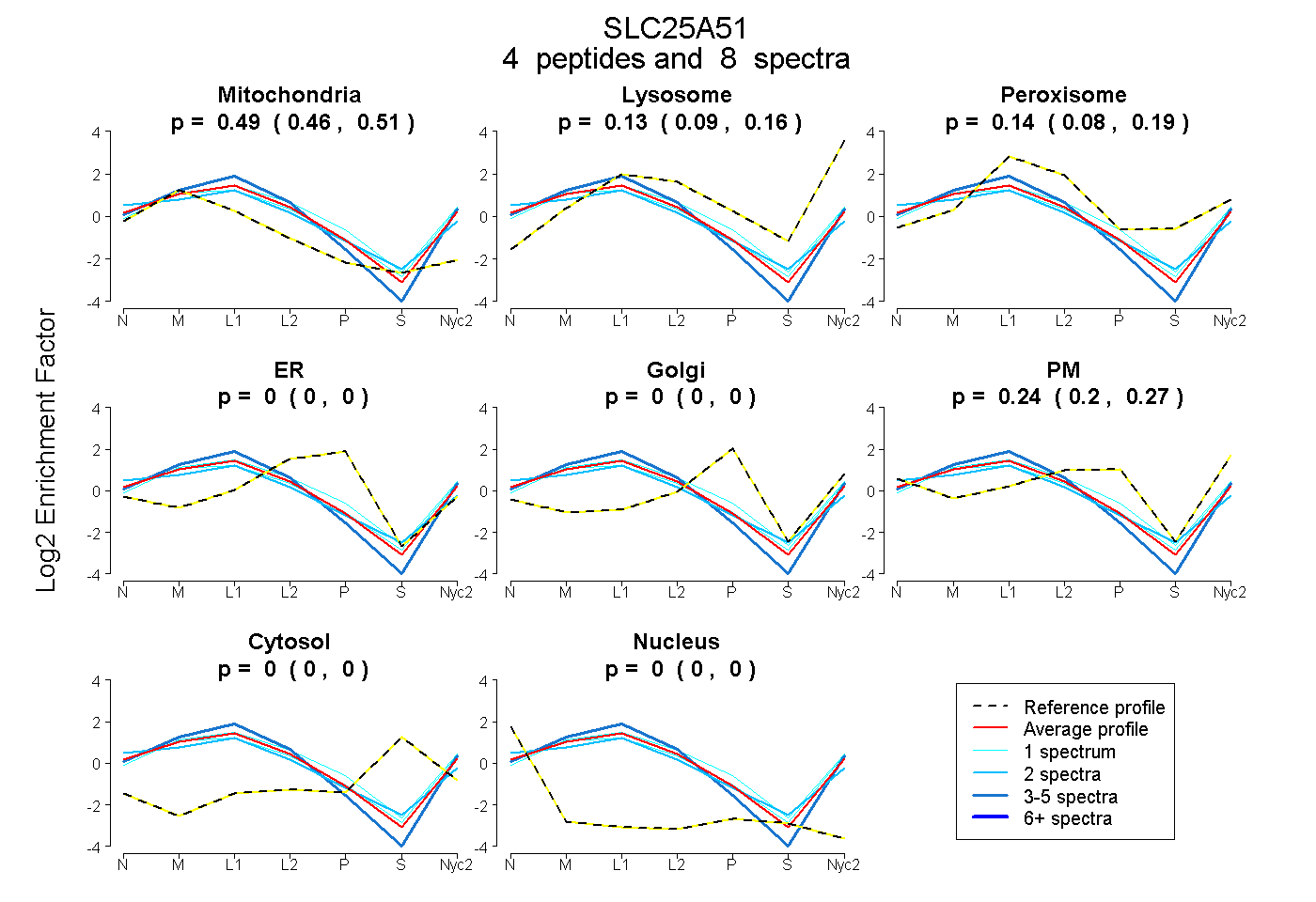 |
0.490
0.464 | 0.512 |
0.128
0.087 | 0.164 |
|
0.144
0.079 | 0.191 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.239
0.197 | 0.273 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 1
1
peptide |
1
spectrum |
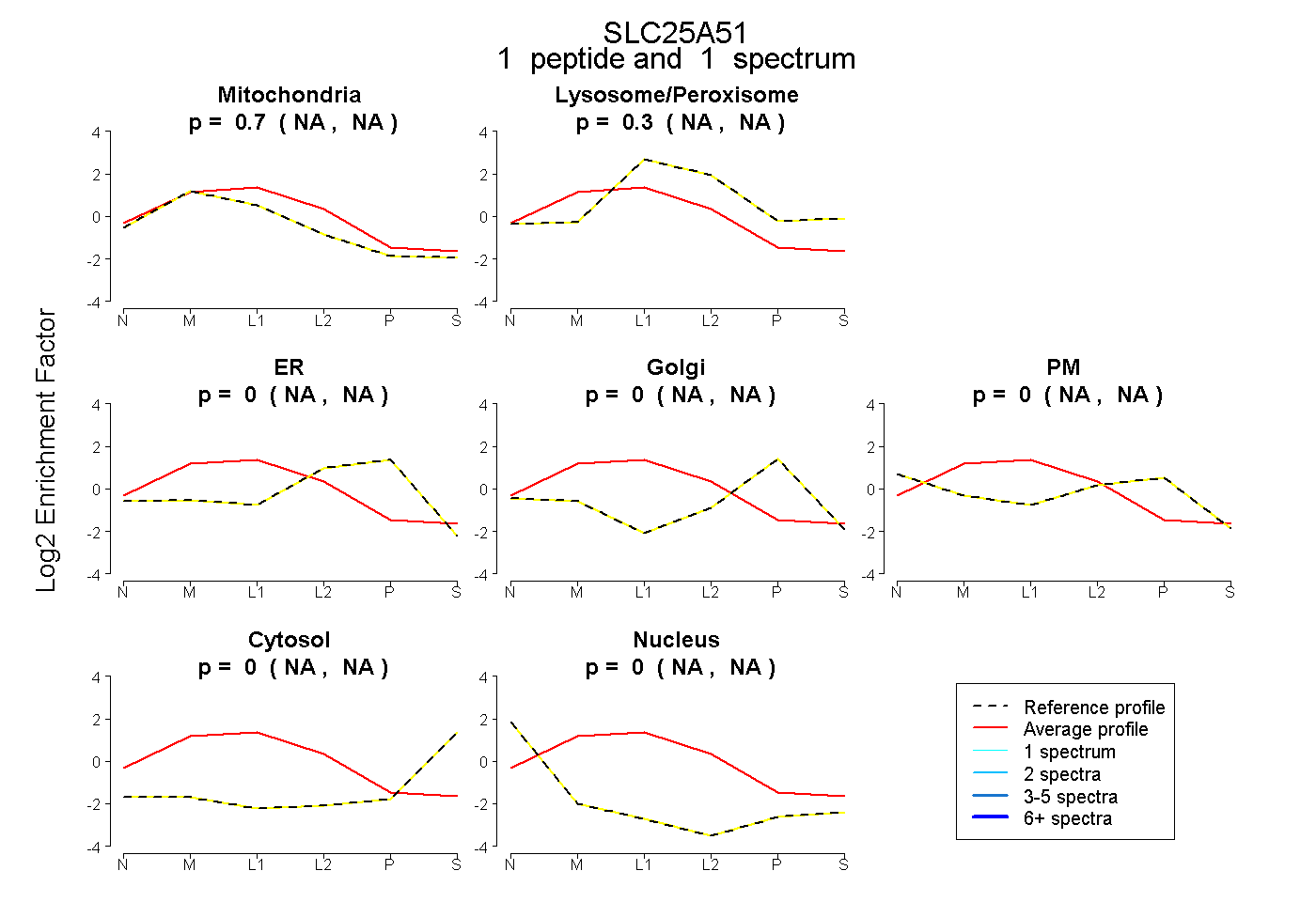 |
0.697
NA | NA |
|
0.303
NA | NA |
|
0.000
NA | NA |
0.000
NA | NA |
0.000
NA | NA |
0.000
NA | NA |
0.000
NA | NA |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 8
8
peptides |
31
spectra |
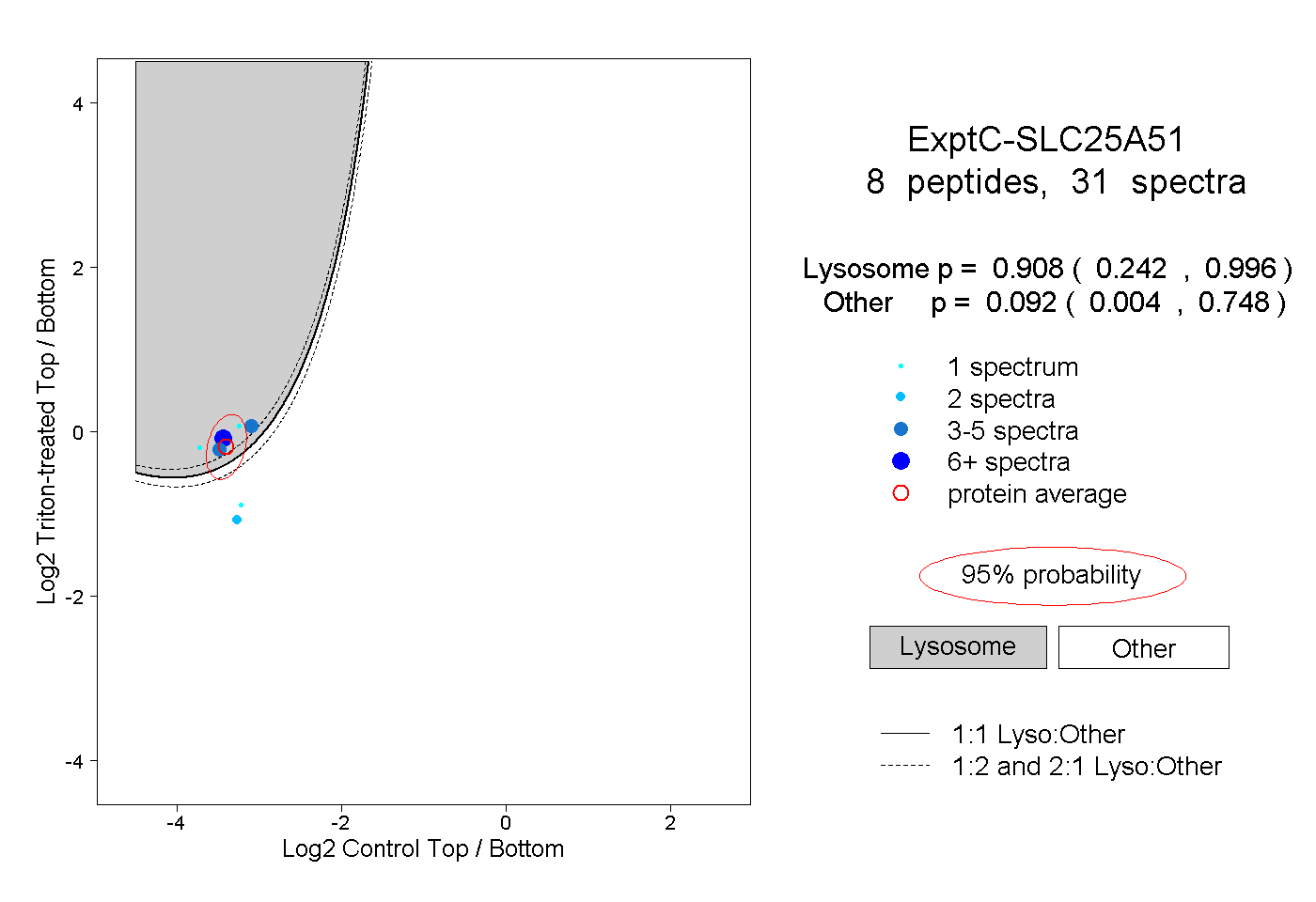 |
|
0.908
0.242 | 0.996 |
|
|
|
|
|
|
|
0.092
0.004 | 0.748 |
| 16 spectra, GLVPILFR |
|
0.976 |
|
|
|
|
|
|
|
0.024 |
| 2 spectra, GILPPLMQK |
|
0.890 |
|
|
|
|
|
|
|
0.110 |
| 3 spectra, FTNTYQAFR |
|
0.915 |
|
|
|
|
|
|
|
0.085 |
| 5 spectra, VQTLLQDHK |
|
0.923 |
|
|
|
|
|
|
|
0.077 |
| 1 spectrum, LINLFR |
|
0.981 |
|
|
|
|
|
|
|
0.019 |
| 1 spectrum, GAHLNHHR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 2 spectra, HVSNAPEFATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QQLYGIK |
|
0.977 |
|
|
|
|
|
|
|
0.023 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 2
2
peptides |
3
spectra |
 |
|
0.002
0.000 | 0.097 |
|
|
|
|
|
|
|
0.998
0.898 | 1.000 |



