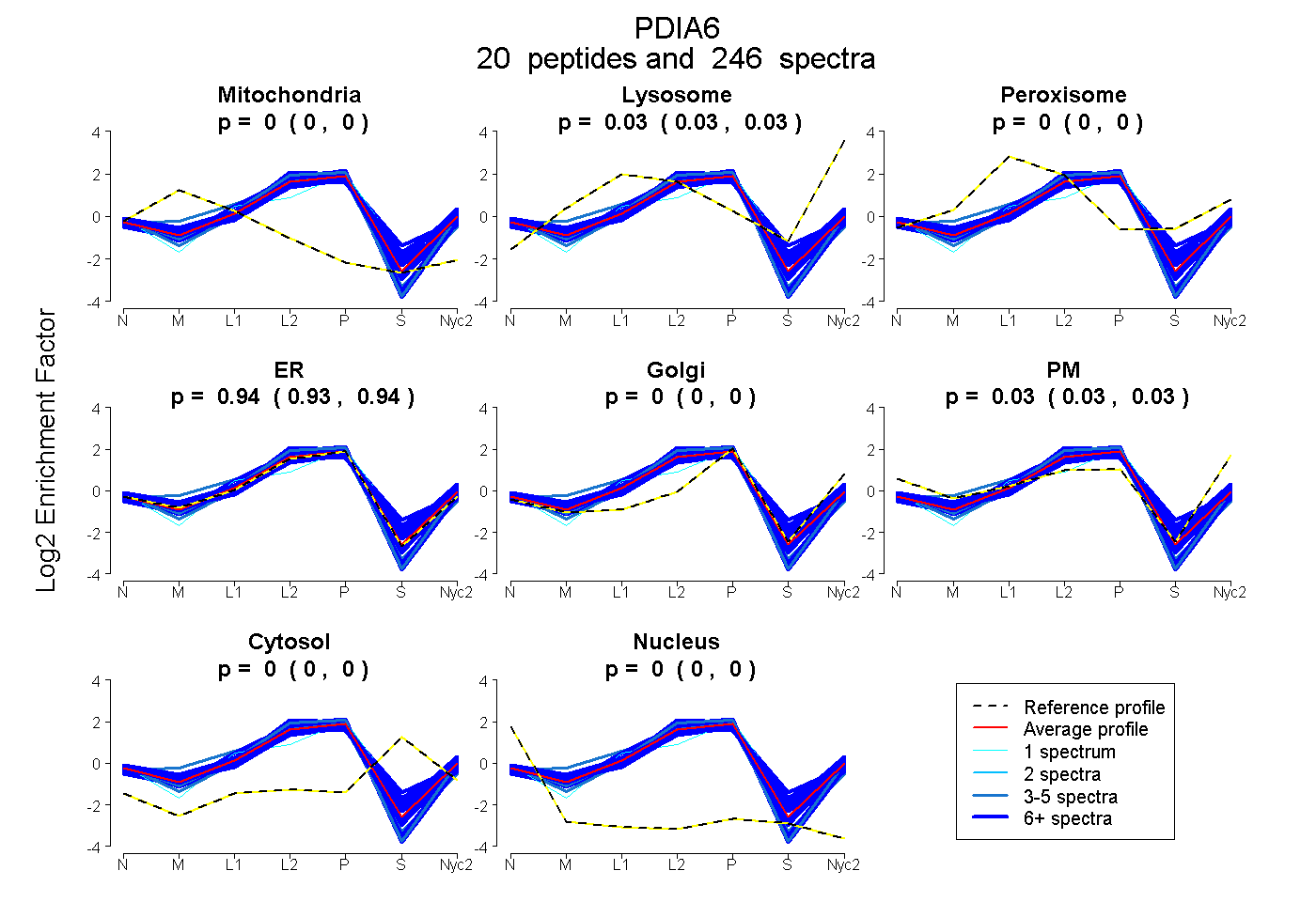
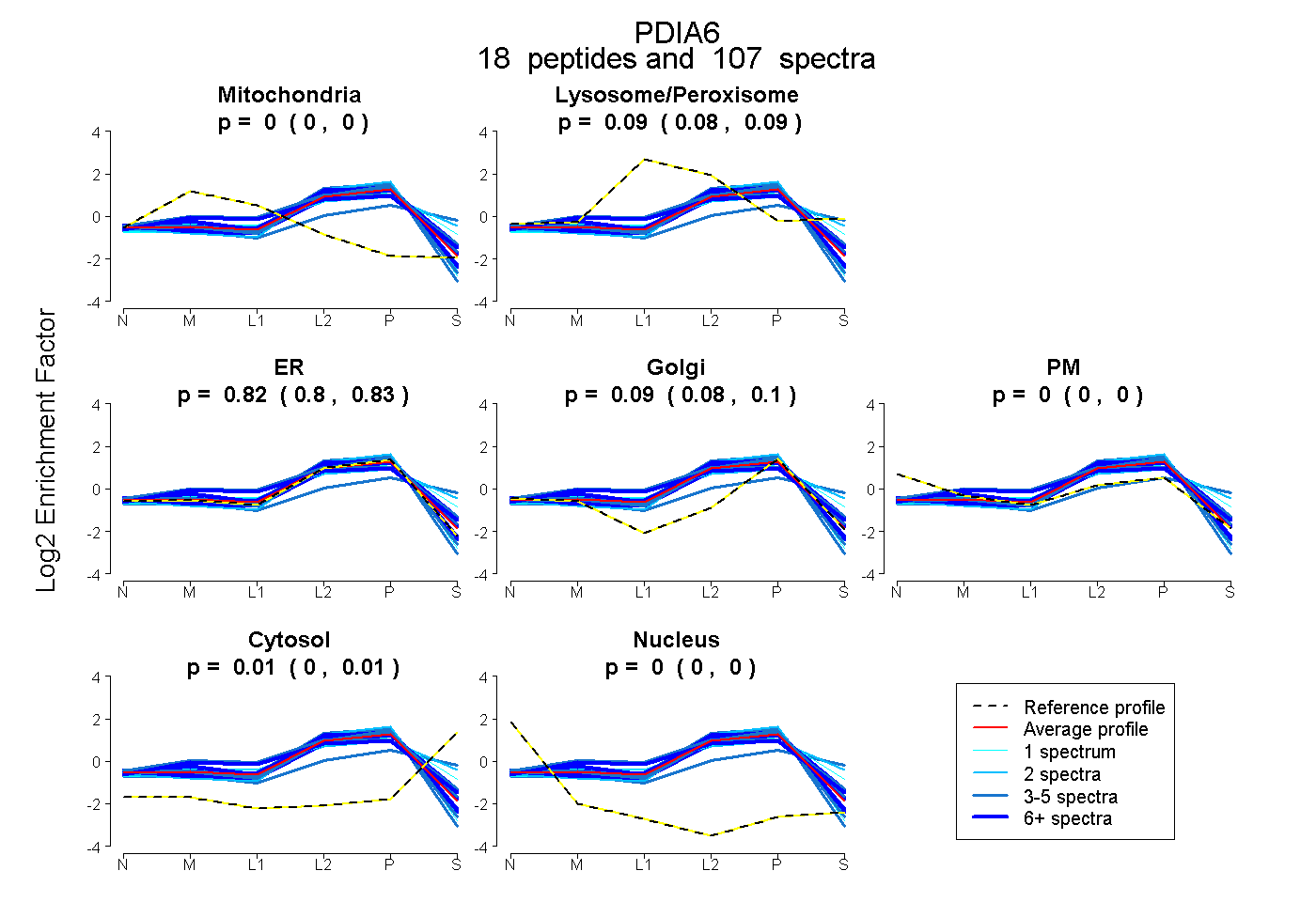
| 22 spectra, GSFSEQGINEFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, GSTAPVGGGSFPNITPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 56 spectra, IFGANK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 39 spectra, ELSFGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 50 spectra, NKPEDYQGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, LAAVDATVNQVLASR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GDSSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, SDIVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 85 spectra, GESPVDYDGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, AASALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, NSYLEVLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, HQSLGGQYGVQGFPTIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 78 spectra, SGGYSSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, TGEAIVDAALSALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FLGADK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 44 spectra, GFPTIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, EPWDGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DVVELTDDTFDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 39 spectra, VGAVNADK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LTPEWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |