peptides
spectra
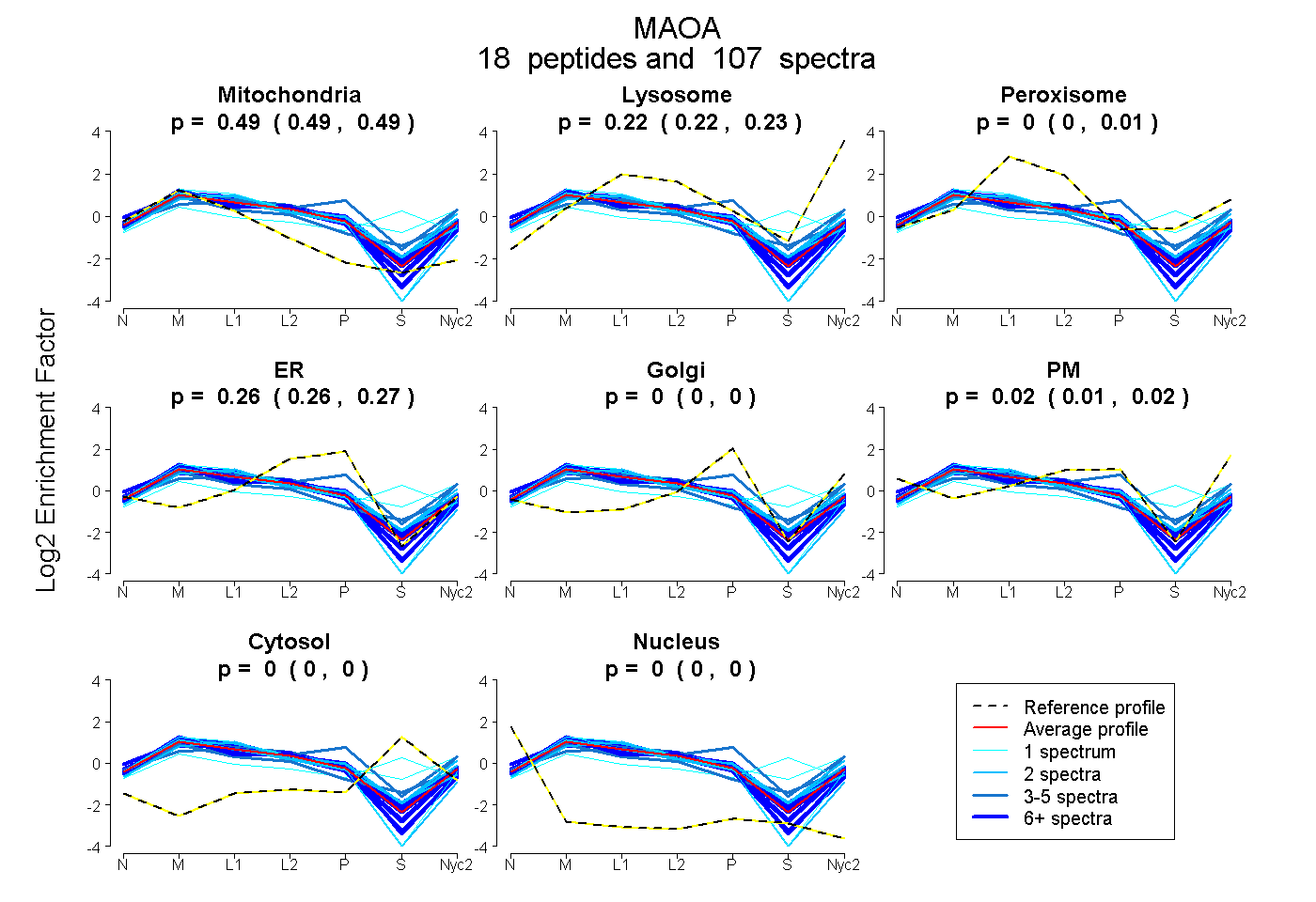
0.488 | 0.493
0.219 | 0.227
0.000 | 0.009
0.259 | 0.269
0.000 | 0.000
0.011 | 0.021
0.000 | 0.000
0.000 | 0.000
peptides
spectra
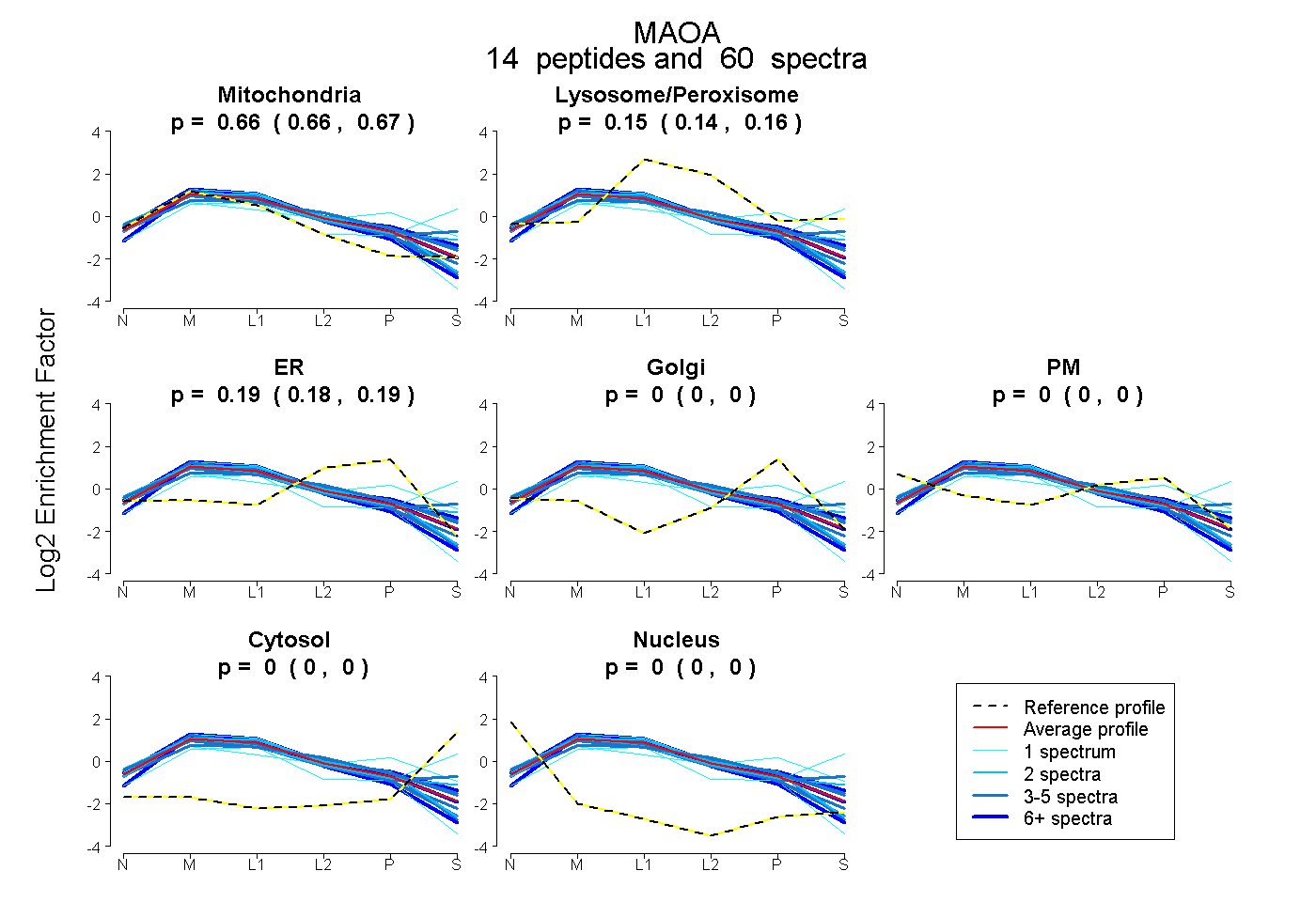
0.658 | 0.666
0.143 | 0.157
0.180 | 0.191
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
107 spectra |
 |
0.491 0.488 | 0.493 |
0.224 0.219 | 0.227 |
0.003 0.000 | 0.009 |
0.265 0.259 | 0.269 |
0.000 0.000 | 0.000 |
0.017 0.011 | 0.021 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
60 spectra |
 |
0.663 0.658 | 0.666 |
0.151 0.143 | 0.157 |
0.186 0.180 | 0.191 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, EVLNALGK | 0.658 | 0.077 | 0.265 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, DVPAIEITHTFLER | 0.557 | 0.260 | 0.055 | 0.129 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VLGSQEALYPVHYEEK | 0.615 | 0.254 | 0.000 | 0.120 | 0.000 | 0.011 | 0.000 | |||
| 5 spectra, IFSVTNGGQER | 0.742 | 0.071 | 0.187 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EIPVDAPWQAR | 0.321 | 0.315 | 0.000 | 0.363 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, NLPSVPGLLK | 0.520 | 0.299 | 0.000 | 0.074 | 0.000 | 0.107 | 0.000 | |||
| 3 spectra, LPMGAVIK | 0.719 | 0.108 | 0.172 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, IHFKPELPPER | 0.665 | 0.175 | 0.160 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YVISAIPPILTAK | 0.566 | 0.205 | 0.203 | 0.000 | 0.026 | 0.000 | 0.000 | |||
| 1 spectrum, LVQYVK | 0.354 | 0.318 | 0.000 | 0.000 | 0.000 | 0.328 | 0.000 | |||
| 1 spectrum, LLSEYK | 0.784 | 0.004 | 0.212 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, WVDVGGAYVGPTQNR | 0.651 | 0.097 | 0.252 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, INVLVLEAR | 0.808 | 0.043 | 0.149 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, HAQEWDK | 0.604 | 0.192 | 0.204 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
590 spectra |
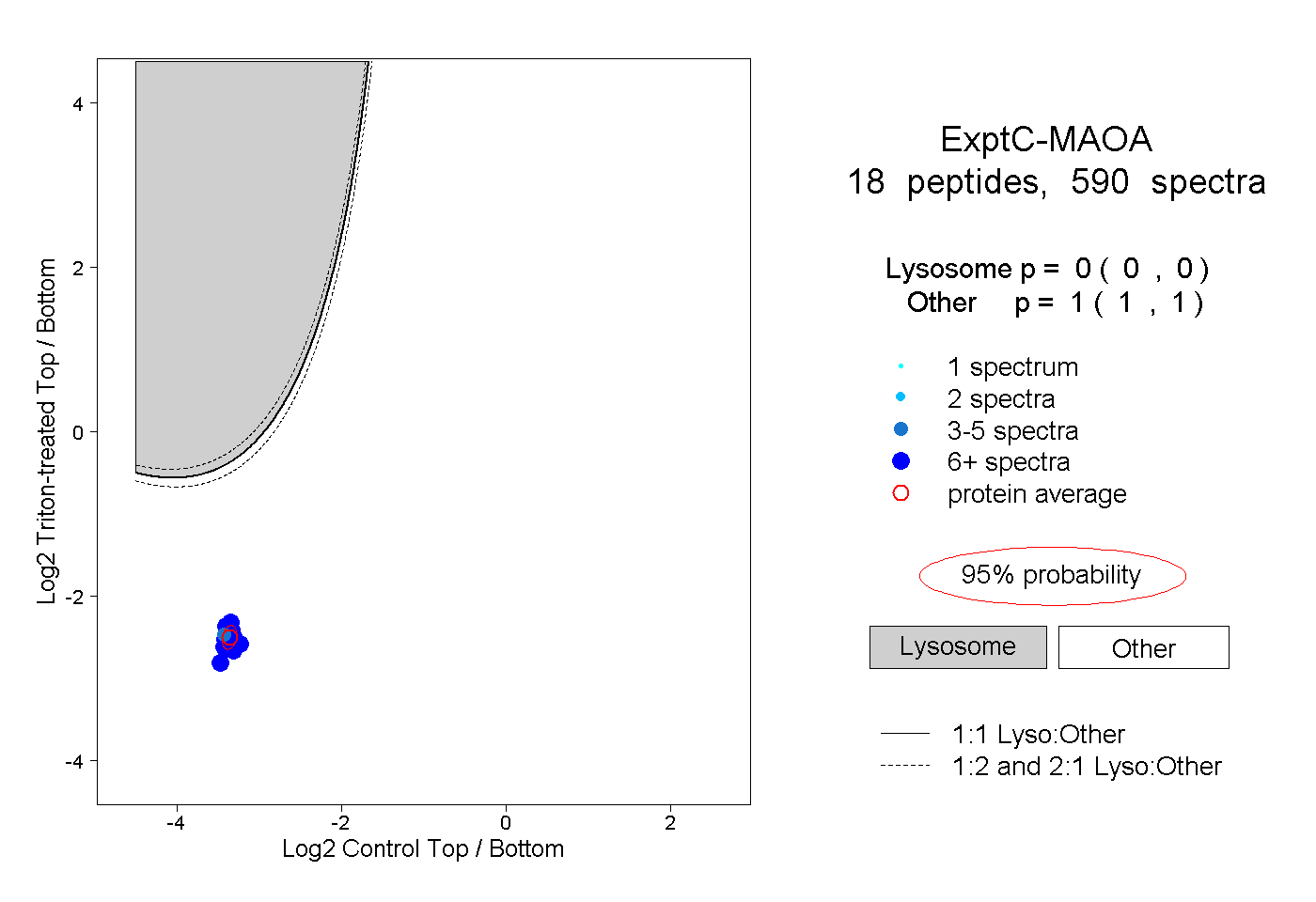 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
53 spectra |
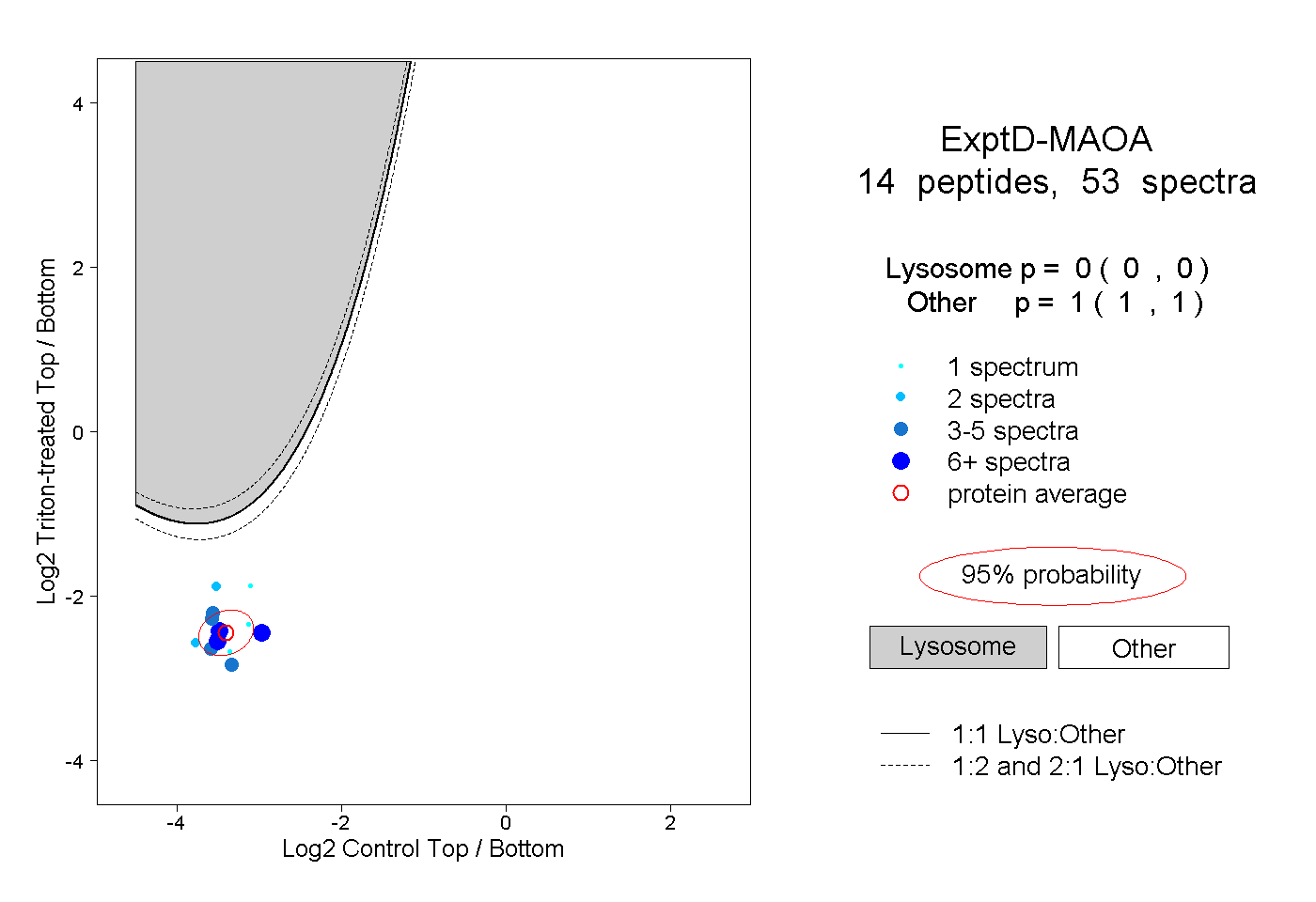 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |