peptides
spectra
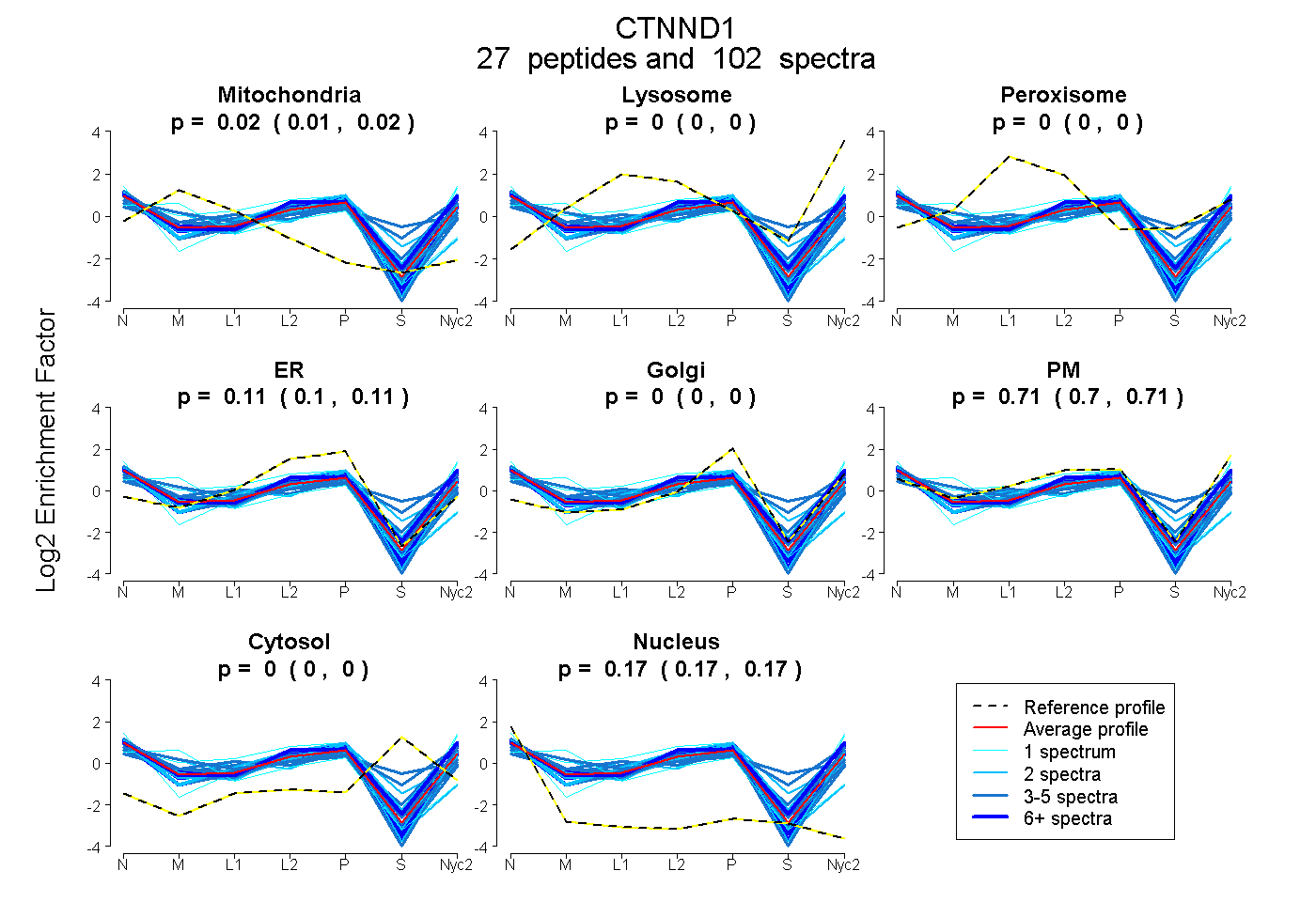
0.014 | 0.019
0.000 | 0.000
0.000 | 0.000
0.103 | 0.114
0.000 | 0.000
0.699 | 0.711
0.000 | 0.000
0.167 | 0.170
peptides
spectra
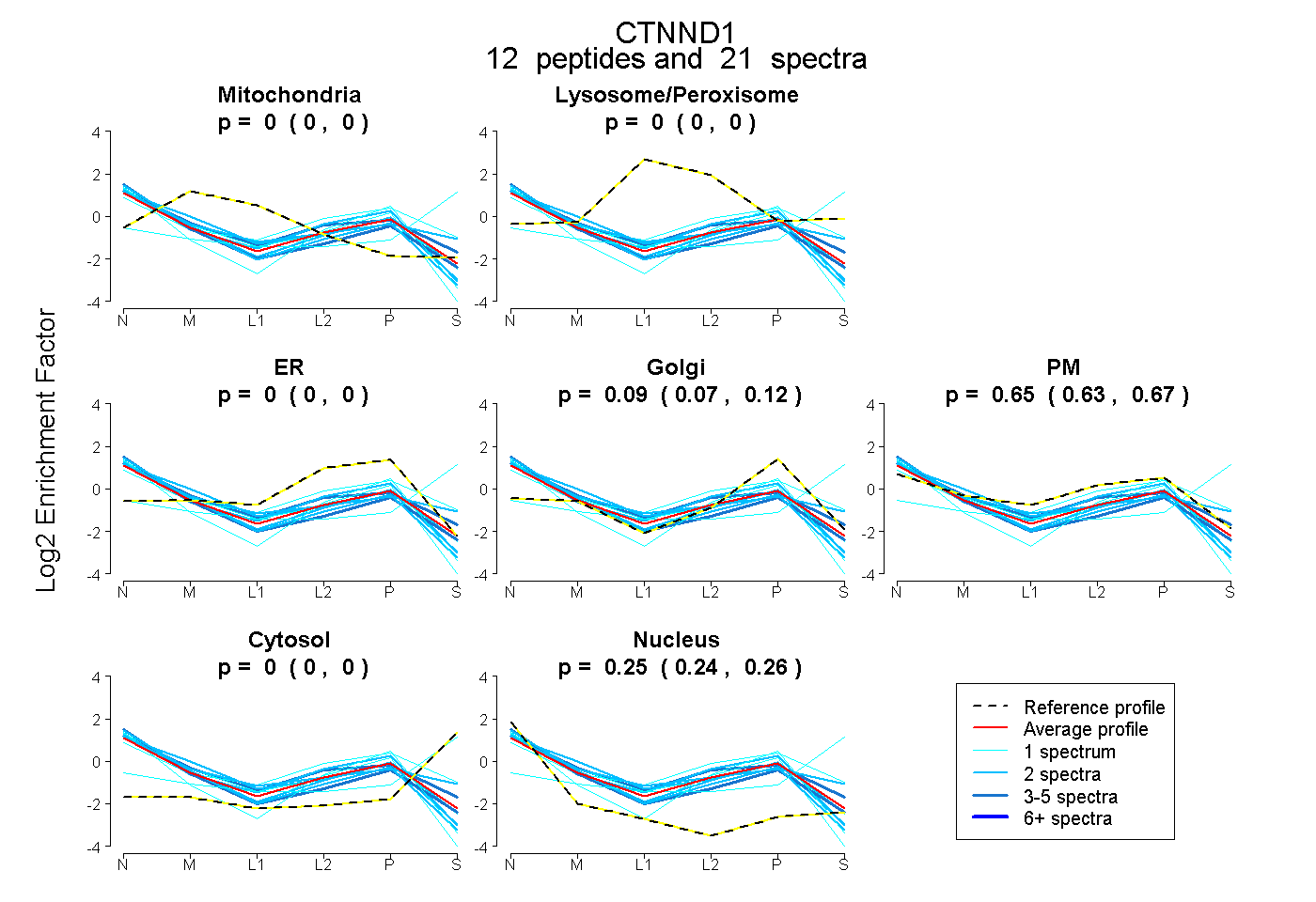
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.066 | 0.115
0.629 | 0.674
0.000 | 0.000
0.242 | 0.260
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
102 spectra |
 |
0.017 0.014 | 0.019 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.109 0.103 | 0.114 |
0.000 0.000 | 0.000 |
0.706 0.699 | 0.711 |
0.000 0.000 | 0.000 |
0.168 0.167 | 0.170 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.095 0.066 | 0.115 |
0.653 0.629 | 0.674 |
0.000 0.000 | 0.000 |
0.252 0.242 | 0.260 |
| 2 spectra, NCDGVPALVR | 0.000 | 0.000 | 0.000 | 0.088 | 0.560 | 0.000 | 0.352 | |||
| 2 spectra, EPNEDCKPR | 0.073 | 0.000 | 0.000 | 0.036 | 0.676 | 0.000 | 0.215 | |||
| 1 spectrum, SDFQVNLNNASR | 0.000 | 0.120 | 0.000 | 0.000 | 0.150 | 0.706 | 0.024 | |||
| 2 spectra, FVGDADLER | 0.000 | 0.000 | 0.136 | 0.000 | 0.643 | 0.000 | 0.221 | |||
| 3 spectra, LVENCVCLLR | 0.000 | 0.000 | 0.000 | 0.084 | 0.532 | 0.000 | 0.385 | |||
| 1 spectrum, EIPQAER | 0.000 | 0.000 | 0.377 | 0.025 | 0.244 | 0.000 | 0.354 | |||
| 1 spectrum, FHPEPYGLEDDQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.859 | 0.141 | 0.000 | |||
| 2 spectra, SNAAAYLQHLCYR | 0.000 | 0.056 | 0.000 | 0.000 | 0.640 | 0.101 | 0.203 | |||
| 1 spectrum, SLDNNYSTLNER | 0.000 | 0.000 | 0.306 | 0.289 | 0.058 | 0.000 | 0.347 | |||
| 1 spectrum, IYISLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.746 | 0.000 | 0.254 | |||
| 3 spectra, ALSAIADLLTSEHER | 0.000 | 0.000 | 0.000 | 0.000 | 0.806 | 0.005 | 0.189 | |||
| 2 spectra, GIPILVGLLDHPK | 0.000 | 0.000 | 0.000 | 0.155 | 0.574 | 0.000 | 0.272 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
152 spectra |
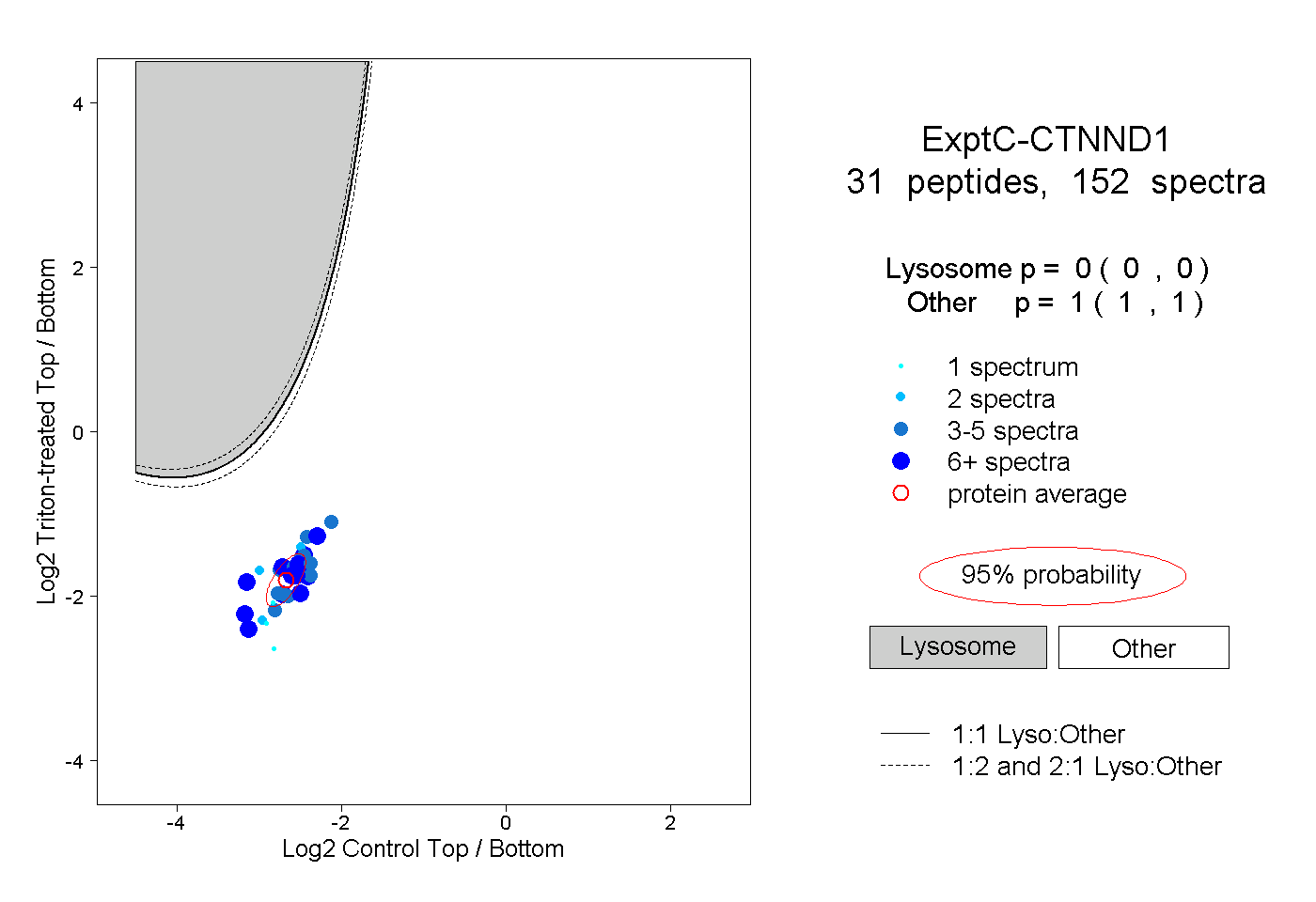 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
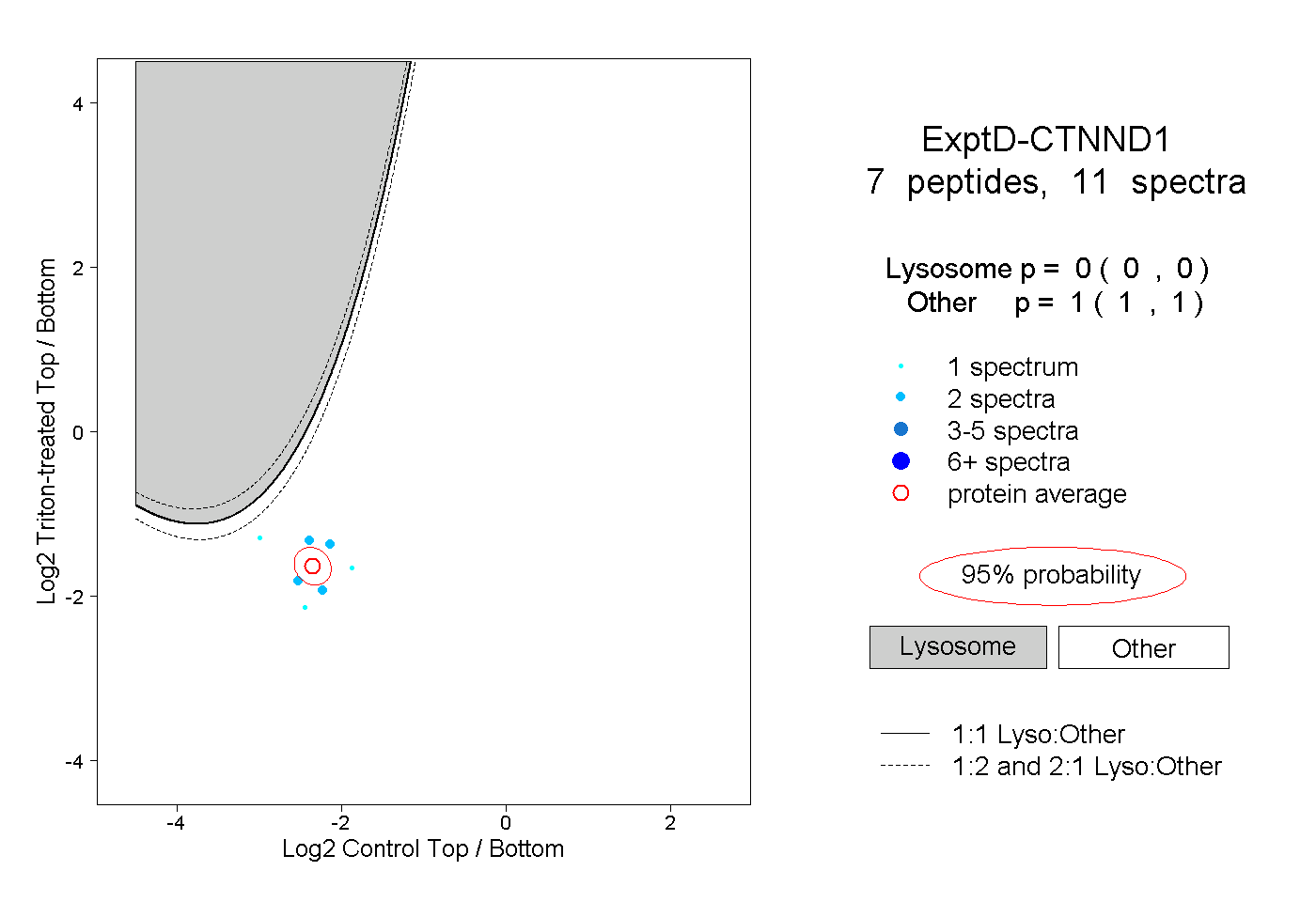 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |