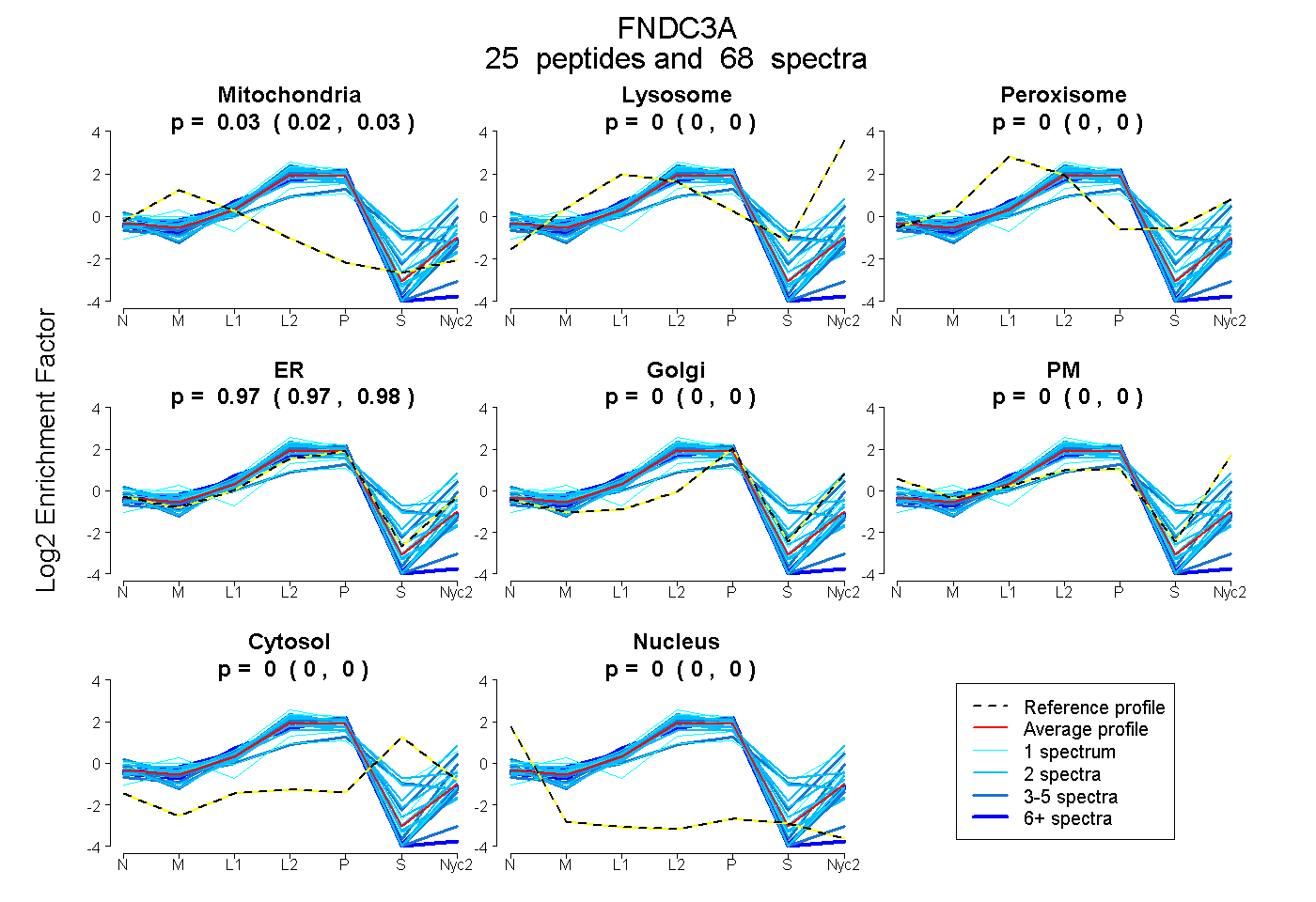
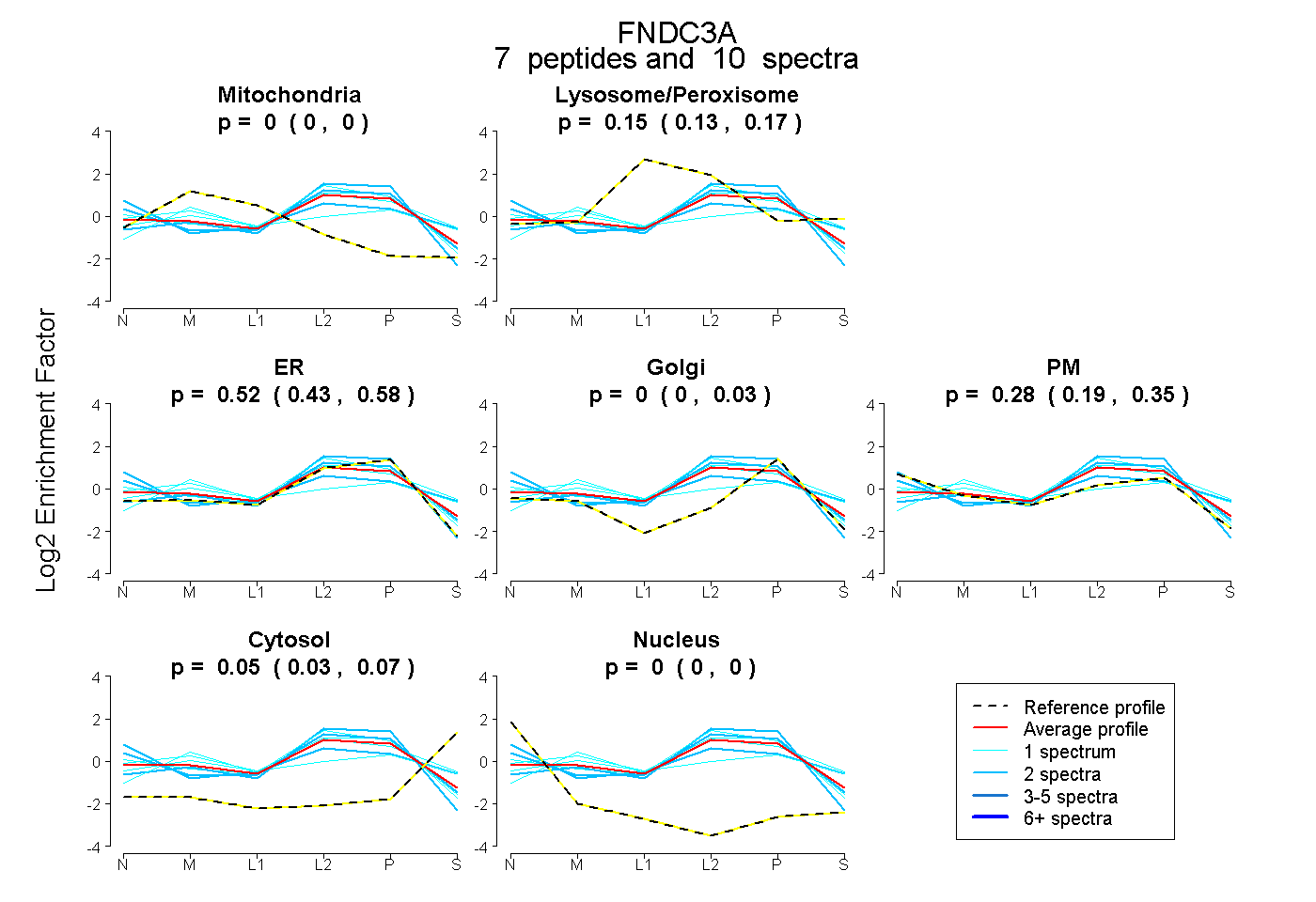
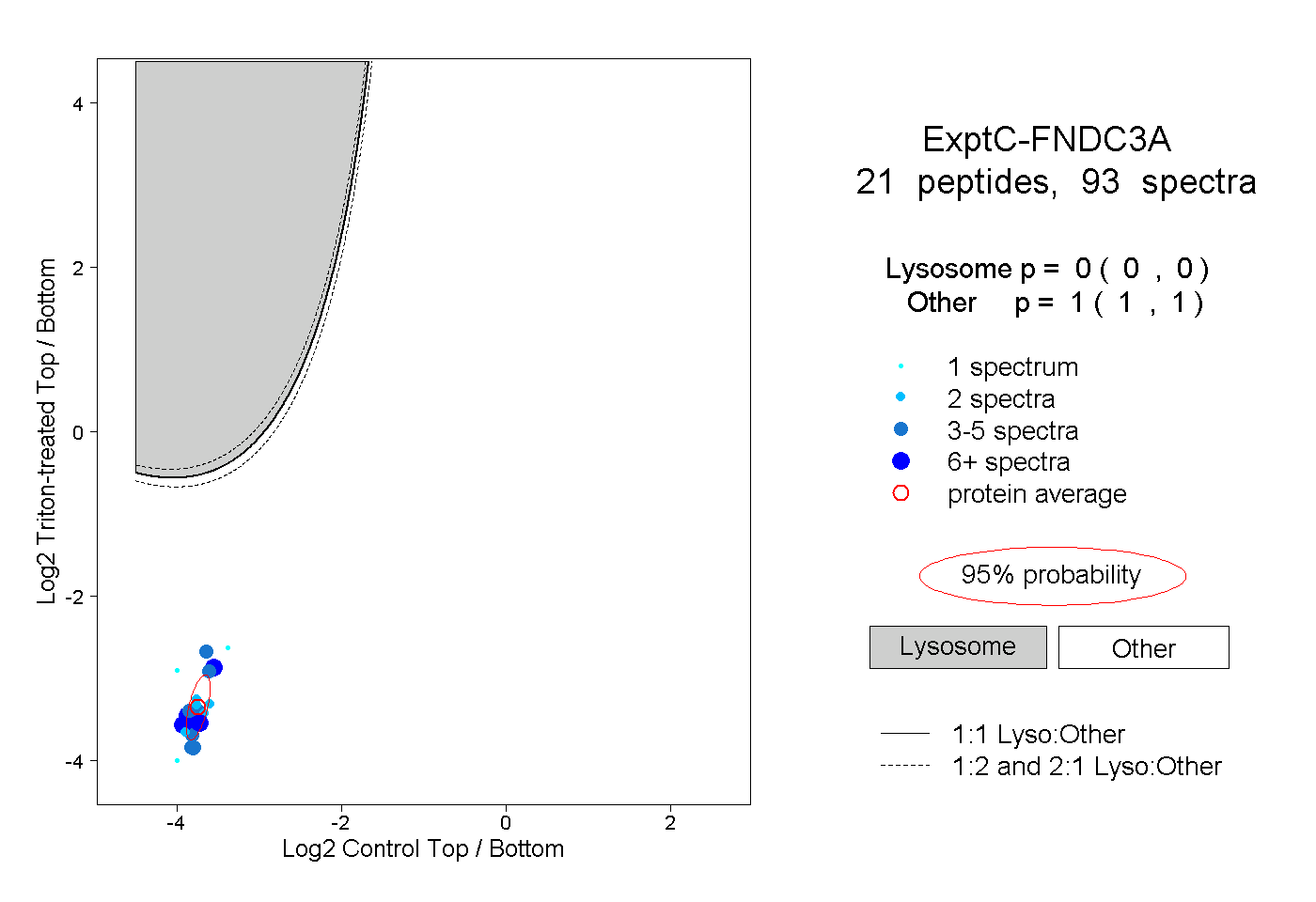
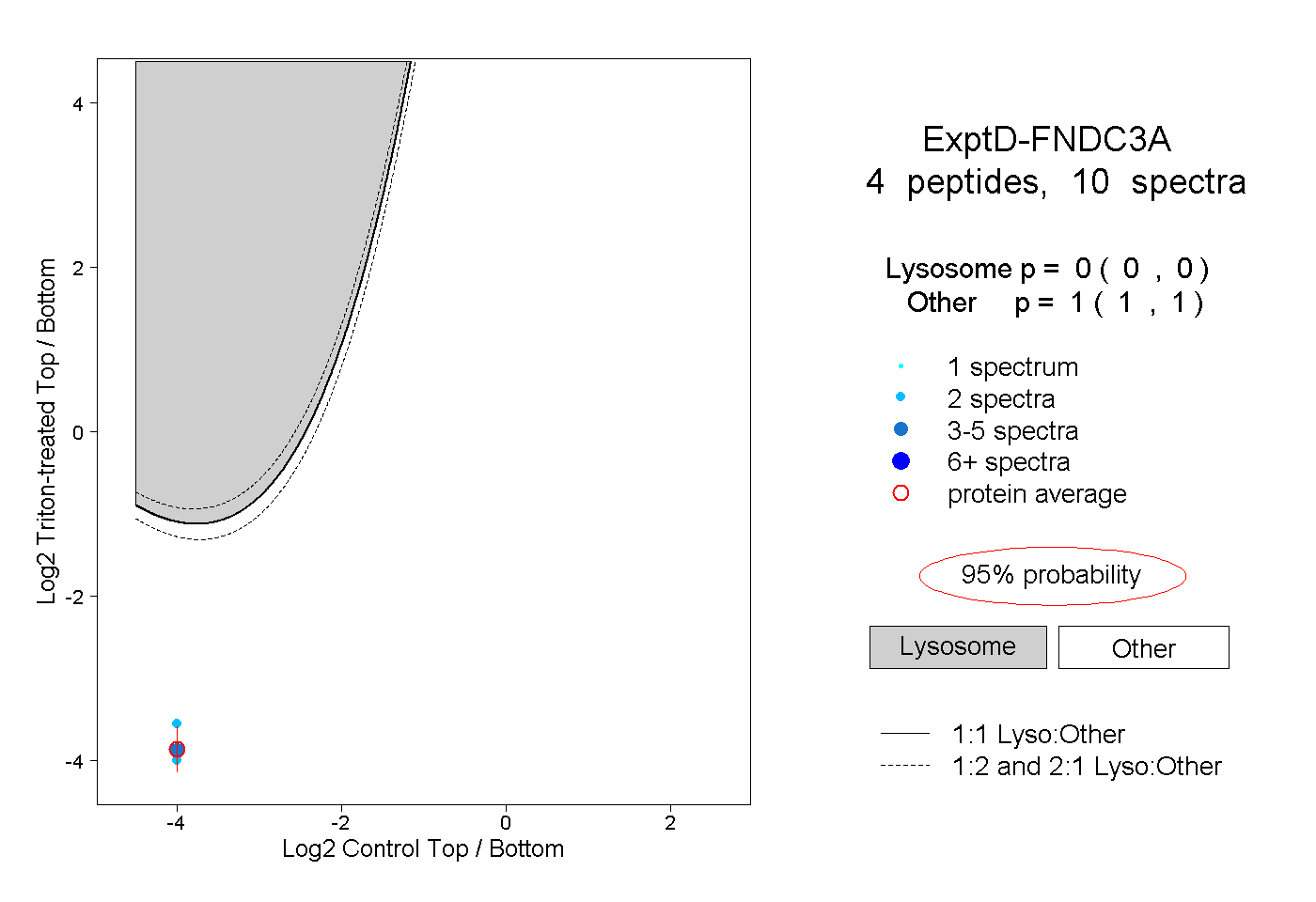
| 2 spectra, YDGEDLAYTVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, IGFGPFSEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GLSPATTYYCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YDITTAPGPPDQCRPPQVTCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LECVAFNHQNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IQALNSLGAGPFSHTIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LTPGCYYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, WGEGTPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, TLATDAVQYHLQMEDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GDPVIYNLQVMVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SVPAALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LSPAMGCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TEPLASSNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GPCHTYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DNGGAPINK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, GPDTSFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LSESTSYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, FVSLYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QPLTVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, VIAYNSEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EHLCDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |