peptides
spectra
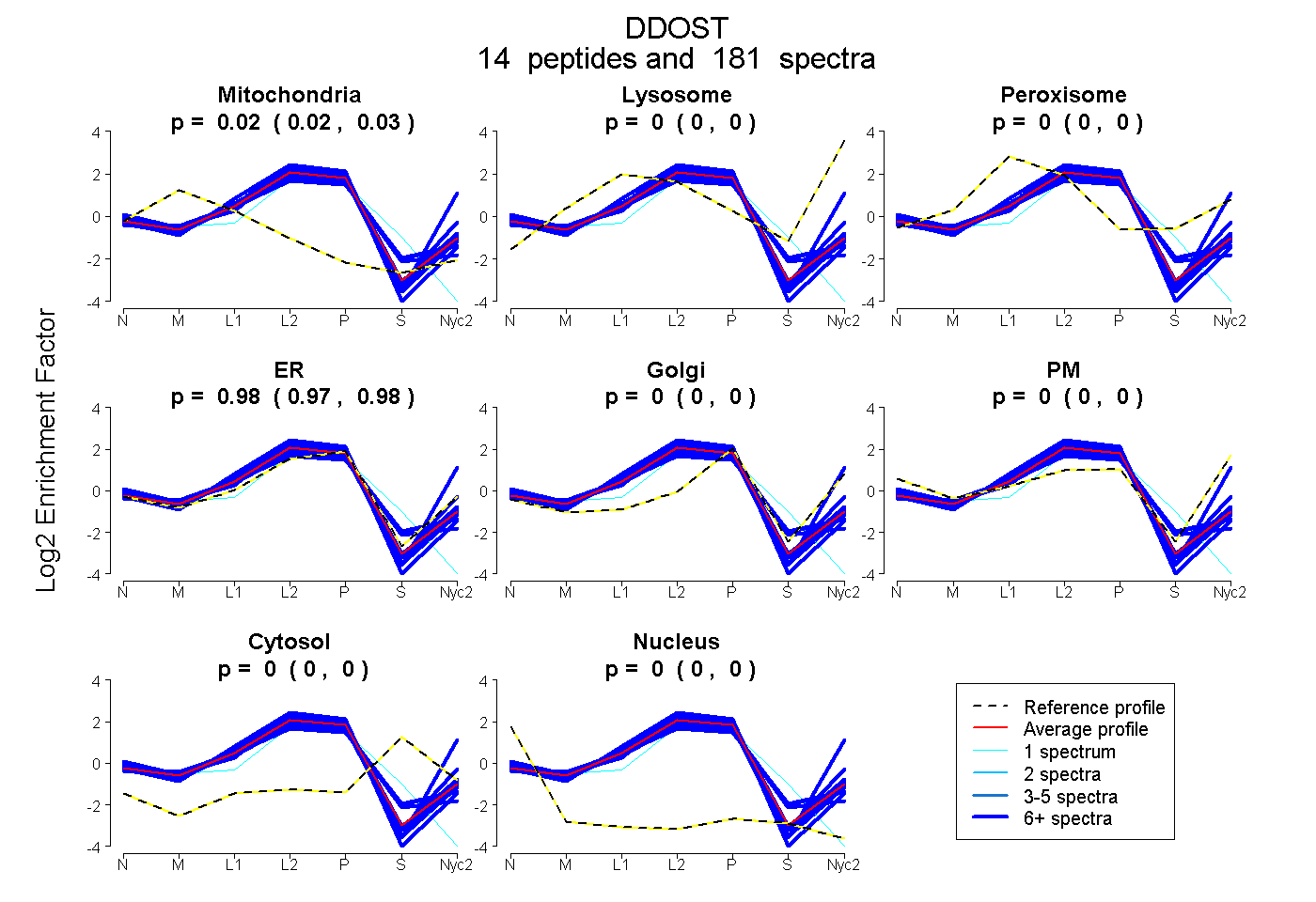
0.022 | 0.026
0.000 | 0.000
0.000 | 0.002
0.973 | 0.977
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra

0.000 | 0.000
0.113 | 0.123
0.876 | 0.886
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
181 spectra |
 |
0.024 0.022 | 0.026 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.976 0.973 | 0.977 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
105 spectra |
 |
0.000 0.000 | 0.000 |
0.118 0.113 | 0.123 |
0.882 0.876 | 0.886 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 13 spectra, TLVLLDNLNVR | 0.028 | 0.246 | 0.726 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, TADDPSLSLIK | 0.000 | 0.256 | 0.744 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LPDVYGVFQFK | 0.000 | 0.077 | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 22 spectra, GFELTFK | 0.000 | 0.143 | 0.857 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YSVQFK | 0.000 | 0.123 | 0.877 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, IDPFVR | 0.000 | 0.178 | 0.822 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, YSQTGNYELAVALSR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, DTHSLFFR | 0.000 | 0.238 | 0.762 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 23 spectra, SSLNPILFR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AAPGAGAR | 0.000 | 0.023 | 0.977 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, NTLLIAGLQAR | 0.000 | 0.072 | 0.928 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
305 spectra |
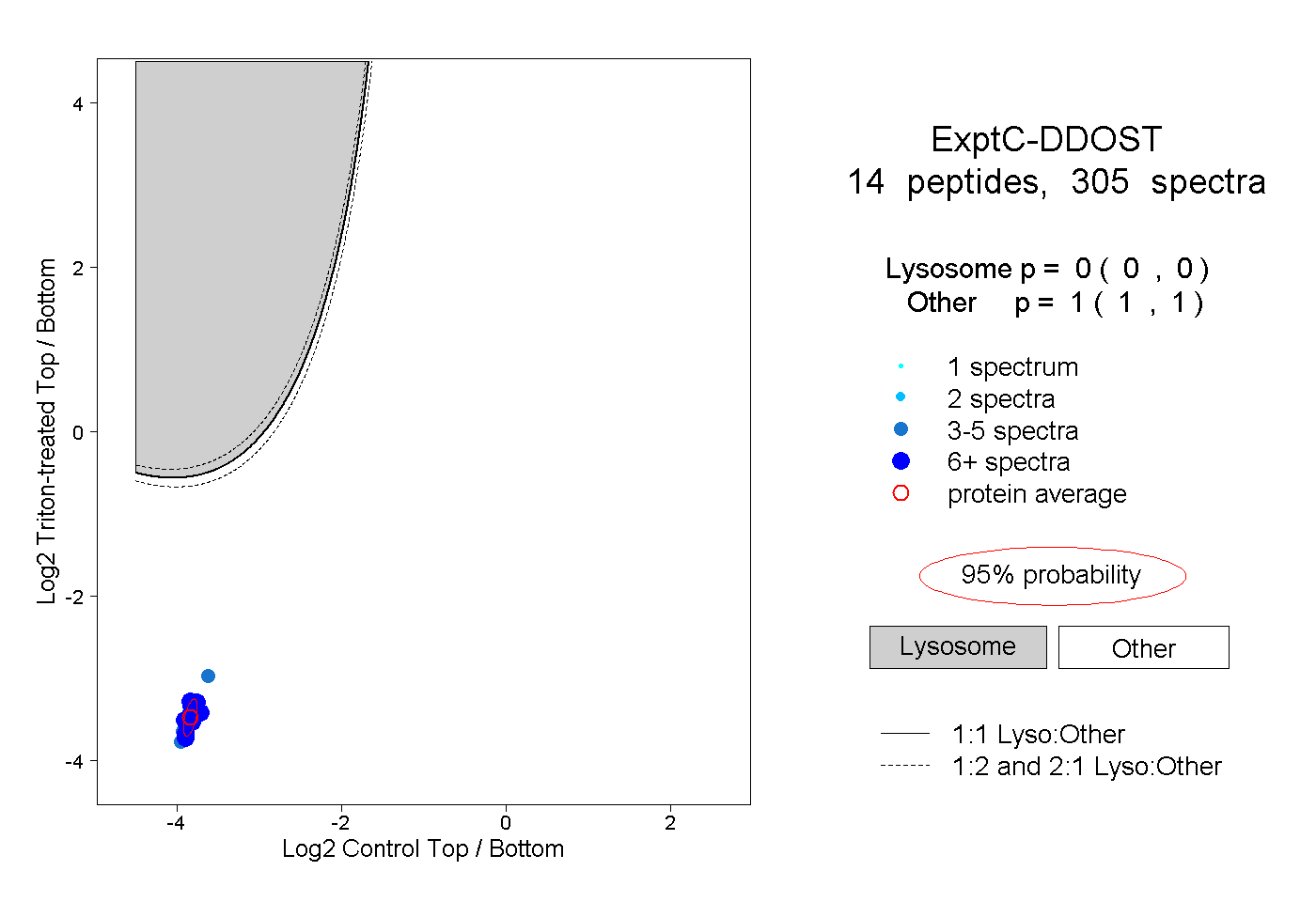 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
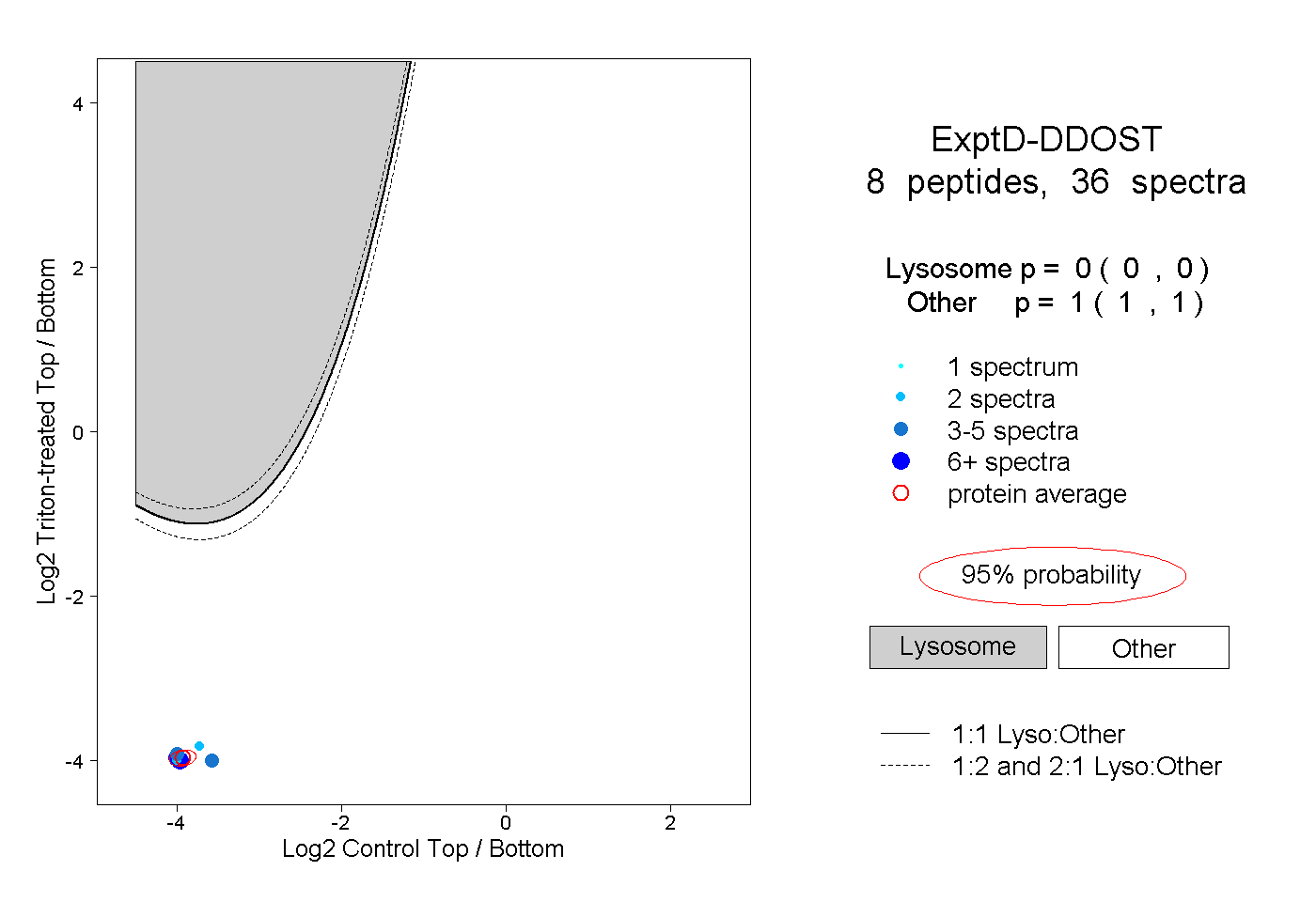 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |