peptides
spectra
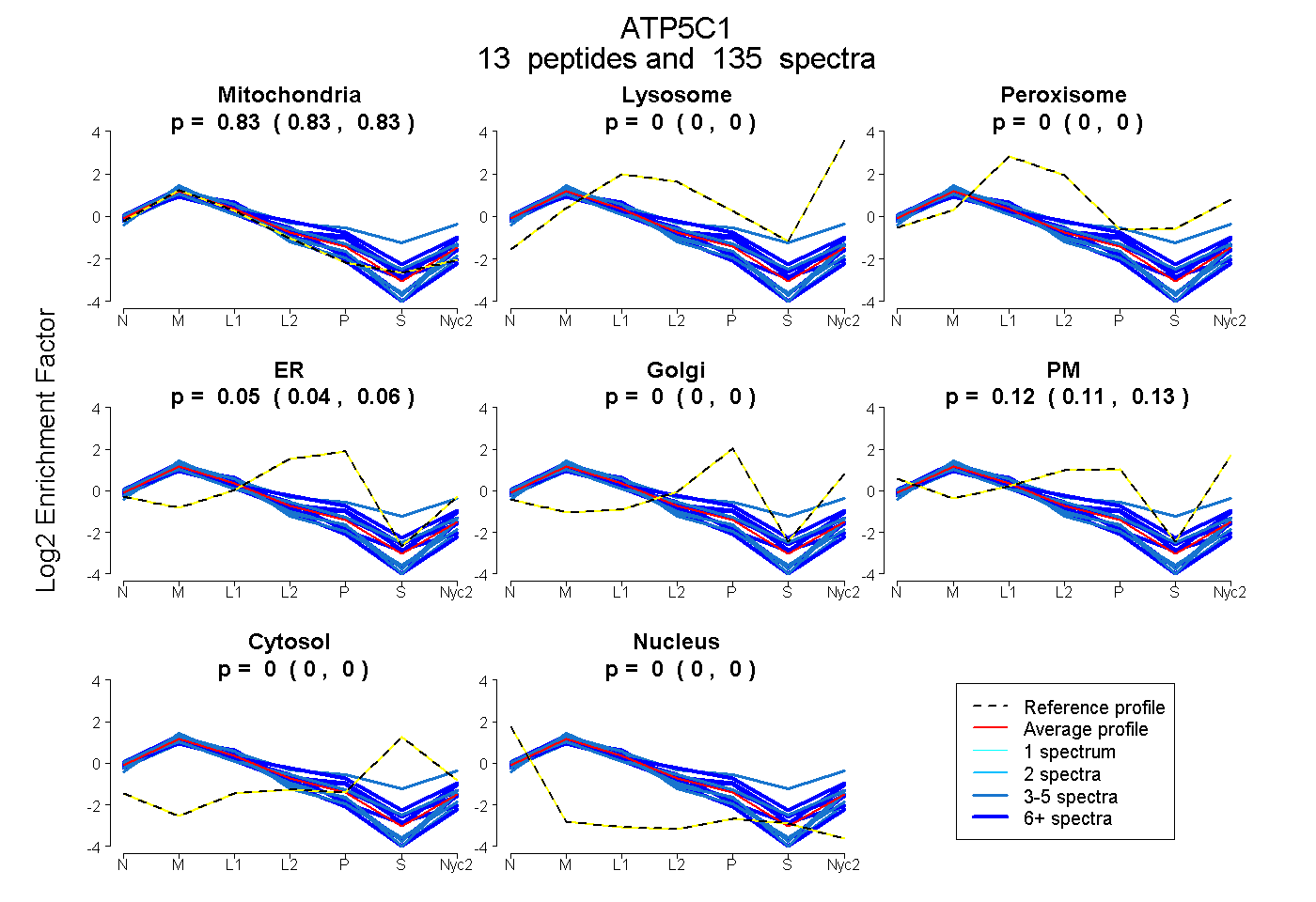
0.825 | 0.833
0.000 | 0.000
0.000 | 0.000
0.040 | 0.056
0.000 | 0.000
0.113 | 0.130
0.000 | 0.000
0.000 | 0.000
peptides
spectra
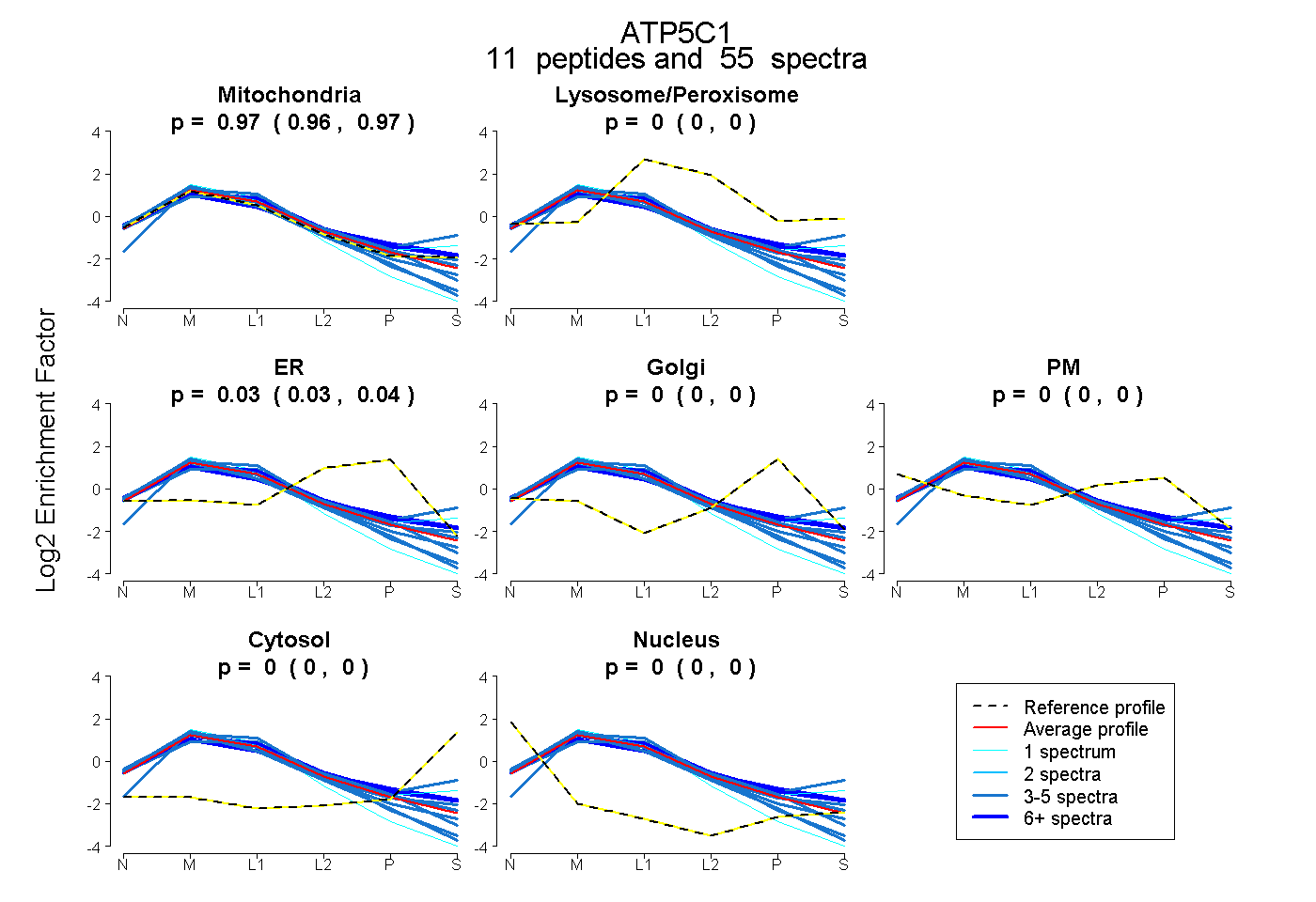
0.960 | 0.973
0.000 | 0.000
0.026 | 0.039
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
135 spectra |
 |
0.830 0.825 | 0.833 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.049 0.040 | 0.056 |
0.000 0.000 | 0.000 |
0.122 0.113 | 0.130 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
55 spectra |
 |
0.967 0.960 | 0.973 |
0.000 0.000 | 0.000 |
0.033 0.026 | 0.039 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, SVISYK | 0.946 | 0.054 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, LTLTFNR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QAVITK | 0.854 | 0.111 | 0.000 | 0.000 | 0.000 | 0.035 | 0.000 | |||
| 1 spectrum, ELKPAR | 0.996 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.004 | |||
| 5 spectra, ESTTSEQSAR | 0.979 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.021 | |||
| 3 spectra, GLCGAIHSSVAK | 0.714 | 0.186 | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | |||
| 4 spectra, THSDQFLVSFK | 0.928 | 0.000 | 0.072 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, HLIIGVSSDR | 0.868 | 0.094 | 0.038 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, NDMAALTAAGK | 0.961 | 0.000 | 0.000 | 0.000 | 0.039 | 0.000 | 0.000 | |||
| 14 spectra, EVMIVGIGEK | 0.804 | 0.061 | 0.000 | 0.059 | 0.076 | 0.000 | 0.000 | |||
| 5 spectra, VYGTGSLALYEK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
648 spectra |
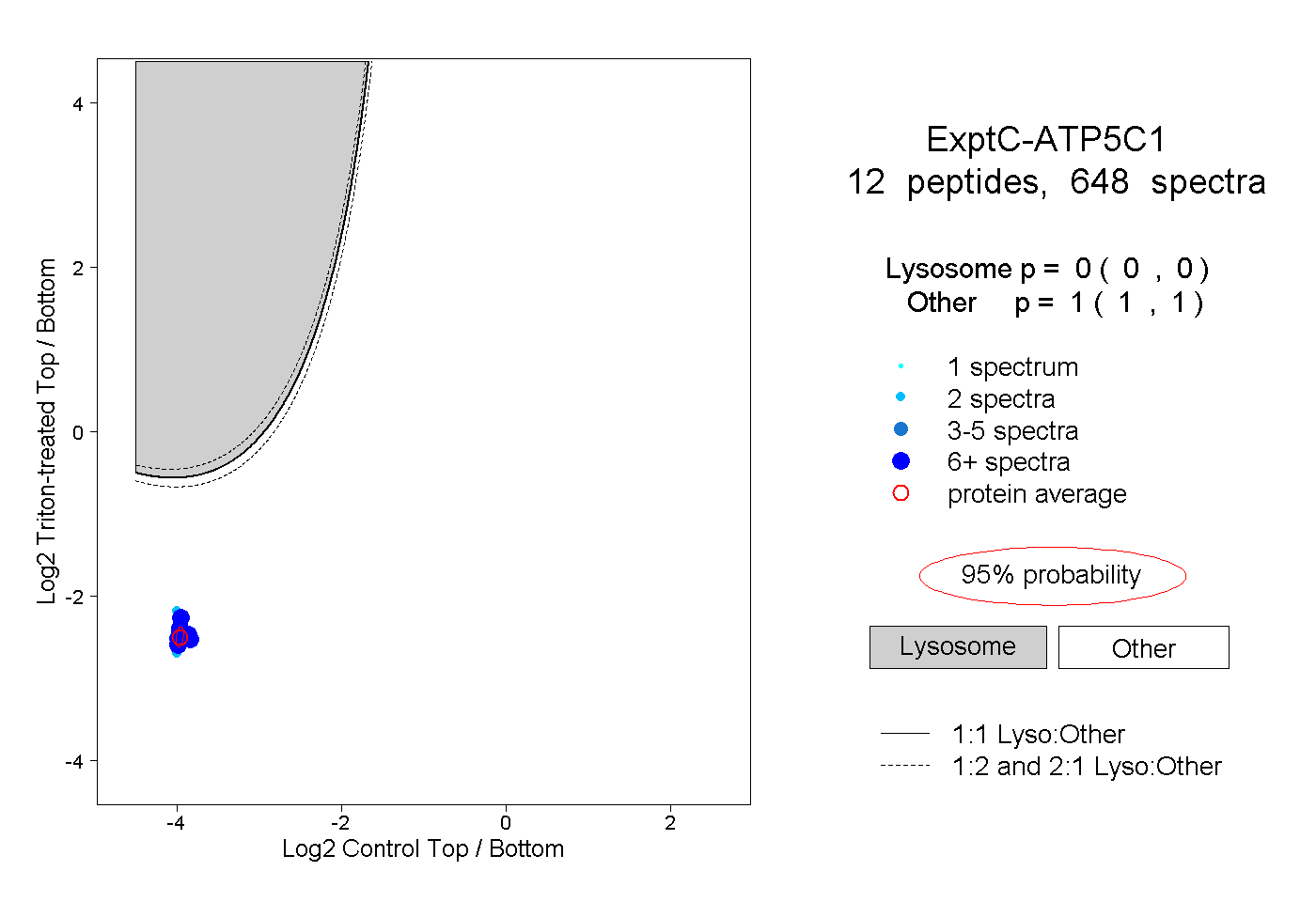 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
45 spectra |
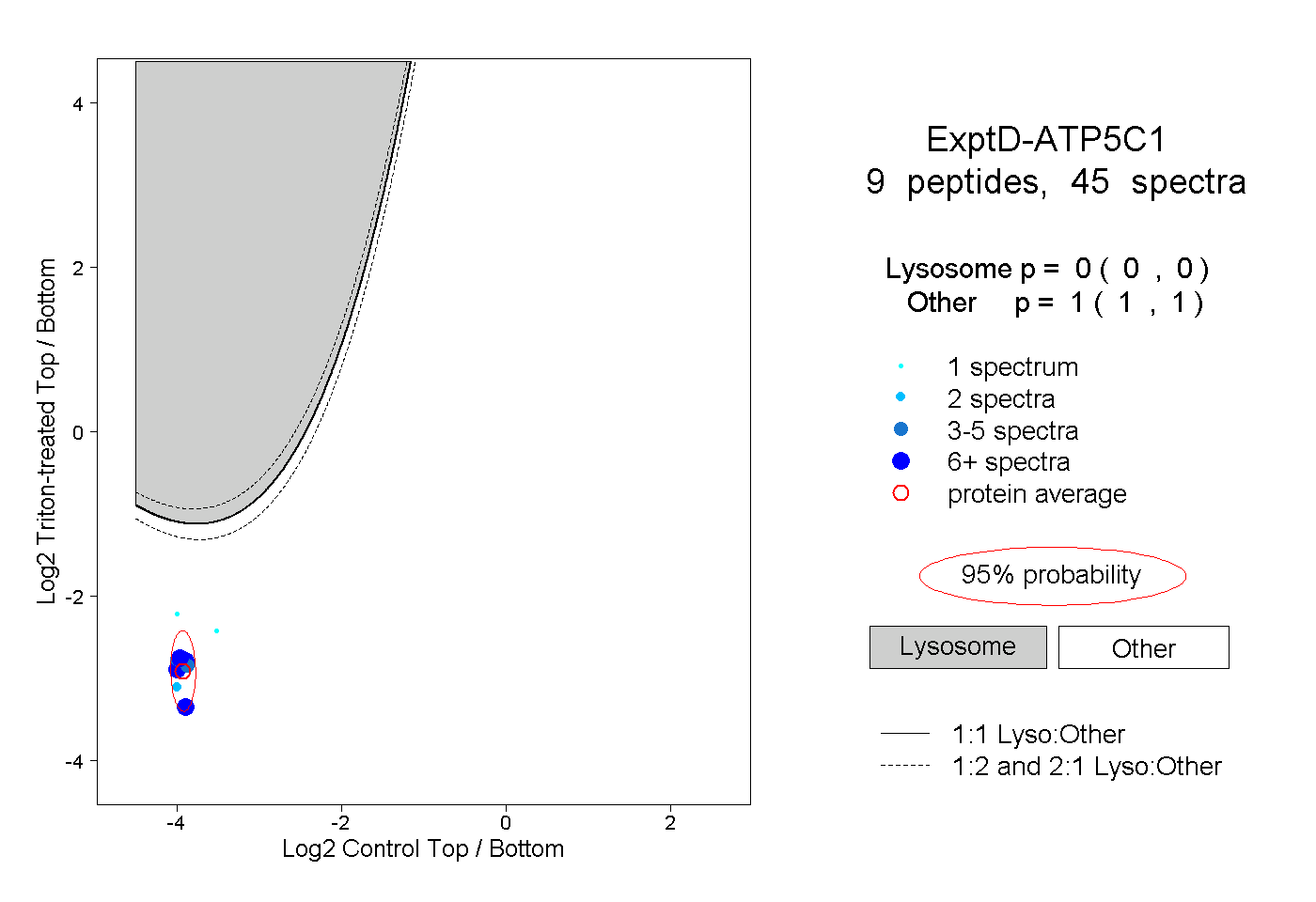 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |