peptides
spectra
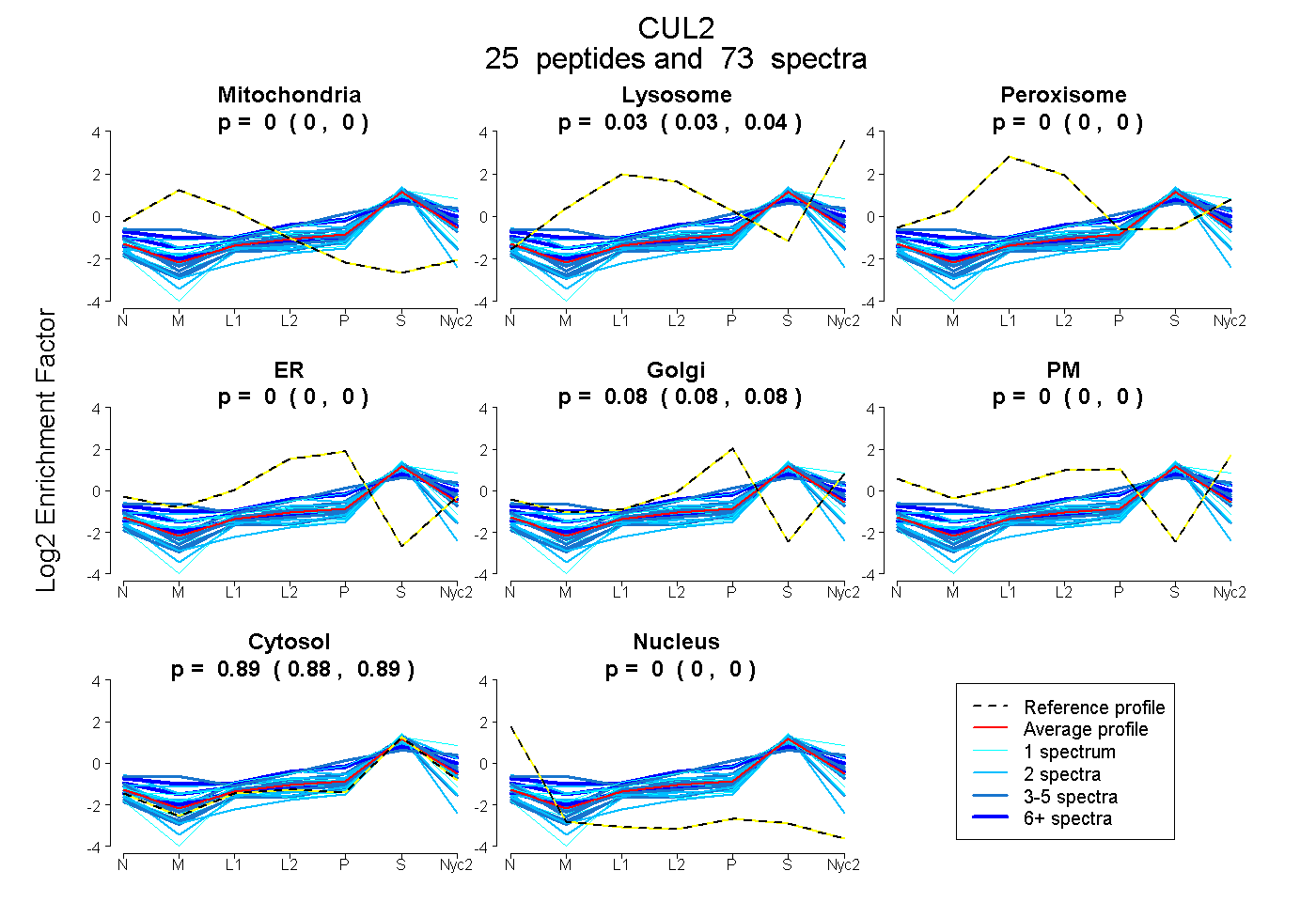
0.000 | 0.000
0.030 | 0.039
0.000 | 0.000
0.000 | 0.000
0.075 | 0.084
0.000 | 0.000
0.882 | 0.888
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
73 spectra |
 |
0.000 0.000 | 0.000 |
0.035 0.030 | 0.039 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.080 0.075 | 0.084 |
0.000 0.000 | 0.000 |
0.885 0.882 | 0.888 |
0.000 0.000 | 0.000 |
| 4 spectra, YLNTQYIK | 0.000 | 0.122 | 0.000 | 0.000 | 0.147 | 0.165 | 0.567 | 0.000 | ||
| 3 spectra, SLLDVK | 0.000 | 0.056 | 0.000 | 0.000 | 0.019 | 0.000 | 0.925 | 0.000 | ||
| 2 spectra, VIHECQQR | 0.085 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.912 | 0.003 | ||
| 1 spectrum, QACGYEFTSK | 0.143 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.857 | 0.000 | ||
| 2 spectra, LLTTIK | 0.006 | 0.000 | 0.013 | 0.000 | 0.120 | 0.000 | 0.862 | 0.000 | ||
| 6 spectra, MYLQAAIVR | 0.000 | 0.059 | 0.000 | 0.000 | 0.028 | 0.000 | 0.913 | 0.000 | ||
| 2 spectra, ITTSMQK | 0.039 | 0.130 | 0.027 | 0.000 | 0.025 | 0.045 | 0.733 | 0.000 | ||
| 6 spectra, FNNFIR | 0.000 | 0.142 | 0.000 | 0.000 | 0.128 | 0.045 | 0.686 | 0.000 | ||
| 4 spectra, GADYMDCLYR | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.000 | 0.866 | 0.027 | ||
| 4 spectra, LMVEPLQNILIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 8 spectra, VLESEEQVLVMYHR | 0.000 | 0.047 | 0.090 | 0.000 | 0.120 | 0.113 | 0.631 | 0.000 | ||
| 2 spectra, YCDNLLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.866 | 0.134 | ||
| 1 spectrum, FNPSISMIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, VVDFDETWNK | 0.000 | 0.017 | 0.000 | 0.000 | 0.000 | 0.087 | 0.896 | 0.000 | ||
| 3 spectra, GMTENEVEDK | 0.000 | 0.000 | 0.000 | 0.013 | 0.068 | 0.000 | 0.919 | 0.000 | ||
| 1 spectrum, QEASNLLQESNCSQYMEK | 0.000 | 0.190 | 0.000 | 0.000 | 0.000 | 0.000 | 0.810 | 0.000 | ||
| 2 spectra, HIHDEGLR | 0.000 | 0.000 | 0.049 | 0.000 | 0.000 | 0.233 | 0.718 | 0.000 | ||
| 2 spectra, LTSFITVFK | 0.004 | 0.078 | 0.000 | 0.000 | 0.007 | 0.000 | 0.911 | 0.000 | ||
| 1 spectrum, MYTDMSVSADLNNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DTPQELEQTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 5 spectra, AVVMLEYVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, GGEDPNQK | 0.000 | 0.002 | 0.005 | 0.000 | 0.000 | 0.115 | 0.878 | 0.000 | ||
| 4 spectra, ELQDSTQMNEK | 0.000 | 0.001 | 0.094 | 0.000 | 0.046 | 0.007 | 0.853 | 0.000 | ||
| 2 spectra, IFLENHVR | 0.000 | 0.047 | 0.000 | 0.000 | 0.041 | 0.000 | 0.912 | 0.000 | ||
| 1 spectrum, YWEEYSK | 0.000 | 0.066 | 0.010 | 0.164 | 0.000 | 0.000 | 0.760 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
19 spectra |
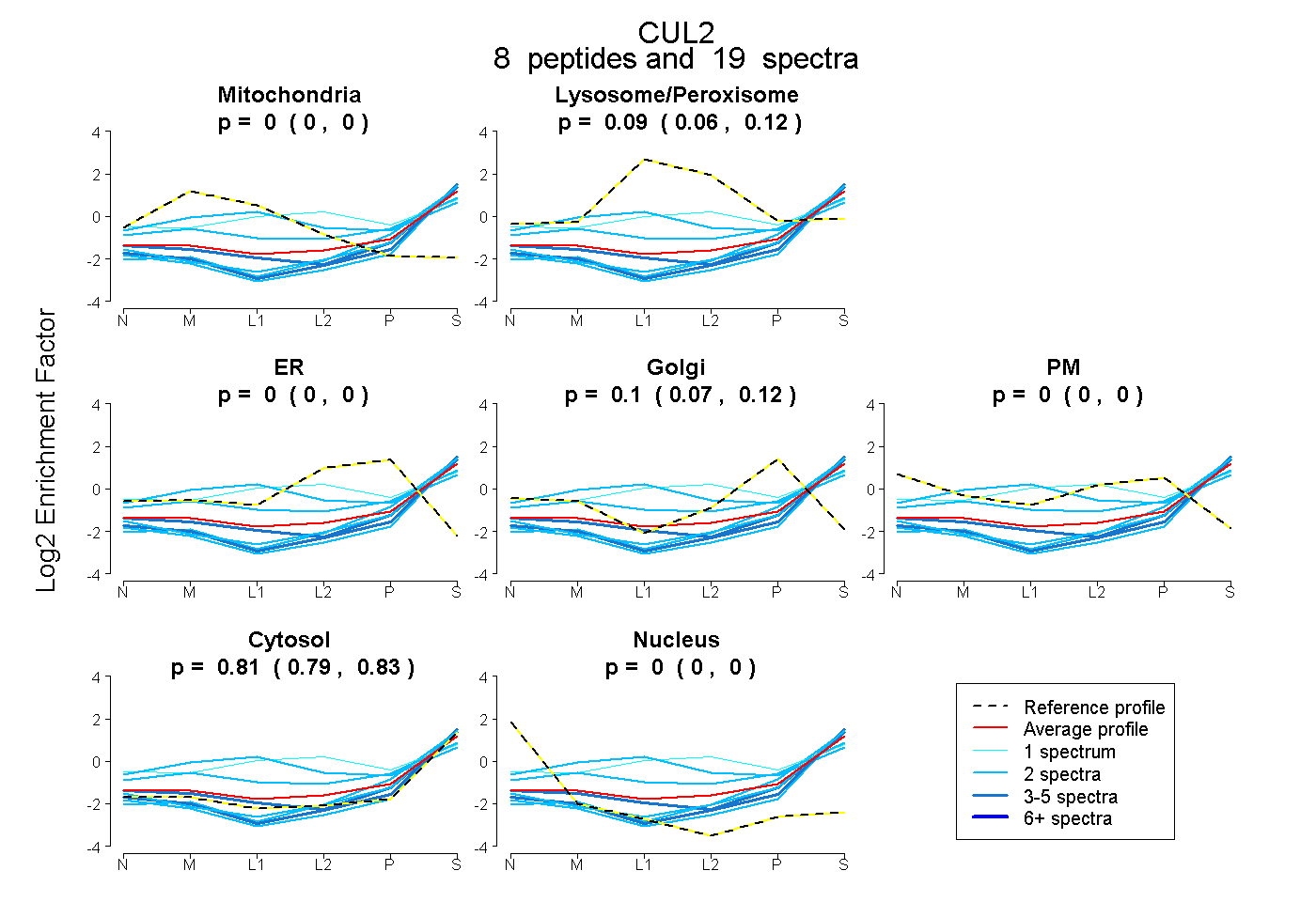 |
0.000 0.000 | 0.000 |
0.091 0.057 | 0.118 |
0.000 0.000 | 0.000 |
0.099 0.073 | 0.121 |
0.000 0.000 | 0.004 |
0.809 0.790 | 0.827 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
60 spectra |
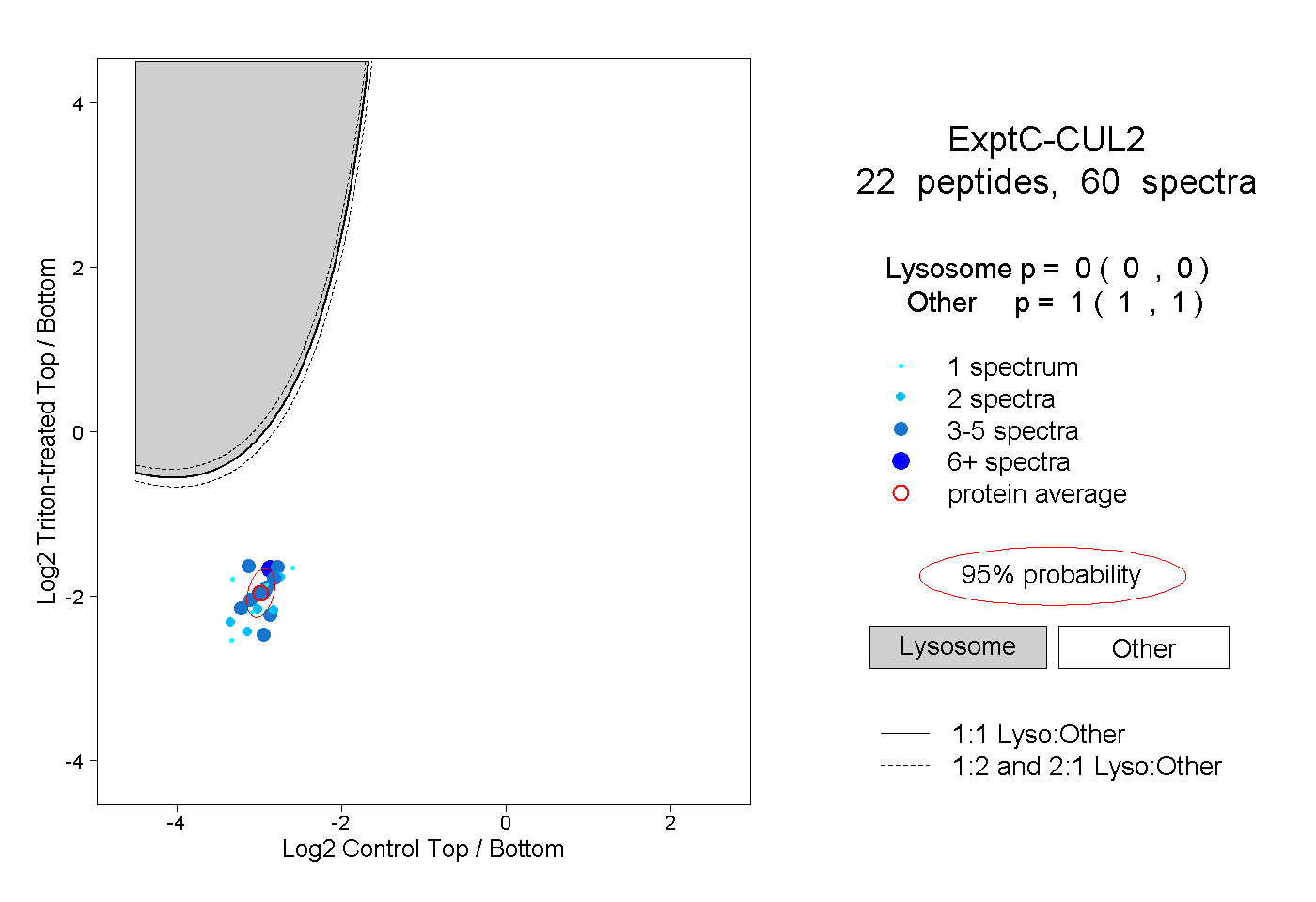 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
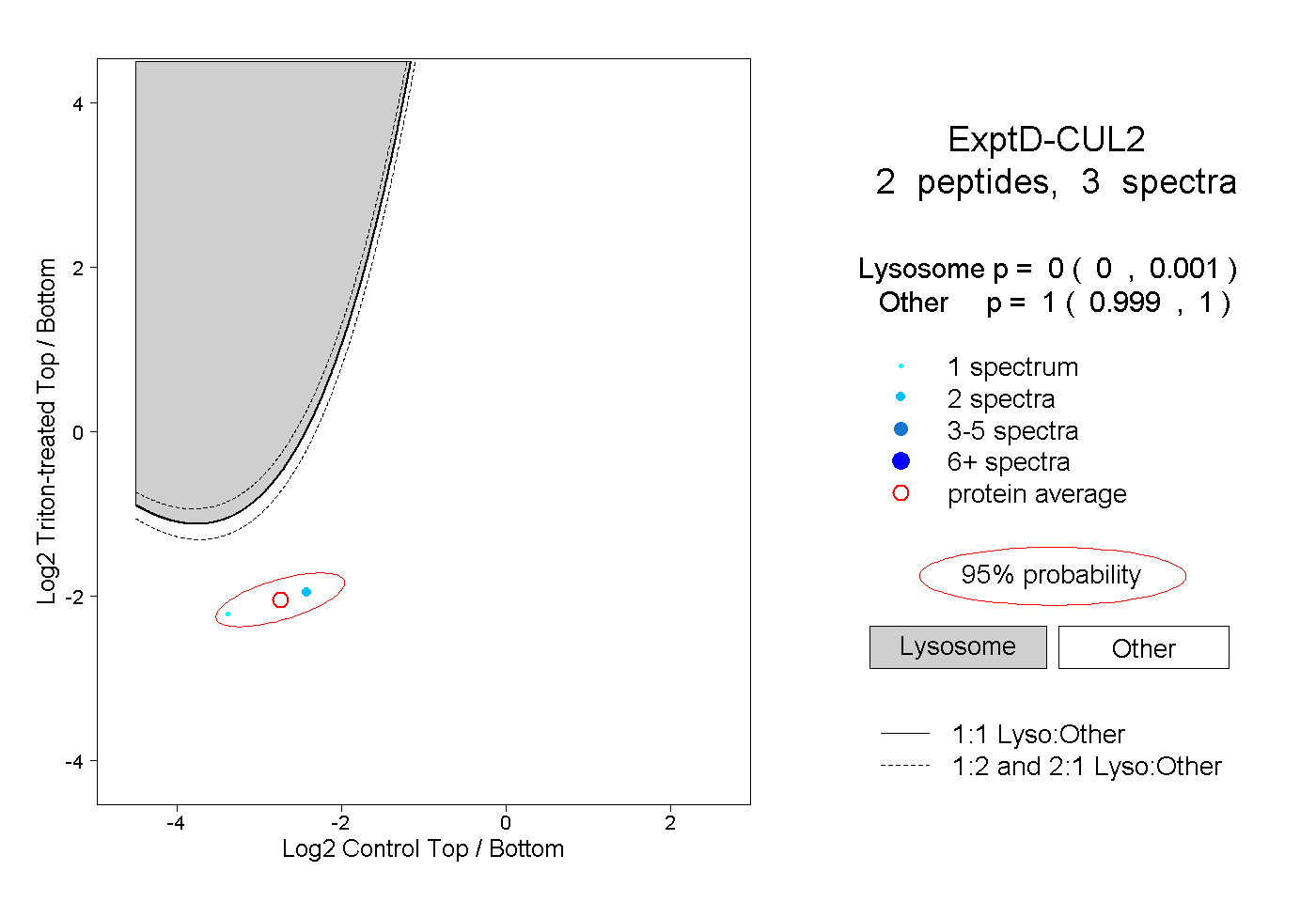 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |