peptides
spectra
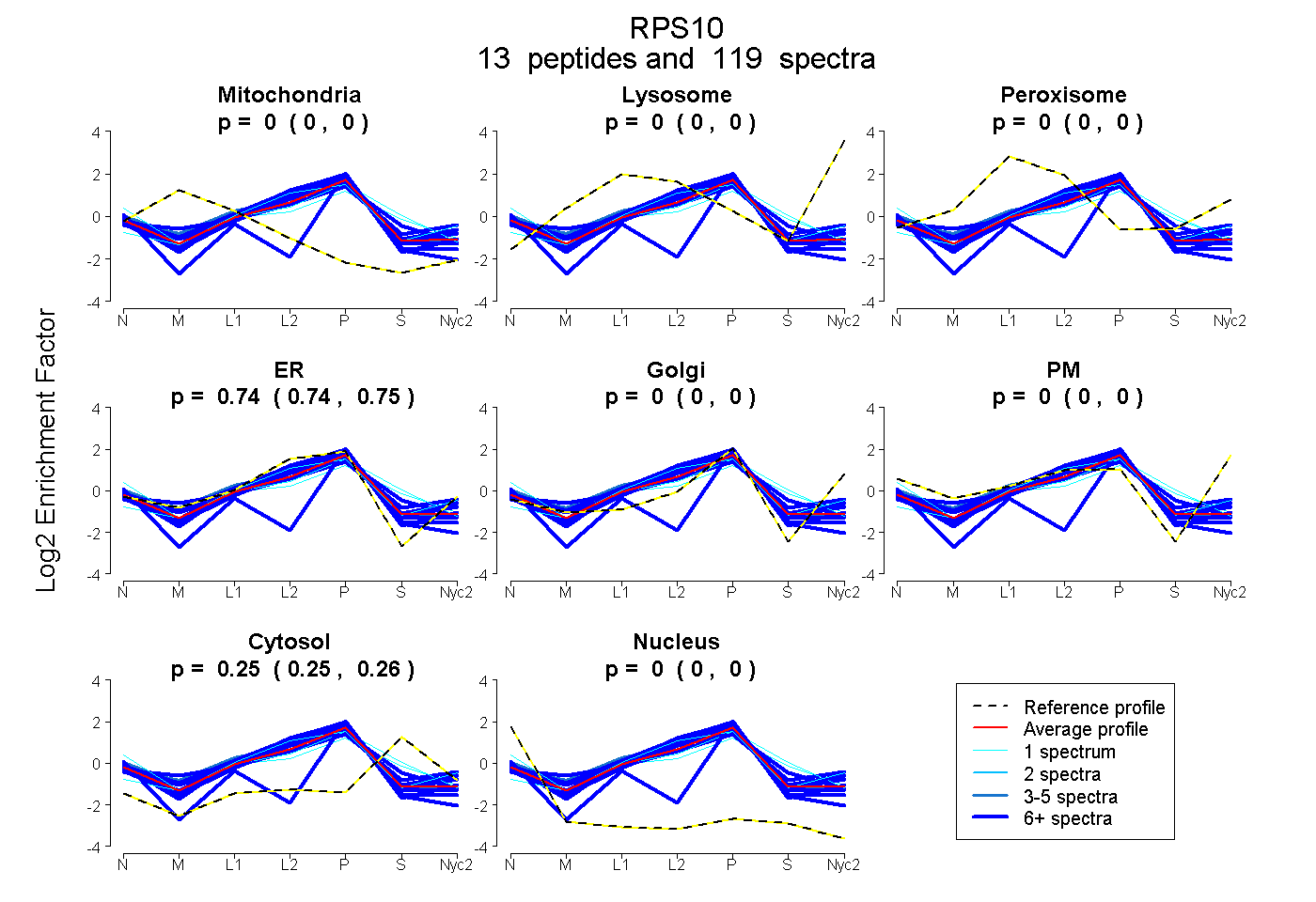
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.741 | 0.748
0.000 | 0.000
0.000 | 0.000
0.250 | 0.257
0.000 | 0.004
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
119 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.745 0.741 | 0.748 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.254 0.250 | 0.257 |
0.001 0.000 | 0.004 |
| 9 spectra, DYLHLPPEIVPATLR | 0.000 | 0.000 | 0.115 | 0.516 | 0.132 | 0.000 | 0.237 | 0.000 | ||
| 11 spectra, SAVPPGADK | 0.000 | 0.000 | 0.000 | 0.158 | 0.426 | 0.000 | 0.145 | 0.270 | ||
| 12 spectra, GPEGERPAR | 0.000 | 0.000 | 0.000 | 0.848 | 0.000 | 0.000 | 0.141 | 0.011 | ||
| 1 spectrum, MLMPK | 0.000 | 0.000 | 0.039 | 0.553 | 0.000 | 0.000 | 0.408 | 0.000 | ||
| 1 spectrum, AEAGAGSATEFQFR | 0.000 | 0.000 | 0.092 | 0.532 | 0.000 | 0.000 | 0.376 | 0.000 | ||
| 9 spectra, NVPNLHVMK | 0.000 | 0.000 | 0.022 | 0.745 | 0.000 | 0.000 | 0.233 | 0.000 | ||
| 13 spectra, IAIYELLFK | 0.000 | 0.000 | 0.000 | 0.818 | 0.000 | 0.000 | 0.157 | 0.025 | ||
| 31 spectra, HPELADK | 0.000 | 0.000 | 0.000 | 0.647 | 0.000 | 0.000 | 0.353 | 0.000 | ||
| 1 spectrum, SRPETGRPRPK | 0.000 | 0.000 | 0.047 | 0.715 | 0.000 | 0.041 | 0.197 | 0.000 | ||
| 15 spectra, EGVMVAK | 0.000 | 0.000 | 0.055 | 0.773 | 0.000 | 0.000 | 0.172 | 0.000 | ||
| 7 spectra, EQFAWR | 0.000 | 0.000 | 0.000 | 0.792 | 0.000 | 0.000 | 0.205 | 0.003 | ||
| 5 spectra, DVHMPK | 0.000 | 0.000 | 0.046 | 0.761 | 0.000 | 0.000 | 0.193 | 0.000 | ||
| 4 spectra, AMQSLK | 0.006 | 0.000 | 0.045 | 0.760 | 0.000 | 0.000 | 0.189 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
52 spectra |
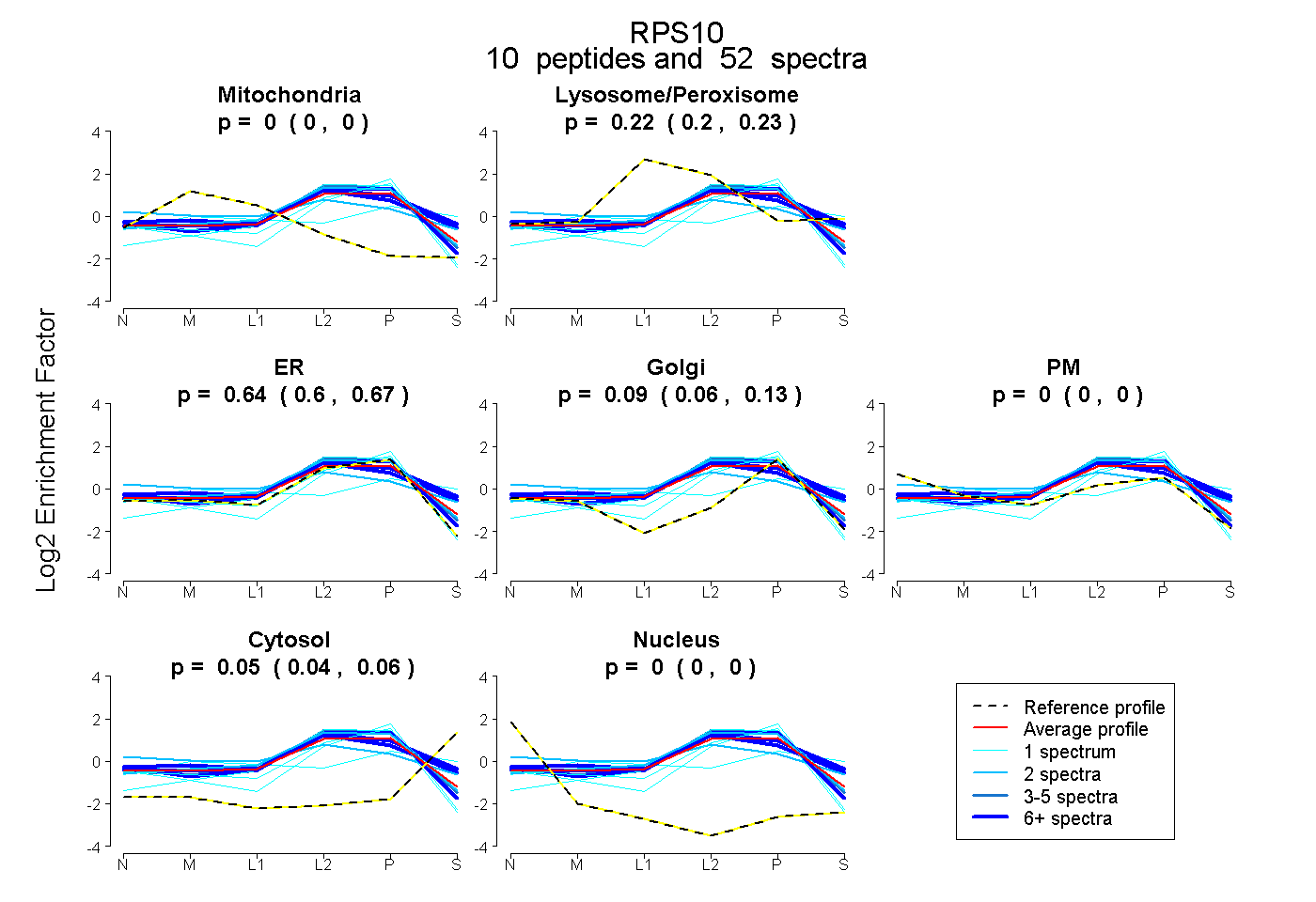 |
0.000 0.000 | 0.000 |
0.217 0.203 | 0.228 |
0.640 0.598 | 0.675 |
0.093 0.056 | 0.125 |
0.000 0.000 | 0.000 |
0.049 0.038 | 0.058 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
163 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
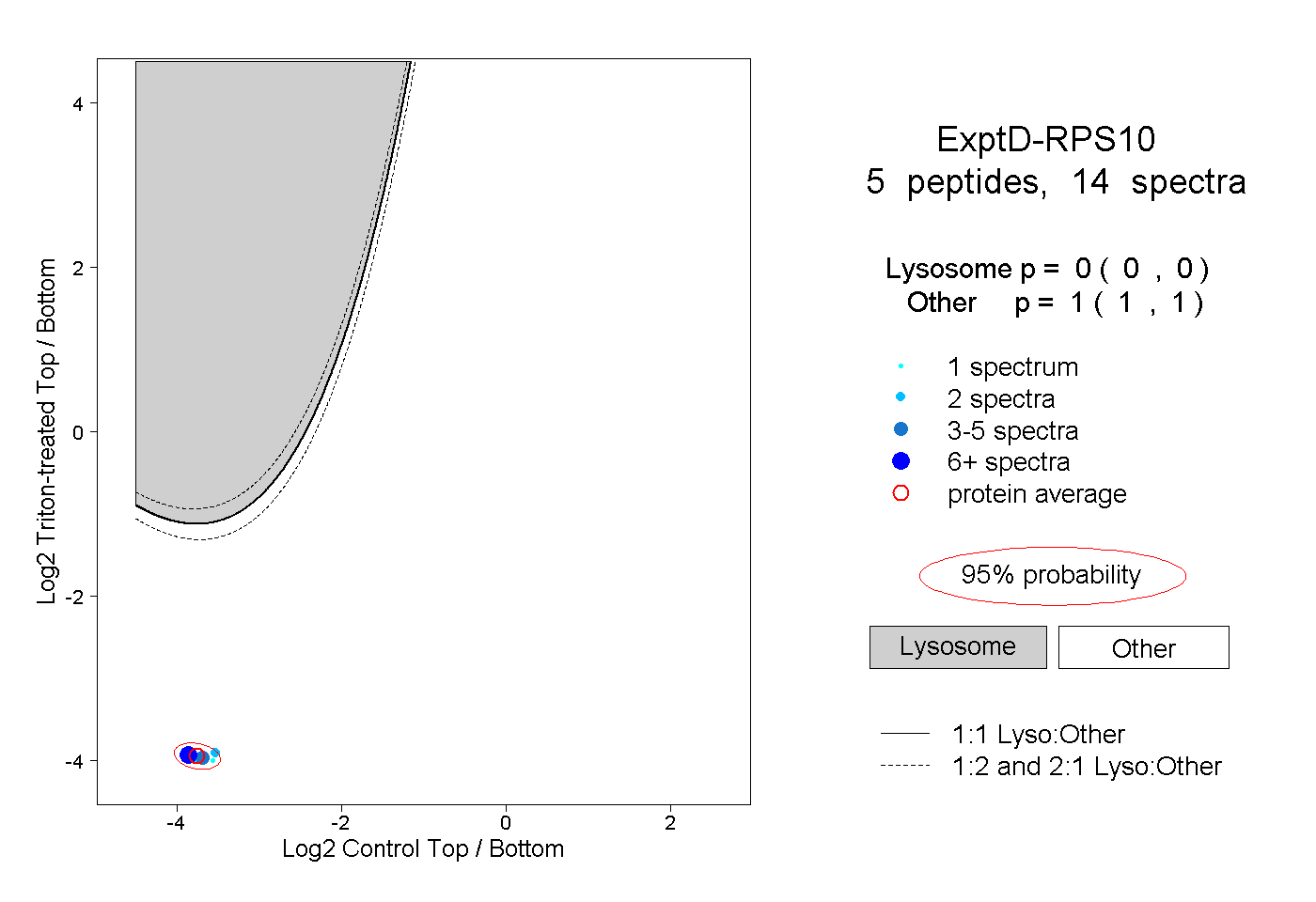 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |