peptides
spectra
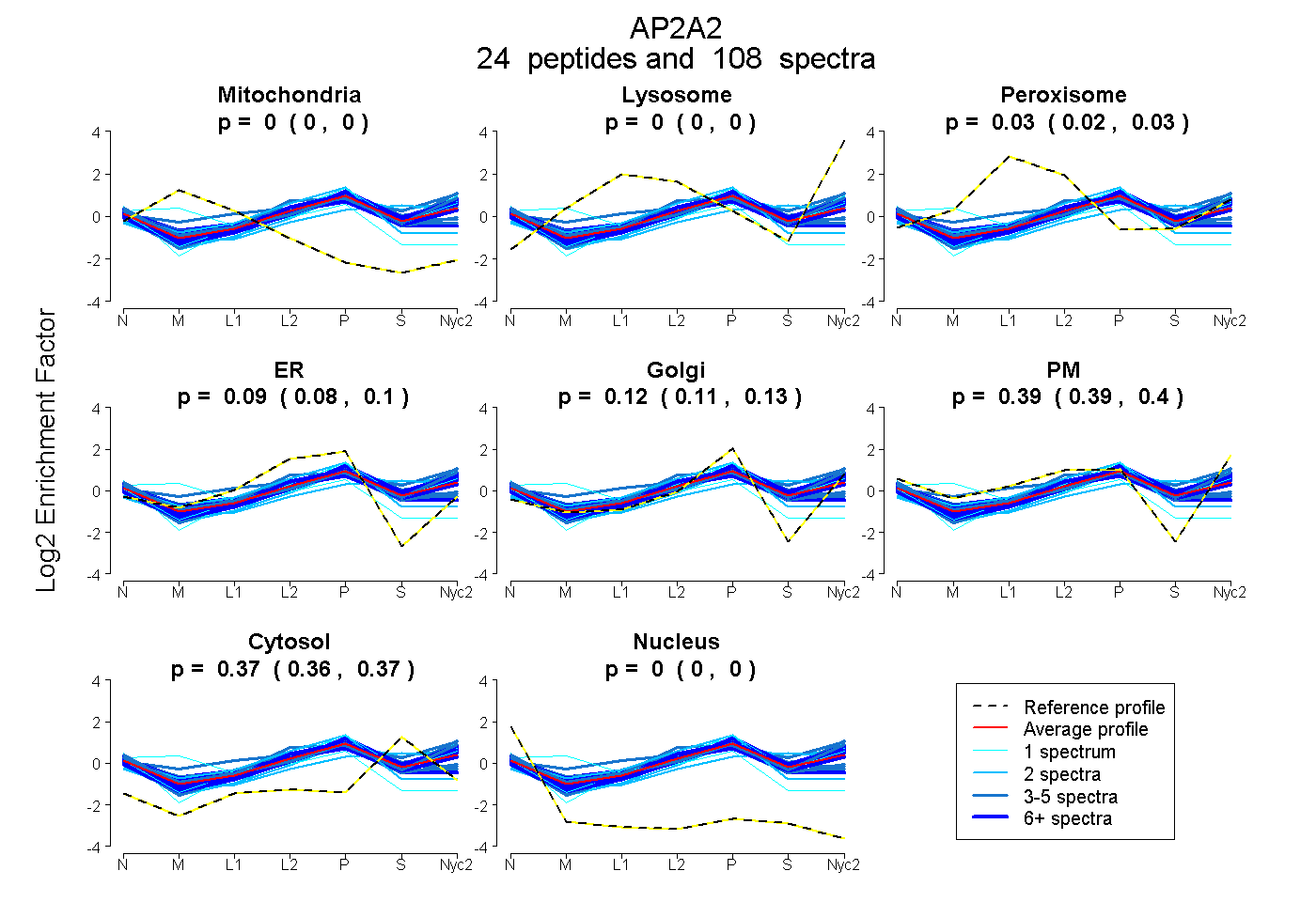
0.000 | 0.000
0.000 | 0.000
0.023 | 0.030
0.085 | 0.103
0.109 | 0.126
0.387 | 0.400
0.364 | 0.369
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
108 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.027 0.023 | 0.030 |
0.094 0.085 | 0.103 |
0.118 0.109 | 0.126 |
0.394 0.387 | 0.400 |
0.367 0.364 | 0.369 |
0.000 0.000 | 0.000 |
| 2 spectra, DTVSQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.246 | 0.335 | 0.420 | 0.000 | ||
| 7 spectra, TSVSLAVSR | 0.000 | 0.019 | 0.029 | 0.000 | 0.162 | 0.477 | 0.312 | 0.000 | ||
| 3 spectra, FHLCSVPTR | 0.000 | 0.000 | 0.082 | 0.360 | 0.000 | 0.204 | 0.353 | 0.000 | ||
| 9 spectra, VIQIVINR | 0.000 | 0.000 | 0.000 | 0.002 | 0.092 | 0.557 | 0.349 | 0.000 | ||
| 7 spectra, SSPLIQFNLLHSK | 0.000 | 0.000 | 0.104 | 0.000 | 0.279 | 0.294 | 0.323 | 0.000 | ||
| 6 spectra, AVEYLR | 0.000 | 0.000 | 0.018 | 0.007 | 0.133 | 0.470 | 0.372 | 0.000 | ||
| 4 spectra, LTECLETILNK | 0.000 | 0.000 | 0.000 | 0.334 | 0.047 | 0.225 | 0.394 | 0.000 | ||
| 3 spectra, THIETVINALK | 0.000 | 0.017 | 0.002 | 0.000 | 0.000 | 0.661 | 0.320 | 0.000 | ||
| 9 spectra, MFIFYGNK | 0.000 | 0.000 | 0.067 | 0.113 | 0.033 | 0.442 | 0.346 | 0.000 | ||
| 8 spectra, SDSQLK | 0.000 | 0.000 | 0.034 | 0.000 | 0.344 | 0.257 | 0.366 | 0.000 | ||
| 4 spectra, LEPNLQAQMYR | 0.000 | 0.000 | 0.002 | 0.035 | 0.237 | 0.318 | 0.408 | 0.000 | ||
| 1 spectrum, ATIQDVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.226 | 0.442 | 0.332 | 0.000 | ||
| 1 spectrum, TVFEALQAPACHENLVK | 0.000 | 0.000 | 0.021 | 0.093 | 0.234 | 0.328 | 0.324 | 0.000 | ||
| 11 spectra, NPEEFK | 0.000 | 0.004 | 0.000 | 0.000 | 0.146 | 0.461 | 0.389 | 0.000 | ||
| 5 spectra, TSPDLVPMGDWTSR | 0.000 | 0.015 | 0.045 | 0.000 | 0.151 | 0.484 | 0.306 | 0.000 | ||
| 9 spectra, AVDLLYAMCDR | 0.000 | 0.000 | 0.000 | 0.375 | 0.013 | 0.209 | 0.367 | 0.036 | ||
| 1 spectrum, QLSNPQQEVQNIFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.230 | 0.421 | 0.350 | 0.000 | ||
| 4 spectra, ILVAGDTMDSVK | 0.000 | 0.128 | 0.000 | 0.000 | 0.033 | 0.408 | 0.431 | 0.000 | ||
| 2 spectra, TTQIGCLLR | 0.007 | 0.000 | 0.034 | 0.673 | 0.000 | 0.000 | 0.284 | 0.002 | ||
| 2 spectra, FVNLFPEVK | 0.000 | 0.089 | 0.000 | 0.024 | 0.219 | 0.238 | 0.431 | 0.000 | ||
| 2 spectra, LPITLNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.066 | 0.368 | 0.566 | 0.000 | ||
| 4 spectra, YGGTFQNVSVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.090 | 0.572 | 0.338 | 0.000 | ||
| 3 spectra, LLQCYPPPEDPAVR | 0.041 | 0.000 | 0.241 | 0.177 | 0.160 | 0.137 | 0.244 | 0.000 | ||
| 1 spectrum, NPTFMGLALHCIANVGSR | 0.365 | 0.000 | 0.000 | 0.399 | 0.096 | 0.000 | 0.137 | 0.003 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
59 spectra |
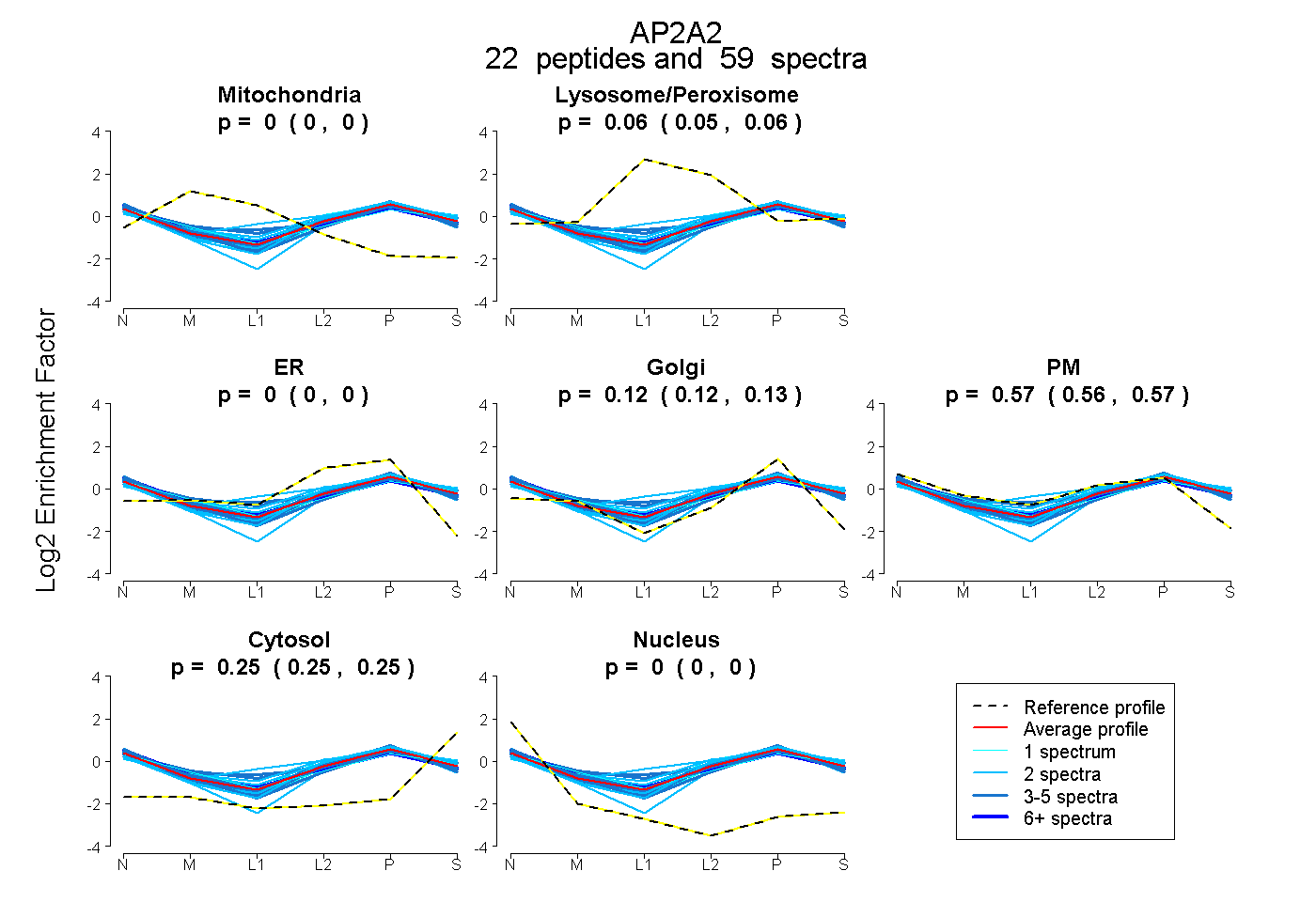 |
0.000 0.000 | 0.000 |
0.058 0.054 | 0.061 |
0.000 0.000 | 0.000 |
0.122 0.117 | 0.126 |
0.569 0.562 | 0.574 |
0.252 0.249 | 0.253 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
273 spectra |
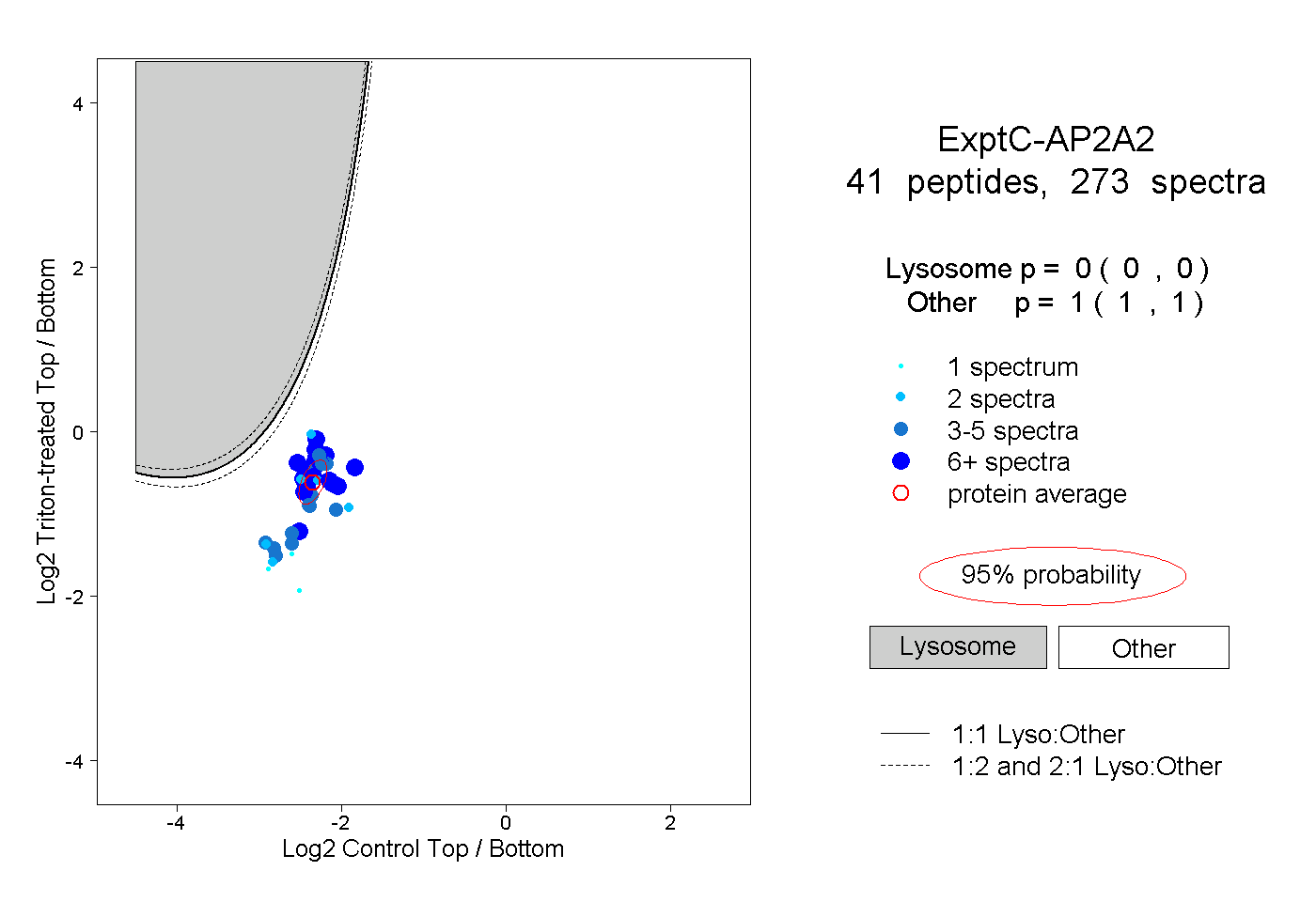 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
29 spectra |
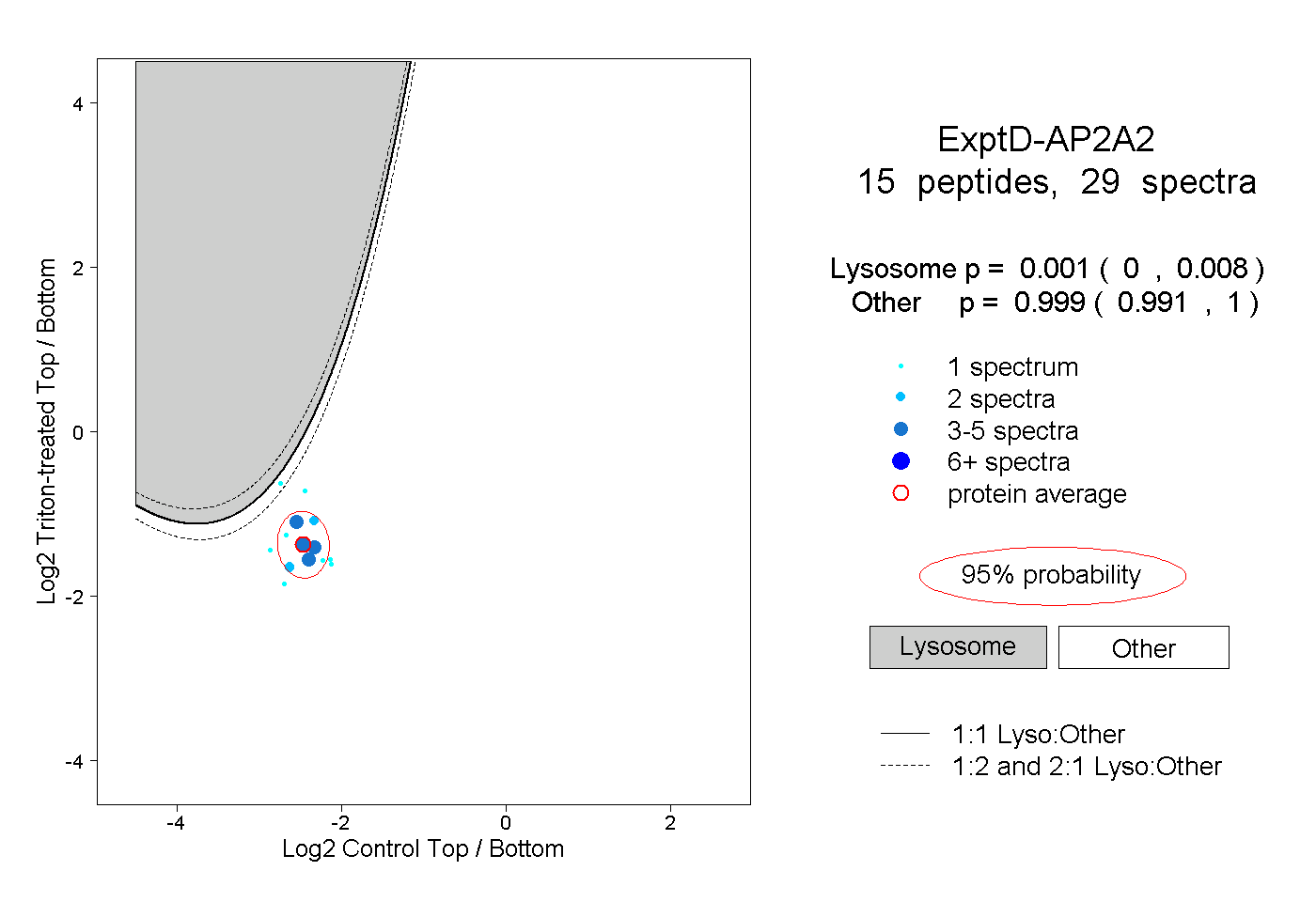 |
0.001 0.000 | 0.008 |
0.999 0.991 | 1.000 |