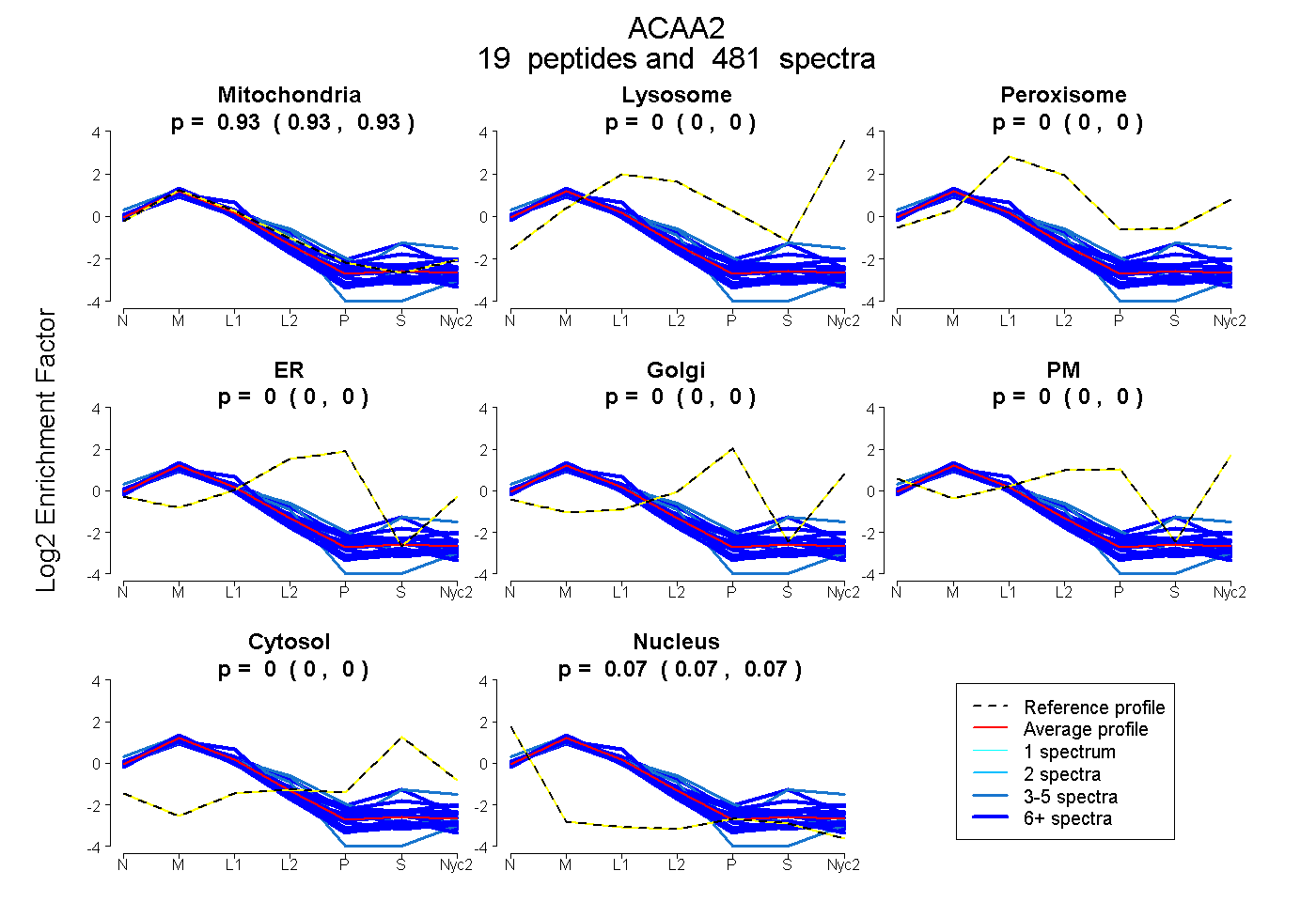
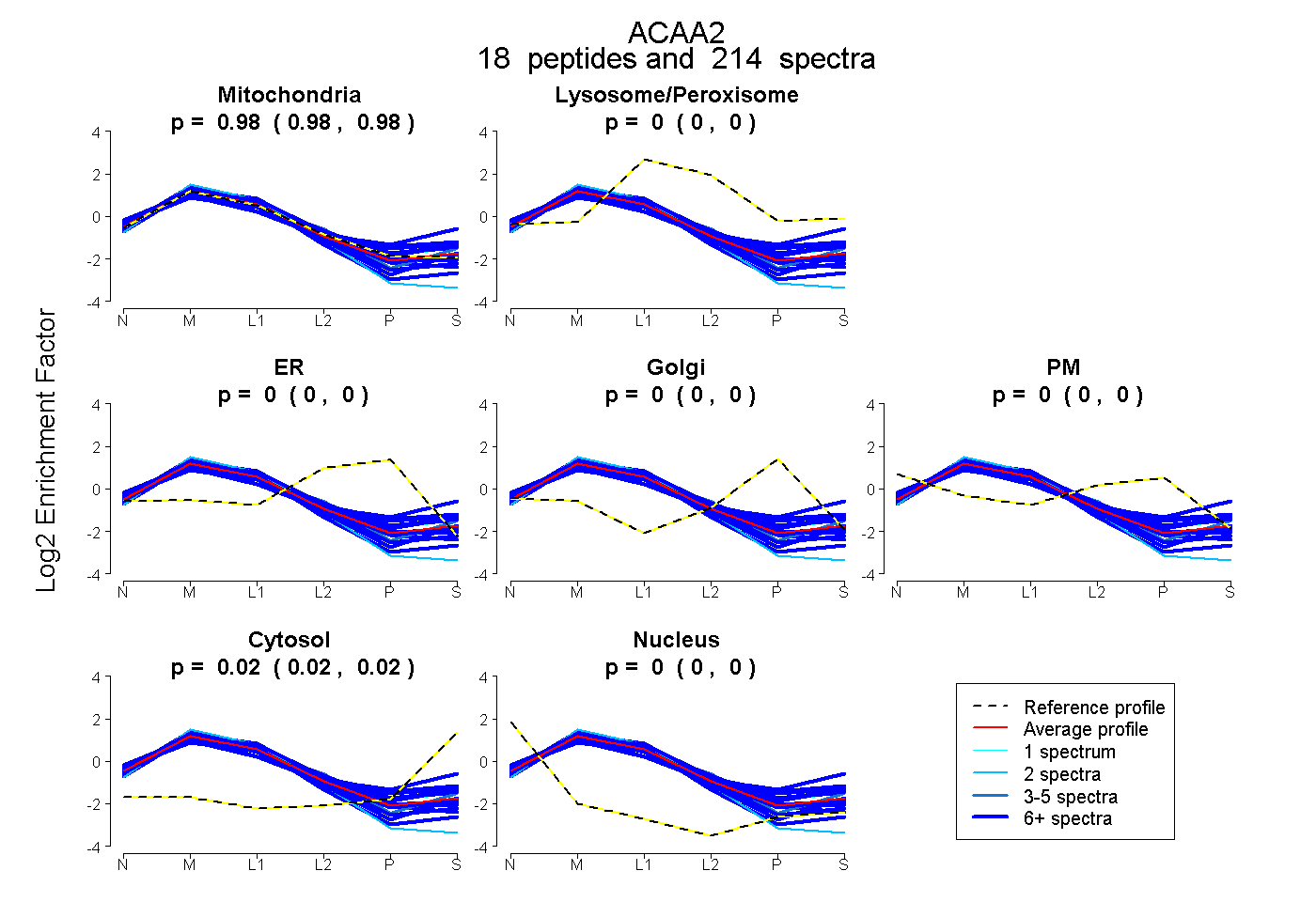
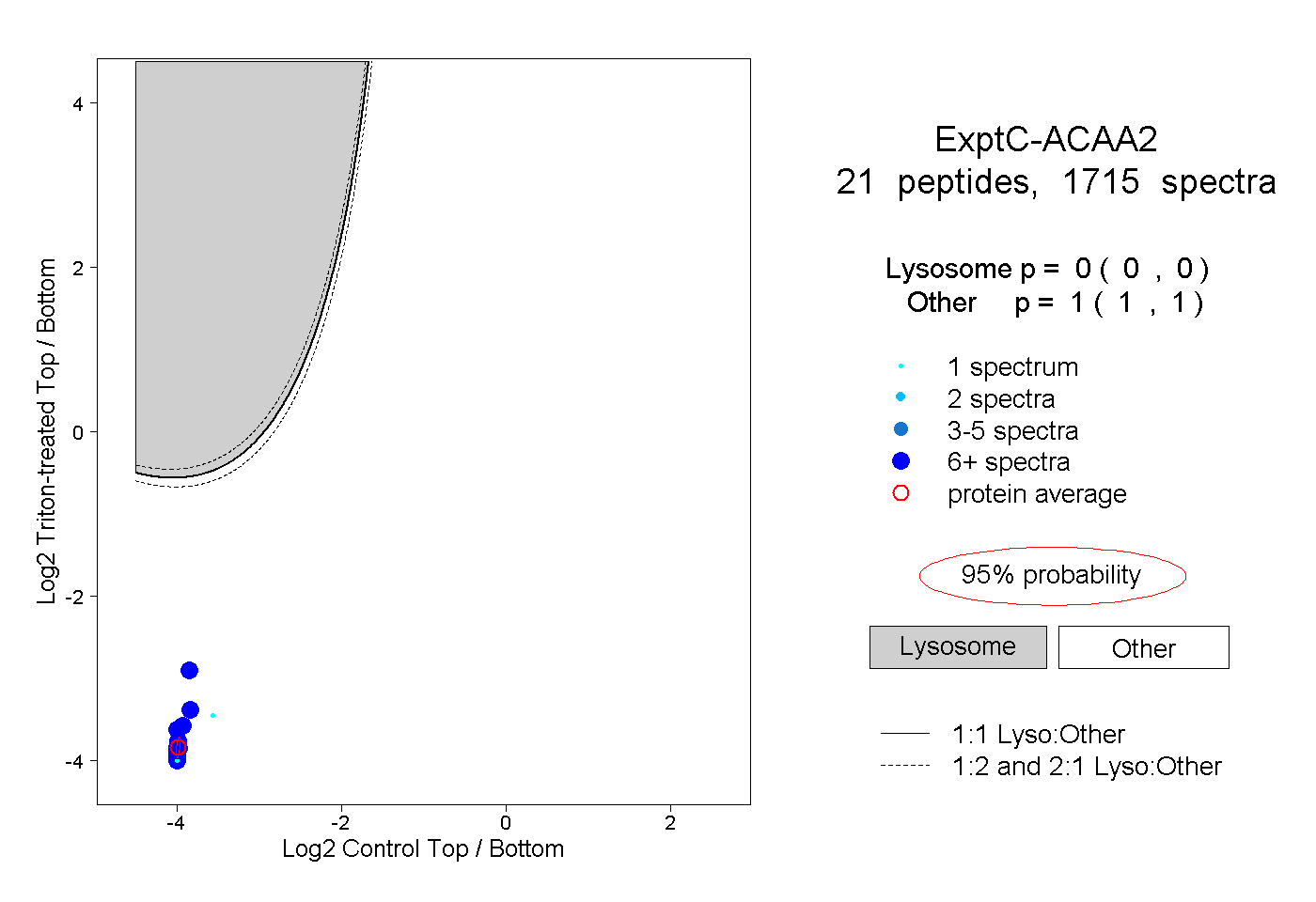
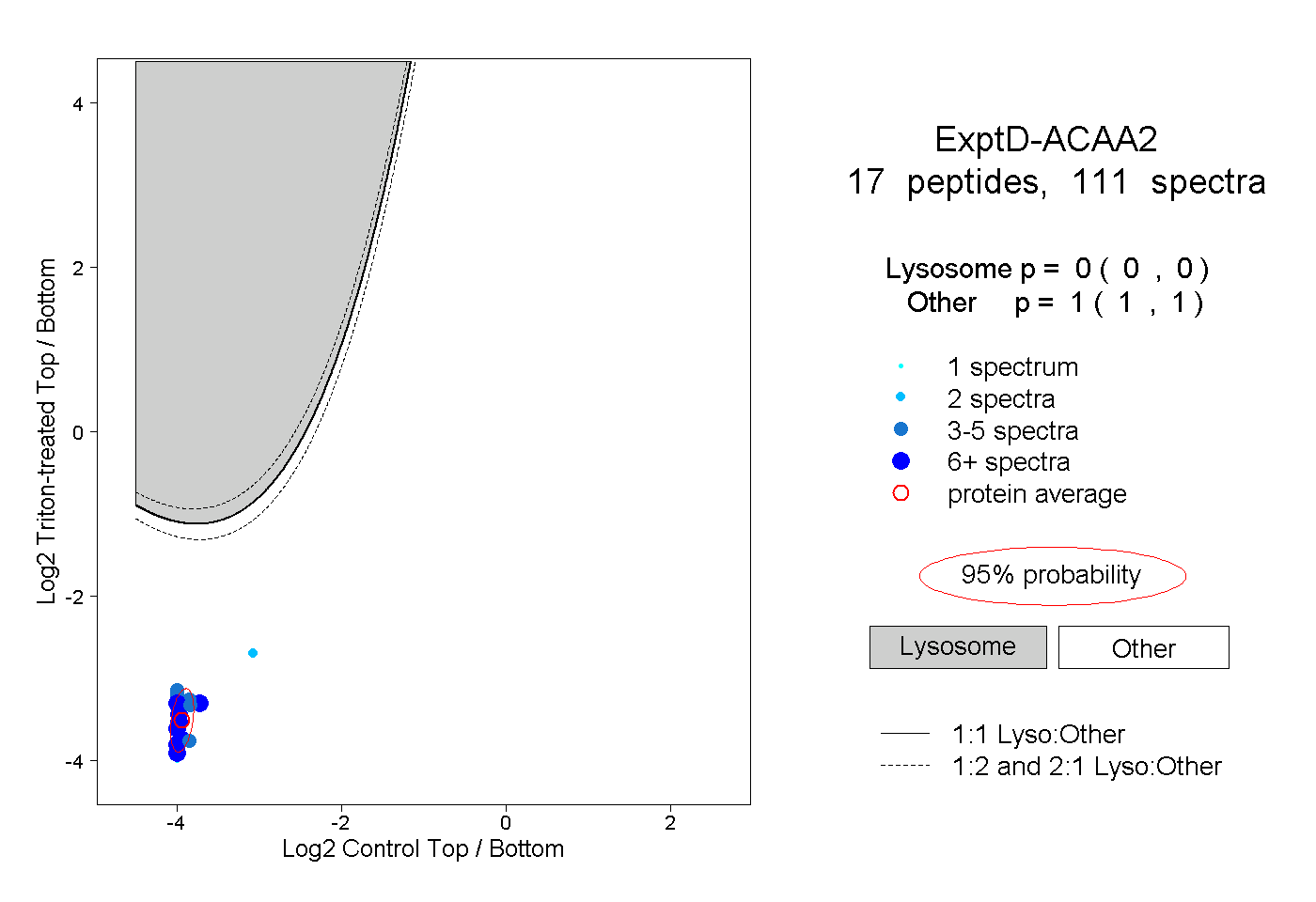
| 156 spectra, GVFIVAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LCGSGFQSIVSGCQEICSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 54 spectra, LEDTLWAGLTDQHVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 89 spectra, AGLSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 94 spectra, SLDLDPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, LPMGMTAENLAAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VPPETIDSVIVGNVMQSSSDAAYLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, TNVSGGAIALGHPLGGSGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 187 spectra, AALSAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 353 spectra, LPPVFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, AANEAGYFNEEMAPIEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 45 spectra, HNFTPLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 149 spectra, YALQSQQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 90 spectra, VGVPTETGALTLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DMDLIDVNEAFAPQFLAVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 198 spectra, DFTATDLTEFAAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 30 spectra, QTMQVDEHARPQTTLEQLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EGTVTAGNASGMSDGAGVVIIASEDAVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VVGYFVSGCDPAIMGIGPVPAITGALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 105 spectra, FGLDLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 92 spectra, TPFGAYGGLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |