peptides
spectra

0.851 | 0.854
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.146 | 0.149
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
195 spectra |
 |
0.852 0.851 | 0.854 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.148 0.146 | 0.149 |
| 7 spectra, SSLYSSDIGK | 0.844 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.156 | ||
| 2 spectra, SVEVPEELQLHSHLLK | 0.700 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.300 | ||
| 13 spectra, DVIIDLLCYR | 0.822 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.178 | ||
| 4 spectra, ASYYAK | 0.819 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.181 | ||
| 9 spectra, TLIFCSGK | 0.835 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.165 | ||
| 1 spectrum, LLLESQEFDHFLATK | 0.808 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.073 | 0.120 | ||
| 9 spectra, LSAYGGITDIIIGMPHR | 0.879 | 0.000 | 0.000 | 0.000 | 0.012 | 0.000 | 0.023 | 0.086 | ||
| 6 spectra, DWFAR | 0.811 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.189 | ||
| 6 spectra, LVTVYCEHGHK | 0.886 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | ||
| 1 spectrum, FATVK | 0.731 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.269 | ||
| 16 spectra, GTFSQR | 0.812 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.188 | ||
| 3 spectra, IGGSIHLIVNNQLGYTTPAER | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.054 | ||
| 2 spectra, QWGHNELDEPFFTNPVMYK | 0.916 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.084 | ||
| 3 spectra, ARPSVDHGLAR | 0.741 | 0.000 | 0.000 | 0.088 | 0.000 | 0.000 | 0.096 | 0.075 | ||
| 19 spectra, LSGQDVGR | 0.886 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | ||
| 1 spectrum, ESLGAK | 0.757 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.243 | ||
| 31 spectra, GVYGYRPR | 0.914 | 0.000 | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | 0.082 | ||
| 3 spectra, LVGCAIIHVNGDSPEEVVR | 0.904 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | ||
| 4 spectra, LEELCPFPLDSLQQEMGK | 0.870 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.090 | 0.040 | ||
| 11 spectra, HFYALLK | 0.873 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.127 | ||
| 7 spectra, DFAILR | 0.758 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.242 | ||
| 10 spectra, ETFTTEER | 0.863 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.137 | ||
| 16 spectra, LAFEYQR | 0.882 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.118 | ||
| 8 spectra, YGGEGAESMMGFFHELLK | 0.817 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.183 | ||
| 3 spectra, HAMVVCQNTDDVYIPLNHMDPNQK | 0.767 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.233 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
115 spectra |
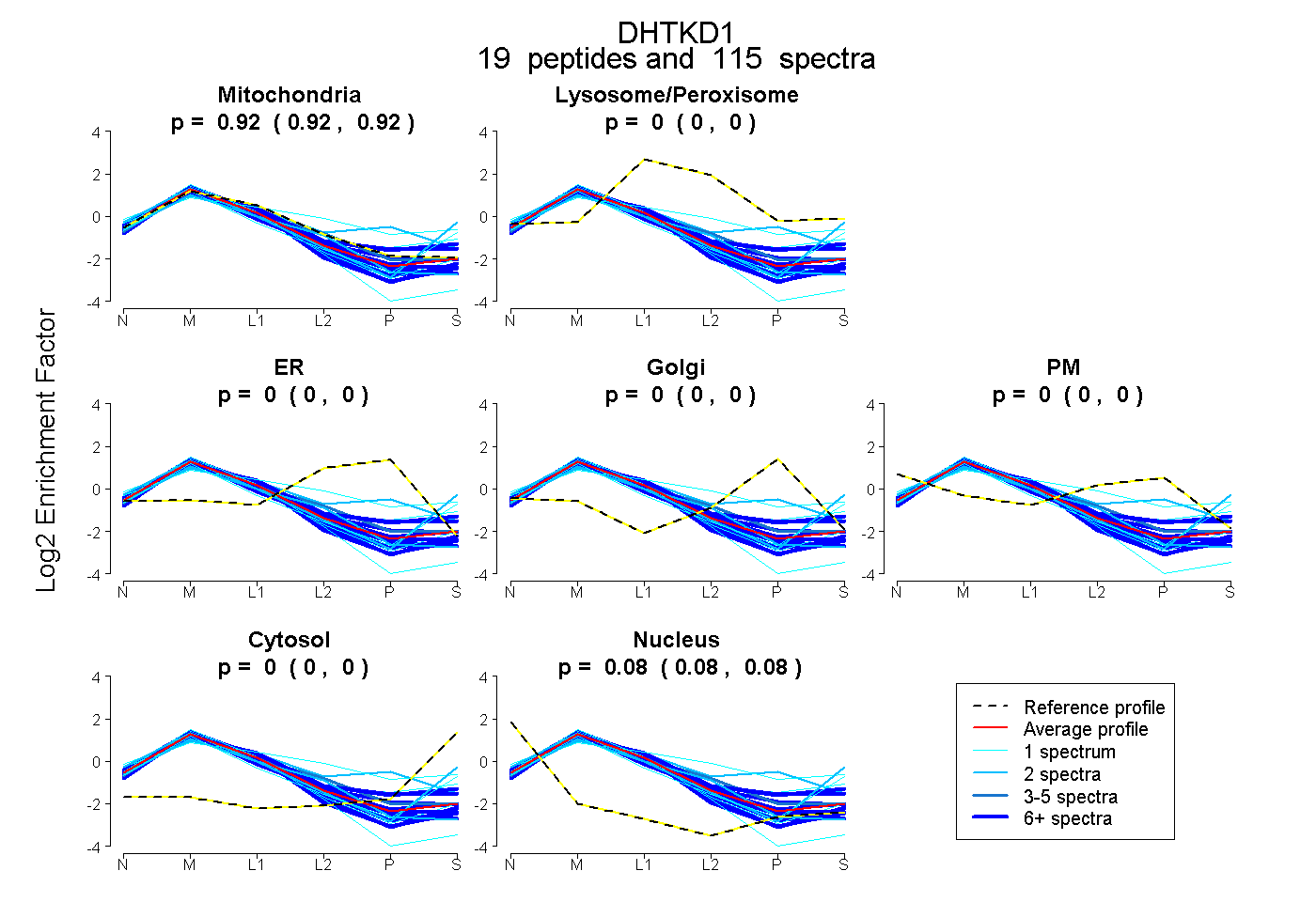 |
0.920 0.918 | 0.922 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.080 0.078 | 0.081 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
546 spectra |
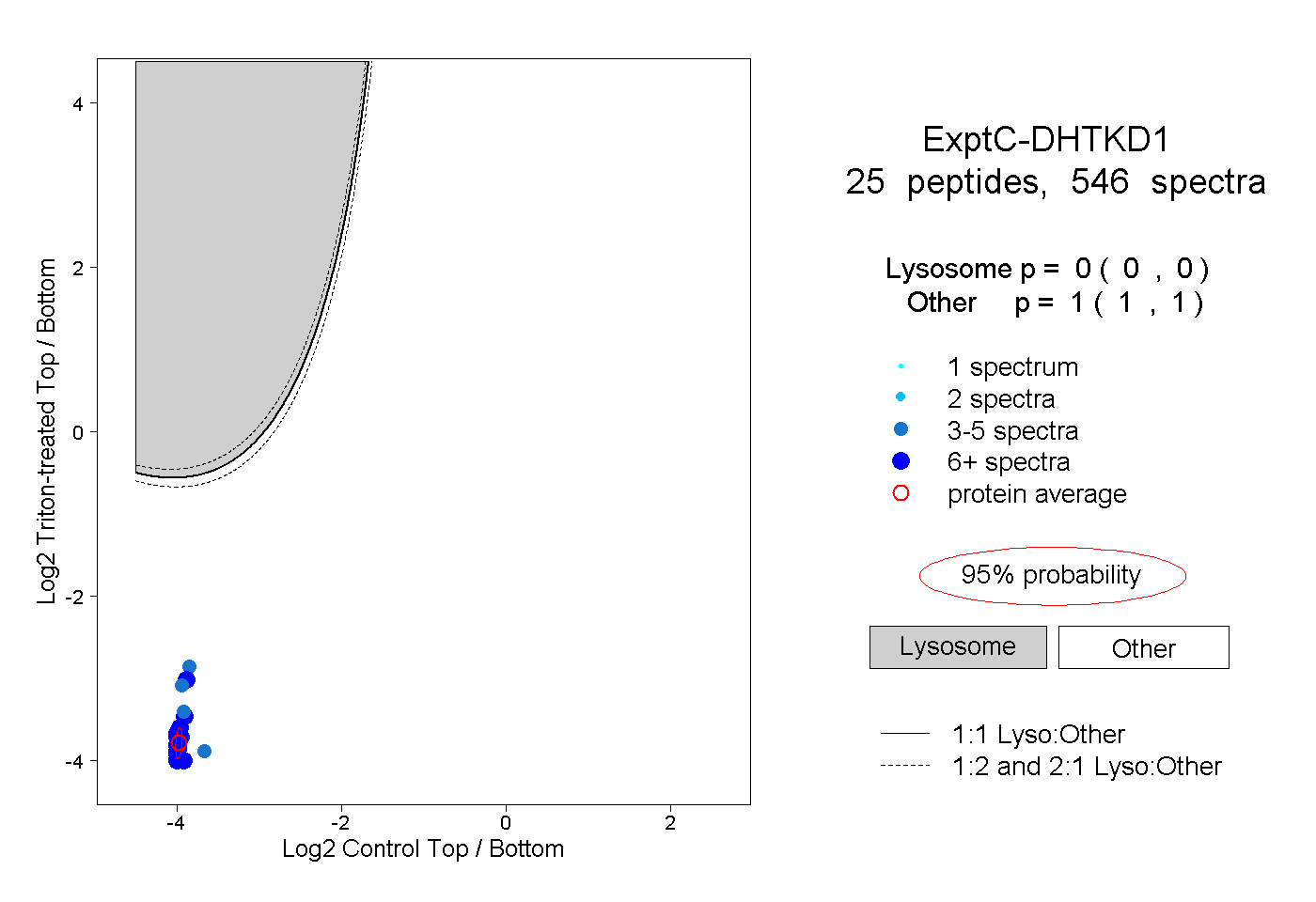 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |