peptides
spectra
0.000 | 0.000
0.707 | 0.733
0.265 | 0.291
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.716 | 0.804
0.046 | 0.194
0.000 | 0.000
0.000 | 0.132
0.010 | 0.065
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
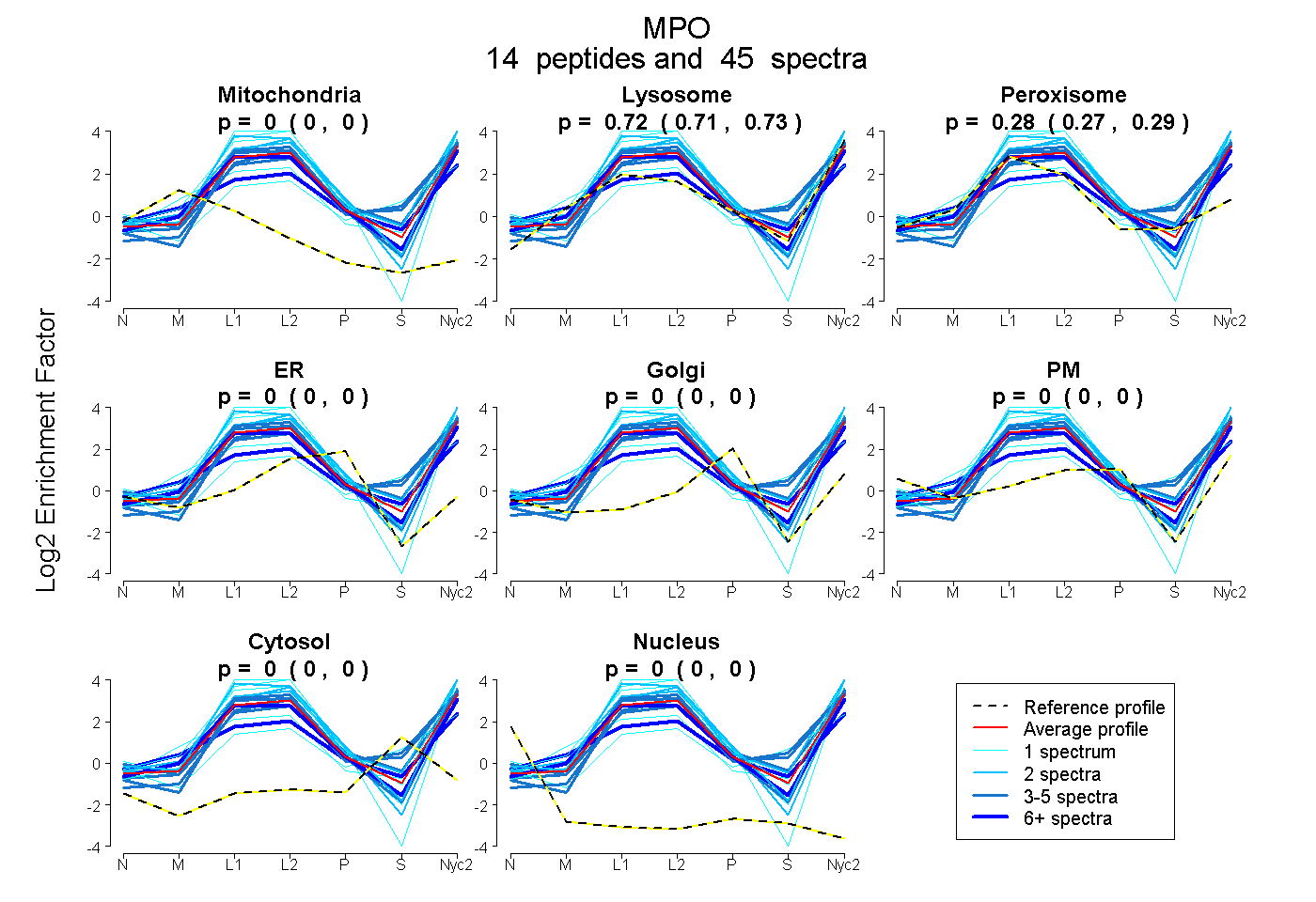
| Expt A |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.722 0.707 | 0.733 |
0.278 0.265 | 0.291 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
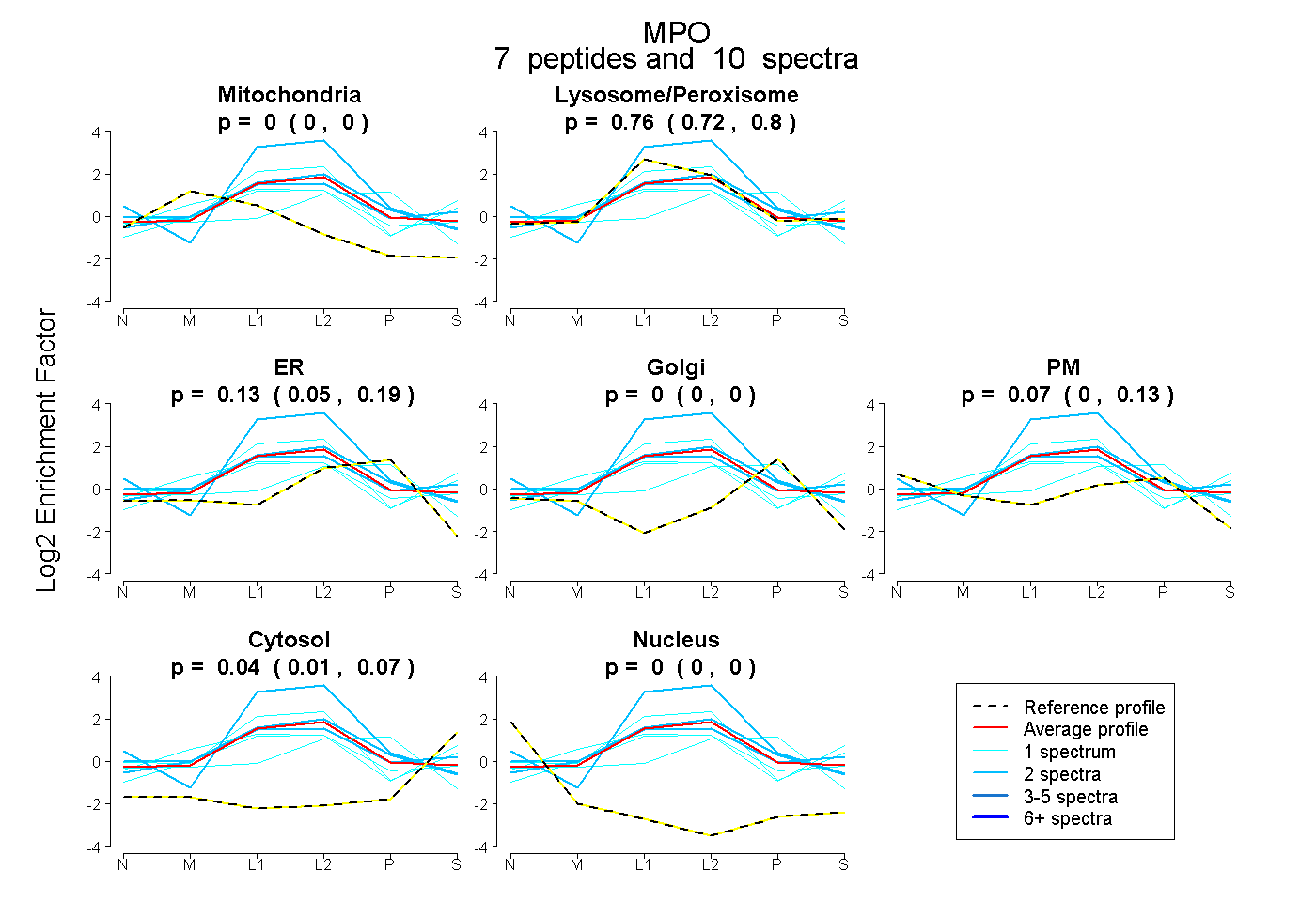
| Expt B |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
0.762 0.716 | 0.804 |
0.128 0.046 | 0.194 |
0.000 0.000 | 0.000 |
0.070 0.000 | 0.132 |
0.040 0.010 | 0.065 |
0.000 0.000 | 0.000 |
| 2 spectra, YGHTLIQPFMFR | 0.000 | 0.785 | 0.057 | 0.046 | 0.000 | 0.111 | 0.000 | |||
| 2 spectra, LNLASWK | 0.000 | 0.712 | 0.197 | 0.000 | 0.091 | 0.000 | 0.000 | |||
| 1 spectrum, QVSNAIVR | 0.000 | 0.728 | 0.000 | 0.000 | 0.000 | 0.272 | 0.000 | |||
| 1 spectrum, IGLDLPALNMQR | 0.000 | 0.284 | 0.535 | 0.161 | 0.020 | 0.000 | 0.000 | |||
| 1 spectrum, QNQIAVDEIR | 0.220 | 0.629 | 0.041 | 0.027 | 0.032 | 0.052 | 0.000 | |||
| 2 spectra, YLPQYR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IPCFLAGDMR | 0.000 | 0.948 | 0.000 | 0.000 | 0.000 | 0.052 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
252 spectra |
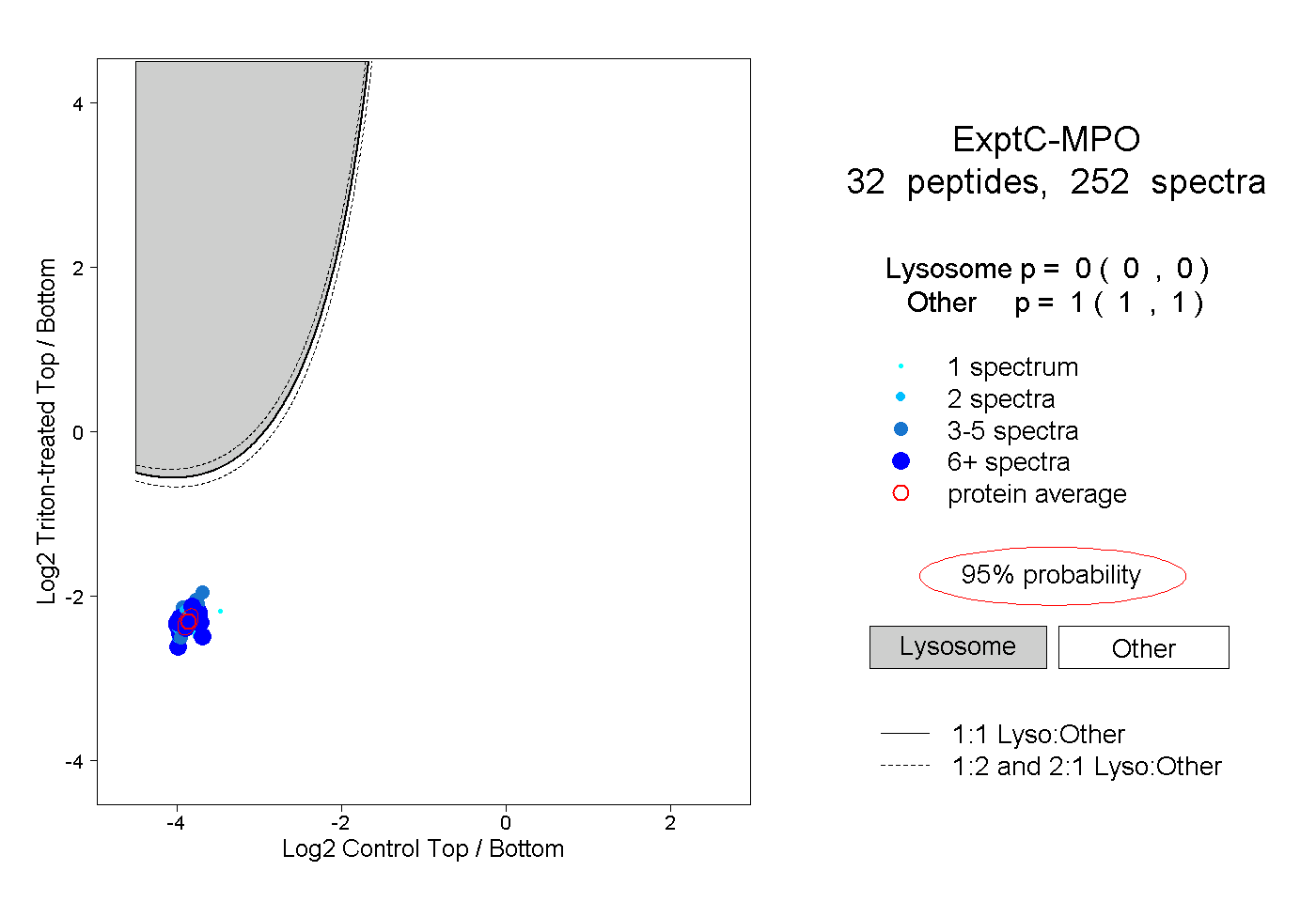 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |