peptides
spectra
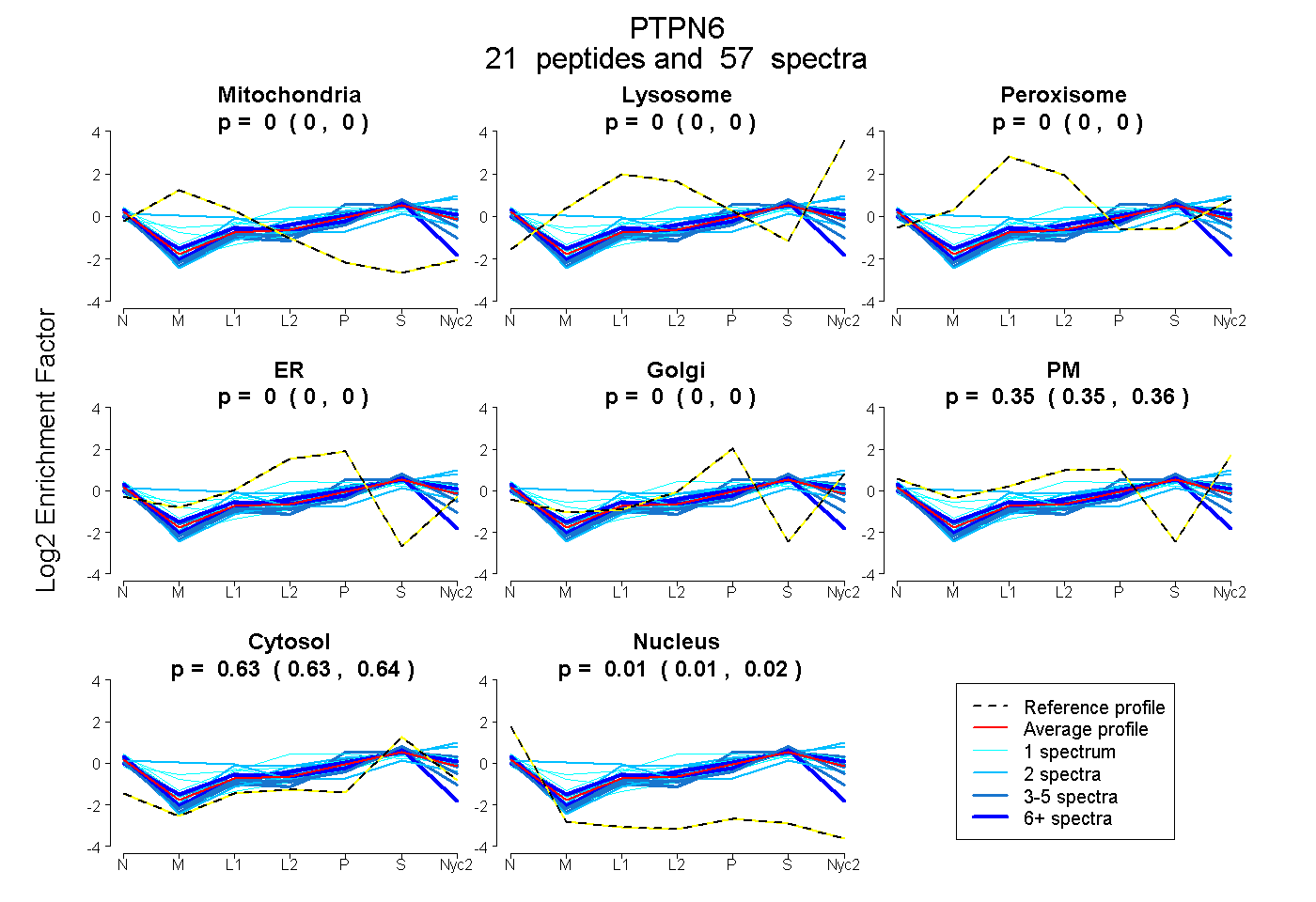
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.350 | 0.356
0.632 | 0.636
0.009 | 0.015
peptides
spectra
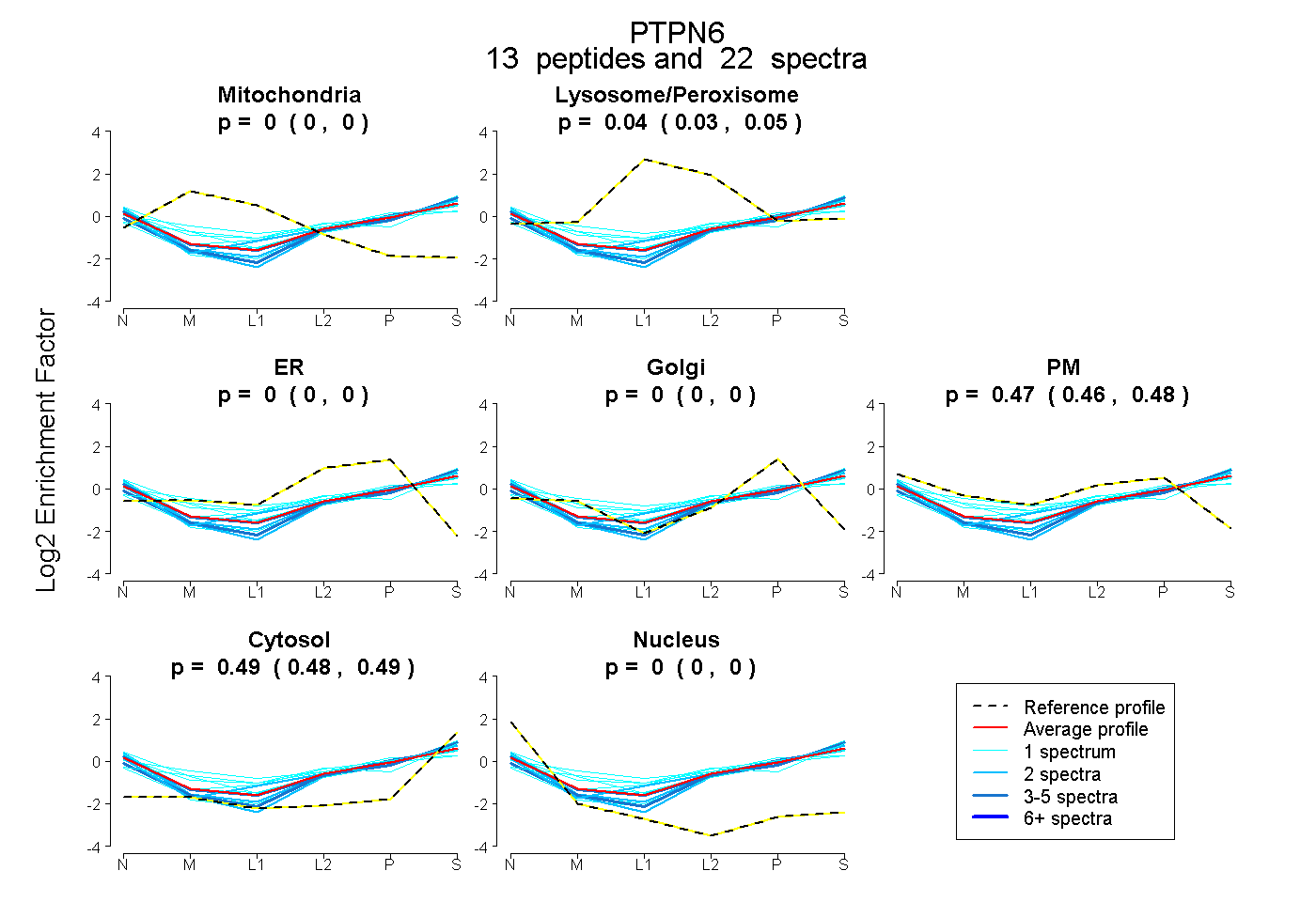
0.000 | 0.000
0.027 | 0.047
0.000 | 0.000
0.000 | 0.000
0.464 | 0.483
0.483 | 0.492
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.353 0.350 | 0.356 |
0.634 0.632 | 0.636 |
0.012 0.009 | 0.015 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.038 0.027 | 0.047 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.474 0.464 | 0.483 |
0.488 0.483 | 0.492 |
0.000 0.000 | 0.000 |
| 1 spectrum, VILQGR | 0.000 | 0.119 | 0.000 | 0.000 | 0.464 | 0.417 | 0.000 | |||
| 2 spectra, AGPGSPLR | 0.000 | 0.000 | 0.000 | 0.110 | 0.374 | 0.515 | 0.000 | |||
| 1 spectrum, TLQISPLDNGDLVR | 0.000 | 0.011 | 0.054 | 0.015 | 0.297 | 0.623 | 0.000 | |||
| 1 spectrum, GLDCDIDIQK | 0.000 | 0.133 | 0.000 | 0.000 | 0.449 | 0.418 | 0.000 | |||
| 2 spectra, GEPWTFLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.511 | 0.489 | 0.000 | |||
| 1 spectrum, YPLNCSDPTSER | 0.000 | 0.218 | 0.000 | 0.000 | 0.284 | 0.498 | 0.000 | |||
| 2 spectra, VNAADIENR | 0.000 | 0.123 | 0.000 | 0.000 | 0.374 | 0.503 | 0.000 | |||
| 3 spectra, VDDQVTHIR | 0.000 | 0.019 | 0.000 | 0.000 | 0.496 | 0.485 | 0.000 | |||
| 5 spectra, VIVMTTR | 0.000 | 0.000 | 0.000 | 0.012 | 0.399 | 0.589 | 0.000 | |||
| 1 spectrum, NILPFDHSR | 0.000 | 0.010 | 0.000 | 0.000 | 0.591 | 0.399 | 0.000 | |||
| 1 spectrum, TGIEEASGAFVYLR | 0.000 | 0.179 | 0.000 | 0.087 | 0.395 | 0.339 | 0.000 | |||
| 1 spectrum, QPYYATR | 0.000 | 0.040 | 0.000 | 0.000 | 0.503 | 0.457 | 0.000 | |||
| 1 spectrum, AGFWEEFESLQK | 0.000 | 0.000 | 0.000 | 0.041 | 0.445 | 0.514 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
57 spectra |
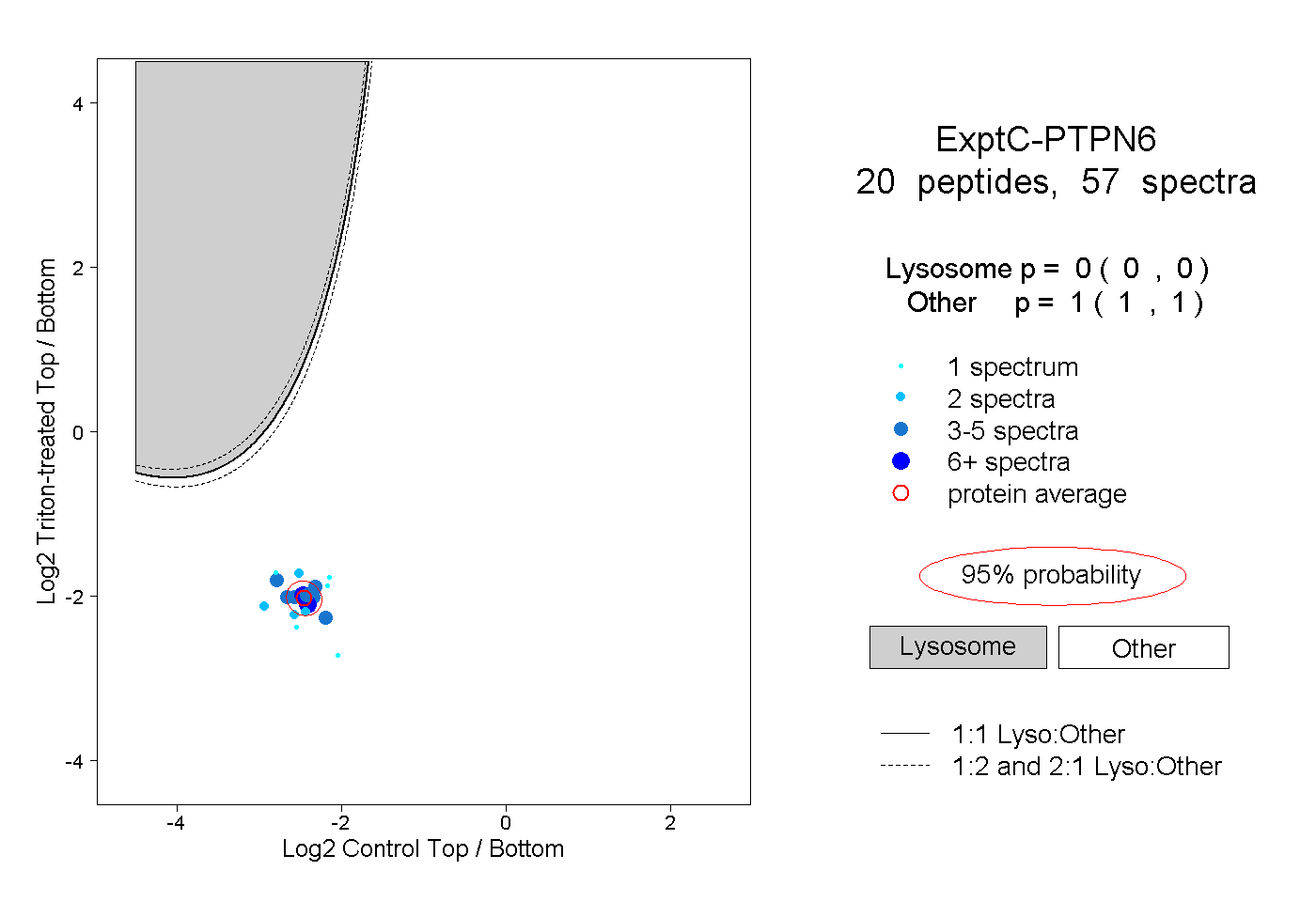 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
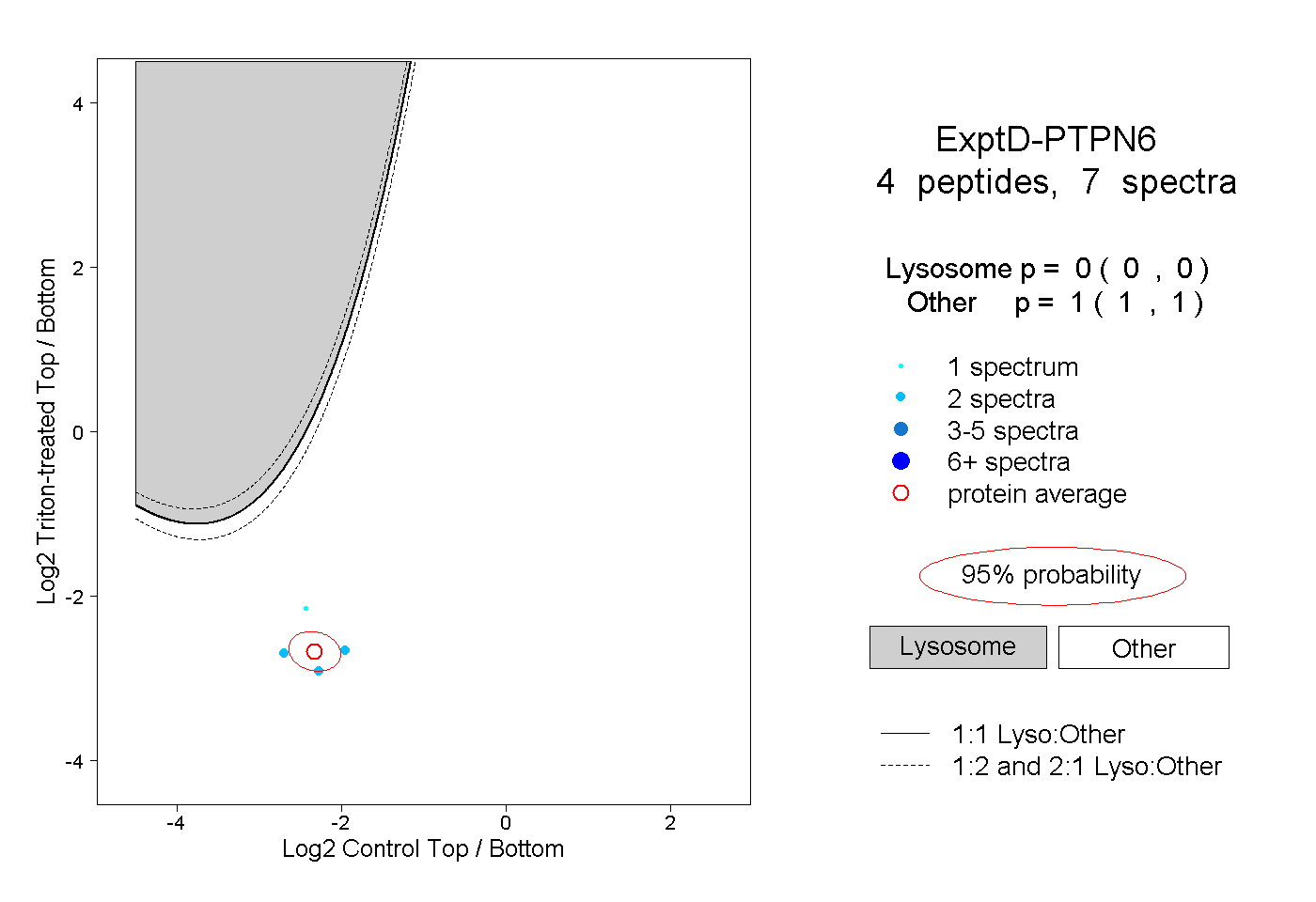 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |