peptides
spectra
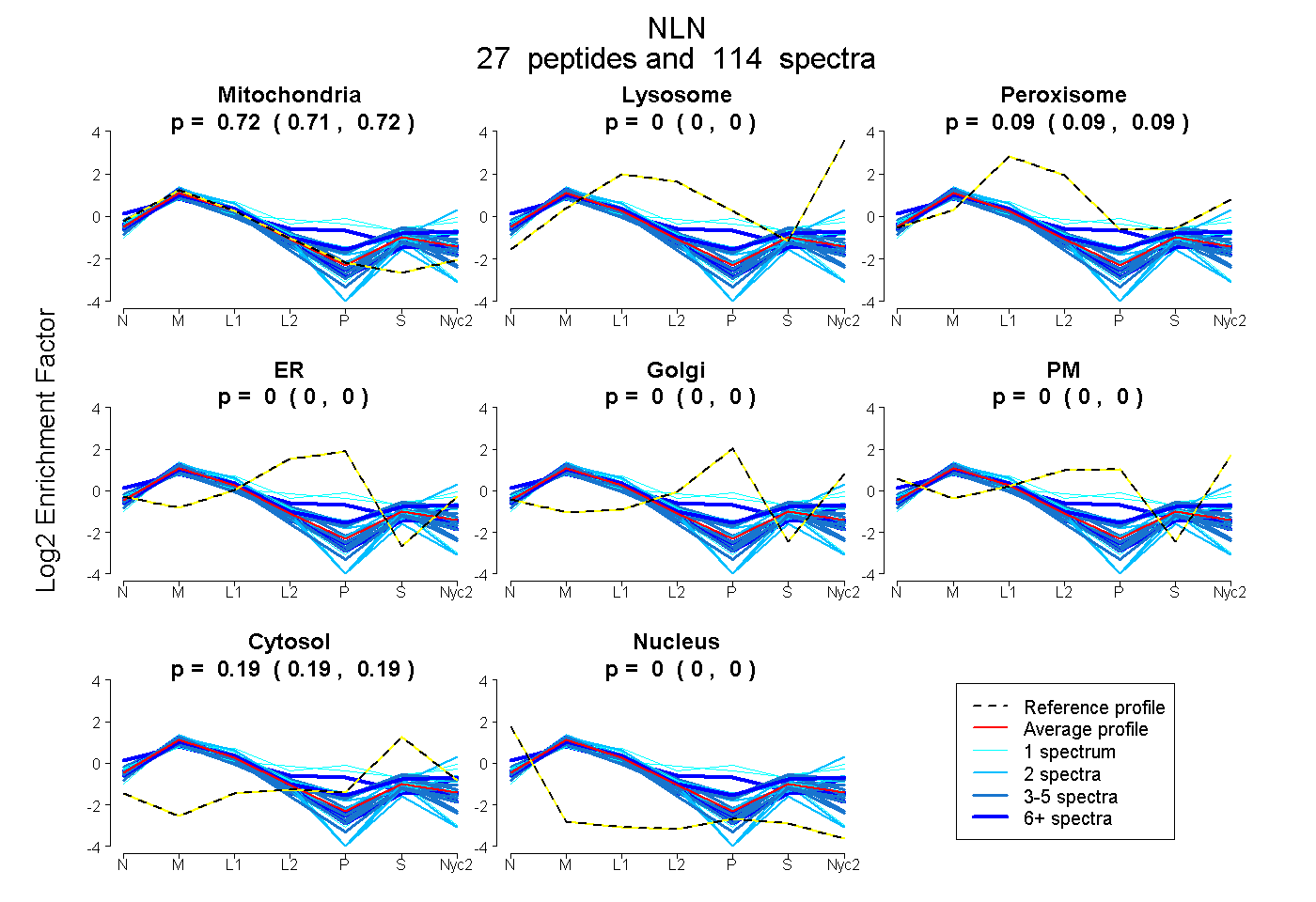
0.714 | 0.721
0.000 | 0.000
0.086 | 0.092
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.192 | 0.195
0.000 | 0.000
peptides
spectra

0.616 | 0.636
0.124 | 0.141
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.235 | 0.244
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
114 spectra |
 |
0.718 0.714 | 0.721 |
0.000 0.000 | 0.000 |
0.089 0.086 | 0.092 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.194 0.192 | 0.195 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
32 spectra |
 |
0.627 0.616 | 0.636 |
0.133 0.124 | 0.141 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.240 0.235 | 0.244 |
0.000 0.000 | 0.000 |
| 2 spectra, TEQLIAQTK | 0.492 | 0.259 | 0.000 | 0.021 | 0.000 | 0.228 | 0.000 | |||
| 6 spectra, VAAFLDDLSQK | 0.769 | 0.057 | 0.000 | 0.000 | 0.000 | 0.174 | 0.000 | |||
| 1 spectrum, MSELCIDFNK | 0.337 | 0.253 | 0.000 | 0.240 | 0.000 | 0.170 | 0.000 | |||
| 5 spectra, QVYDTVGTIALK | 0.822 | 0.000 | 0.000 | 0.000 | 0.000 | 0.178 | 0.000 | |||
| 2 spectra, YNHAACFGLQPGCLLPDGSR | 0.455 | 0.281 | 0.000 | 0.000 | 0.000 | 0.265 | 0.000 | |||
| 2 spectra, SVSLYTVK | 0.810 | 0.000 | 0.000 | 0.000 | 0.000 | 0.190 | 0.000 | |||
| 3 spectra, AFLMSR | 0.672 | 0.000 | 0.000 | 0.000 | 0.000 | 0.328 | 0.000 | |||
| 1 spectrum, NLNEDDTSLVFSK | 0.381 | 0.291 | 0.000 | 0.000 | 0.000 | 0.328 | 0.000 | |||
| 1 spectrum, LKPLGEAER | 0.683 | 0.118 | 0.000 | 0.000 | 0.000 | 0.199 | 0.000 | |||
| 2 spectra, LVNTGLLTLR | 0.852 | 0.000 | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | |||
| 1 spectrum, CCVPETR | 0.587 | 0.196 | 0.000 | 0.000 | 0.000 | 0.216 | 0.000 | |||
| 1 spectrum, AELGALPDDFIDSLEK | 0.337 | 0.291 | 0.000 | 0.000 | 0.017 | 0.355 | 0.000 | |||
| 2 spectra, IVHLQETCDLEK | 0.351 | 0.314 | 0.000 | 0.068 | 0.000 | 0.267 | 0.000 | |||
| 3 spectra, EFILSLK | 0.691 | 0.129 | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
272 spectra |
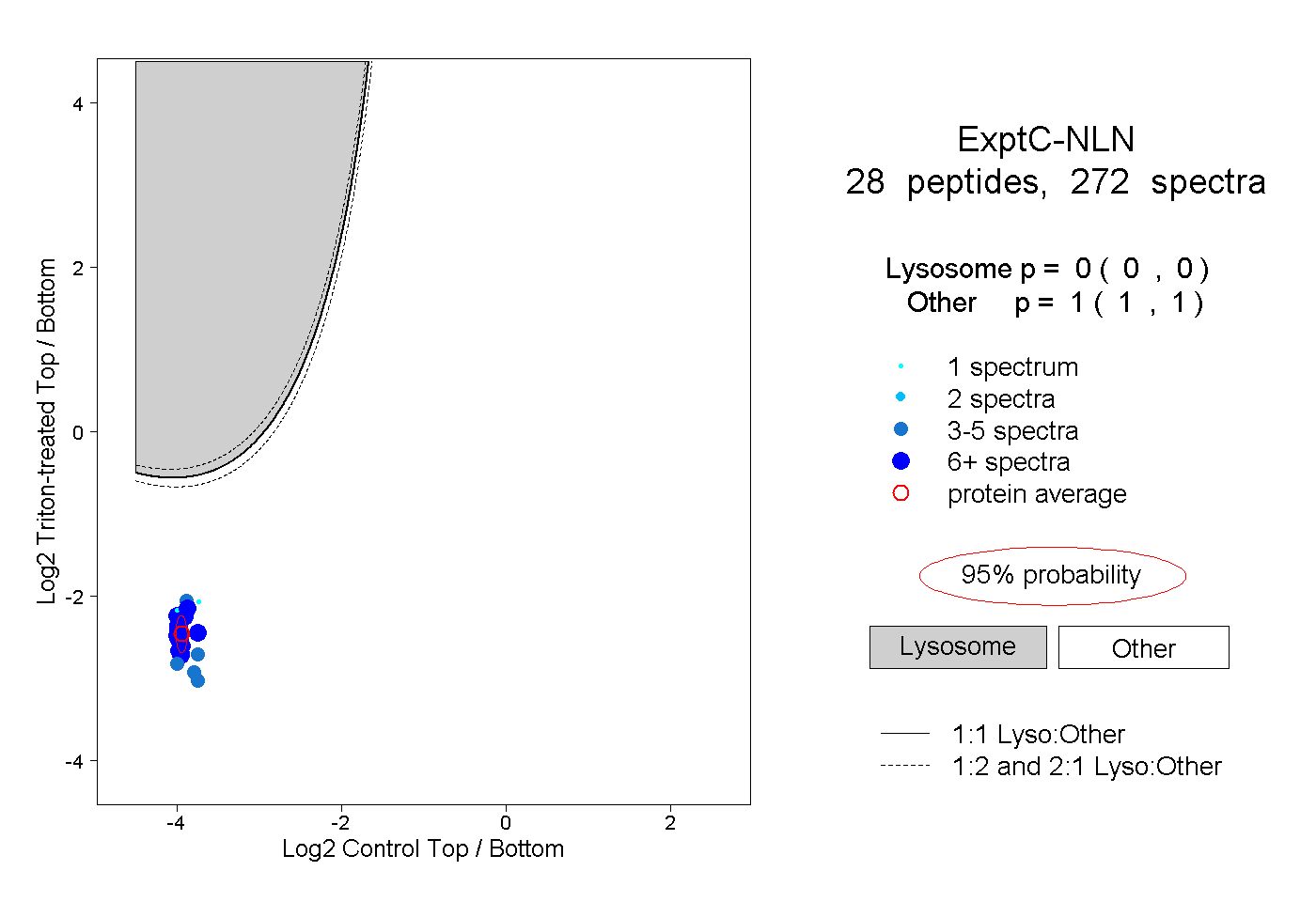 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |