peptides
spectra
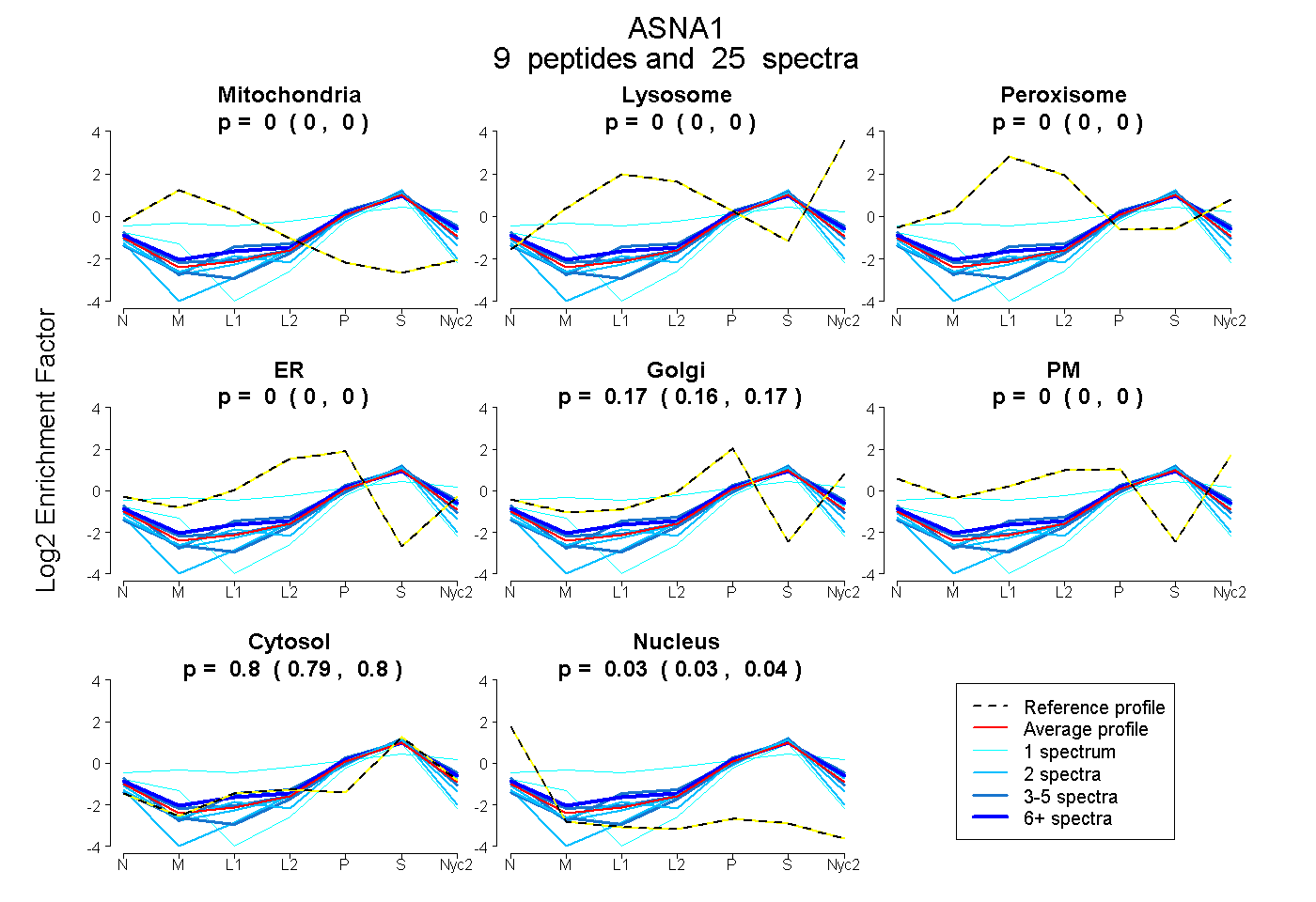
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.158 | 0.175
0.000 | 0.000
0.791 | 0.805
0.026 | 0.042
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.167 0.158 | 0.175 |
0.000 0.000 | 0.000 |
0.799 0.791 | 0.805 |
0.035 0.026 | 0.042 |
| 3 spectra, LIQELAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.211 | 0.000 | 0.789 | 0.000 | ||
| 2 spectra, LEETLPVIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | 0.817 | 0.013 | ||
| 1 spectrum, ESVLIISTDPAHNISDAFDQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.019 | 0.000 | 0.703 | 0.278 | ||
| 2 spectra, TTCSCSLAVQLSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.872 | 0.128 | ||
| 4 spectra, WIFVGGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.090 | 0.000 | 0.861 | 0.049 | ||
| 4 spectra, LLNFPTIVER | 0.000 | 0.000 | 0.000 | 0.000 | 0.224 | 0.000 | 0.776 | 0.000 | ||
| 6 spectra, LPLLPHEVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.236 | 0.000 | 0.764 | 0.000 | ||
| 2 spectra, YLDQMEDLYEDFHIVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.091 | 0.000 | 0.853 | 0.056 | ||
| 1 spectrum, GMNFSVVVFDTAPTGHTLR | 0.022 | 0.029 | 0.206 | 0.000 | 0.163 | 0.128 | 0.452 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
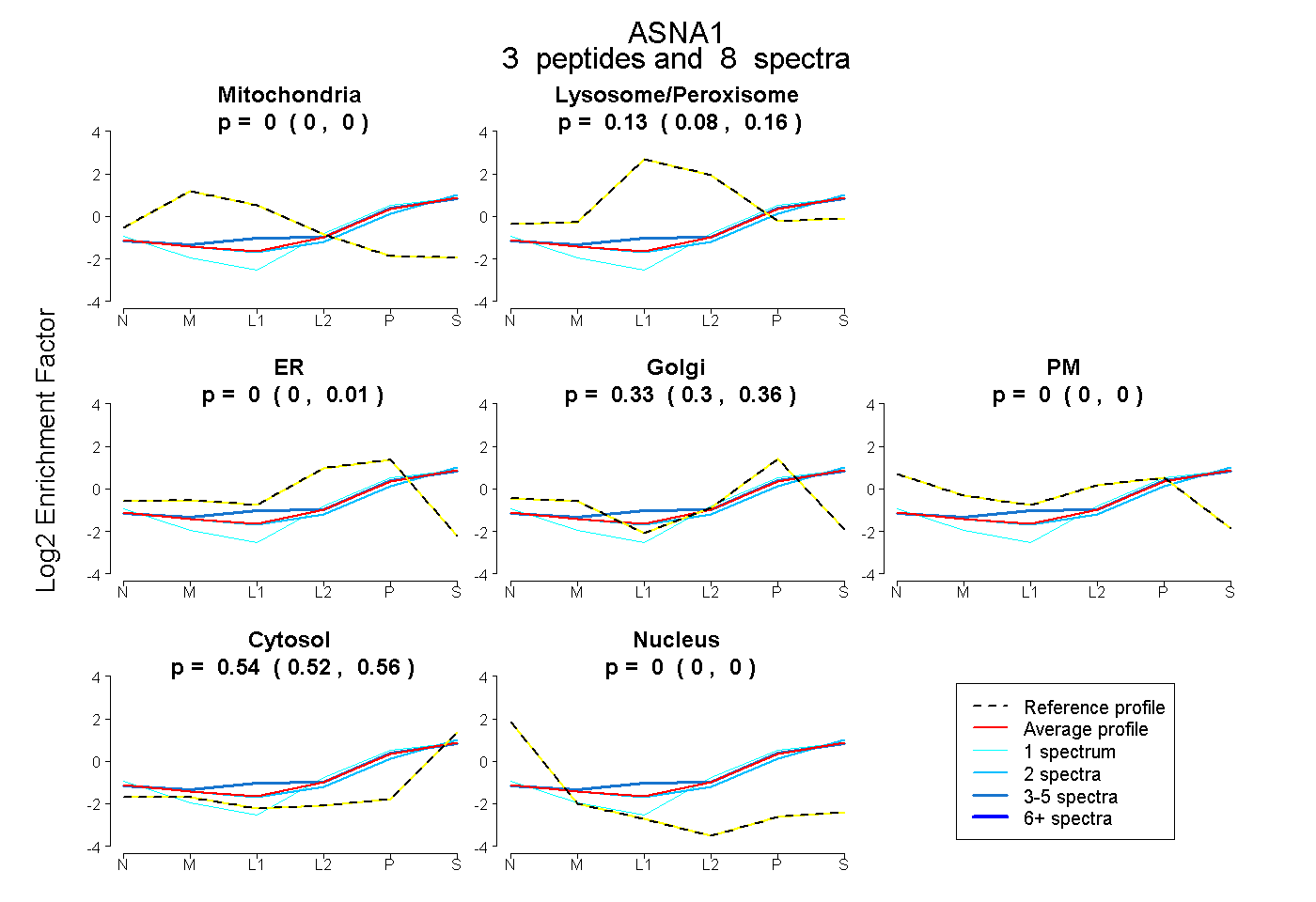 |
0.000 0.000 | 0.000 |
0.126 0.080 | 0.158 |
0.000 0.000 | 0.006 |
0.334 0.303 | 0.357 |
0.000 0.000 | 0.000 |
0.540 0.522 | 0.556 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
17 spectra |
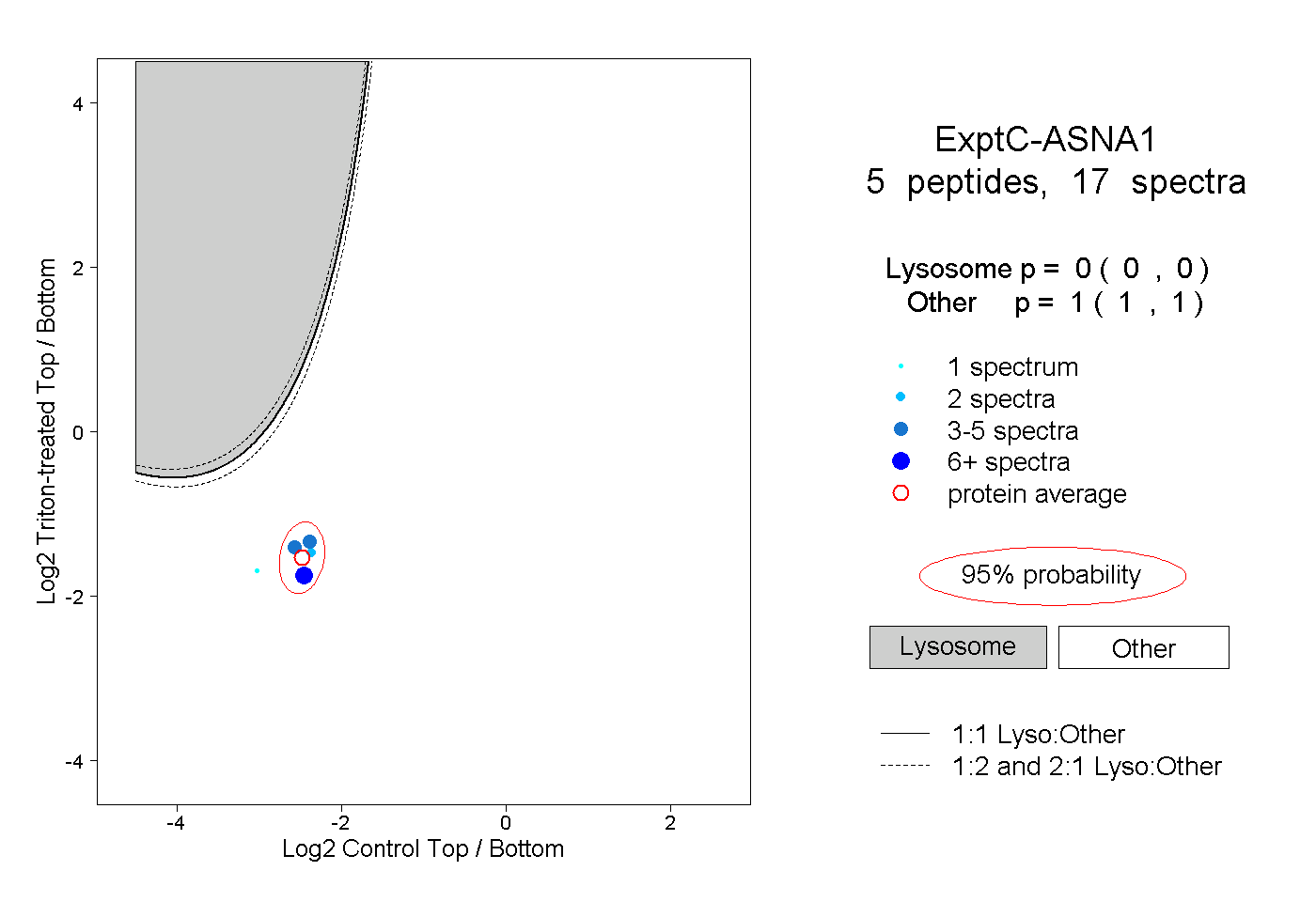 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
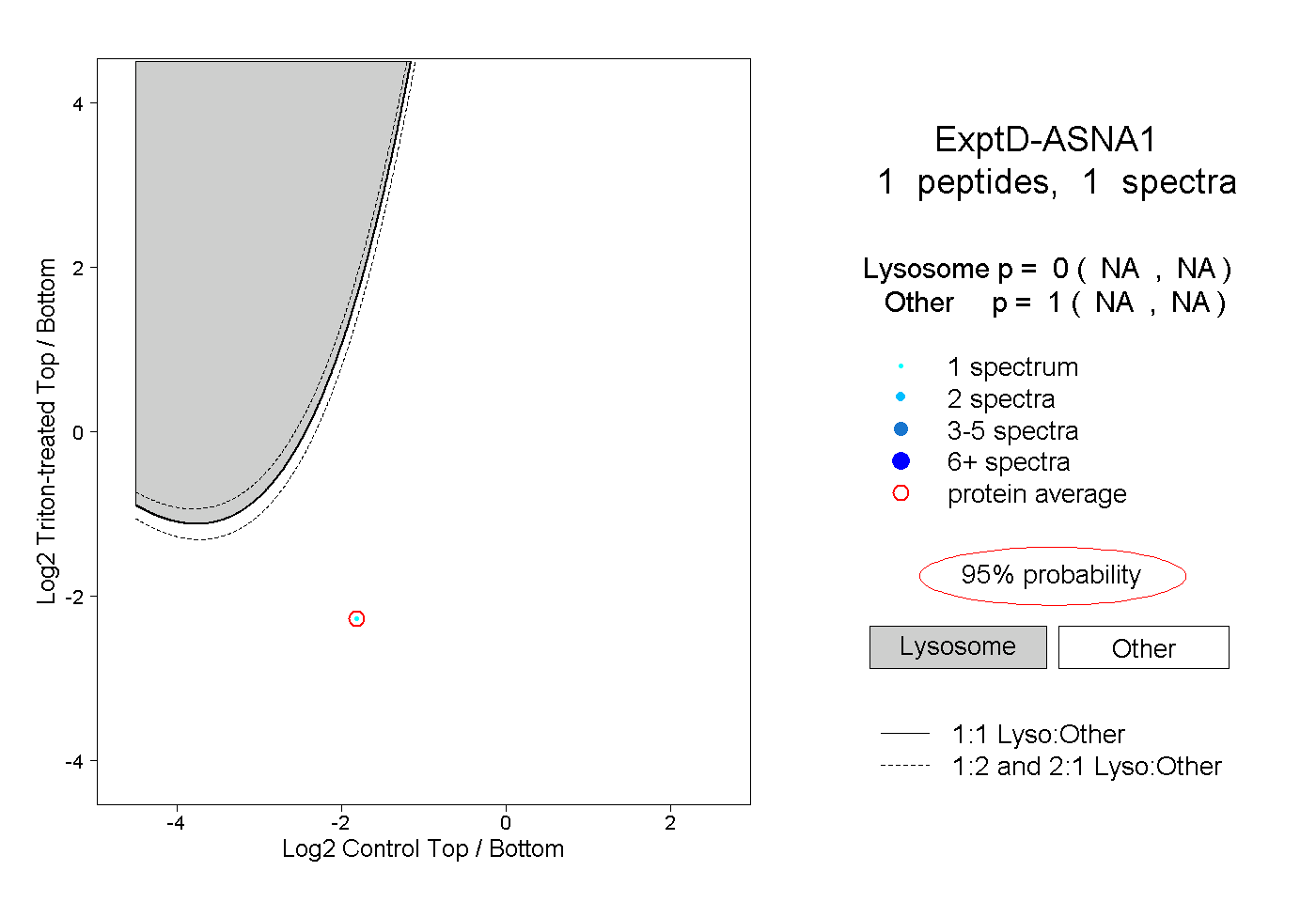 |
0.000 NA | NA |
1.000 NA | NA |