peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.024 | 0.030
0.181 | 0.194
0.000 | 0.000
0.699 | 0.716
0.008 | 0.019
0.058 | 0.065
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.024 | 0.030 |
0.189 0.181 | 0.194 |
0.000 0.000 | 0.000 |
0.708 0.699 | 0.716 |
0.014 0.008 | 0.019 |
0.062 0.058 | 0.065 |
| 2 spectra, LTDEMVMIMGGK | 0.000 | 0.000 | 0.000 | 0.133 | 0.000 | 0.575 | 0.292 | 0.000 | ||
| 2 spectra, ALGHIAVALR | 0.000 | 0.000 | 0.000 | 0.145 | 0.000 | 0.809 | 0.000 | 0.046 | ||
| 1 spectrum, DEQGAENLCIK | 0.018 | 0.000 | 0.146 | 0.419 | 0.000 | 0.343 | 0.000 | 0.075 | ||
| 2 spectra, DIAIDNICR | 0.000 | 0.000 | 0.000 | 0.730 | 0.000 | 0.104 | 0.000 | 0.166 | ||
| 2 spectra, IPEELEGVR | 0.000 | 0.000 | 0.000 | 0.131 | 0.000 | 0.758 | 0.073 | 0.038 | ||
| 1 spectrum, LTAMLISSK | 0.000 | 0.000 | 0.000 | 0.474 | 0.000 | 0.526 | 0.000 | 0.000 | ||
| 1 spectrum, EYILWAAAK | 0.000 | 0.106 | 0.000 | 0.306 | 0.000 | 0.588 | 0.000 | 0.000 | ||
| 2 spectra, DTLYYMK | 0.000 | 0.000 | 0.033 | 0.028 | 0.000 | 0.784 | 0.111 | 0.043 | ||
| 2 spectra, SLDAAVAR | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.850 | 0.000 | 0.043 | ||
| 1 spectrum, NDTVTPAELNELR | 0.042 | 0.000 | 0.073 | 0.164 | 0.000 | 0.430 | 0.290 | 0.000 | ||
| 3 spectra, FPVVVHSVTPSLR | 0.183 | 0.000 | 0.000 | 0.166 | 0.000 | 0.622 | 0.000 | 0.028 | ||
| 2 spectra, ILHDADR | 0.000 | 0.000 | 0.000 | 0.077 | 0.000 | 0.816 | 0.107 | 0.000 | ||
| 1 spectrum, VGDDCR | 0.000 | 0.000 | 0.000 | 0.274 | 0.000 | 0.623 | 0.050 | 0.053 | ||
| 2 spectra, YAIPCLIGISR | 0.043 | 0.000 | 0.000 | 0.786 | 0.000 | 0.013 | 0.000 | 0.158 | ||
| 2 spectra, MEATPFK | 0.016 | 0.000 | 0.011 | 0.206 | 0.000 | 0.709 | 0.007 | 0.051 | ||
| 1 spectrum, ACLSALSEVK | 0.113 | 0.000 | 0.052 | 0.244 | 0.000 | 0.414 | 0.155 | 0.023 | ||
| 1 spectrum, SQLLAHQFIWNMK | 0.024 | 0.000 | 0.000 | 0.018 | 0.000 | 0.958 | 0.000 | 0.000 | ||
| 4 spectra, HVAAIGPR | 0.000 | 0.000 | 0.000 | 0.154 | 0.000 | 0.795 | 0.000 | 0.051 | ||
| 1 spectrum, QYGDESTLAFQQAR | 0.000 | 0.000 | 0.122 | 0.243 | 0.167 | 0.221 | 0.248 | 0.000 | ||
| 1 spectrum, SNLDITVGSR | 0.219 | 0.000 | 0.000 | 0.067 | 0.024 | 0.690 | 0.000 | 0.000 | ||
| 1 spectrum, YAGEVHGMIR | 0.000 | 0.000 | 0.385 | 0.000 | 0.132 | 0.425 | 0.057 | 0.000 | ||
| 4 spectra, VPPHSLR | 0.000 | 0.000 | 0.000 | 0.067 | 0.000 | 0.809 | 0.108 | 0.016 | ||
| 2 spectra, EFYIPLEMLR | 0.000 | 0.000 | 0.000 | 0.140 | 0.000 | 0.832 | 0.000 | 0.028 | ||
| 1 spectrum, HAQFLLVNFNHIHK | 0.000 | 0.162 | 0.000 | 0.000 | 0.000 | 0.702 | 0.136 | 0.000 | ||
| 1 spectrum, YLSGLVDK | 0.044 | 0.000 | 0.155 | 0.000 | 0.000 | 0.544 | 0.257 | 0.000 | ||
| 1 spectrum, VFDAFLNMMAEK | 0.000 | 0.000 | 0.071 | 0.246 | 0.000 | 0.499 | 0.184 | 0.000 | ||
| 1 spectrum, FSGATGQMSDLNK | 0.000 | 0.038 | 0.192 | 0.000 | 0.000 | 0.562 | 0.208 | 0.000 | ||
| 4 spectra, EFDFFNK | 0.068 | 0.000 | 0.000 | 0.082 | 0.002 | 0.818 | 0.000 | 0.030 | ||
| 3 spectra, LDPGAVSDVPEAIK | 0.000 | 0.000 | 0.000 | 0.155 | 0.000 | 0.725 | 0.081 | 0.038 | ||
| 2 spectra, IIQNCFLSNR | 0.083 | 0.000 | 0.000 | 0.793 | 0.000 | 0.000 | 0.000 | 0.124 | ||
| 2 spectra, ITVPDTYEAR | 0.000 | 0.000 | 0.000 | 0.029 | 0.026 | 0.814 | 0.121 | 0.010 | ||
| 2 spectra, IVEEPVLK | 0.000 | 0.000 | 0.000 | 0.072 | 0.011 | 0.821 | 0.077 | 0.020 | ||
| 2 spectra, YSNSEESLLSK | 0.020 | 0.000 | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | 0.055 | ||
| 2 spectra, TSSVSSISQVSPER | 0.000 | 0.000 | 0.000 | 0.038 | 0.000 | 0.935 | 0.000 | 0.027 | ||
| 1 spectrum, YLTASQLVPPDNQDTR | 0.000 | 0.000 | 0.001 | 0.047 | 0.000 | 0.921 | 0.015 | 0.015 | ||
| 2 spectra, VMEPILQILQQK | 0.000 | 0.000 | 0.005 | 0.038 | 0.000 | 0.786 | 0.171 | 0.000 | ||
| 1 spectrum, NTEAIGNEVTR | 0.000 | 0.000 | 0.000 | 0.103 | 0.022 | 0.828 | 0.000 | 0.047 | ||
| 2 spectra, WAPTVTK | 0.000 | 0.000 | 0.000 | 0.104 | 0.008 | 0.854 | 0.000 | 0.035 | ||
| 1 spectrum, FSPNMTER | 0.000 | 0.000 | 0.000 | 0.195 | 0.000 | 0.799 | 0.000 | 0.006 | ||
| 2 spectra, ELLNLVK | 0.000 | 0.000 | 0.000 | 0.173 | 0.062 | 0.693 | 0.000 | 0.072 | ||
| 2 spectra, NQPSMYEQLR | 0.000 | 0.000 | 0.102 | 0.000 | 0.098 | 0.640 | 0.160 | 0.000 | ||
| 1 spectrum, QDMLALQIIDLFK | 0.079 | 0.000 | 0.097 | 0.306 | 0.000 | 0.346 | 0.159 | 0.015 | ||
| 1 spectrum, FGLFSAETK | 0.268 | 0.000 | 0.024 | 0.000 | 0.000 | 0.595 | 0.114 | 0.000 | ||
| 1 spectrum, TLLLSLLATEIER | 0.000 | 0.000 | 0.000 | 0.068 | 0.000 | 0.932 | 0.000 | 0.000 | ||
| 1 spectrum, FWTAMFSDK | 0.000 | 0.000 | 0.000 | 0.082 | 0.000 | 0.918 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.086 0.038 | 0.122 |
0.818 0.785 | 0.846 |
0.029 0.000 | 0.069 |
0.067 0.037 | 0.085 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
81 spectra |
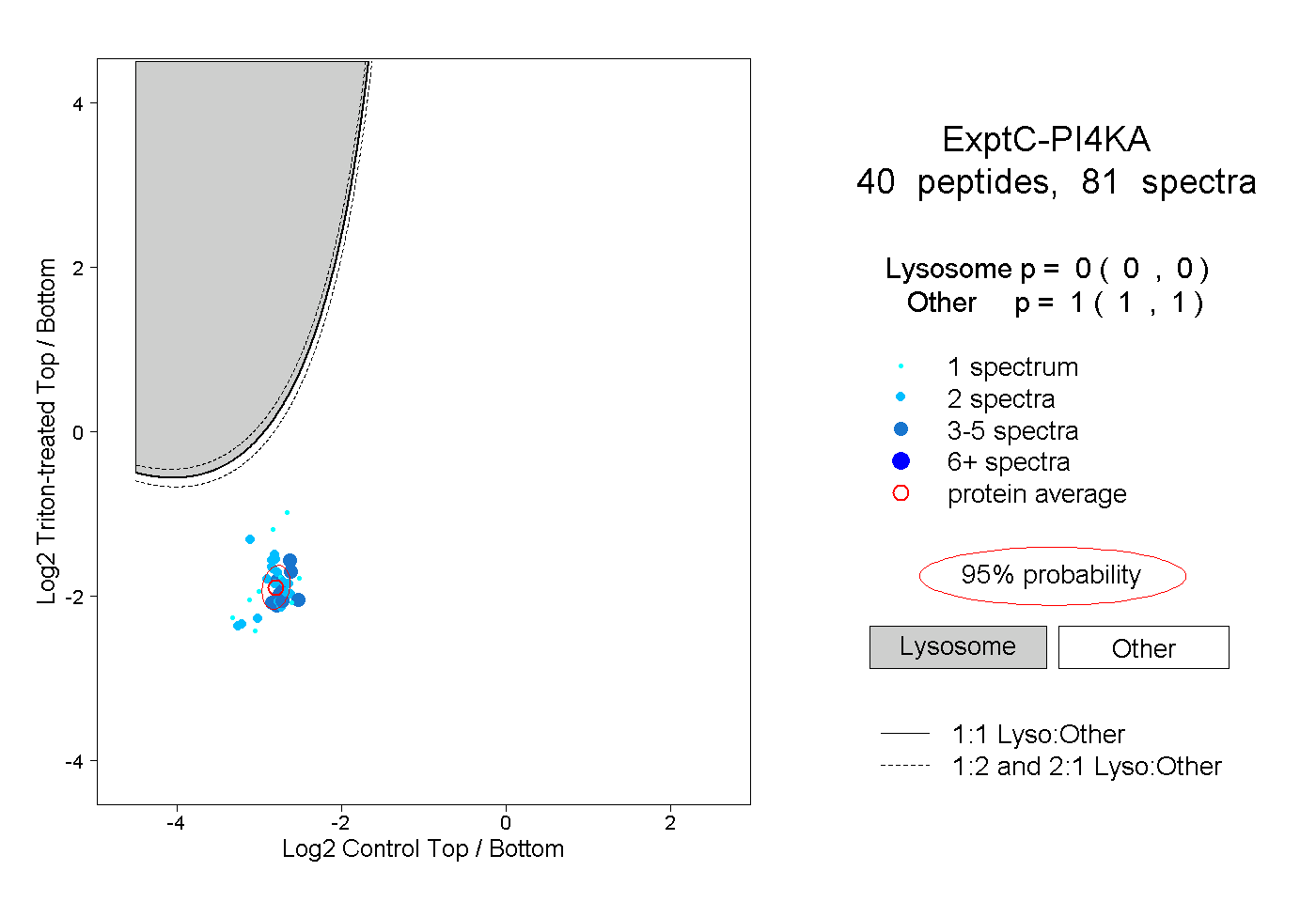 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
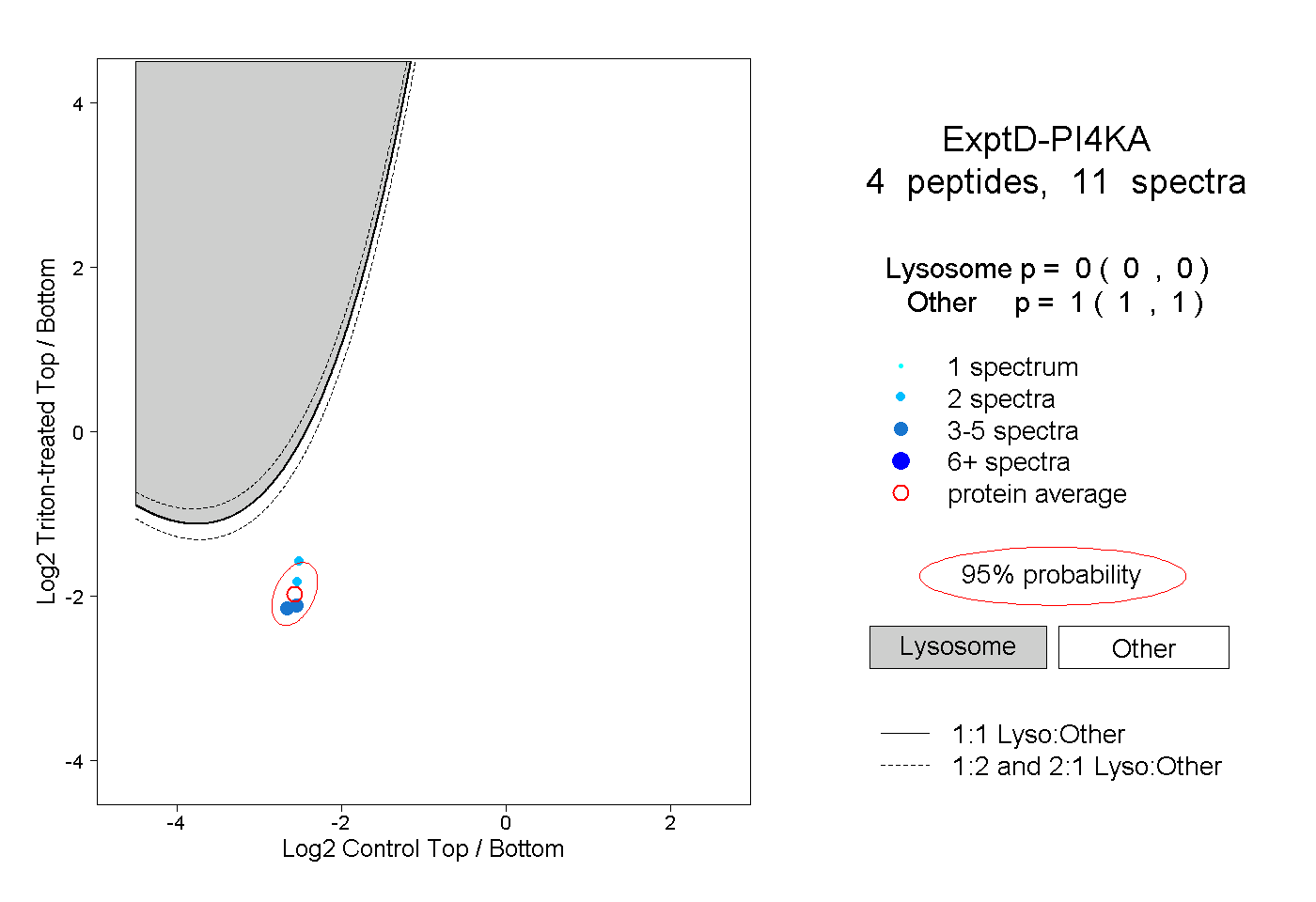 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |