peptides
spectra
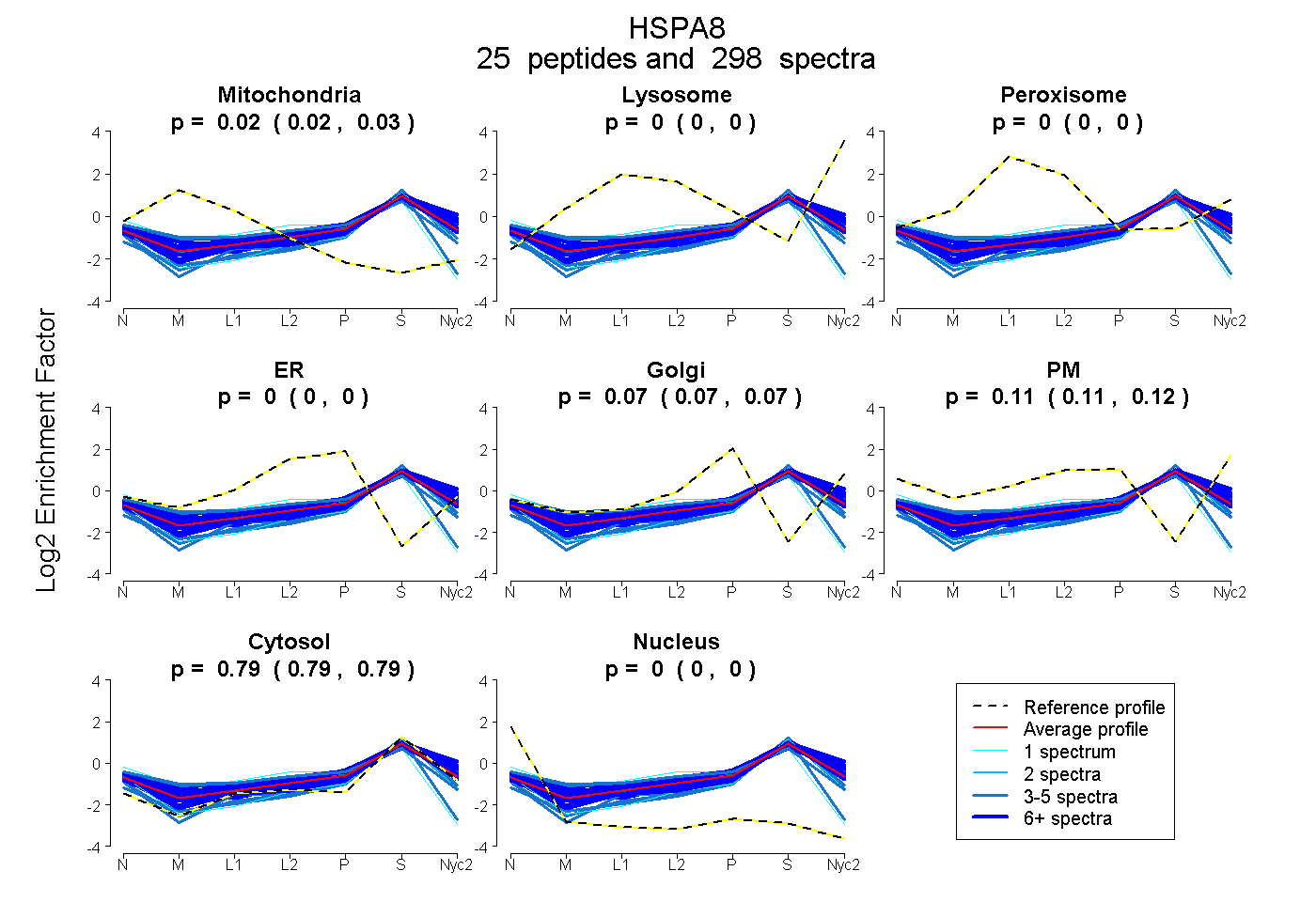
0.022 | 0.025
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.067 | 0.072
0.109 | 0.116
0.792 | 0.794
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
298 spectra |
 |
0.024 0.022 | 0.025 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.070 0.067 | 0.072 |
0.113 0.109 | 0.116 |
0.793 0.792 | 0.794 |
0.000 0.000 | 0.000 |
| 20 spectra, SQIHDIVLVGGSTR | 0.046 | 0.000 | 0.050 | 0.000 | 0.185 | 0.000 | 0.719 | 0.000 | ||
| 43 spectra, STAGDTHLGGEDFDNR | 0.000 | 0.000 | 0.000 | 0.092 | 0.012 | 0.107 | 0.789 | 0.000 | ||
| 1 spectrum, TVTNAVVTVPAYFNDSQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.867 | 0.102 | ||
| 14 spectra, LLQDFFNGK | 0.042 | 0.000 | 0.000 | 0.000 | 0.000 | 0.214 | 0.743 | 0.000 | ||
| 11 spectra, HWPFMVVNDAGRPK | 0.000 | 0.016 | 0.000 | 0.000 | 0.039 | 0.167 | 0.778 | 0.000 | ||
| 5 spectra, NQVAMNPTNTVFDAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | 0.224 | 0.762 | 0.000 | ||
| 13 spectra, VQVEYK | 0.087 | 0.000 | 0.000 | 0.000 | 0.101 | 0.010 | 0.802 | 0.000 | ||
| 4 spectra, FDDAVVQSDMK | 0.070 | 0.000 | 0.000 | 0.000 | 0.138 | 0.000 | 0.793 | 0.000 | ||
| 3 spectra, ATVEDEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | 0.000 | 0.925 | 0.065 | ||
| 13 spectra, NSLESYAFNMK | 0.000 | 0.000 | 0.009 | 0.000 | 0.000 | 0.275 | 0.716 | 0.000 | ||
| 5 spectra, ITITNDK | 0.046 | 0.000 | 0.087 | 0.000 | 0.023 | 0.155 | 0.689 | 0.000 | ||
| 6 spectra, FELTGIPPAPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.178 | 0.822 | 0.000 | ||
| 1 spectrum, CNEIISWLDK | 0.195 | 0.000 | 0.000 | 0.157 | 0.000 | 0.000 | 0.579 | 0.069 | ||
| 18 spectra, MVNHFIAEFK | 0.003 | 0.000 | 0.061 | 0.000 | 0.147 | 0.039 | 0.750 | 0.000 | ||
| 15 spectra, DAGTIAGLNVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.101 | 0.035 | 0.852 | 0.013 | ||
| 17 spectra, SFYPEEVSSMVLTK | 0.000 | 0.000 | 0.017 | 0.000 | 0.026 | 0.213 | 0.743 | 0.000 | ||
| 3 spectra, GPAVGIDLGTTYSCVGVFQHGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.835 | 0.165 | ||
| 27 spectra, TTPSYVAFTDTER | 0.000 | 0.000 | 0.000 | 0.000 | 0.047 | 0.128 | 0.825 | 0.000 | ||
| 18 spectra, FEELNADLFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.120 | 0.835 | 0.000 | ||
| 22 spectra, MVQEAEK | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.178 | 0.756 | 0.000 | ||
| 14 spectra, GTLDPVEK | 0.054 | 0.005 | 0.000 | 0.000 | 0.000 | 0.249 | 0.691 | 0.000 | ||
| 7 spectra, EIAEAYLGK | 0.028 | 0.000 | 0.000 | 0.000 | 0.120 | 0.046 | 0.805 | 0.000 | ||
| 5 spectra, VCNPIITK | 0.142 | 0.000 | 0.028 | 0.179 | 0.000 | 0.000 | 0.651 | 0.000 | ||
| 4 spectra, EEFEHQQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | 0.000 | 0.899 | 0.061 | ||
| 9 spectra, DNNLLGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.206 | 0.794 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
12 spectra |
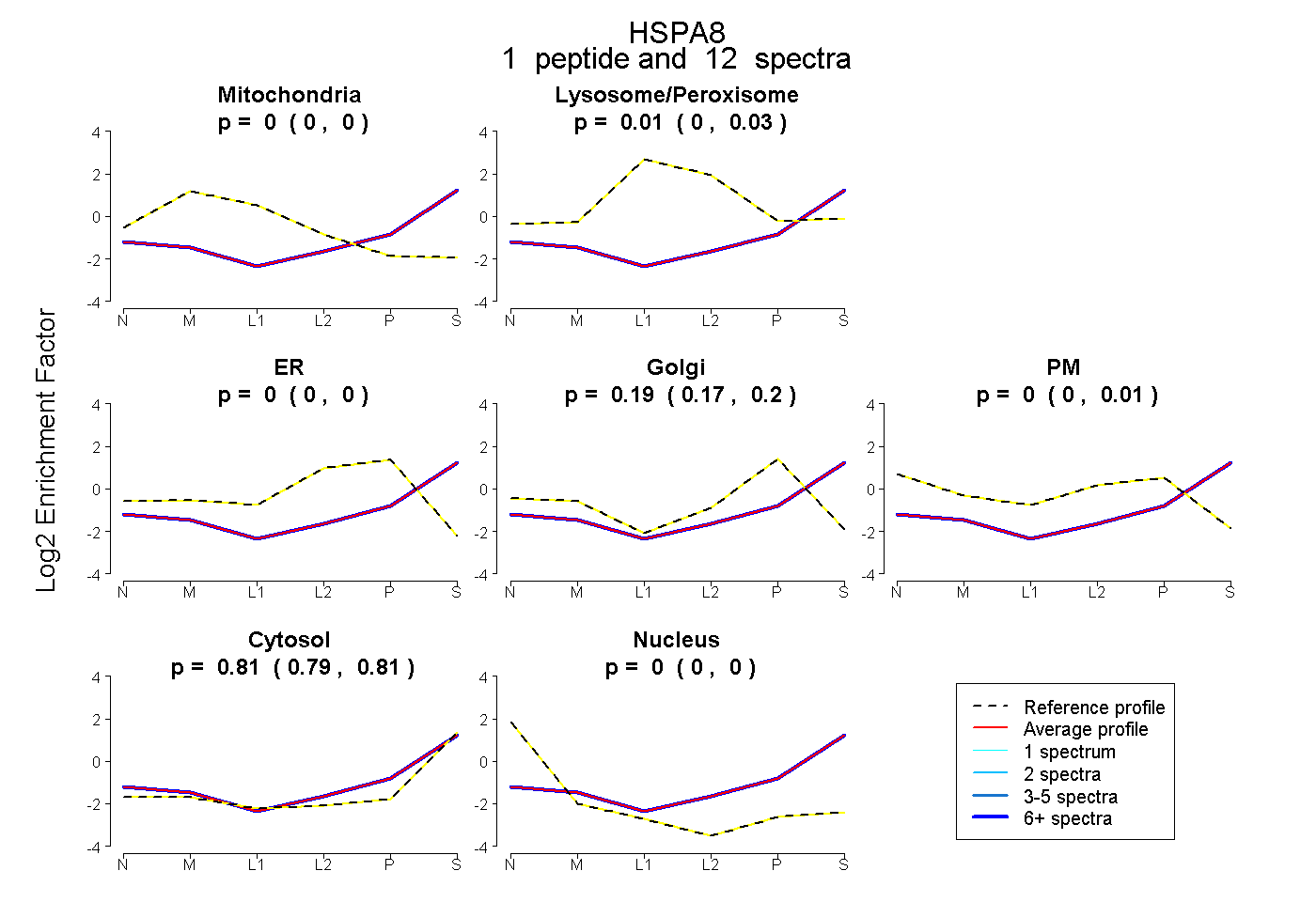 |
0.000 0.000 | 0.000 |
0.006 0.000 | 0.028 |
0.000 0.000 | 0.000 |
0.188 0.166 | 0.197 |
0.000 0.000 | 0.014 |
0.806 0.793 | 0.815 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3 spectra |
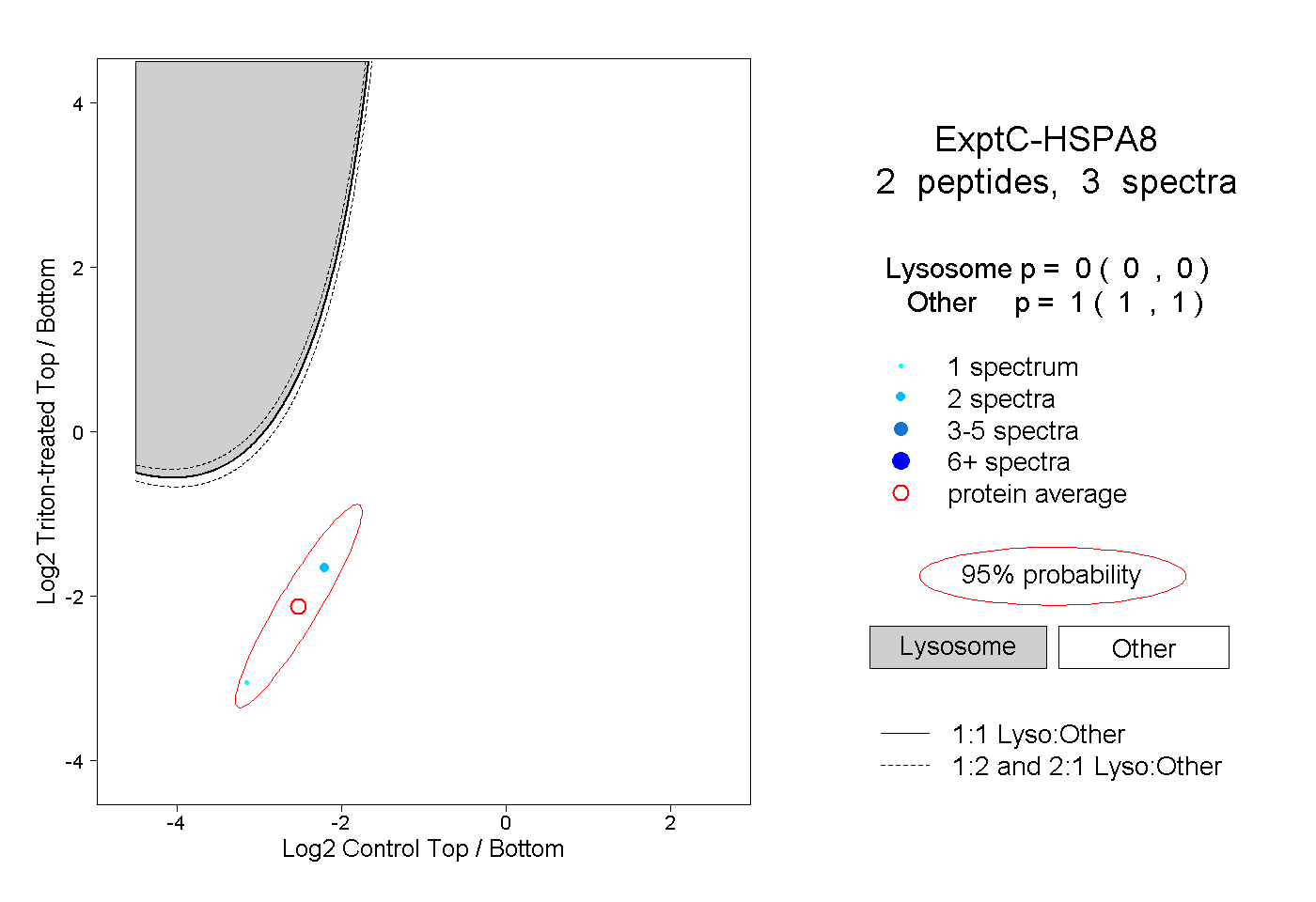 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |