peptides
spectra
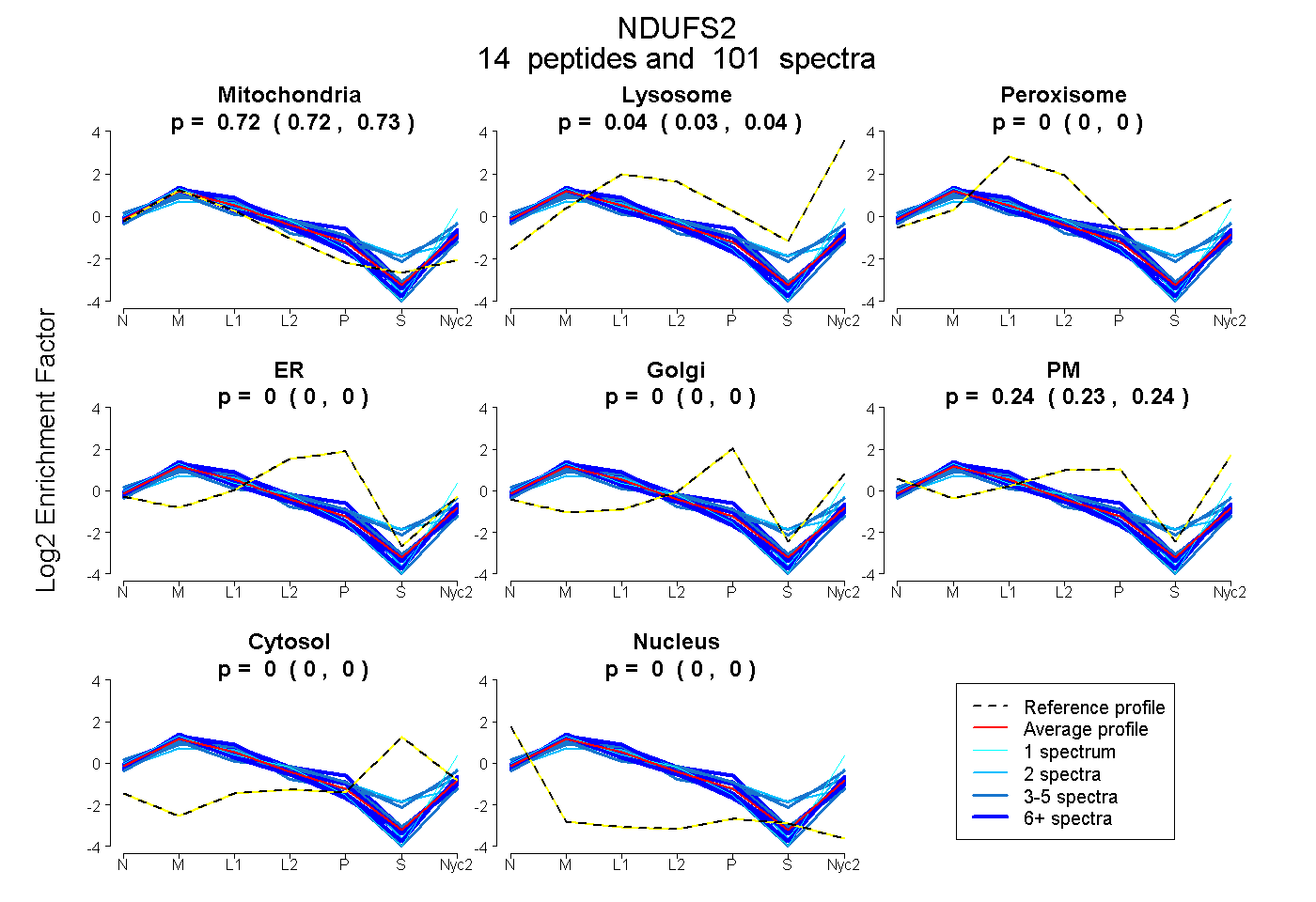
0.722 | 0.727
0.034 | 0.040
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.234 | 0.242
0.000 | 0.000
0.000 | 0.000
peptides
spectra
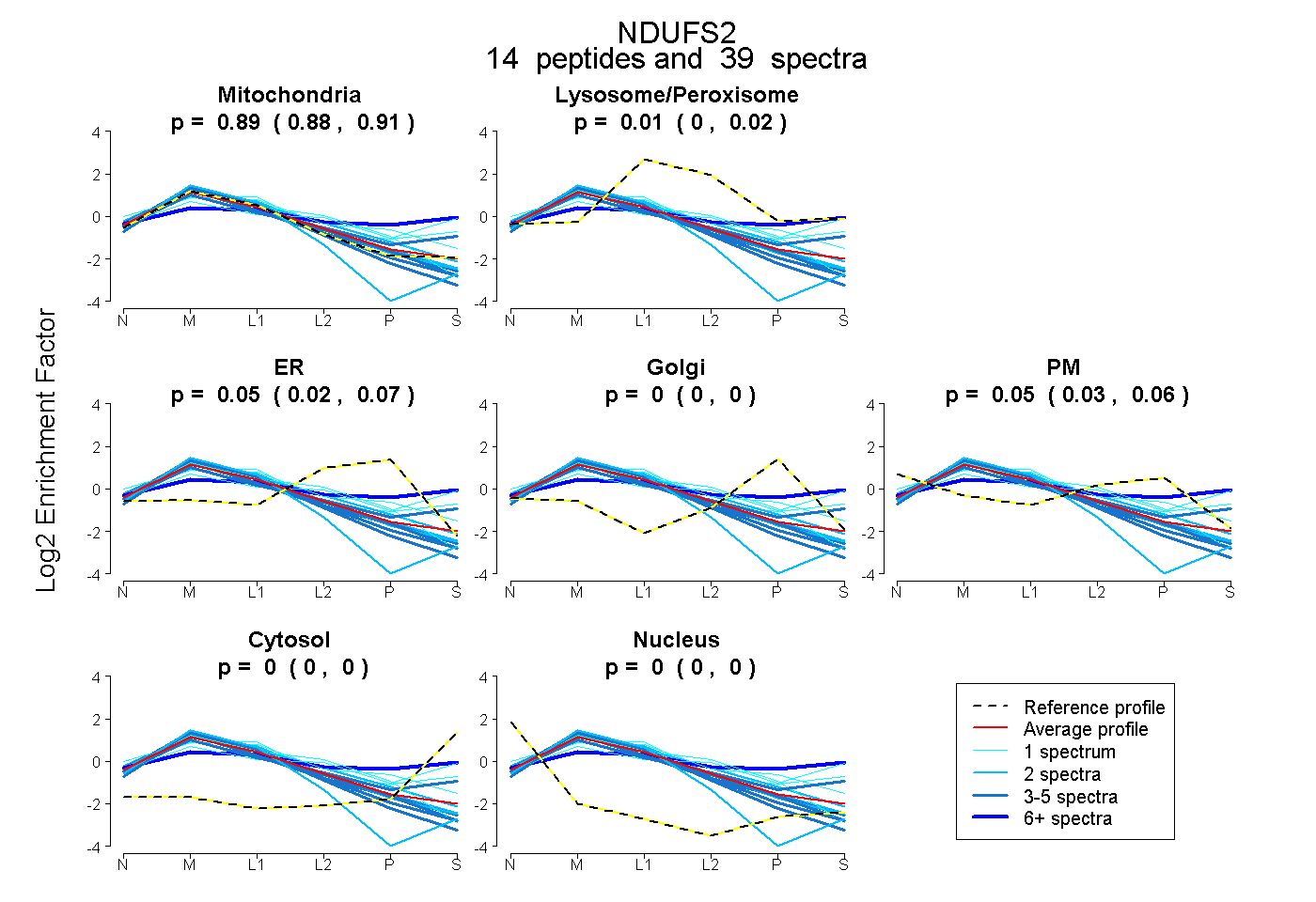
0.876 | 0.905
0.000 | 0.021
0.025 | 0.072
0.000 | 0.000
0.029 | 0.064
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
101 spectra |
 |
0.724 0.722 | 0.727 |
0.037 0.034 | 0.040 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.238 0.234 | 0.242 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
39 spectra |
 |
0.891 0.876 | 0.905 |
0.010 0.000 | 0.021 |
0.050 0.025 | 0.072 |
0.000 0.000 | 0.000 |
0.049 0.029 | 0.064 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, APGFAHLAGLDK | 0.933 | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GDCYDR | 0.790 | 0.050 | 0.086 | 0.000 | 0.074 | 0.000 | 0.000 | |||
| 2 spectra, GSGIQWDLR | 0.927 | 0.000 | 0.055 | 0.000 | 0.012 | 0.000 | 0.006 | |||
| 1 spectrum, ETAHWKPPPWNDVDVLK | 0.628 | 0.237 | 0.000 | 0.000 | 0.036 | 0.099 | 0.000 | |||
| 3 spectra, MFEFYER | 0.918 | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, VLFGEITR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MPPGEIK | 0.378 | 0.286 | 0.000 | 0.000 | 0.104 | 0.231 | 0.000 | |||
| 2 spectra, VVTNVTLNFGPQHPAAHGVLR | 0.949 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.051 | |||
| 1 spectrum, LVLELSGEMVR | 0.578 | 0.168 | 0.000 | 0.000 | 0.254 | 0.000 | 0.000 | |||
| 3 spectra, TYLQALPYFDR | 0.672 | 0.118 | 0.000 | 0.000 | 0.079 | 0.131 | 0.000 | |||
| 5 spectra, GEFGVYLVSDGSSRPYR | 0.911 | 0.000 | 0.046 | 0.005 | 0.011 | 0.000 | 0.026 | |||
| 5 spectra, IDEVEEMLTNNR | 0.983 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.017 | |||
| 1 spectrum, TSMESLIHHFK | 0.738 | 0.000 | 0.262 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, LLNIQPPPR | 0.255 | 0.353 | 0.000 | 0.129 | 0.058 | 0.205 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
220 spectra |
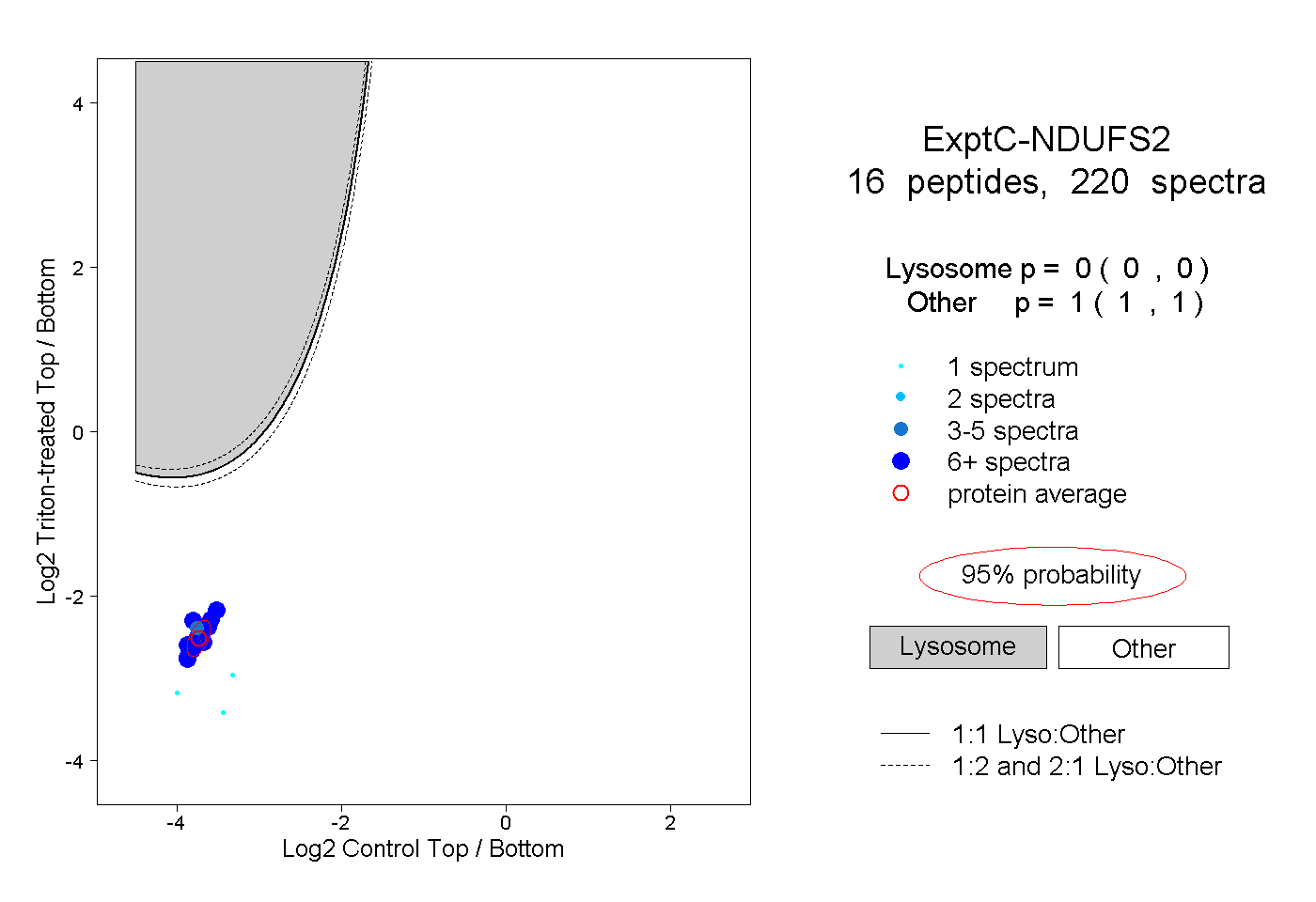 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
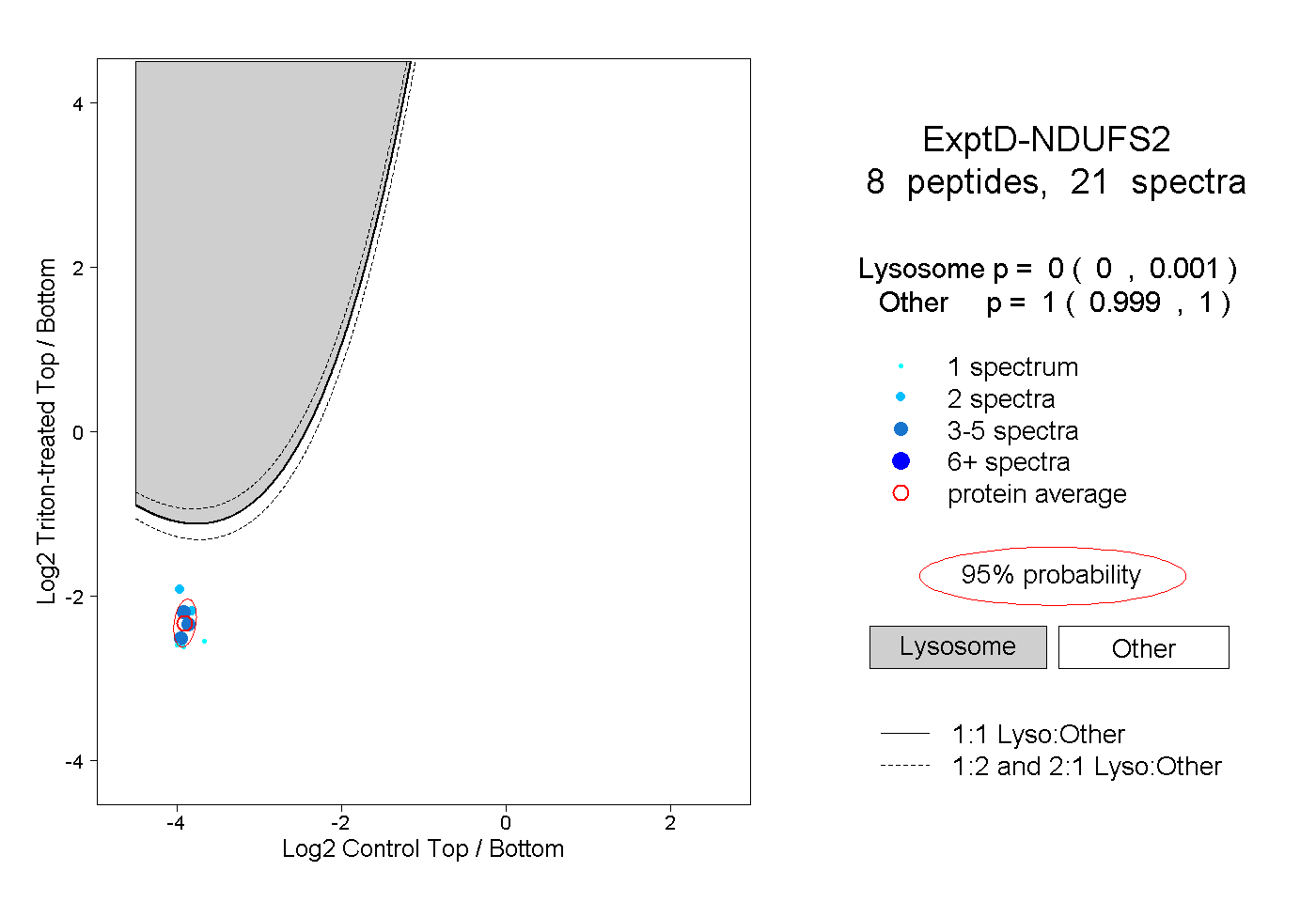 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |