peptides
spectra
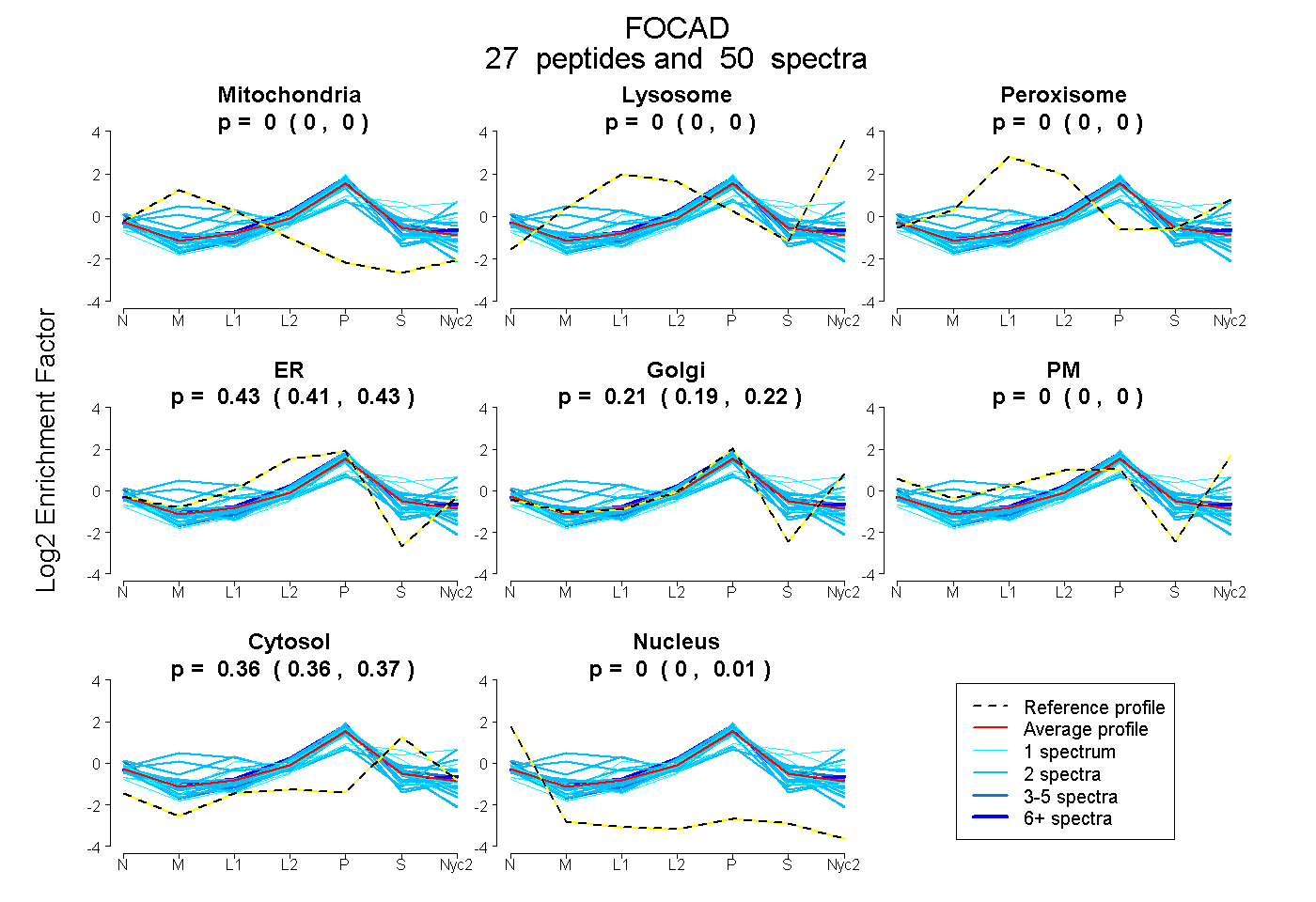
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.415 | 0.435
0.193 | 0.218
0.000 | 0.000
0.360 | 0.368
0.000 | 0.006
peptides
spectra
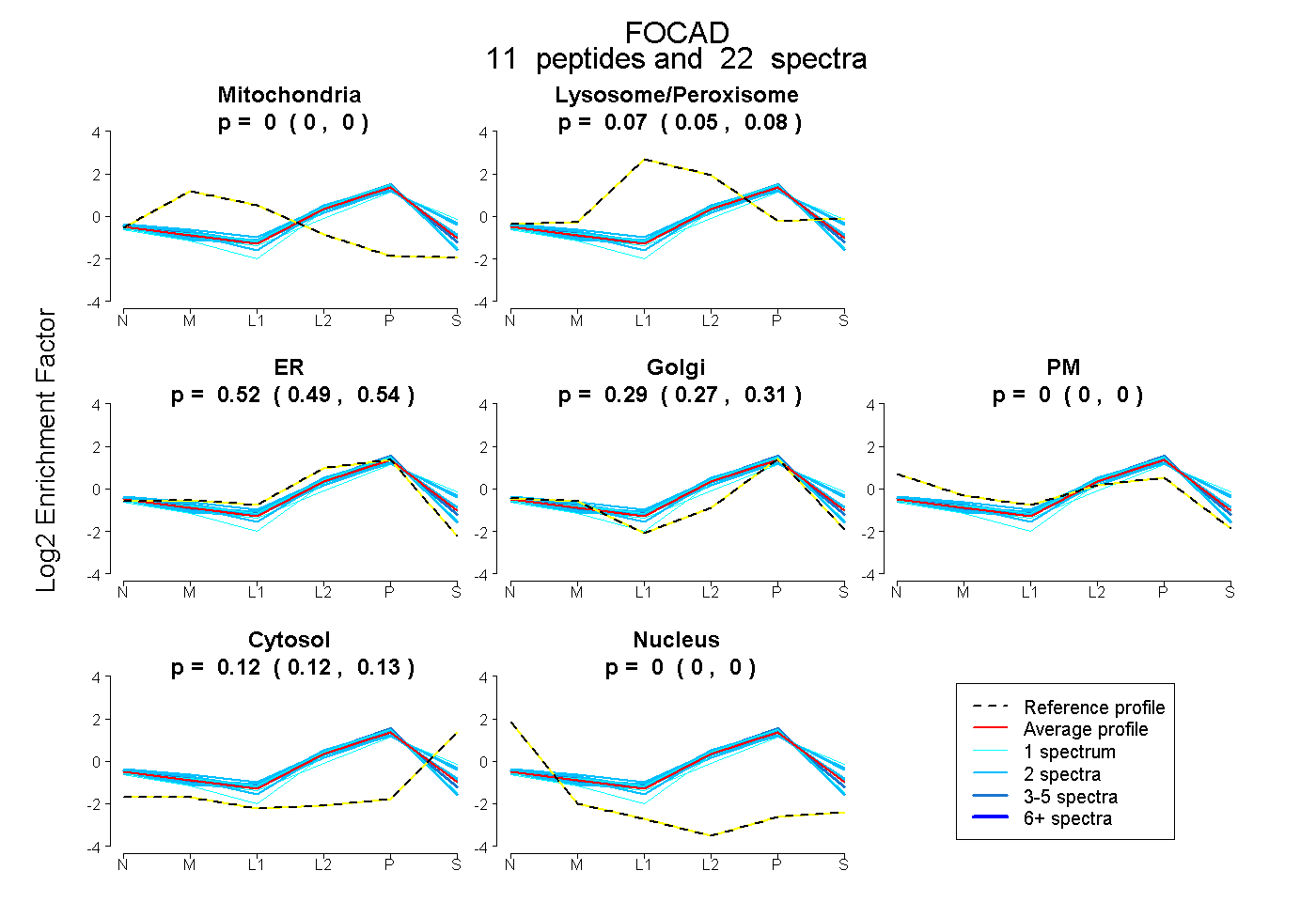
0.000 | 0.000
0.054 | 0.075
0.490 | 0.539
0.273 | 0.309
0.000 | 0.000
0.117 | 0.131
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
50 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.425 0.415 | 0.435 |
0.207 0.193 | 0.218 |
0.000 0.000 | 0.000 |
0.364 0.360 | 0.368 |
0.003 0.000 | 0.006 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.065 0.054 | 0.075 |
0.517 0.490 | 0.539 |
0.293 0.273 | 0.309 |
0.000 0.000 | 0.000 |
0.125 0.117 | 0.131 |
0.000 0.000 | 0.000 |
| 2 spectra, LLTSLWEK | 0.000 | 0.125 | 0.403 | 0.254 | 0.000 | 0.217 | 0.000 | |||
| 2 spectra, LLSLTEGQR | 0.000 | 0.200 | 0.303 | 0.416 | 0.000 | 0.081 | 0.000 | |||
| 2 spectra, AAIGFFITGGK | 0.000 | 0.126 | 0.343 | 0.326 | 0.000 | 0.204 | 0.000 | |||
| 2 spectra, TVAGIPNFILK | 0.000 | 0.041 | 0.644 | 0.272 | 0.000 | 0.043 | 0.000 | |||
| 4 spectra, IFDLLPNR | 0.000 | 0.071 | 0.555 | 0.284 | 0.000 | 0.090 | 0.000 | |||
| 2 spectra, LYLISQGR | 0.000 | 0.000 | 0.597 | 0.236 | 0.000 | 0.167 | 0.000 | |||
| 3 spectra, ATLLSLR | 0.000 | 0.036 | 0.624 | 0.288 | 0.000 | 0.053 | 0.000 | |||
| 1 spectrum, VLLQPR | 0.000 | 0.039 | 0.623 | 0.278 | 0.000 | 0.060 | 0.000 | |||
| 2 spectra, VIQLLGTTPR | 0.000 | 0.040 | 0.637 | 0.272 | 0.000 | 0.051 | 0.000 | |||
| 1 spectrum, DLQDLYSIR | 0.000 | 0.163 | 0.155 | 0.455 | 0.000 | 0.226 | 0.000 | |||
| 1 spectrum, AEDLGNR | 0.000 | 0.000 | 0.453 | 0.411 | 0.000 | 0.135 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
41 spectra |
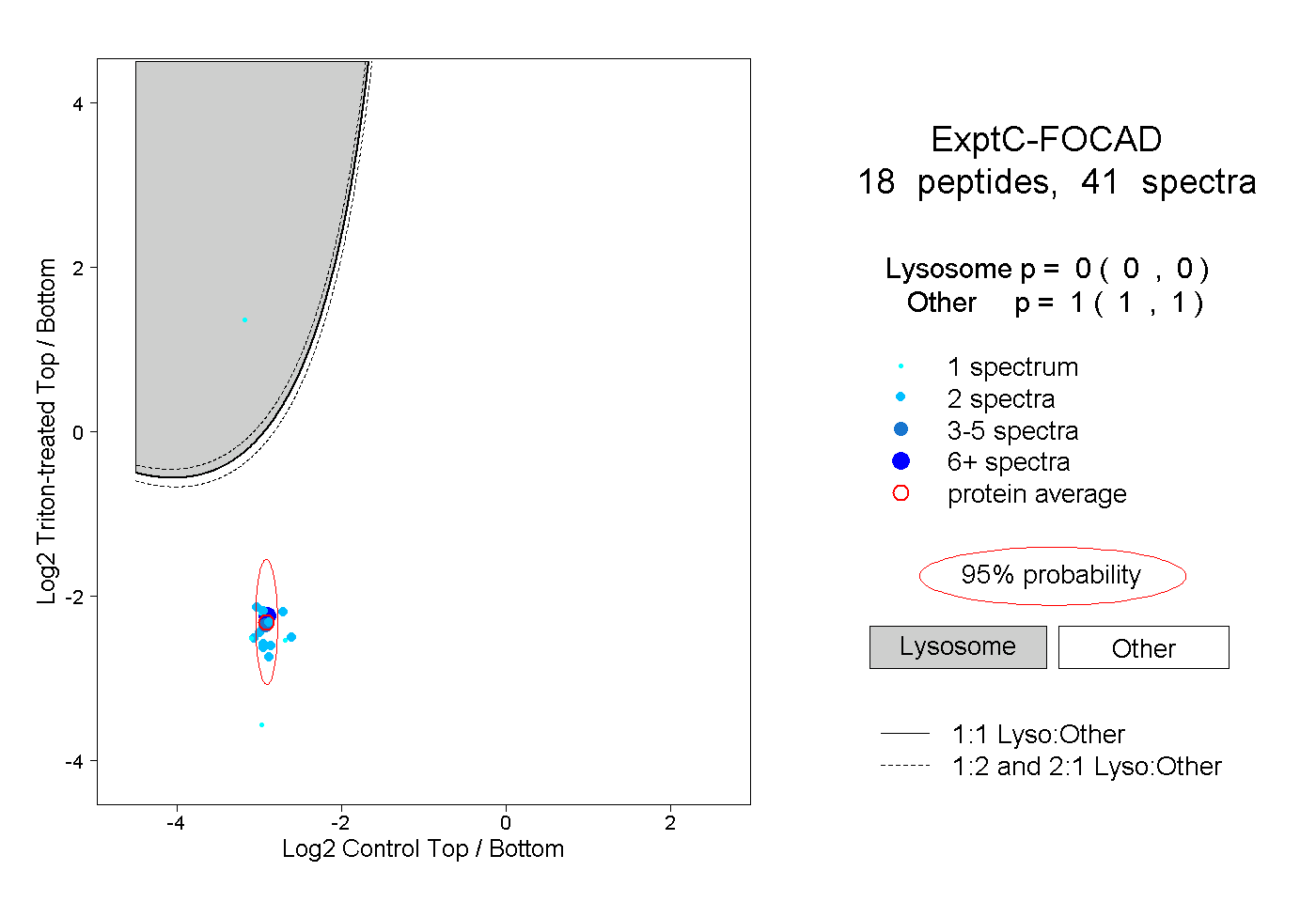 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
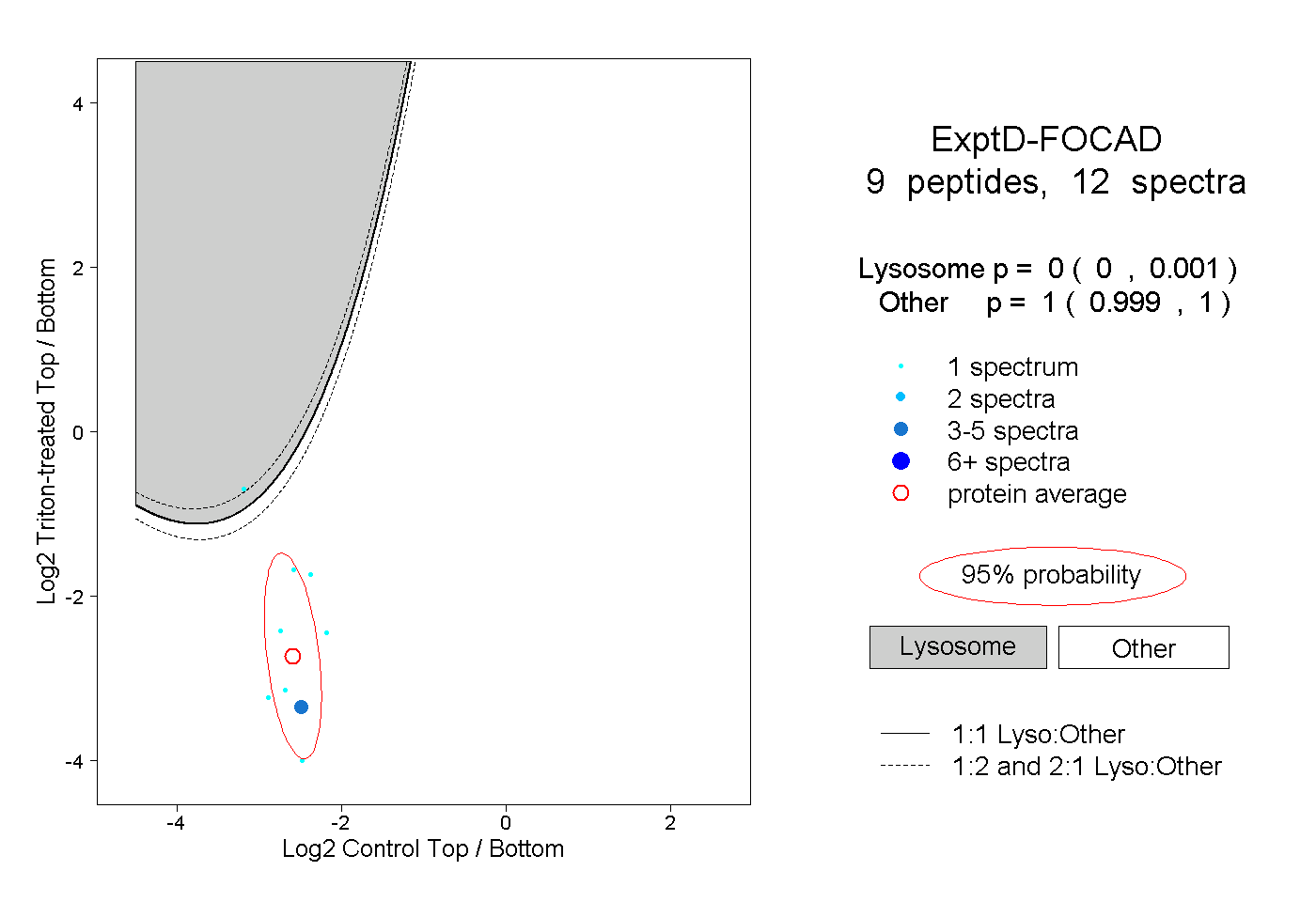 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |