peptides
spectra
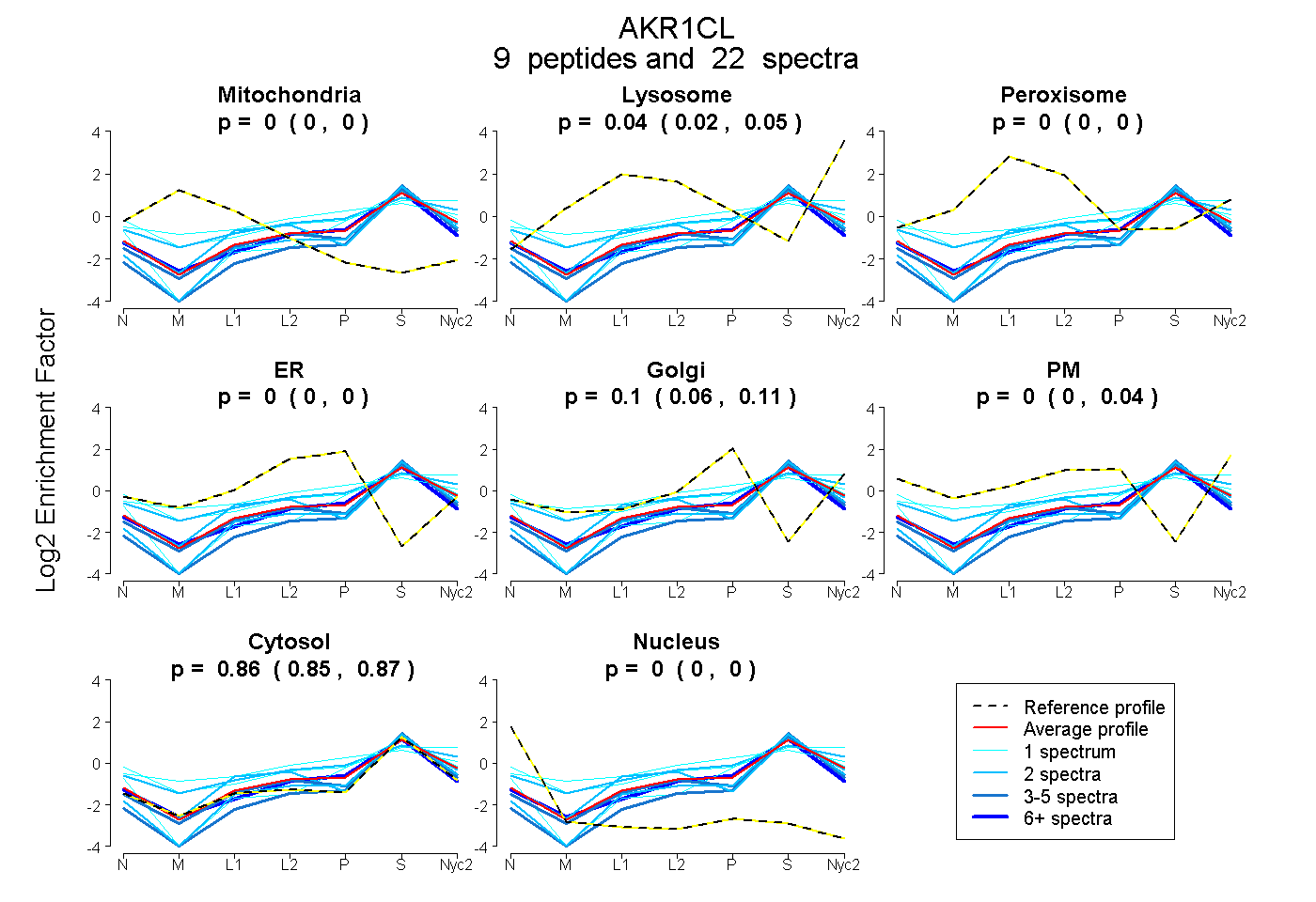
0.000 | 0.000
0.015 | 0.050
0.000 | 0.000
0.000 | 0.002
0.058 | 0.113
0.000 | 0.042
0.849 | 0.874
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.038 0.015 | 0.050 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.100 0.058 | 0.113 |
0.000 0.000 | 0.042 |
0.862 0.849 | 0.874 |
0.000 0.000 | 0.000 |
| 4 spectra, TIDSLNR | 0.000 | 0.024 | 0.000 | 0.020 | 0.000 | 0.000 | 0.956 | 0.000 | ||
| 1 spectrum, AAEATK | 0.000 | 0.074 | 0.000 | 0.000 | 0.000 | 0.316 | 0.611 | 0.000 | ||
| 1 spectrum, HNQTPGQVALR | 0.000 | 0.002 | 0.196 | 0.000 | 0.209 | 0.093 | 0.500 | 0.000 | ||
| 2 spectra, VAIDVGFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, FIFDTVDIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, ENFQVFDFELTPEDMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.893 | 0.000 | ||
| 2 spectra, LNDGNLMPVLGFGTFASK | 0.000 | 0.003 | 0.152 | 0.000 | 0.000 | 0.000 | 0.845 | 0.000 | ||
| 6 spectra, DTWEALEK | 0.000 | 0.000 | 0.000 | 0.054 | 0.045 | 0.000 | 0.900 | 0.000 | ||
| 2 spectra, EDLFYTTK | 0.000 | 0.102 | 0.003 | 0.000 | 0.000 | 0.238 | 0.657 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
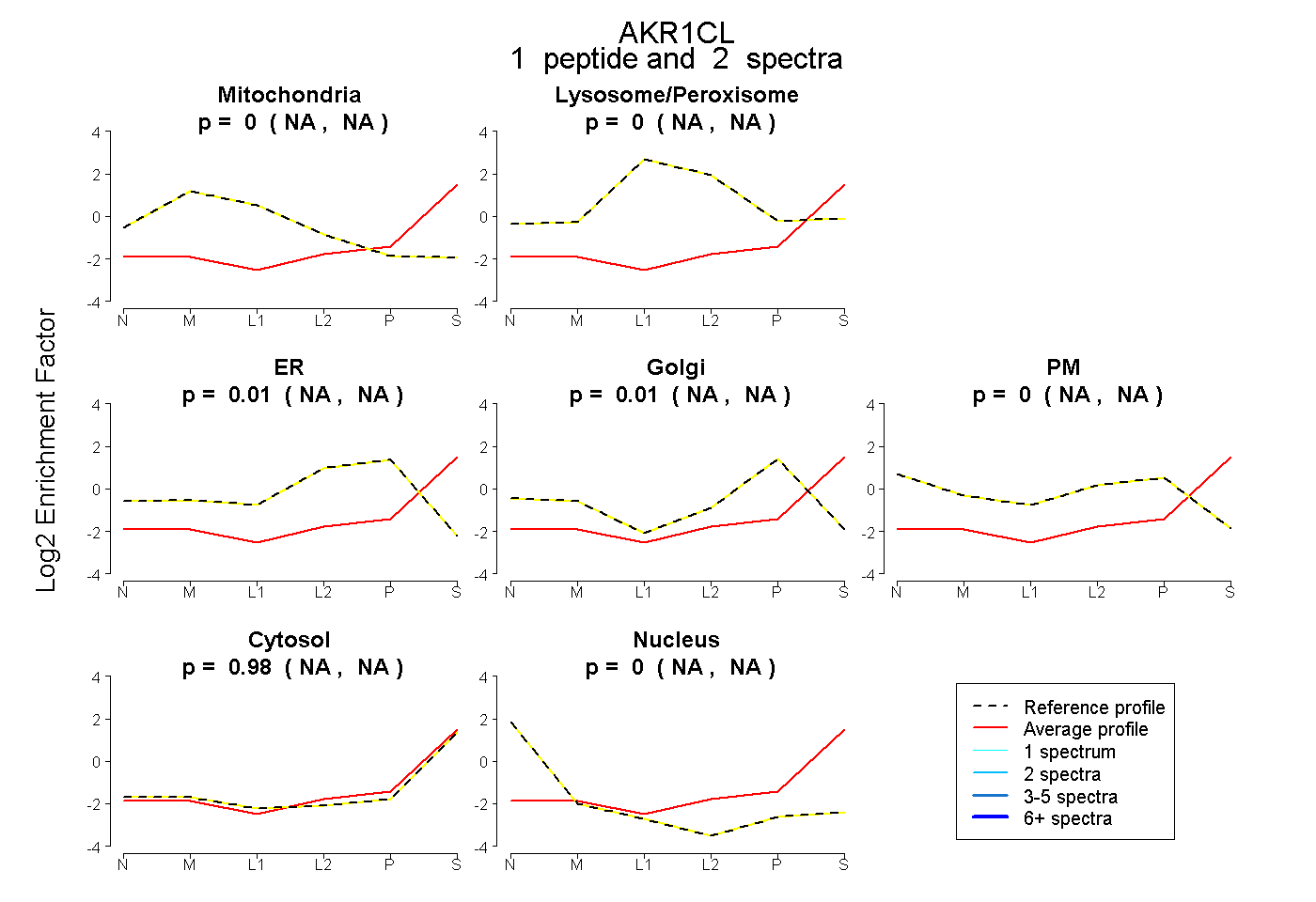 |
0.000 NA | NA |
0.000 NA | NA |
0.011 NA | NA |
0.012 NA | NA |
0.000 NA | NA |
0.977 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
36 spectra |
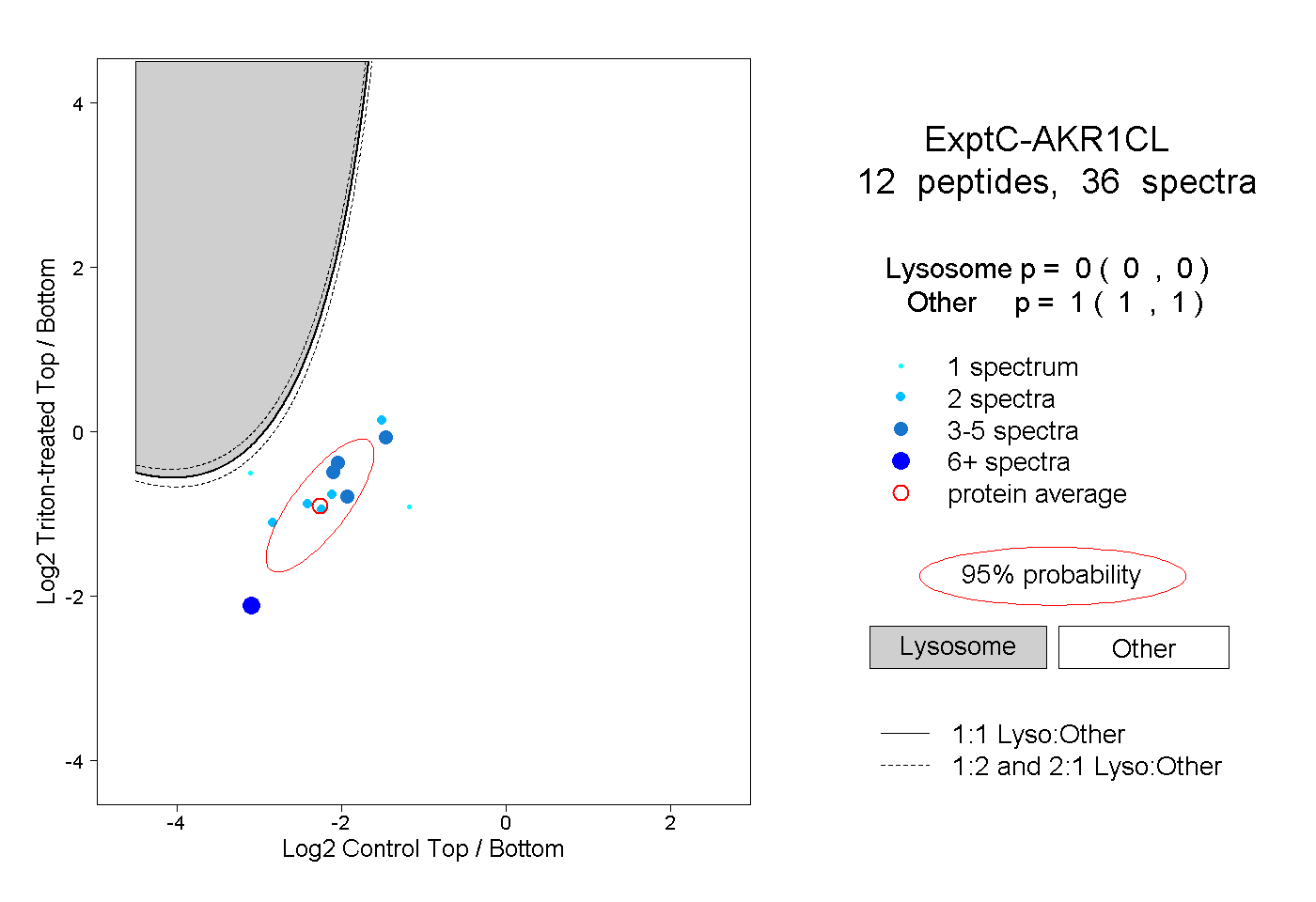 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |