peptides
spectra
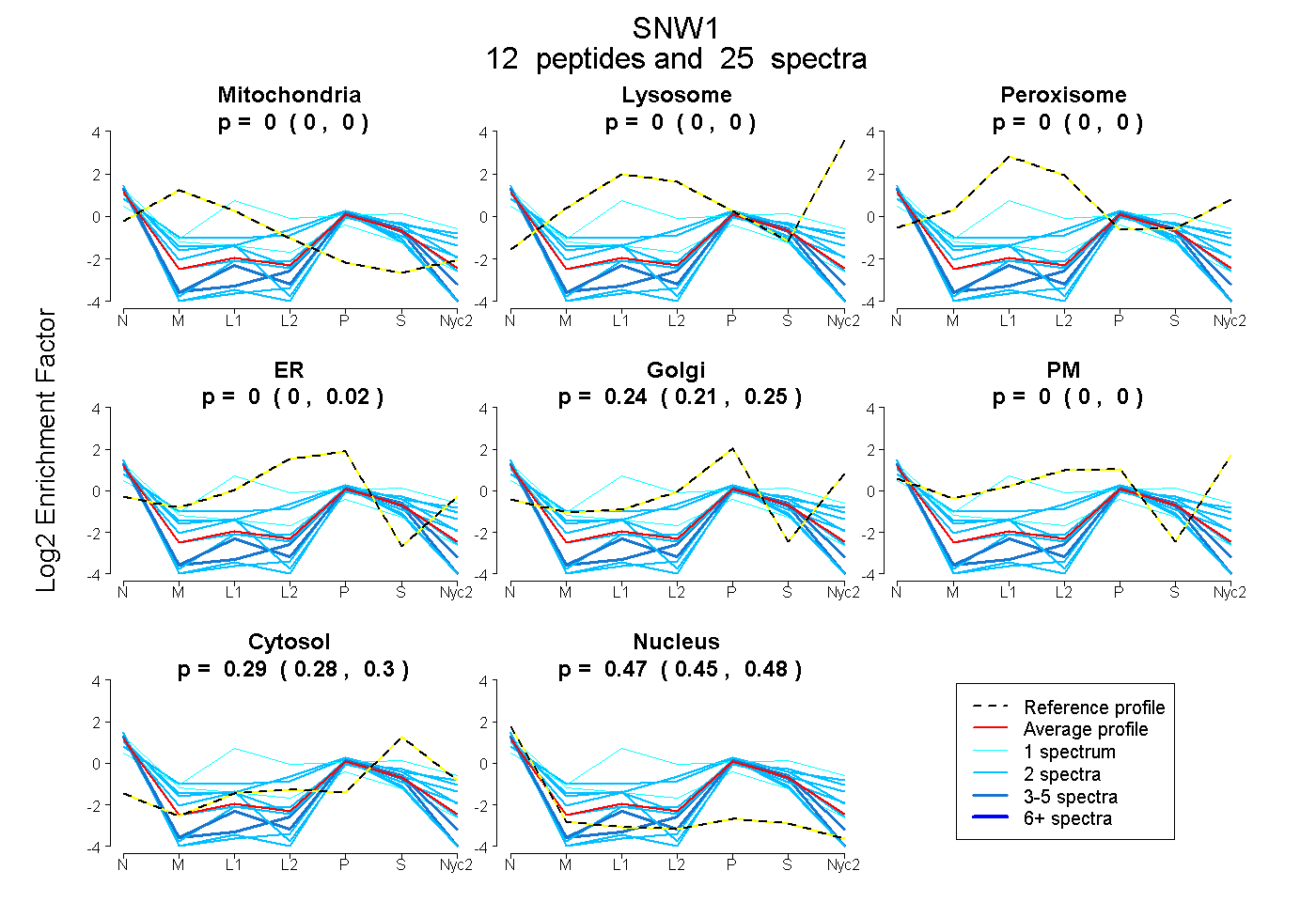
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.021
0.206 | 0.248
0.000 | 0.000
0.284 | 0.302
0.454 | 0.480
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.021 |
0.237 0.206 | 0.248 |
0.000 0.000 | 0.000 |
0.293 0.284 | 0.302 |
0.469 0.454 | 0.480 |
| 2 spectra, YTDLVPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.275 | 0.000 | 0.297 | 0.428 | ||
| 1 spectrum, LAADGR | 0.109 | 0.000 | 0.012 | 0.263 | 0.000 | 0.000 | 0.160 | 0.455 | ||
| 3 spectra, LAEALYIADR | 0.000 | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 | 0.263 | 0.679 | ||
| 2 spectra, EHEHEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.044 | 0.000 | 0.168 | 0.788 | ||
| 4 spectra, VAAAMPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.089 | 0.000 | 0.315 | 0.597 | ||
| 2 spectra, TSNEVQYDQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | 0.000 | 0.196 | 0.803 | ||
| 2 spectra, QTSLVSSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.304 | 0.000 | 0.240 | 0.457 | ||
| 2 spectra, EQQEWK | 0.011 | 0.000 | 0.042 | 0.044 | 0.108 | 0.271 | 0.333 | 0.192 | ||
| 1 spectrum, IPPCISNWK | 0.000 | 0.000 | 0.436 | 0.088 | 0.067 | 0.003 | 0.291 | 0.114 | ||
| 2 spectra, EPPPYGYR | 0.000 | 0.000 | 0.000 | 0.370 | 0.000 | 0.000 | 0.347 | 0.283 | ||
| 2 spectra, DMAQSIYRPSK | 0.047 | 0.000 | 0.000 | 0.066 | 0.204 | 0.000 | 0.270 | 0.413 | ||
| 2 spectra, LAPAQYIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.210 | 0.000 | 0.421 | 0.369 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
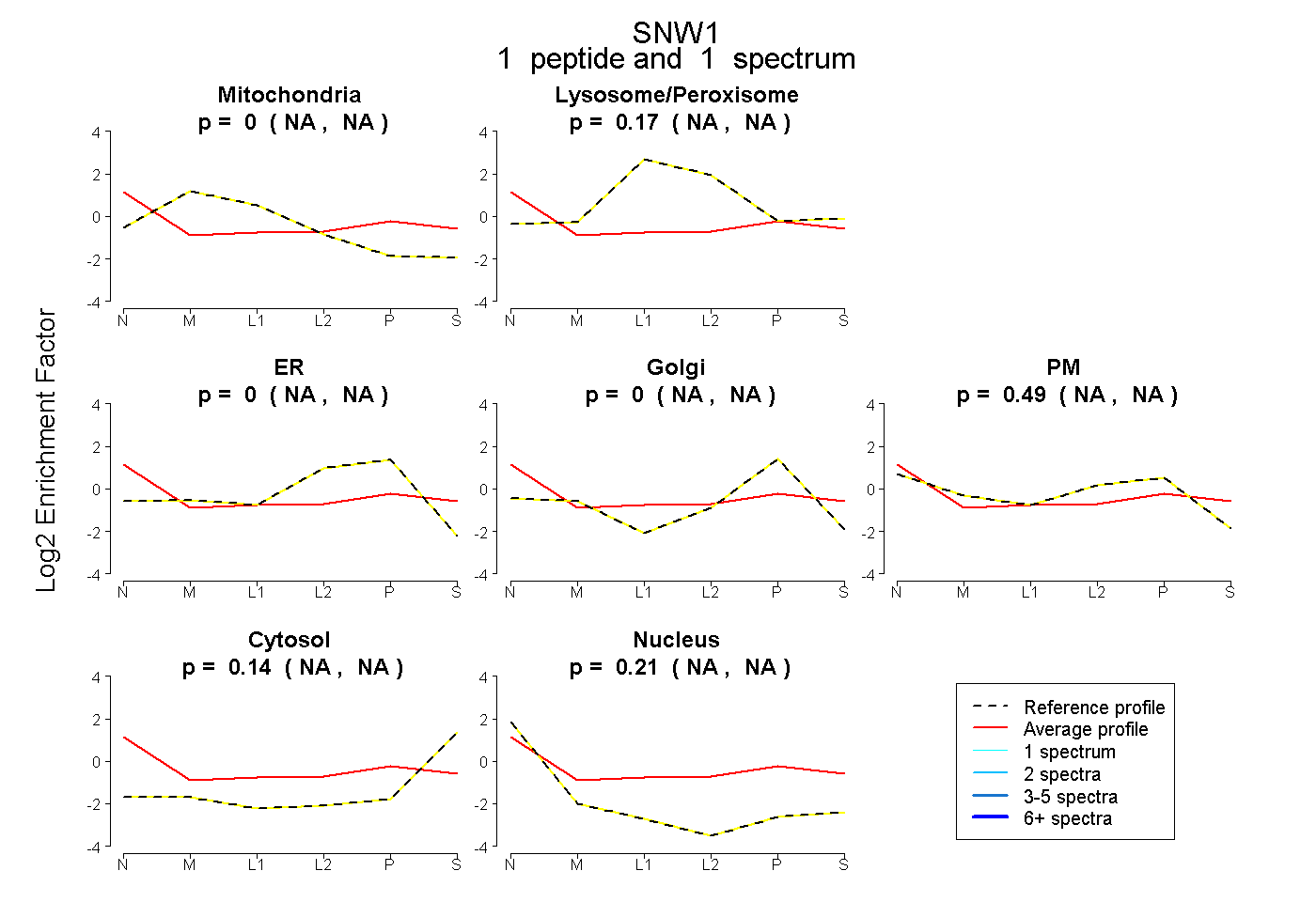 |
0.000 NA | NA |
0.171 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.486 NA | NA |
0.138 NA | NA |
0.205 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
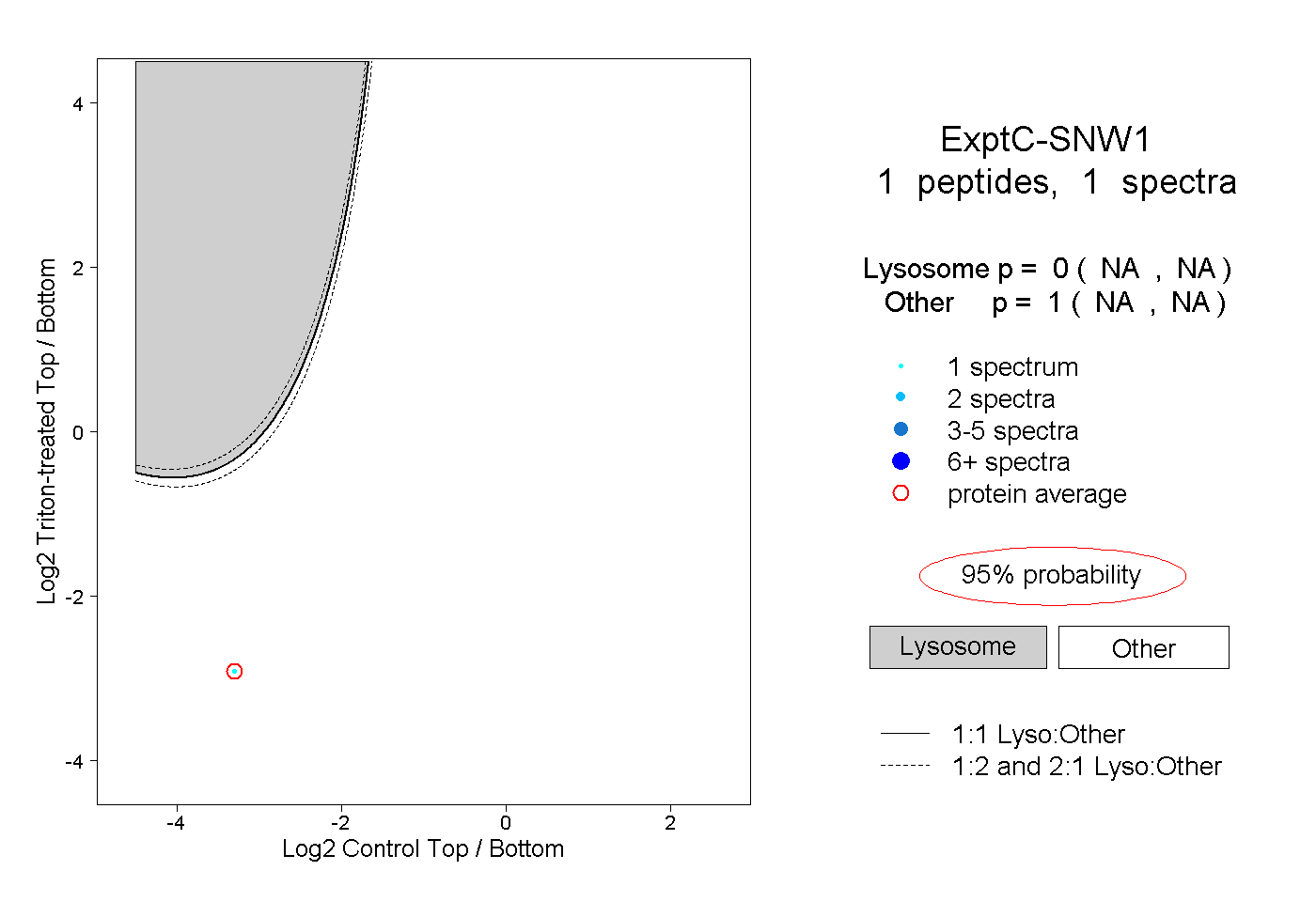 |
0.000 NA | NA |
1.000 NA | NA |