peptides
spectra

0.000 | 0.000
0.368 | 0.372
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.005 | 0.010
0.621 | 0.623
0.000 | 0.000
peptides
spectra
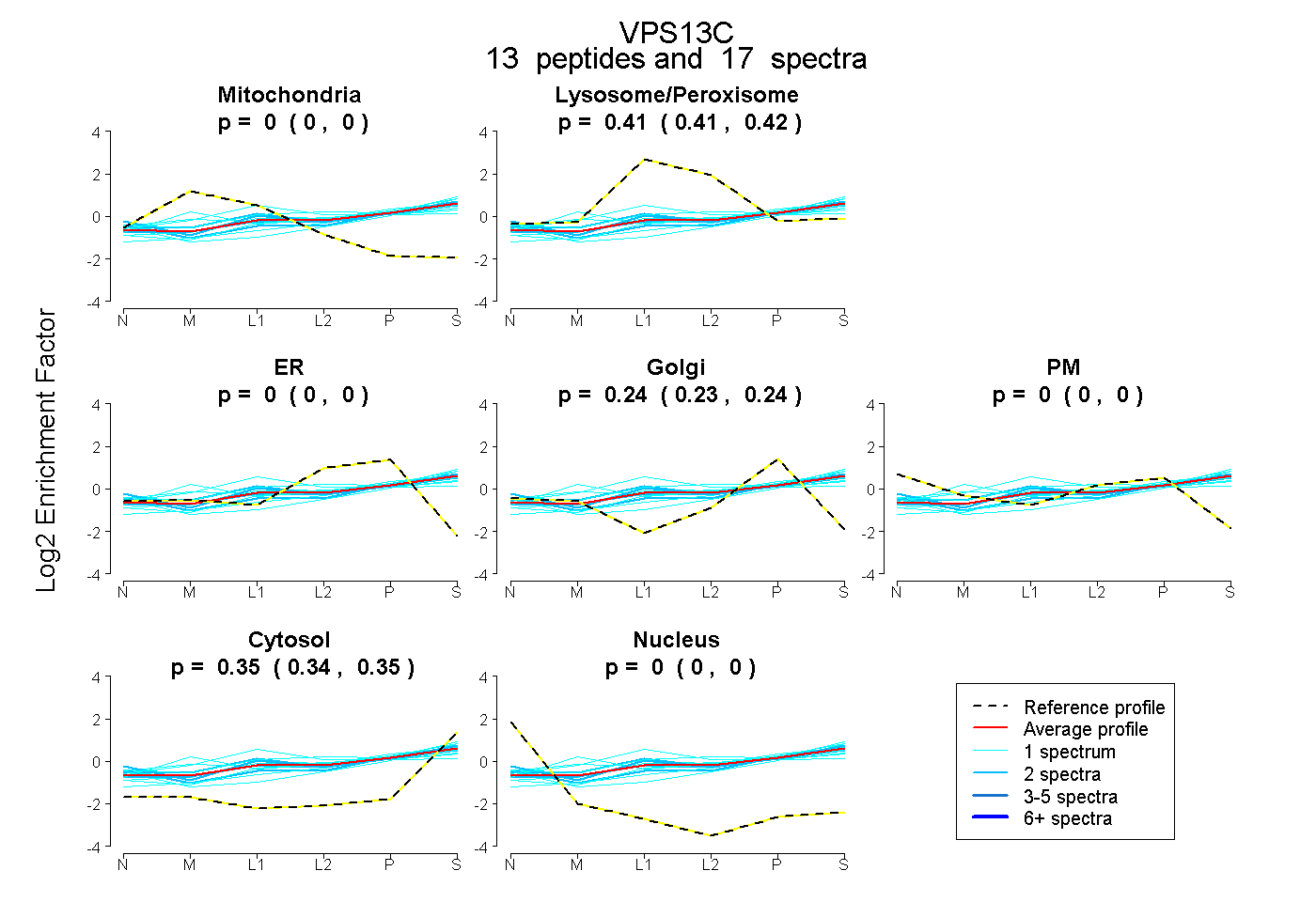
0.000 | 0.000
0.406 | 0.419
0.000 | 0.000
0.231 | 0.244
0.000 | 0.000
0.344 | 0.354
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
107 spectra |
 |
0.000 0.000 | 0.000 |
0.370 0.368 | 0.372 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.008 0.005 | 0.010 |
0.622 0.621 | 0.623 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.413 0.406 | 0.419 |
0.000 0.000 | 0.000 |
0.238 0.231 | 0.244 |
0.000 0.000 | 0.000 |
0.349 0.344 | 0.354 |
0.000 0.000 | 0.000 |
| 1 spectrum, LATQVIK | 0.000 | 0.409 | 0.000 | 0.251 | 0.057 | 0.283 | 0.000 | |||
| 1 spectrum, VPVVEIK | 0.000 | 0.489 | 0.000 | 0.231 | 0.000 | 0.279 | 0.000 | |||
| 1 spectrum, LLMDIDLK | 0.000 | 0.335 | 0.000 | 0.203 | 0.000 | 0.462 | 0.000 | |||
| 2 spectra, VLACPFLR | 0.000 | 0.417 | 0.000 | 0.179 | 0.065 | 0.339 | 0.000 | |||
| 1 spectrum, ISGEIIELVLVK | 0.000 | 0.421 | 0.000 | 0.237 | 0.000 | 0.343 | 0.000 | |||
| 1 spectrum, IQGLDSSLSLQSK | 0.000 | 0.282 | 0.000 | 0.252 | 0.000 | 0.466 | 0.000 | |||
| 1 spectrum, QIMLLEQSYQK | 0.080 | 0.361 | 0.000 | 0.307 | 0.000 | 0.251 | 0.000 | |||
| 1 spectrum, NLLPYSIR | 0.000 | 0.544 | 0.000 | 0.197 | 0.000 | 0.259 | 0.000 | |||
| 2 spectra, LLSTSIVVR | 0.000 | 0.407 | 0.000 | 0.213 | 0.000 | 0.380 | 0.000 | |||
| 2 spectra, DSDVIGFR | 0.000 | 0.356 | 0.000 | 0.257 | 0.000 | 0.387 | 0.000 | |||
| 1 spectrum, VLESVVADLLNR | 0.000 | 0.400 | 0.000 | 0.201 | 0.000 | 0.399 | 0.000 | |||
| 2 spectra, IVTLTPFCTVANK | 0.000 | 0.454 | 0.000 | 0.226 | 0.000 | 0.320 | 0.000 | |||
| 1 spectrum, IEEALQK | 0.000 | 0.443 | 0.000 | 0.232 | 0.000 | 0.325 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
176 spectra |
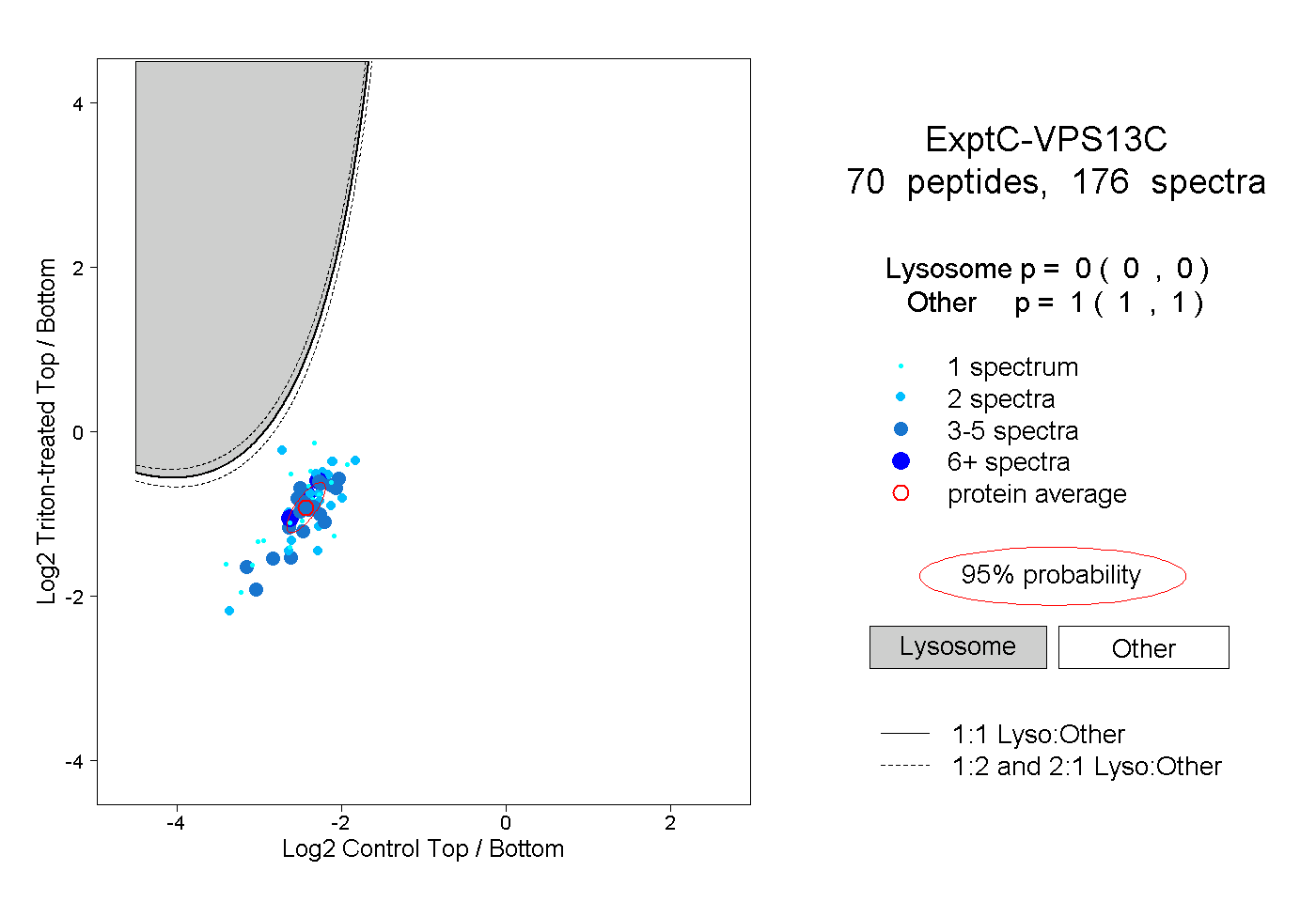 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
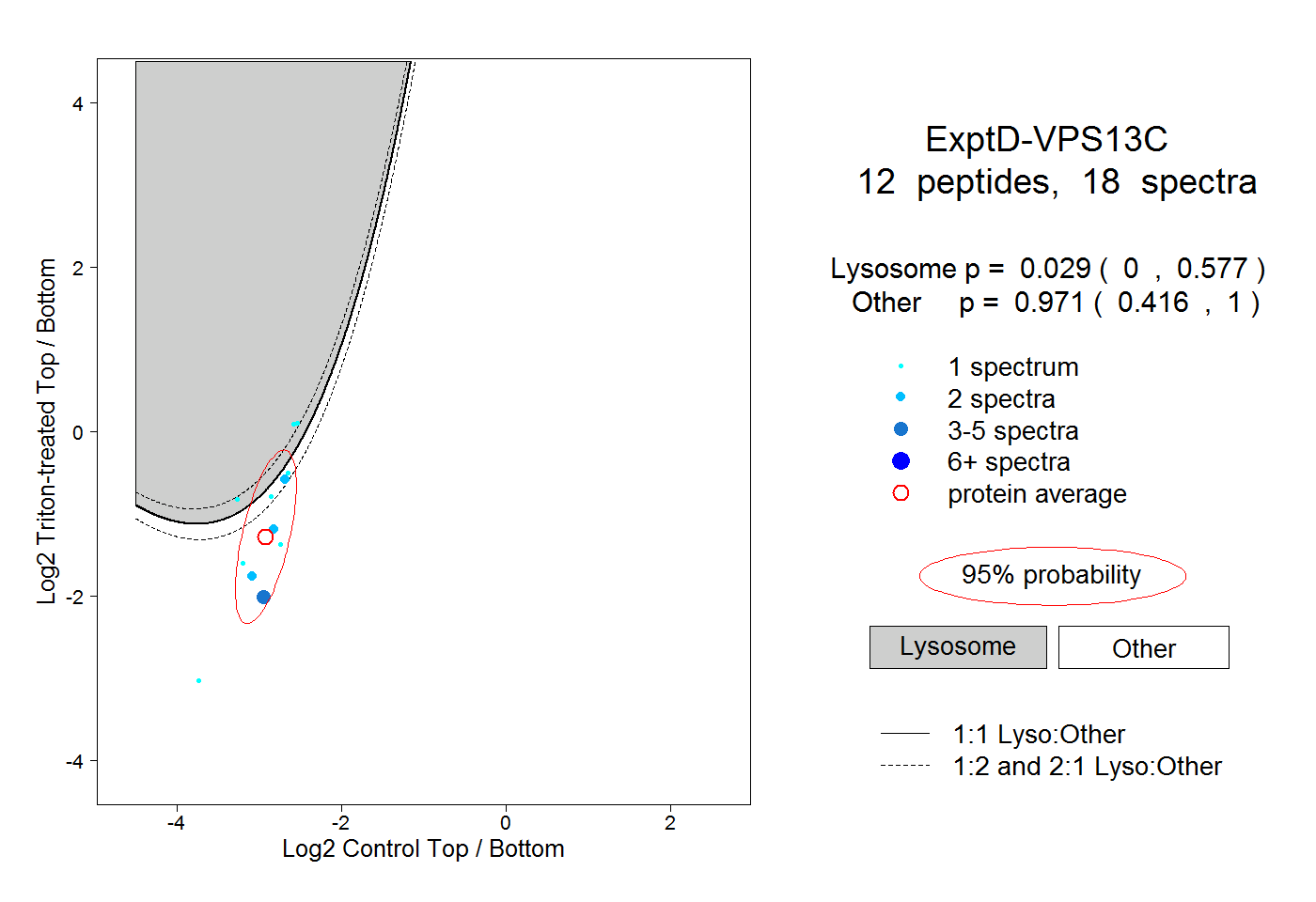 |
0.029 0.000 | 0.577 |
0.971 0.416 | 1.000 |