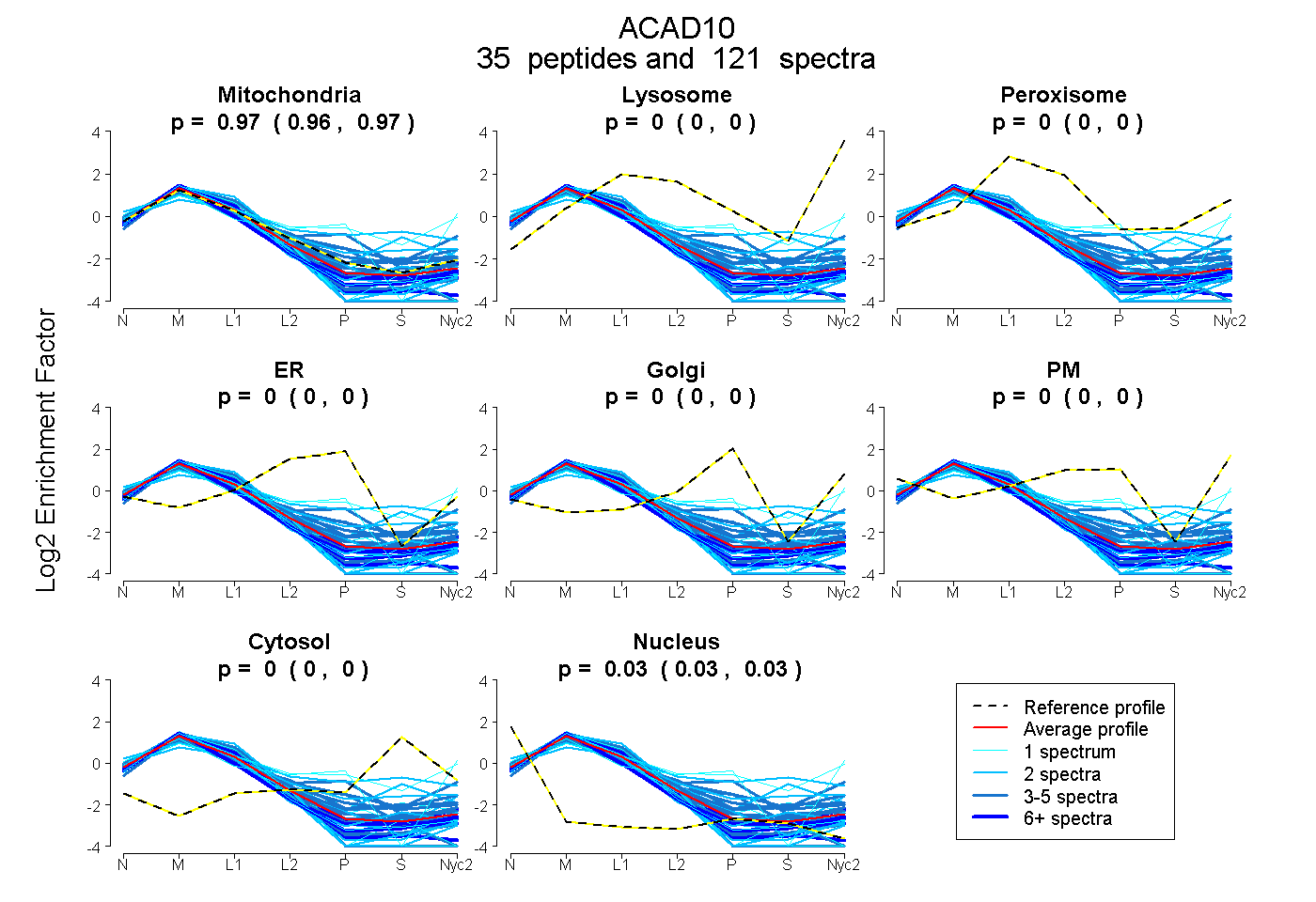
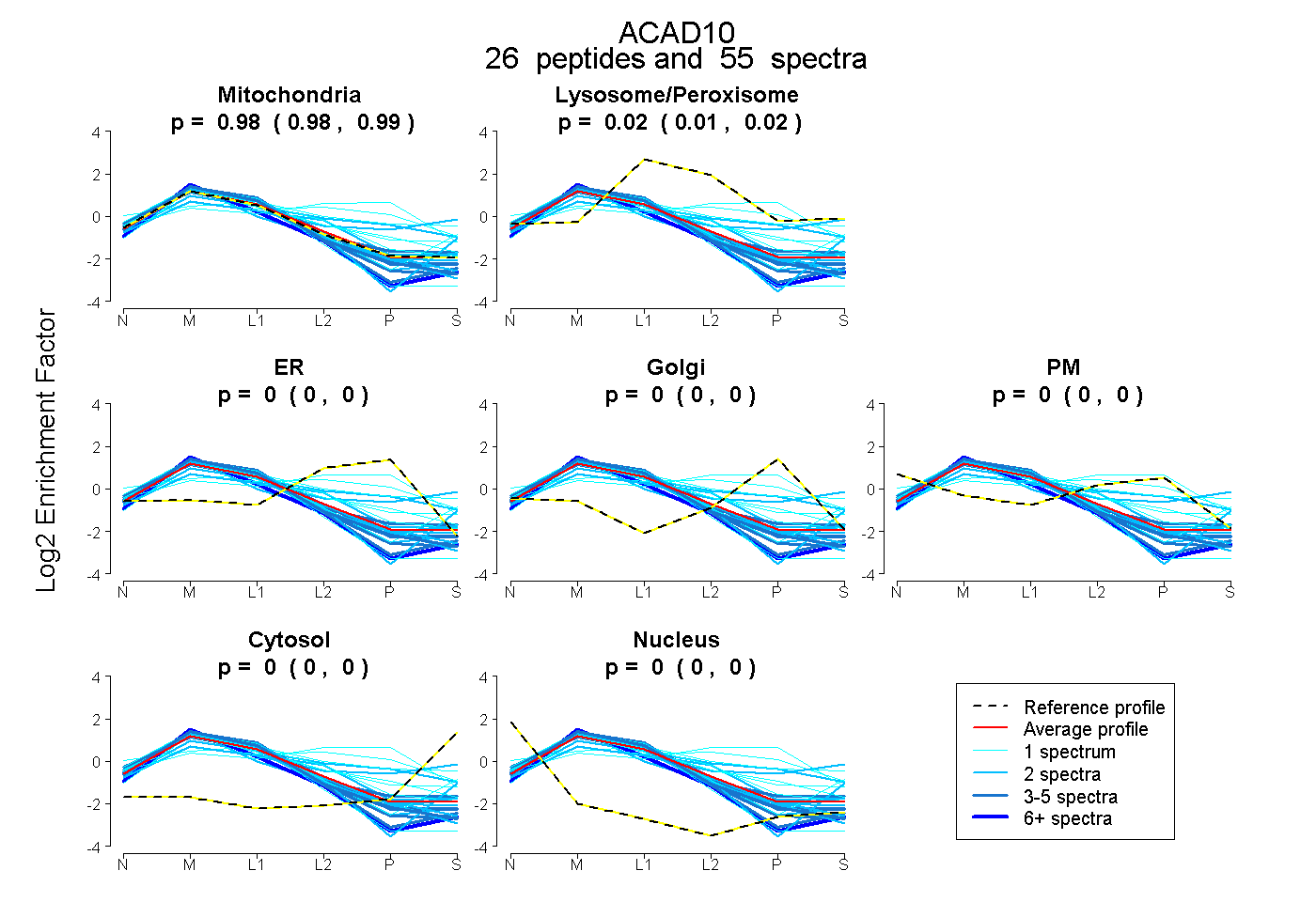
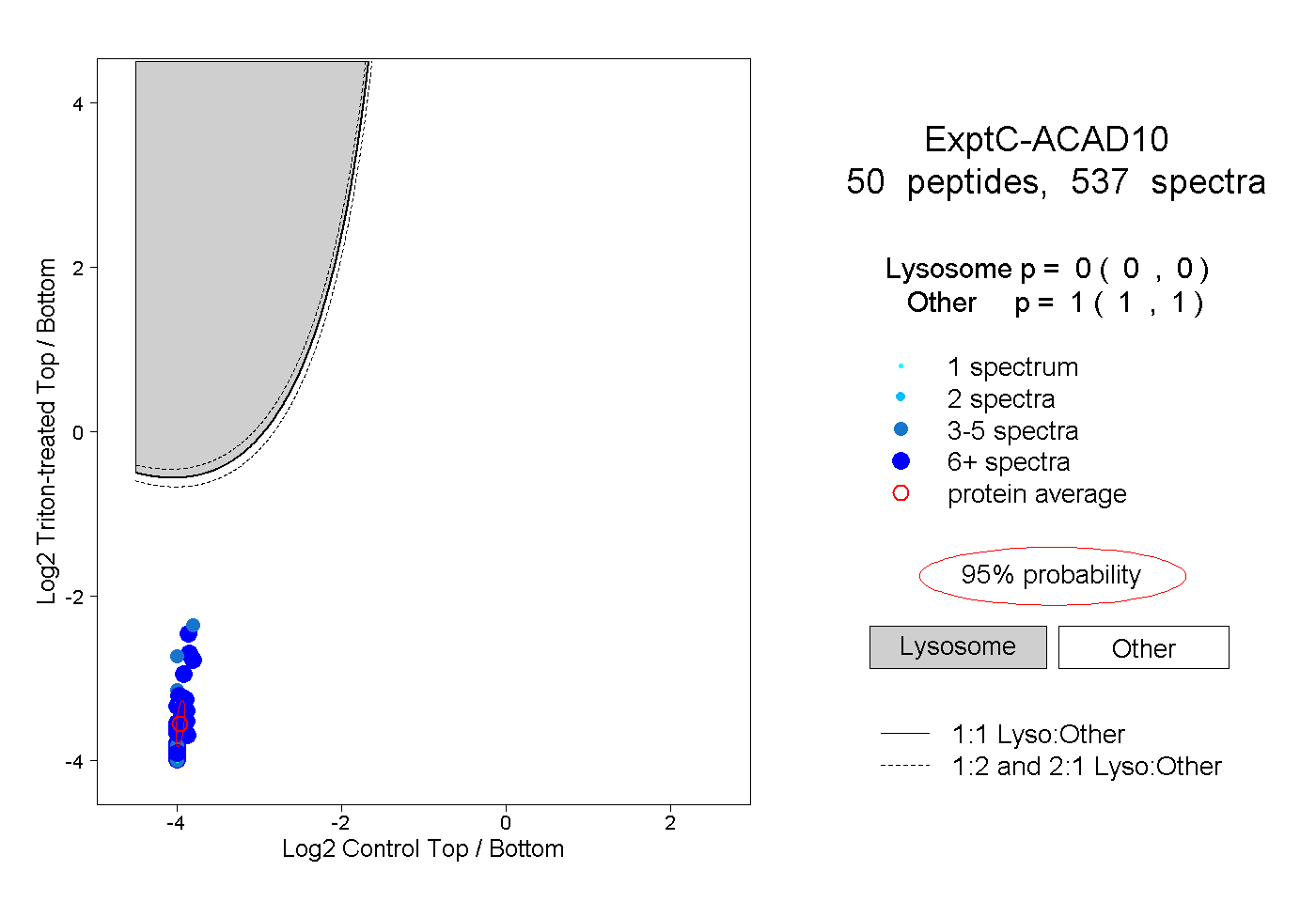
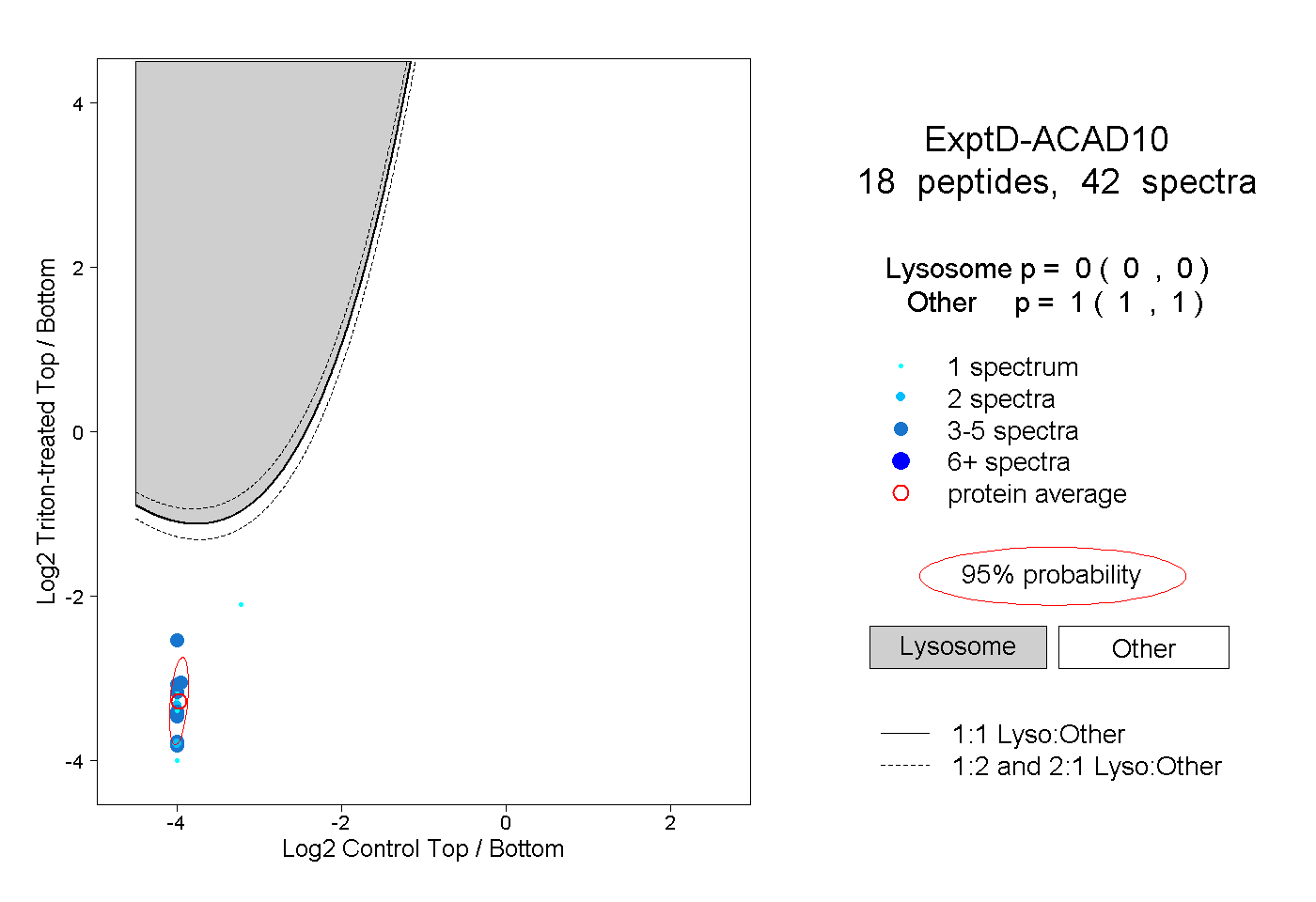
| 13 spectra, LDNLMFRPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AQAEGLWNLFLPLETDPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ELEDLLGFPLHGGVPNTRPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QFDVVVESCVEGVCKPDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VAAILQGVYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, LCVFMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, FLEEFGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, GGLIISPEGLSPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, ALELMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LYDQLLQFMEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, YGTEEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, DPSLPGLEPSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, EAIYTAMNQVLCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TMEIPQDALETYLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, WWISGILDPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, GGDSGPWMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, AAETSSIPAMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, TDPQAPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, QFPVMTQAVSQIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, AAHLMDVAGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SFIPVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, VDIEQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, GFEIAQGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, IFQLCLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, SFLPLDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LIQWLPLHLPQQQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, MVAPSMAYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, FADGPDEVHQLTVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, VDNPETAVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GEMTMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GLLGTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, VAASLGIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, QVQTWTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, LQEPAAPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LLQFDHGQSNPTYYIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, WLAPLLEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, AAALEIAMIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, HQQQSMLLVPMDTPGIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, YTGPMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IHSVDLQATGLDGFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VIRPLSVFGLEDPPGGHGEVQFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ENILLGPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, LCSEIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, LIGYSER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LTESMAELAWDFAIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, QGDYISR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, AMPATTTLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, TTVVHGDFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EEDGSYVINGHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, ELGIPTVEEYFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |