peptides
spectra

0.153 | 0.159
0.018 | 0.029
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.275 | 0.287
0.000 | 0.000
0.535 | 0.541
peptides
spectra
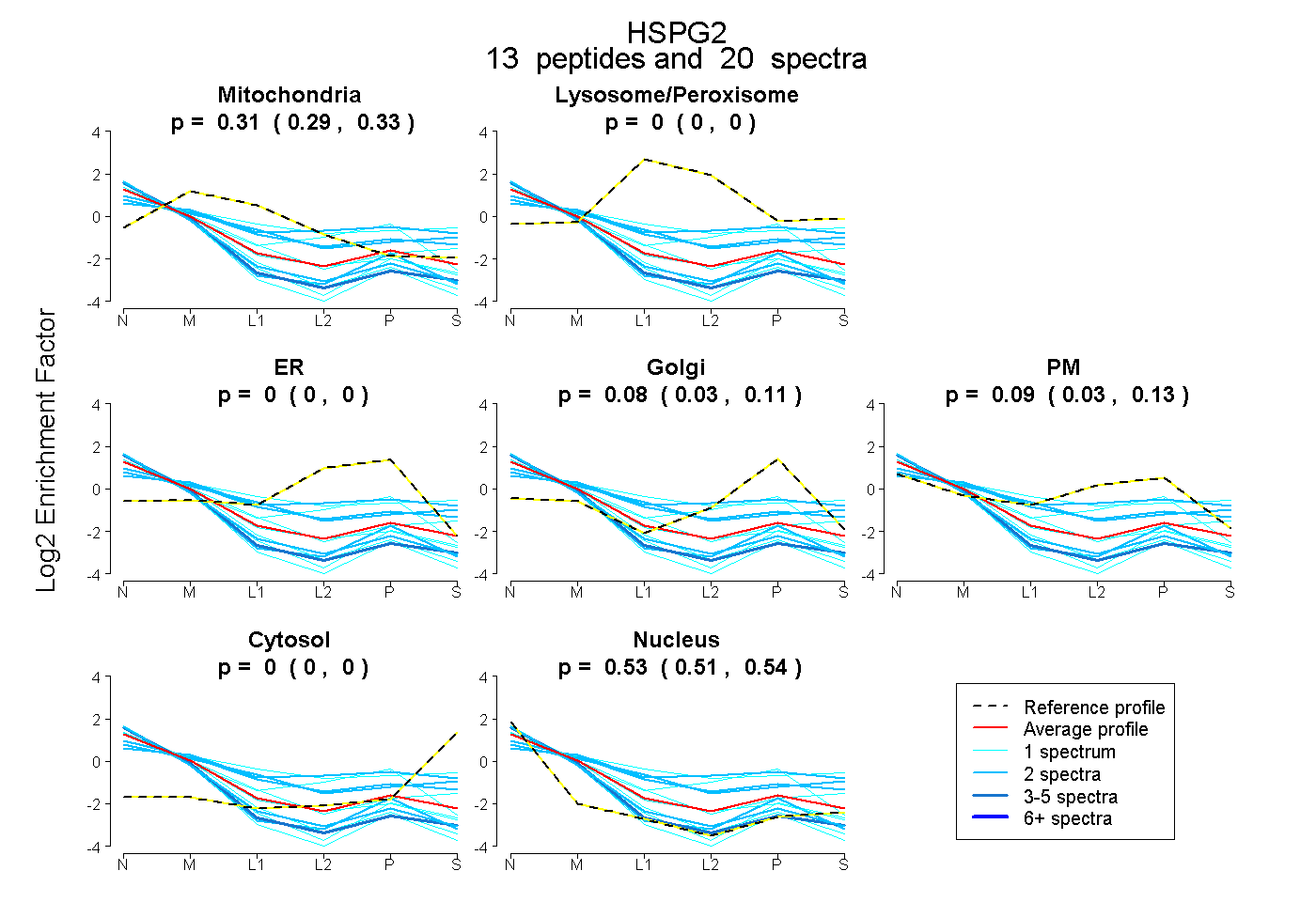
0.291 | 0.331
0.000 | 0.000
0.000 | 0.000
0.030 | 0.112
0.029 | 0.134
0.000 | 0.000
0.506 | 0.541
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
163 spectra |
 |
0.156 0.153 | 0.159 |
0.024 0.018 | 0.029 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.282 0.275 | 0.287 |
0.000 0.000 | 0.000 |
0.538 0.535 | 0.541 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.313 0.291 | 0.331 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.076 0.030 | 0.112 |
0.086 0.029 | 0.134 |
0.000 0.000 | 0.000 |
0.525 0.506 | 0.541 |
| 1 spectrum, ATFSSVPR | 0.064 | 0.000 | 0.000 | 0.000 | 0.664 | 0.000 | 0.272 | |||
| 1 spectrum, FLVHDAFWALPK | 0.248 | 0.130 | 0.000 | 0.000 | 0.376 | 0.167 | 0.079 | |||
| 1 spectrum, GSSLPAR | 0.365 | 0.000 | 0.000 | 0.000 | 0.110 | 0.023 | 0.502 | |||
| 3 spectra, SLEPLALGR | 0.203 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.797 | |||
| 1 spectrum, IPGDQIVSVVFIK | 0.325 | 0.000 | 0.000 | 0.000 | 0.085 | 0.000 | 0.590 | |||
| 1 spectrum, QPDFISFGLVGGRPEFR | 0.108 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.892 | |||
| 2 spectra, GTLIIR | 0.116 | 0.000 | 0.000 | 0.140 | 0.000 | 0.000 | 0.744 | |||
| 2 spectra, IAHVELADAGQYR | 0.254 | 0.006 | 0.000 | 0.000 | 0.550 | 0.167 | 0.023 | |||
| 2 spectra, VQVSPER | 0.247 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.751 | |||
| 1 spectrum, IEGNTLVIPR | 0.262 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.738 | |||
| 2 spectra, DGSLQVDGGRPVLR | 0.340 | 0.000 | 0.000 | 0.000 | 0.361 | 0.052 | 0.247 | |||
| 2 spectra, DITLECVSSGEPR | 0.342 | 0.071 | 0.000 | 0.000 | 0.232 | 0.112 | 0.243 | |||
| 1 spectrum, EDGRPLPSGAQQR | 0.175 | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | 0.788 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
88 spectra |
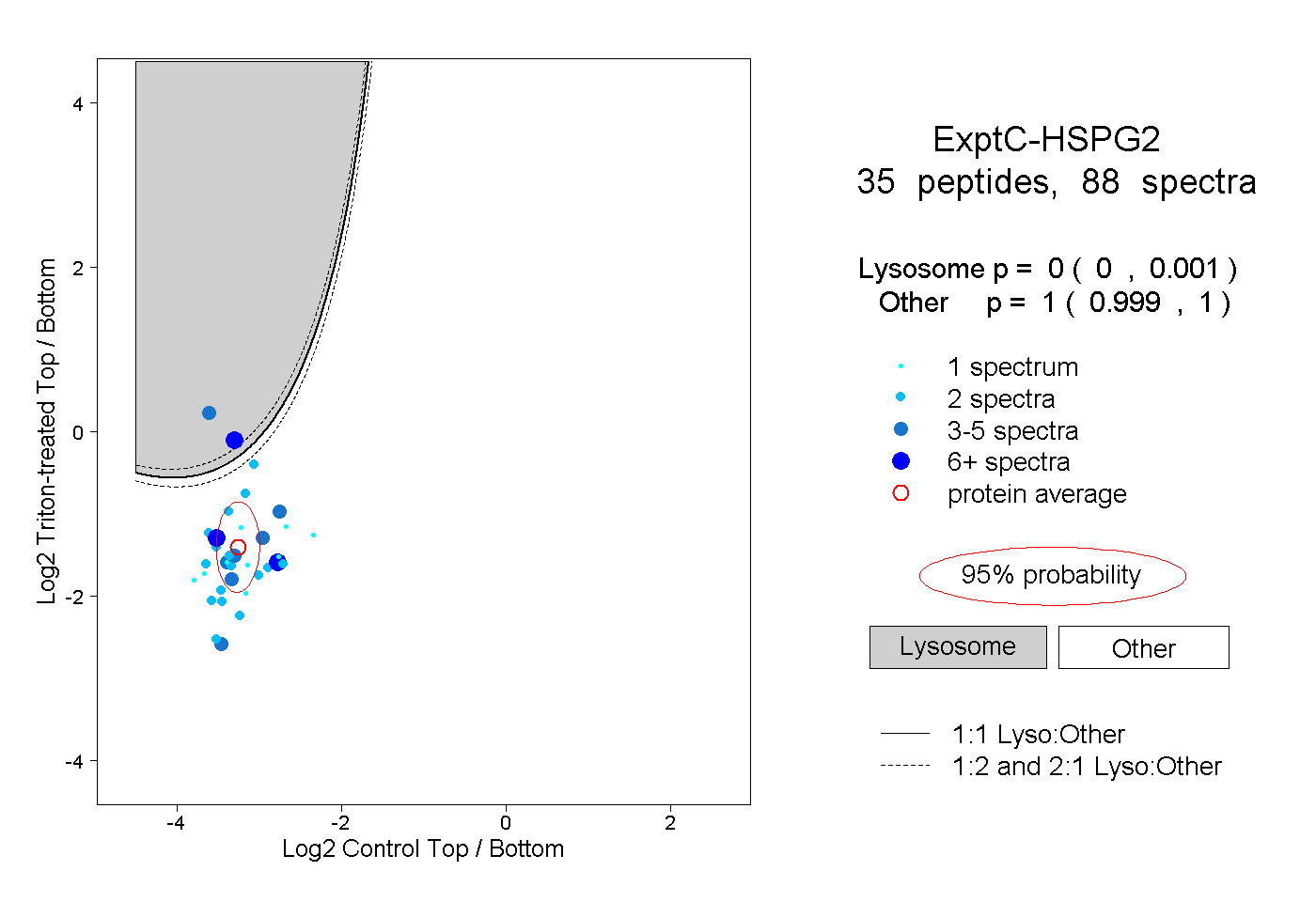 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
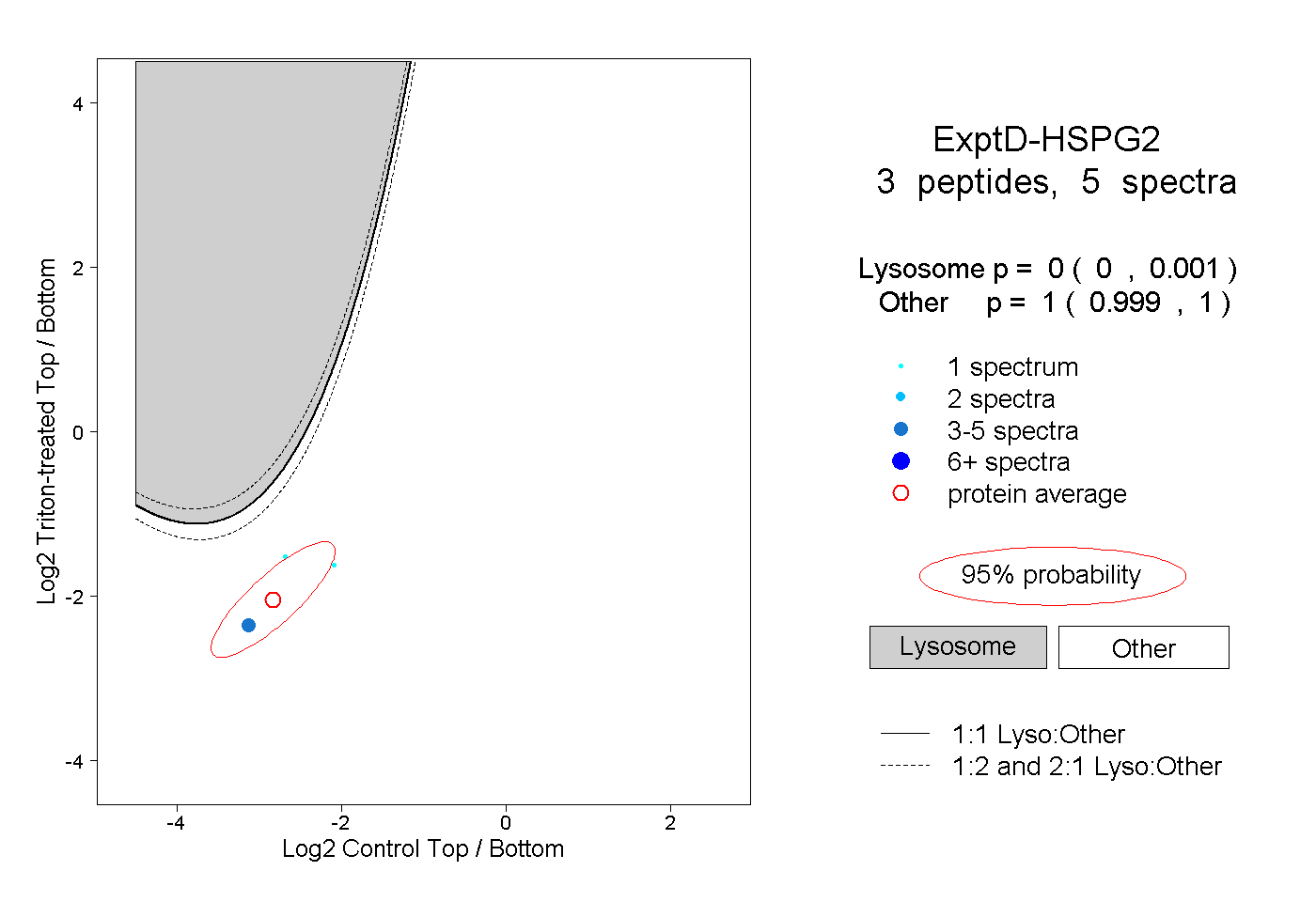 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |