peptides
spectra
0.000 | 0.009
0.000 | 0.040
0.012 | 0.052
0.000 | 0.010
0.010 | 0.039
0.000 | 0.000
0.903 | 0.922
0.000 | 0.000
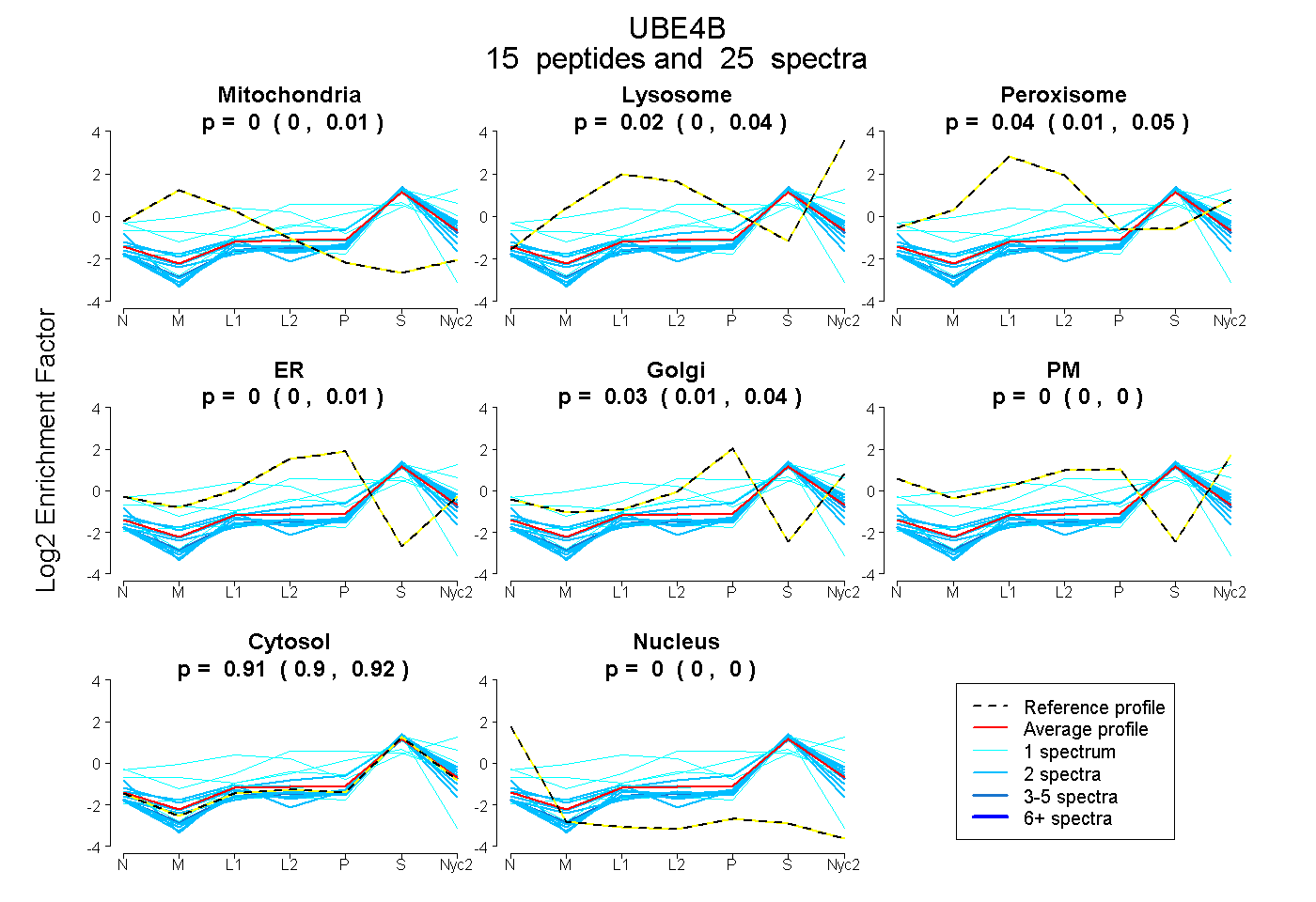
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.000 0.000 | 0.009 |
0.019 0.000 | 0.040 |
0.037 0.012 | 0.052 |
0.000 0.000 | 0.010 |
0.031 0.010 | 0.039 |
0.000 0.000 | 0.000 |
0.913 0.903 | 0.922 |
0.000 0.000 | 0.000 |
| 2 spectra, NLPYGFIQELVR | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.000 | ||
| 1 spectrum, YHISTIFK | 0.000 | 0.133 | 0.000 | 0.000 | 0.000 | 0.000 | 0.867 | 0.000 | ||
| 2 spectra, AIADDQR | 0.000 | 0.101 | 0.000 | 0.000 | 0.086 | 0.000 | 0.814 | 0.000 | ||
| 3 spectra, ELFEEVISK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, AQMQADDR | 0.060 | 0.000 | 0.097 | 0.109 | 0.155 | 0.000 | 0.579 | 0.000 | ||
| 1 spectrum, ILHSILLNGETR | 0.000 | 0.000 | 0.149 | 0.367 | 0.000 | 0.000 | 0.484 | 0.000 | ||
| 1 spectrum, EQIQAWMR | 0.000 | 0.161 | 0.000 | 0.024 | 0.008 | 0.000 | 0.807 | 0.000 | ||
| 1 spectrum, ETDMLNYLIECFDR | 0.075 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.826 | 0.100 | ||
| 2 spectra, LPSGTIMDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ACADAGLLDESFLR | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.000 | 0.926 | 0.044 | ||
| 2 spectra, ECSLDSDYFK | 0.110 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.866 | 0.024 | ||
| 1 spectrum, SQCISHTALVLQGSLTQPR | 0.051 | 0.304 | 0.205 | 0.000 | 0.000 | 0.056 | 0.384 | 0.000 | ||
| 2 spectra, ITLPNDETR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, TTHQDEEVFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, YPLMALGELCETK | 0.032 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.958 | 0.010 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
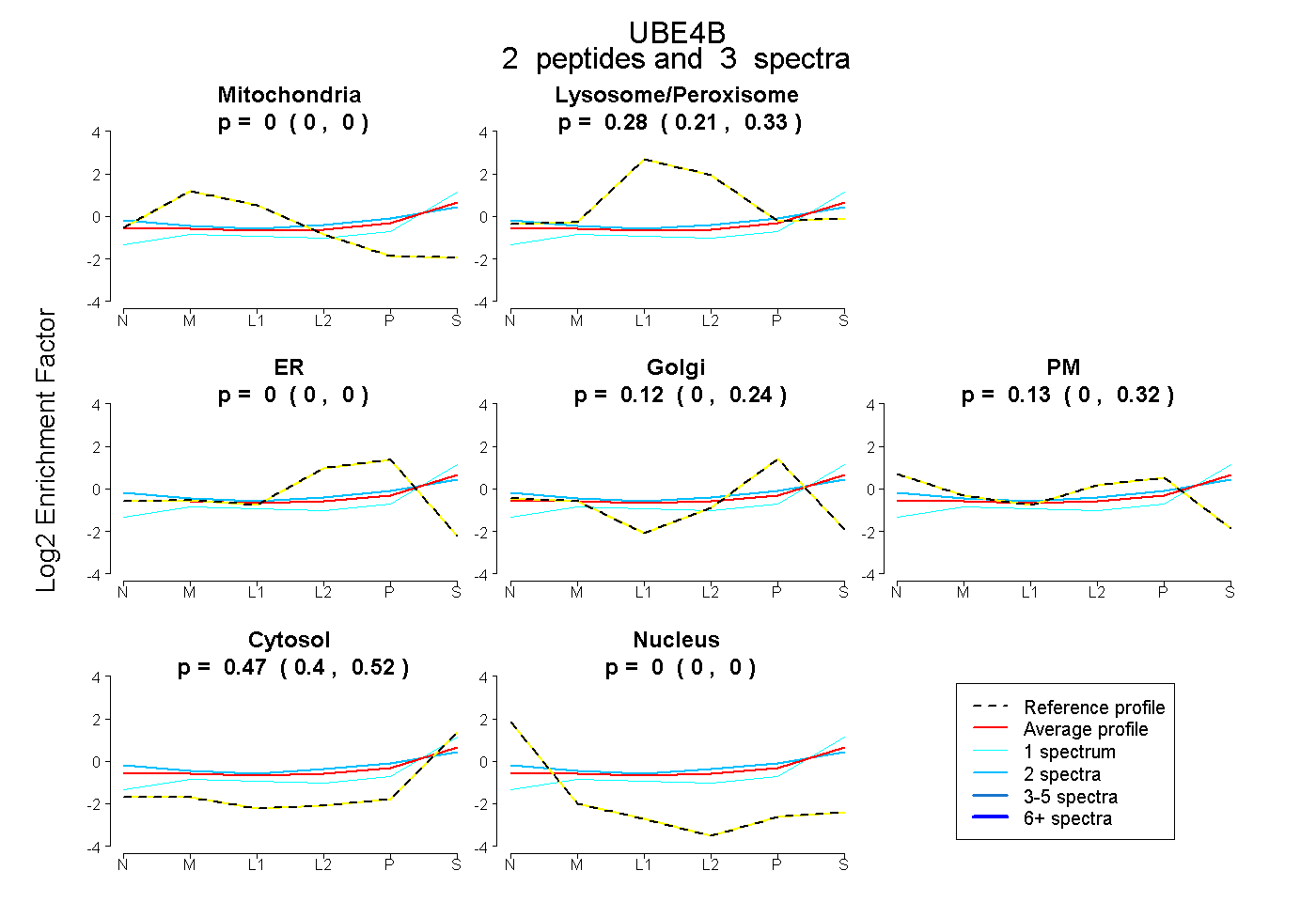 |
0.000 0.000 | 0.000 |
0.284 0.206 | 0.333 |
0.000 0.000 | 0.000 |
0.122 0.000 | 0.243 |
0.126 0.000 | 0.324 |
0.468 0.403 | 0.516 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
13 spectra |
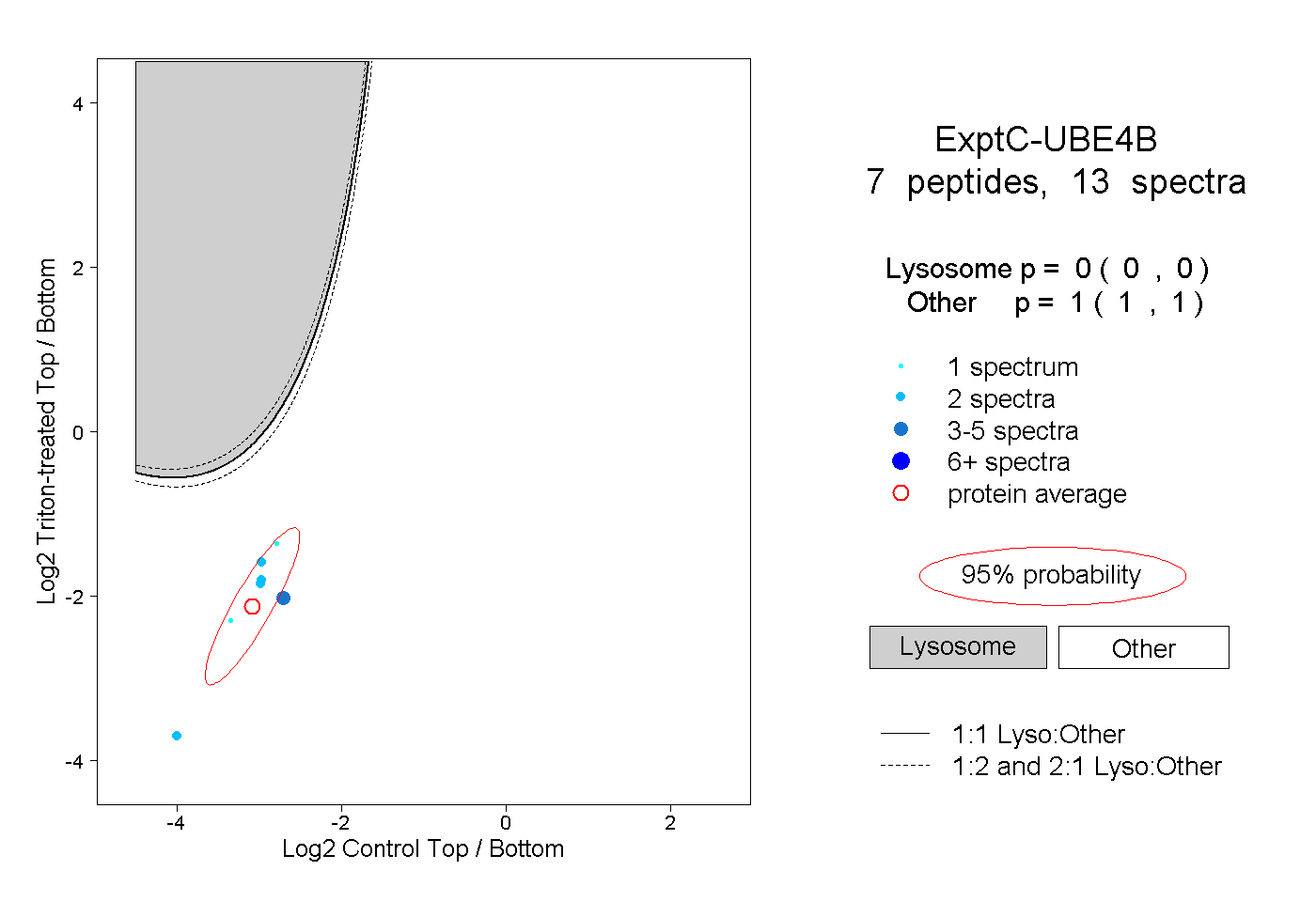 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |