peptides
spectra
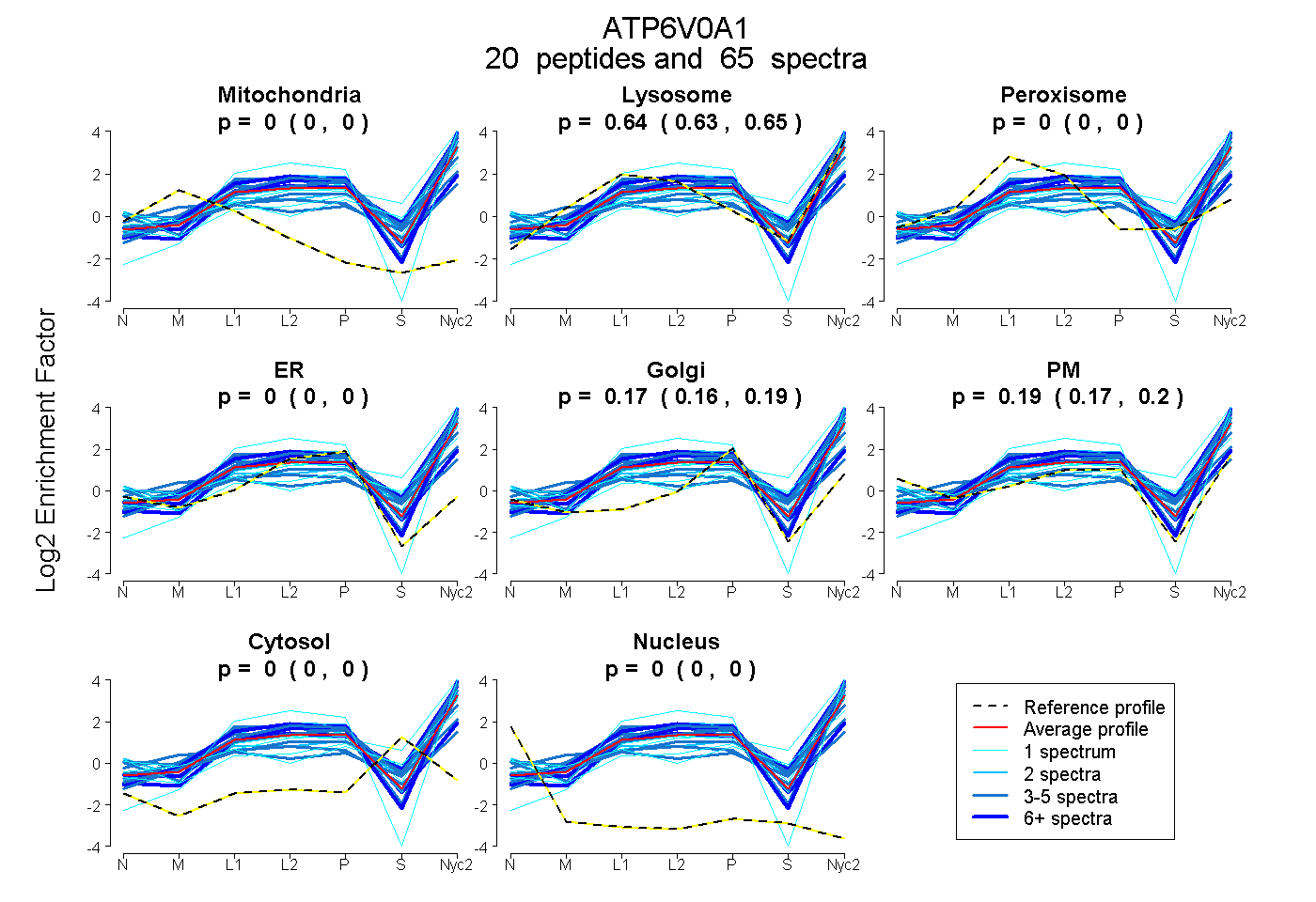
0.000 | 0.000
0.629 | 0.646
0.000 | 0.000
0.000 | 0.000
0.160 | 0.186
0.168 | 0.203
0.000 | 0.000
0.000 | 0.000
peptides
spectra
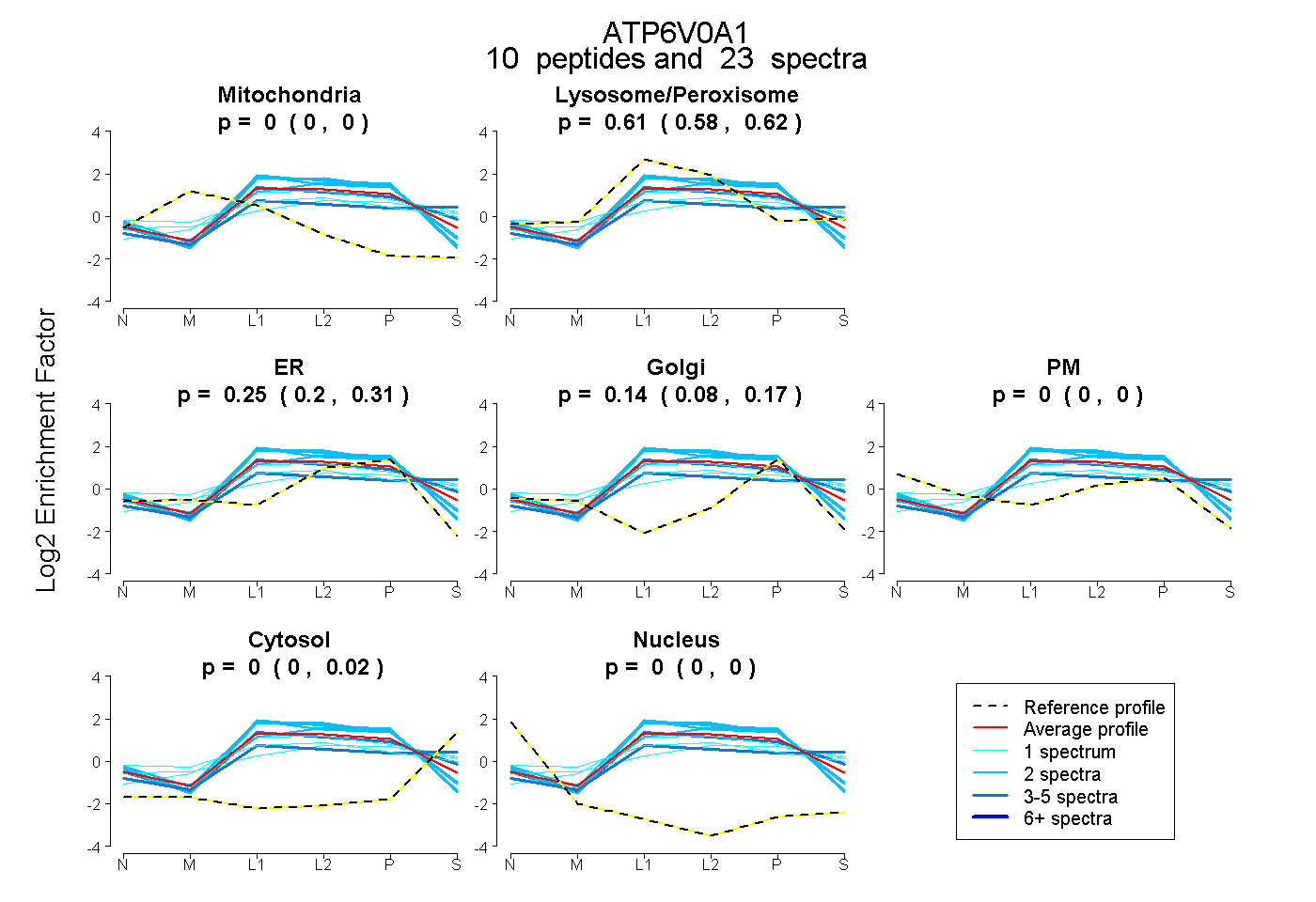
0.000 | 0.000
0.579 | 0.622
0.202 | 0.310
0.082 | 0.169
0.000 | 0.000
0.000 | 0.019
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
65 spectra |
 |
0.000 0.000 | 0.000 |
0.638 0.629 | 0.646 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.175 0.160 | 0.186 |
0.187 0.168 | 0.203 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.000 0.000 | 0.000 |
0.605 0.579 | 0.622 |
0.253 0.202 | 0.310 |
0.138 0.082 | 0.169 |
0.000 0.000 | 0.000 |
0.003 0.000 | 0.019 |
0.000 0.000 | 0.000 |
| 2 spectra, HLGTLNFGGIR | 0.000 | 0.467 | 0.533 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GNVFLR | 0.000 | 0.603 | 0.397 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LGFVAGVINR | 0.000 | 0.552 | 0.448 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LTFLNSFK | 0.000 | 0.544 | 0.456 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ICEGFR | 0.000 | 0.598 | 0.402 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VLQAAAK | 0.000 | 0.618 | 0.000 | 0.281 | 0.018 | 0.083 | 0.000 | |||
| 1 spectrum, FTHGFQNIVDAYGIGTYR | 0.000 | 0.606 | 0.244 | 0.005 | 0.000 | 0.145 | 0.000 | |||
| 5 spectra, FLPFSFEHIR | 0.000 | 0.643 | 0.151 | 0.141 | 0.000 | 0.065 | 0.000 | |||
| 5 spectra, NFLELTELK | 0.000 | 0.557 | 0.079 | 0.101 | 0.000 | 0.263 | 0.000 | |||
| 1 spectrum, IDDLQMVLNQTEDHR | 0.000 | 0.535 | 0.000 | 0.335 | 0.000 | 0.129 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
141 spectra |
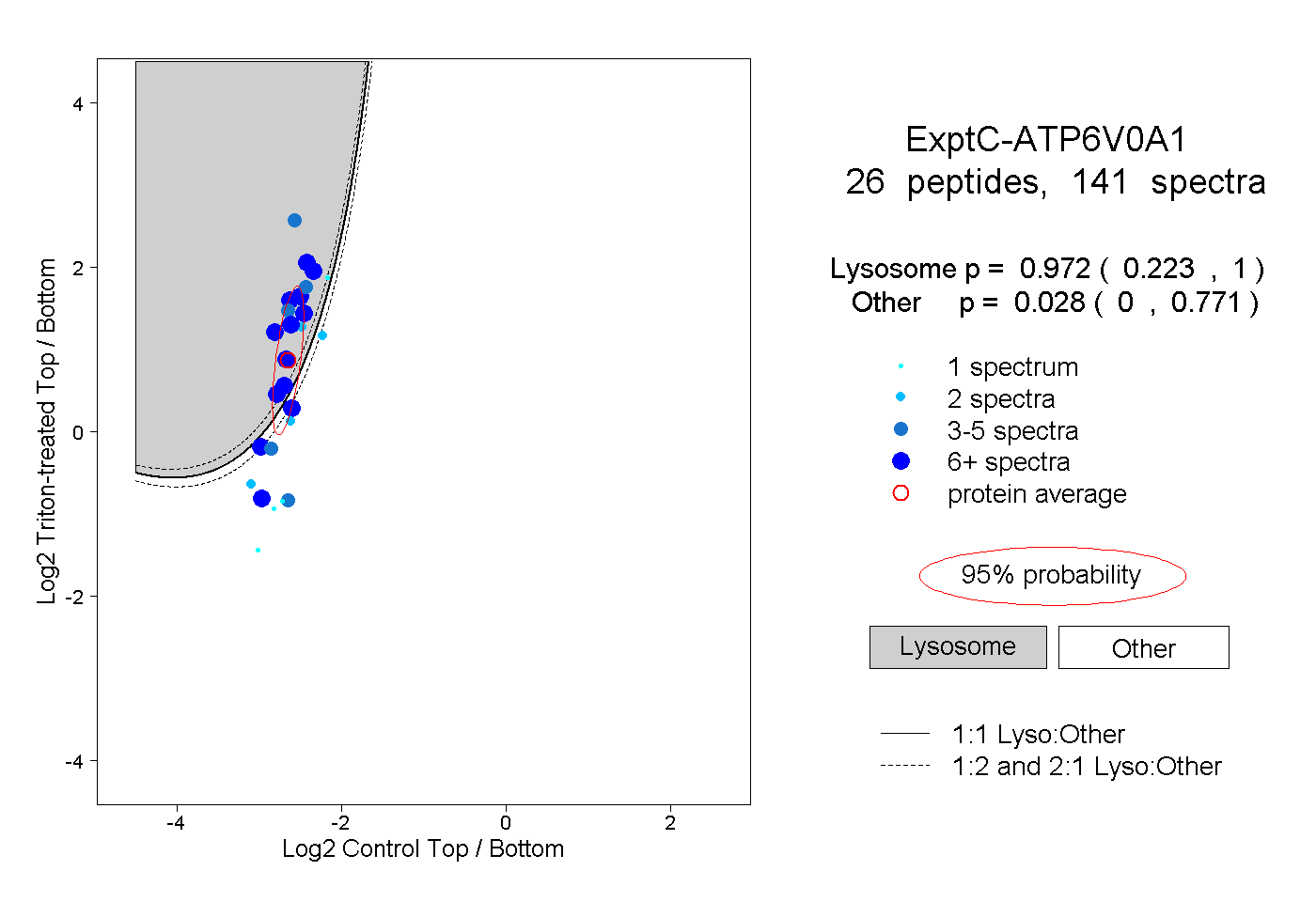 |
0.972 0.223 | 1.000 |
0.028 0.000 | 0.771 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
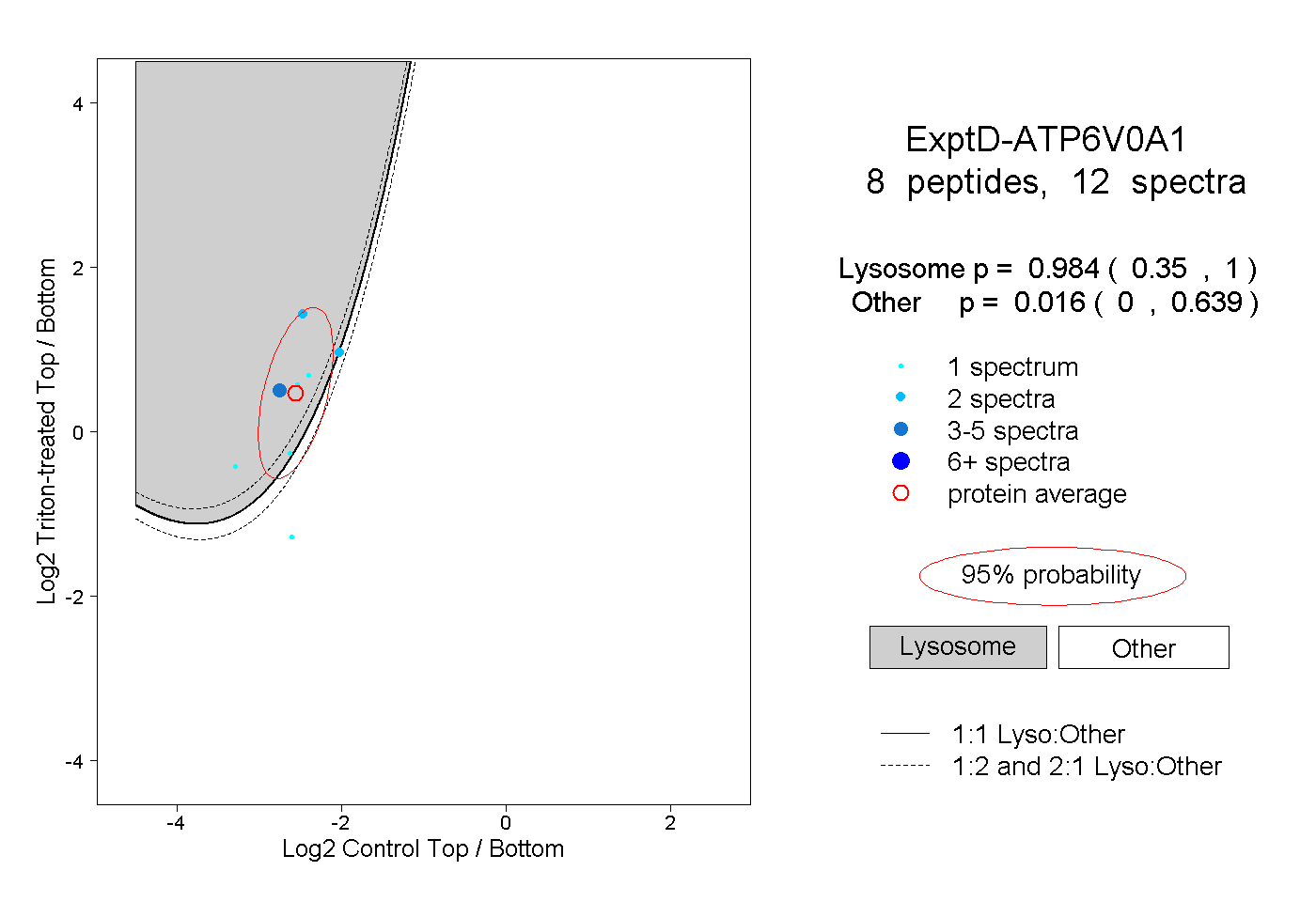 |
0.984 0.350 | 1.000 |
0.016 0.000 | 0.639 |