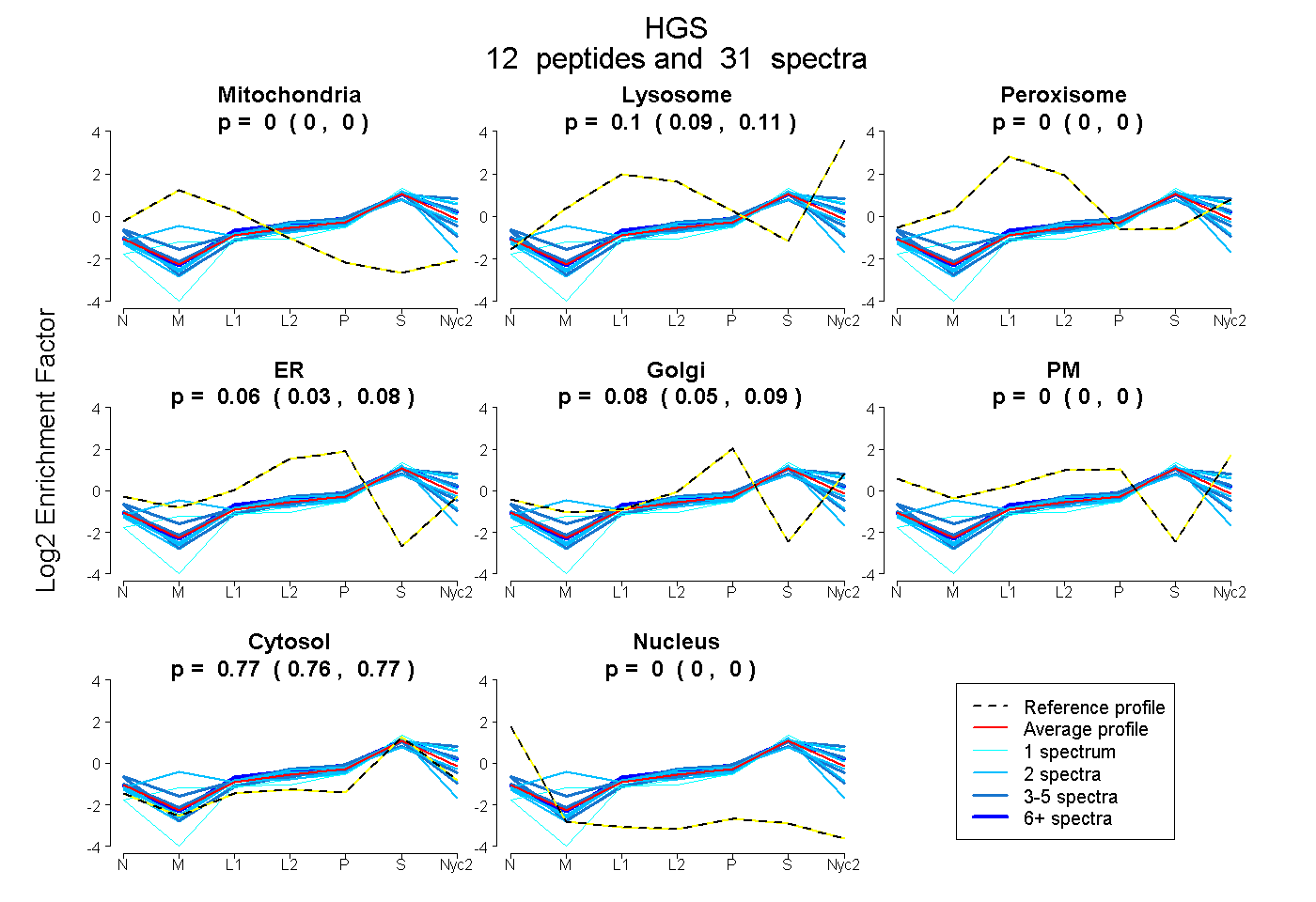
HGS
[ENSRNOP00000051849]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 12
12
peptides |
31
spectra |
 |
0.000
0.000 | 0.000 |
0.098
0.086 | 0.108 |
|
0.000
0.000 | 0.000 |
0.061
0.035 | 0.084 |
0.075
0.053 | 0.094 |
0.000
0.000 | 0.000 |
0.765
0.759 | 0.771 |
0.000
0.000 | 0.000 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
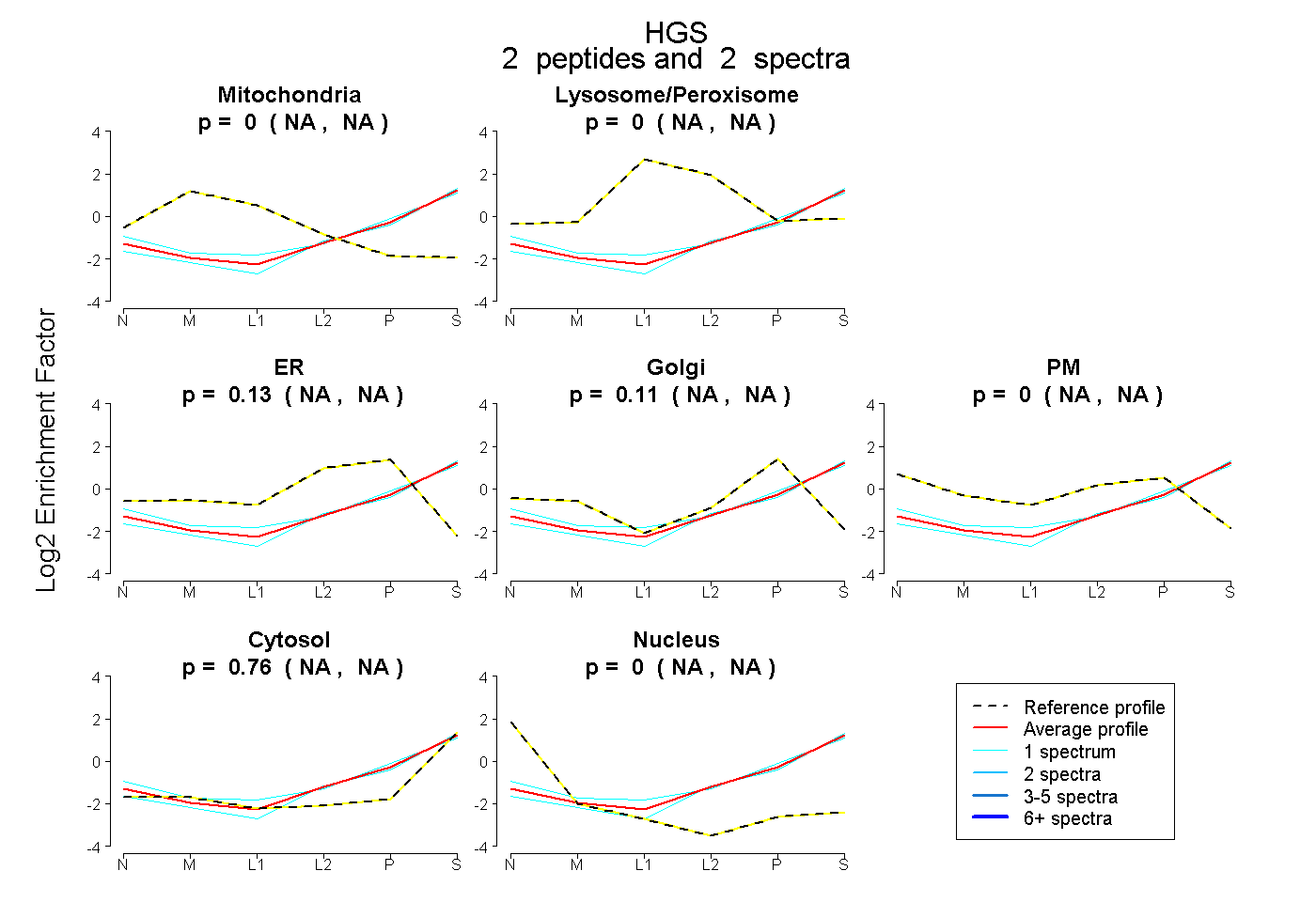
| Expt B |
 2
2
peptides |
2
spectra |
 |
0.000
NA | NA |
|
0.000
NA | NA |
|
0.132
NA | NA |
0.111
NA | NA |
0.000
NA | NA |
0.756
NA | NA |
0.000
NA | NA |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
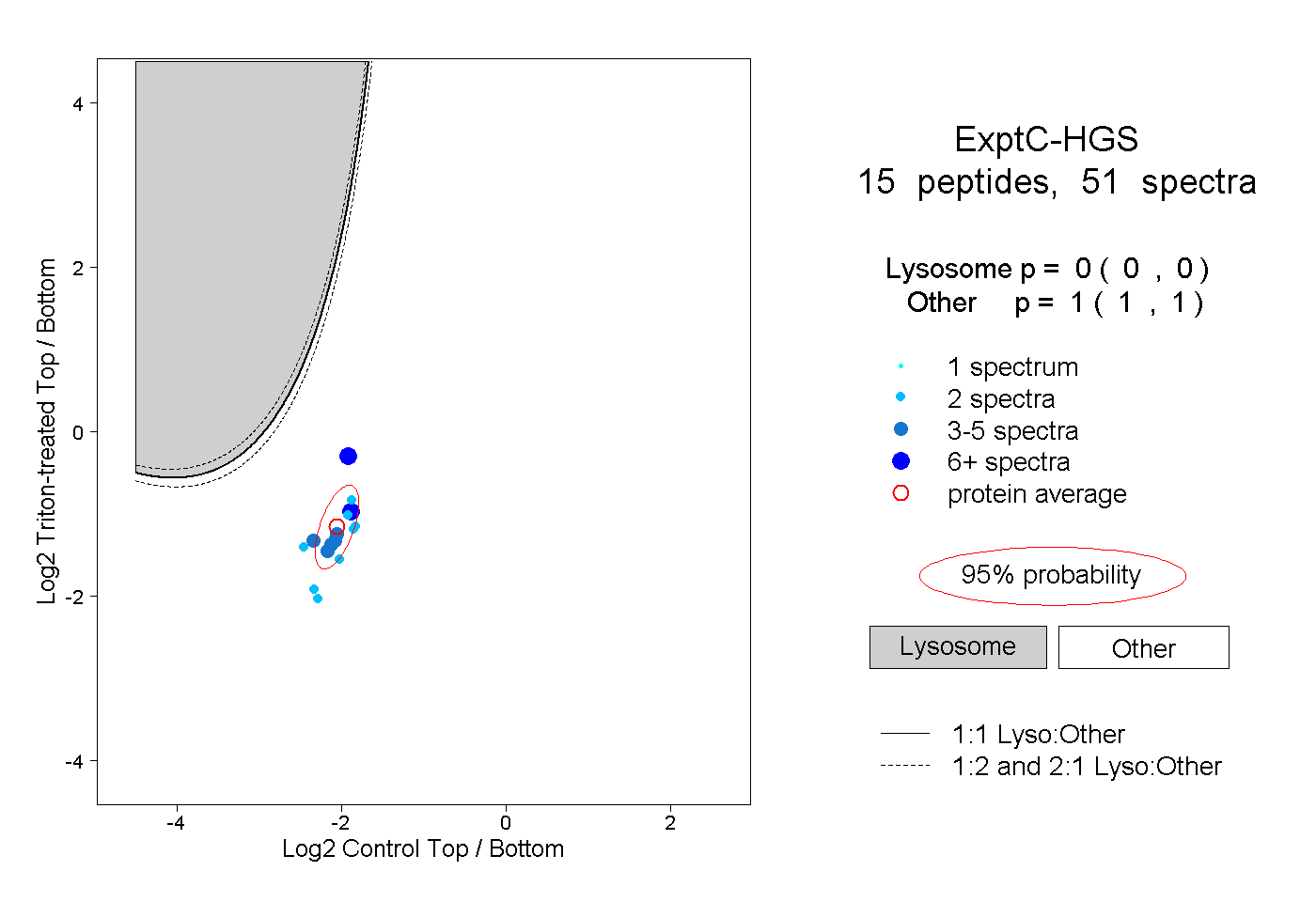
| Expt C |
 15
15
peptides |
51
spectra |
 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 8 spectra, QGDTQAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VQFGVVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LYYEGLQDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GALSALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, ESDAMFAAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YSTIPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, APDWVDAEECHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ACGQIFCGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VEGHVFPEFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LQEQEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QVEVNVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QEYLEVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YAVNSIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QIQLAQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VVQDTYQIMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
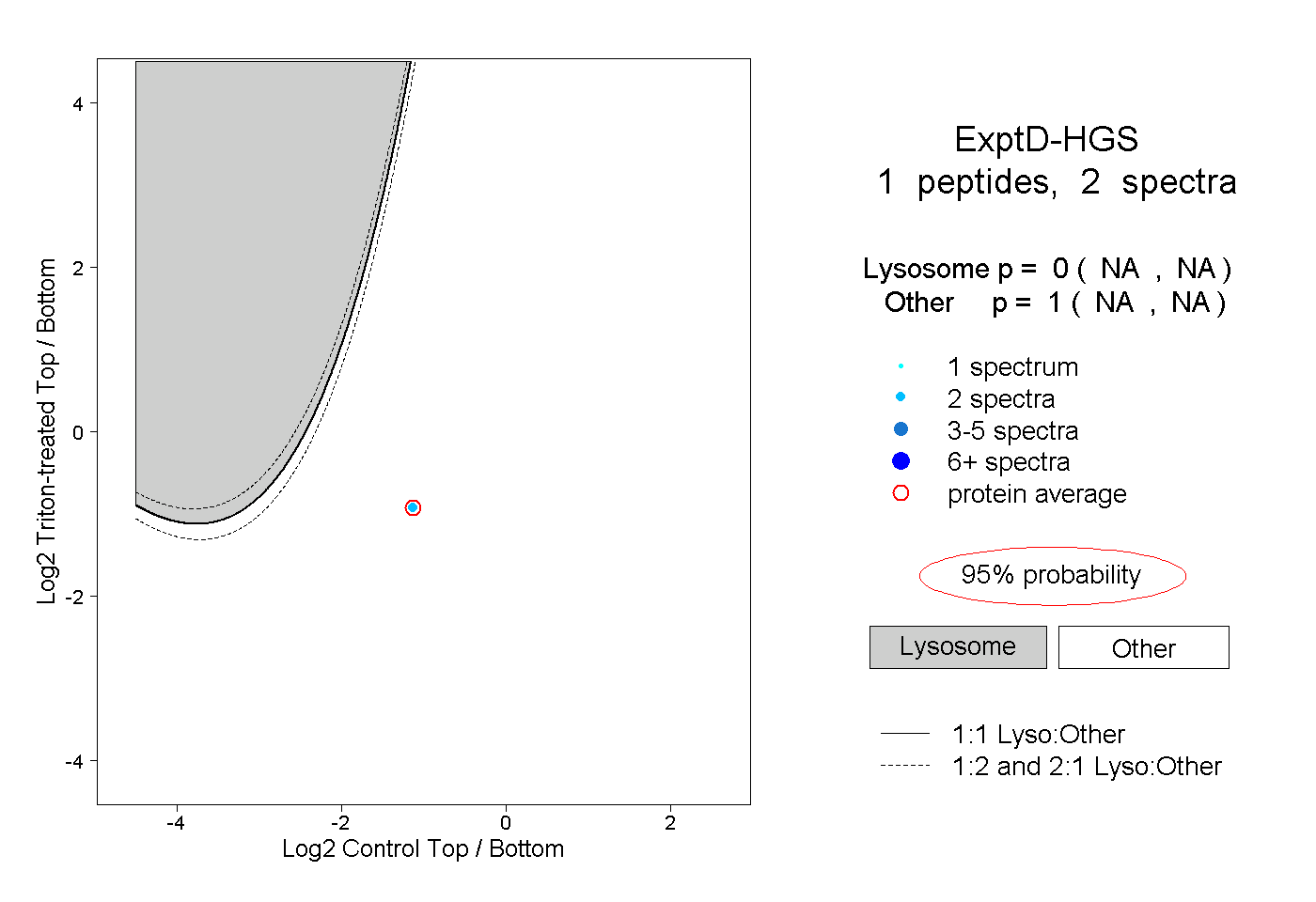
| Expt D |
 1
1
peptide |
2
spectra |
 |
|
0.000
NA | NA |
|
|
|
|
|
|
|
1.000
NA | NA |



