peptides
spectra
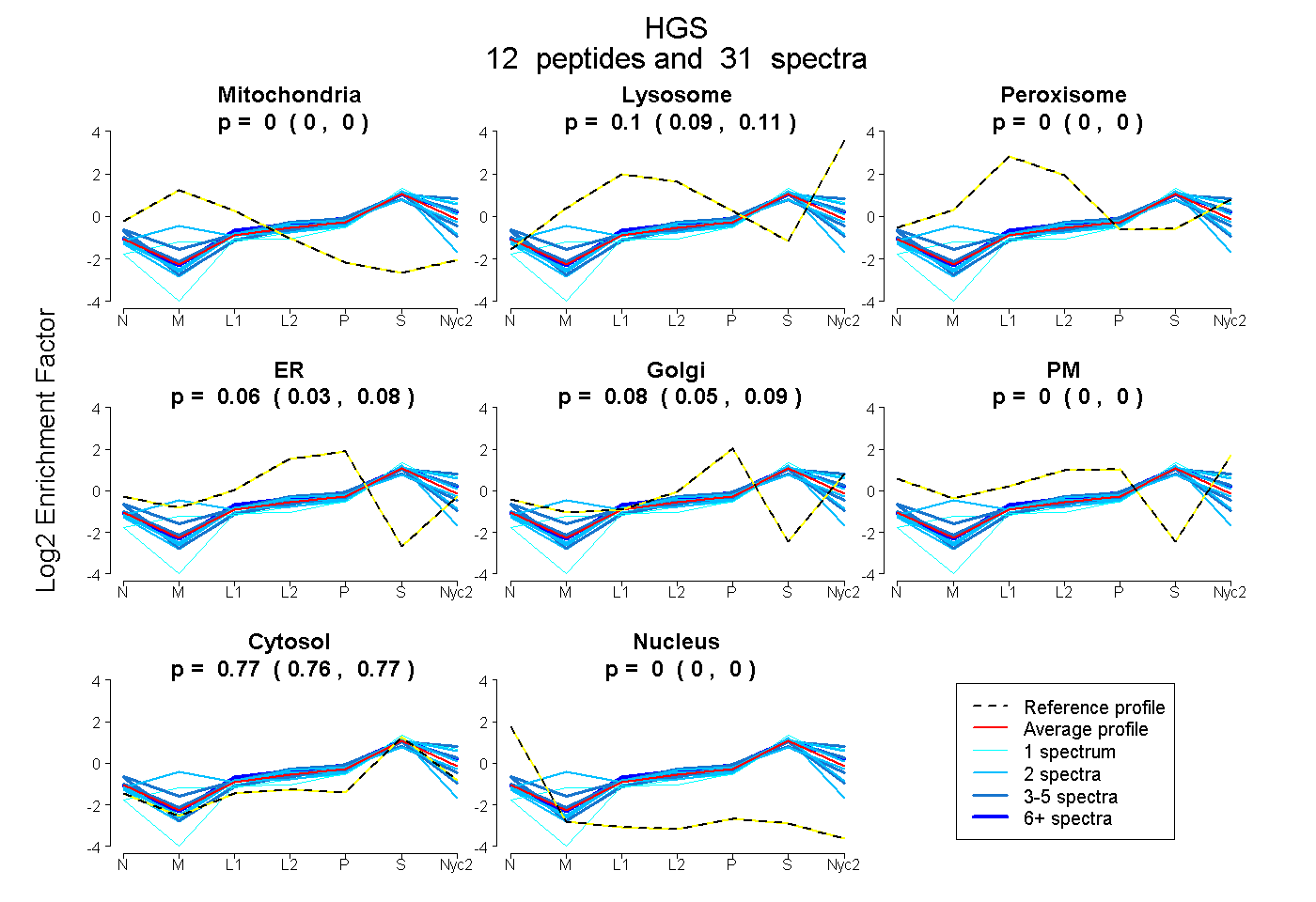
0.000 | 0.000
0.086 | 0.108
0.000 | 0.000
0.035 | 0.084
0.053 | 0.094
0.000 | 0.000
0.759 | 0.771
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
31 spectra |
 |
0.000 0.000 | 0.000 |
0.098 0.086 | 0.108 |
0.000 0.000 | 0.000 |
0.061 0.035 | 0.084 |
0.075 0.053 | 0.094 |
0.000 0.000 | 0.000 |
0.765 0.759 | 0.771 |
0.000 0.000 | 0.000 |
| 1 spectrum, LYYEGLQDK | 0.000 | 0.254 | 0.000 | 0.000 | 0.008 | 0.000 | 0.739 | 0.000 | ||
| 1 spectrum, GALSALR | 0.000 | 0.033 | 0.000 | 0.000 | 0.034 | 0.000 | 0.933 | 0.000 | ||
| 6 spectra, ESDAMFAAER | 0.000 | 0.165 | 0.000 | 0.036 | 0.082 | 0.000 | 0.718 | 0.000 | ||
| 3 spectra, APDWVDAEECHR | 0.000 | 0.000 | 0.000 | 0.175 | 0.000 | 0.000 | 0.825 | 0.000 | ||
| 2 spectra, ACGQIFCGK | 0.000 | 0.000 | 0.000 | 0.120 | 0.000 | 0.000 | 0.880 | 0.000 | ||
| 2 spectra, VCEPCYEQLNK | 0.000 | 0.000 | 0.028 | 0.123 | 0.000 | 0.000 | 0.849 | 0.000 | ||
| 2 spectra, VEGHVFPEFK | 0.000 | 0.150 | 0.000 | 0.045 | 0.008 | 0.000 | 0.797 | 0.000 | ||
| 2 spectra, QLALQR | 0.000 | 0.165 | 0.000 | 0.000 | 0.089 | 0.000 | 0.746 | 0.000 | ||
| 2 spectra, QTMEELK | 0.065 | 0.096 | 0.110 | 0.000 | 0.148 | 0.000 | 0.581 | 0.000 | ||
| 3 spectra, NCGQTVHDEVANK | 0.000 | 0.000 | 0.084 | 0.163 | 0.017 | 0.065 | 0.672 | 0.000 | ||
| 3 spectra, QIQLAQK | 0.000 | 0.136 | 0.000 | 0.000 | 0.149 | 0.000 | 0.715 | 0.000 | ||
| 4 spectra, ALQNAVSTFVNR | 0.000 | 0.146 | 0.000 | 0.000 | 0.000 | 0.135 | 0.719 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
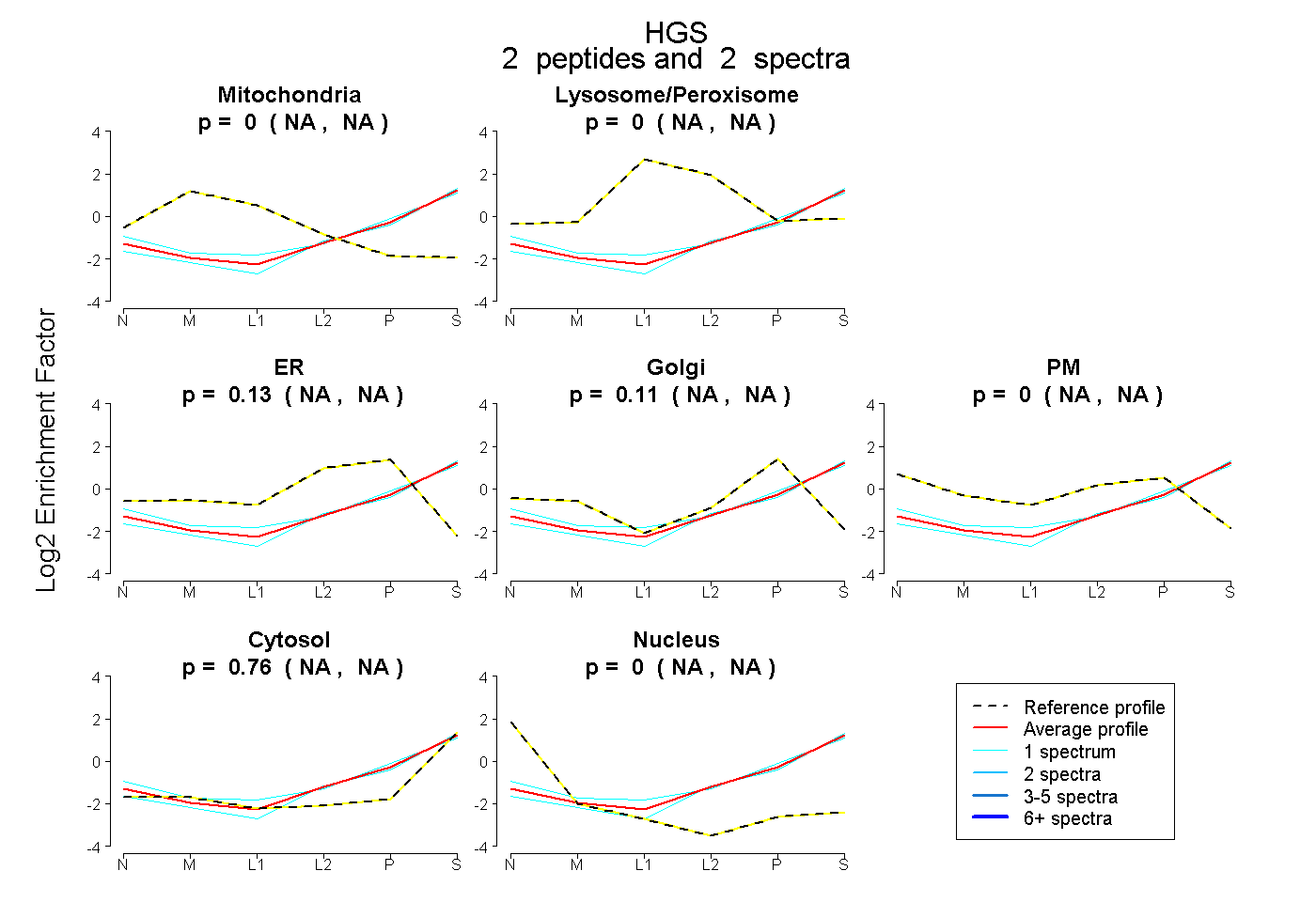 |
0.000 NA | NA |
0.000 NA | NA |
0.132 NA | NA |
0.111 NA | NA |
0.000 NA | NA |
0.756 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
51 spectra |
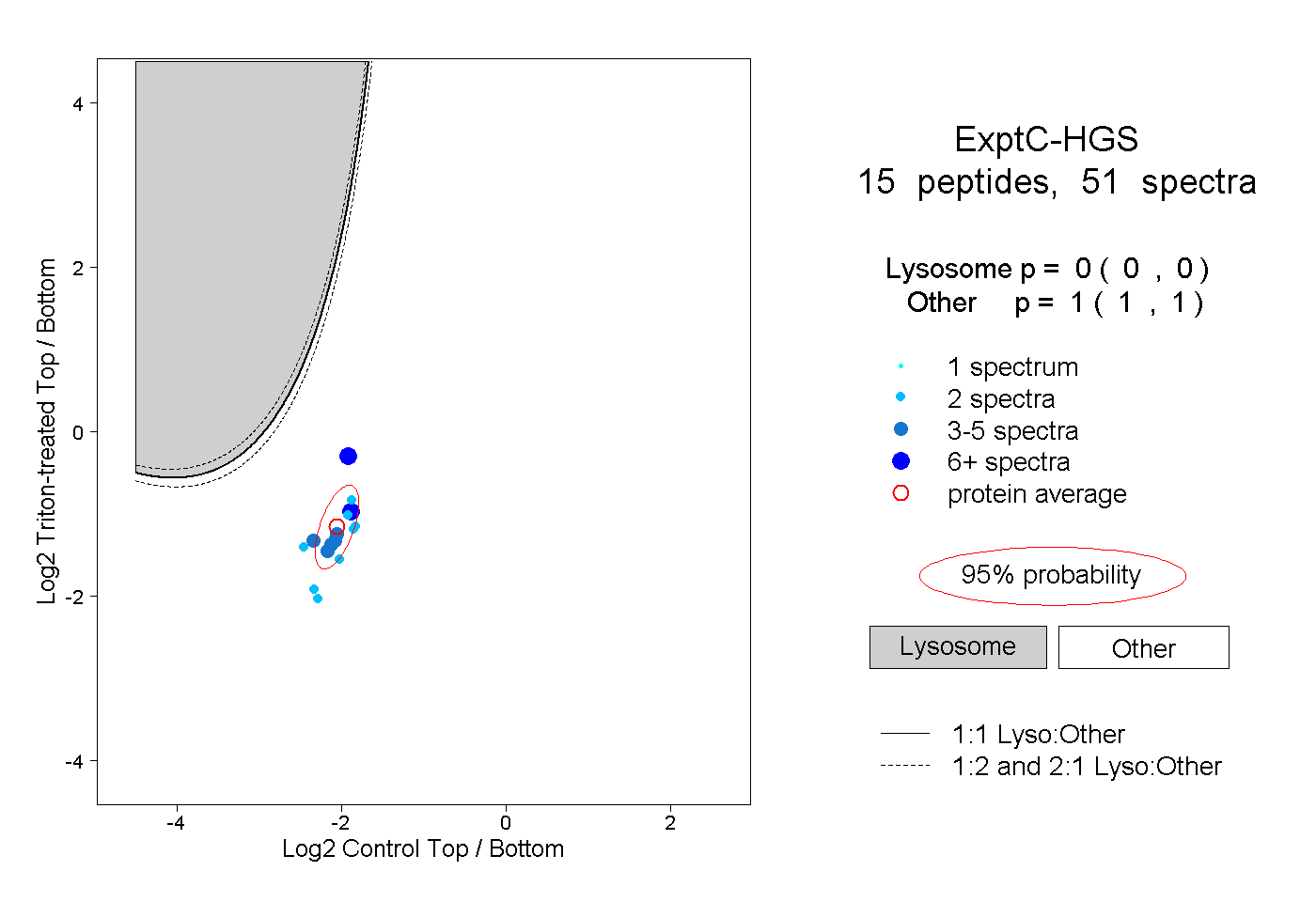 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
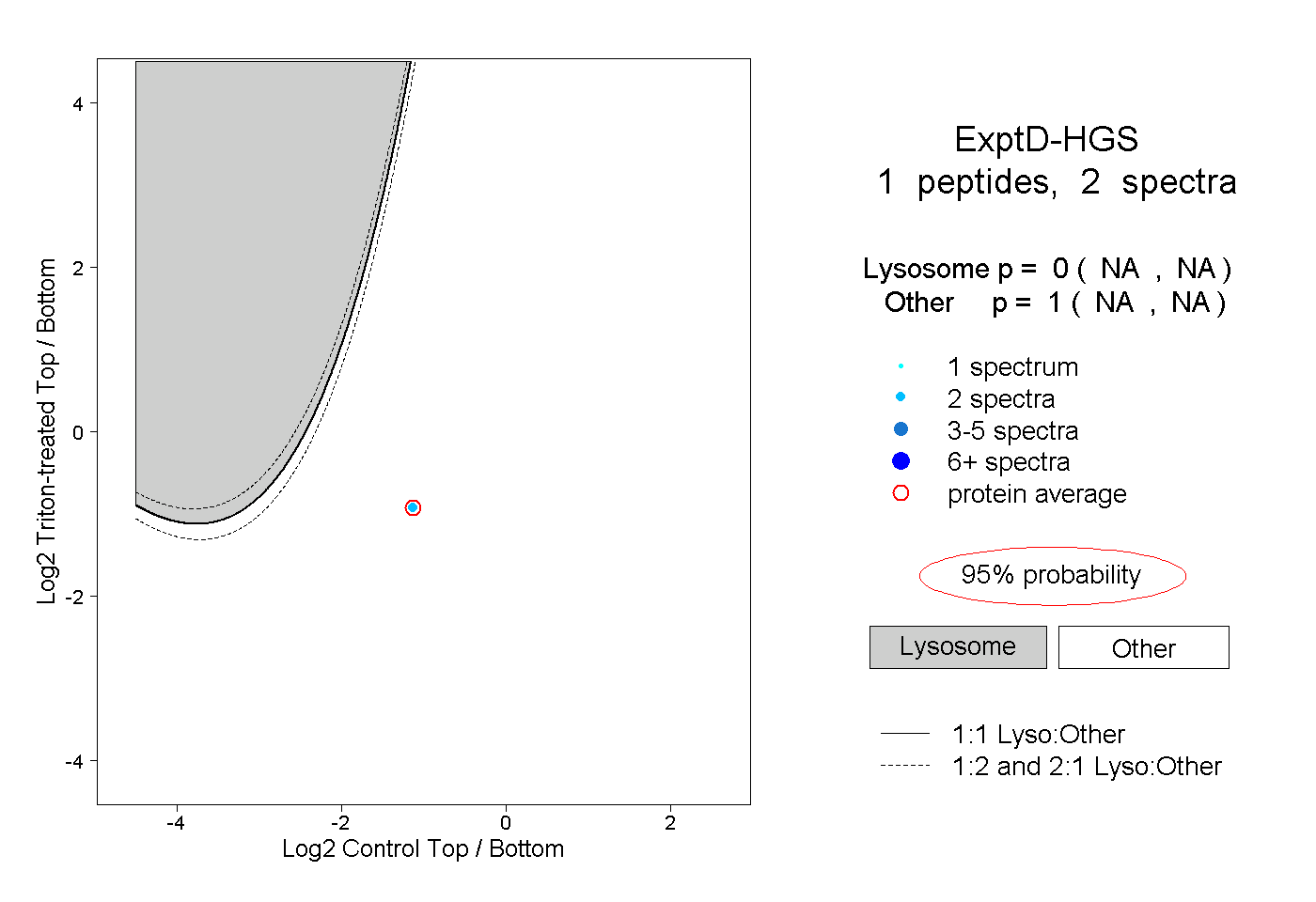 |
0.000 NA | NA |
1.000 NA | NA |