peptides
spectra
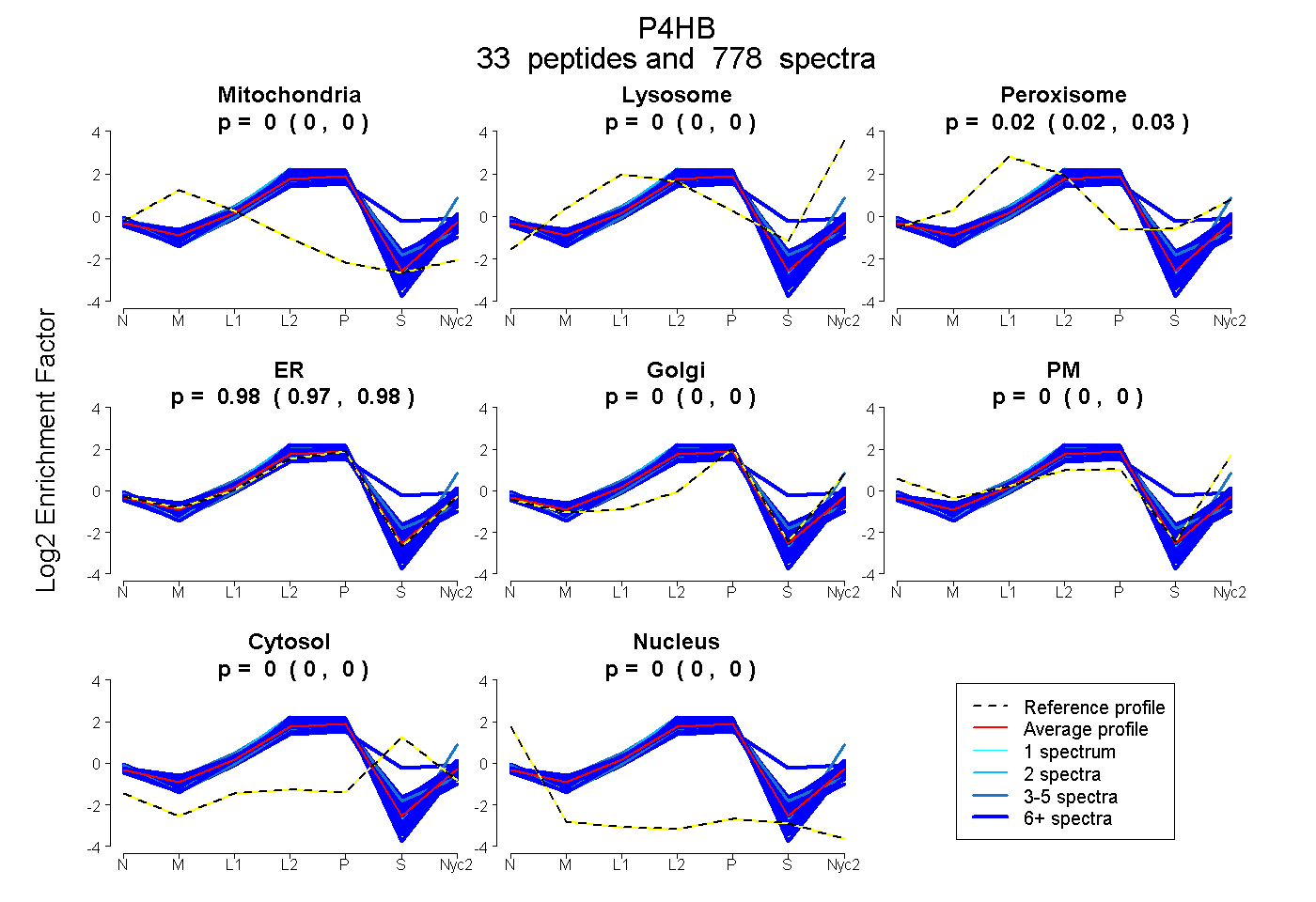
0.000 | 0.000
0.000 | 0.000
0.024 | 0.025
0.975 | 0.976
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
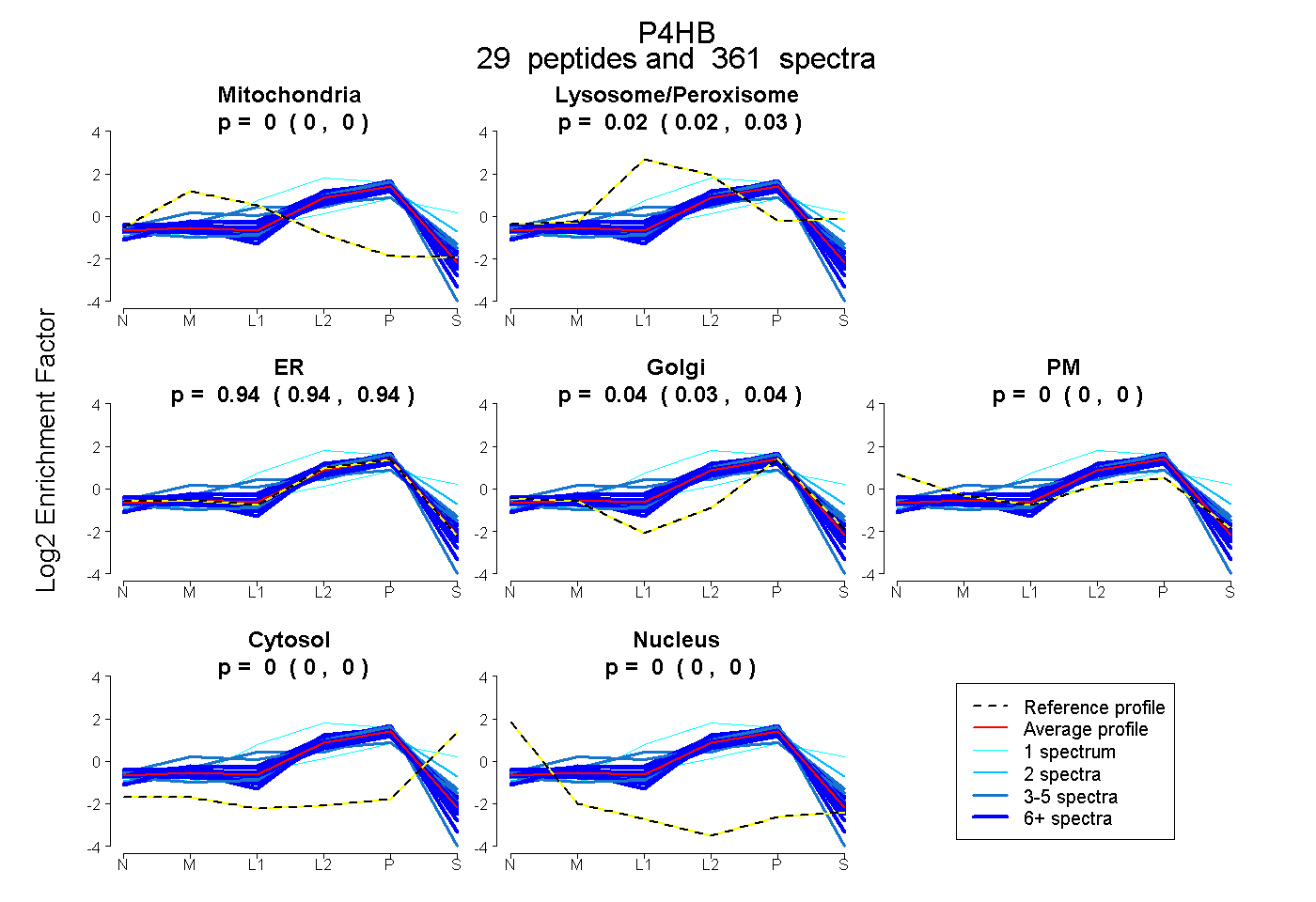
0.000 | 0.002
0.021 | 0.026
0.936 | 0.944
0.032 | 0.038
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
778 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.024 | 0.025 |
0.975 0.975 | 0.976 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
361 spectra |
 |
0.001 0.000 | 0.002 |
0.024 0.021 | 0.026 |
0.940 0.936 | 0.944 |
0.035 0.032 | 0.038 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, EYTAGR | 0.000 | 0.365 | 0.306 | 0.328 | 0.000 | 0.000 | 0.000 | |||
| 21 spectra, VHSFPTLK | 0.034 | 0.075 | 0.891 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, GYPTIK | 0.000 | 0.075 | 0.799 | 0.126 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DHENIVIAK | 0.000 | 0.128 | 0.736 | 0.000 | 0.000 | 0.136 | 0.000 | |||
| 10 spectra, QLAPIWDK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, VDATEESDLAQQYGVR | 0.066 | 0.000 | 0.785 | 0.039 | 0.110 | 0.000 | 0.000 | |||
| 7 spectra, LIDFLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 16 spectra, EADDIVNWLK | 0.000 | 0.000 | 0.919 | 0.052 | 0.000 | 0.029 | 0.000 | |||
| 3 spectra, DAGSDSAK | 0.000 | 0.183 | 0.499 | 0.302 | 0.000 | 0.016 | 0.000 | |||
| 18 spectra, MDSTANEVEAVK | 0.000 | 0.000 | 0.915 | 0.000 | 0.000 | 0.085 | 0.000 | |||
| 23 spectra, ILEFFGLK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, HNQLPLVIEFTEQTAPK | 0.062 | 0.058 | 0.880 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 30 spectra, FFPASADR | 0.000 | 0.000 | 0.877 | 0.123 | 0.000 | 0.000 | 0.000 | |||
| 47 spectra, ITQFCHHFLEGK | 0.000 | 0.047 | 0.953 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, EECPAVR | 0.000 | 0.086 | 0.708 | 0.197 | 0.000 | 0.009 | 0.000 | |||
| 3 spectra, NGDTASPK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 26 spectra, ILFIFIDSDHTDNQR | 0.016 | 0.103 | 0.880 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, IFGGEIK | 0.000 | 0.000 | 0.976 | 0.024 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, THILLFLPK | 0.126 | 0.246 | 0.444 | 0.184 | 0.000 | 0.000 | 0.000 | |||
| 29 spectra, LITLEEEMTK | 0.000 | 0.000 | 0.901 | 0.099 | 0.000 | 0.000 | 0.000 | |||
| 20 spectra, TVIDYNGER | 0.000 | 0.045 | 0.804 | 0.151 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, NFEEVAFDEK | 0.000 | 0.000 | 0.901 | 0.072 | 0.000 | 0.027 | 0.000 | |||
| 3 spectra, TLDGFK | 0.000 | 0.000 | 0.968 | 0.009 | 0.000 | 0.023 | 0.000 | |||
| 12 spectra, NNFEGEITK | 0.002 | 0.032 | 0.917 | 0.049 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, SVSDYDGK | 0.006 | 0.000 | 0.967 | 0.026 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, DGVVLFK | 0.000 | 0.117 | 0.650 | 0.145 | 0.000 | 0.088 | 0.000 | |||
| 10 spectra, ALAPEYAK | 0.015 | 0.019 | 0.865 | 0.070 | 0.031 | 0.000 | 0.000 | |||
| 1 spectrum, AEGSEIR | 0.000 | 0.370 | 0.000 | 0.419 | 0.000 | 0.211 | 0.000 | |||
| 1 spectrum, AAEGFK | 0.000 | 0.165 | 0.835 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1635 spectra |
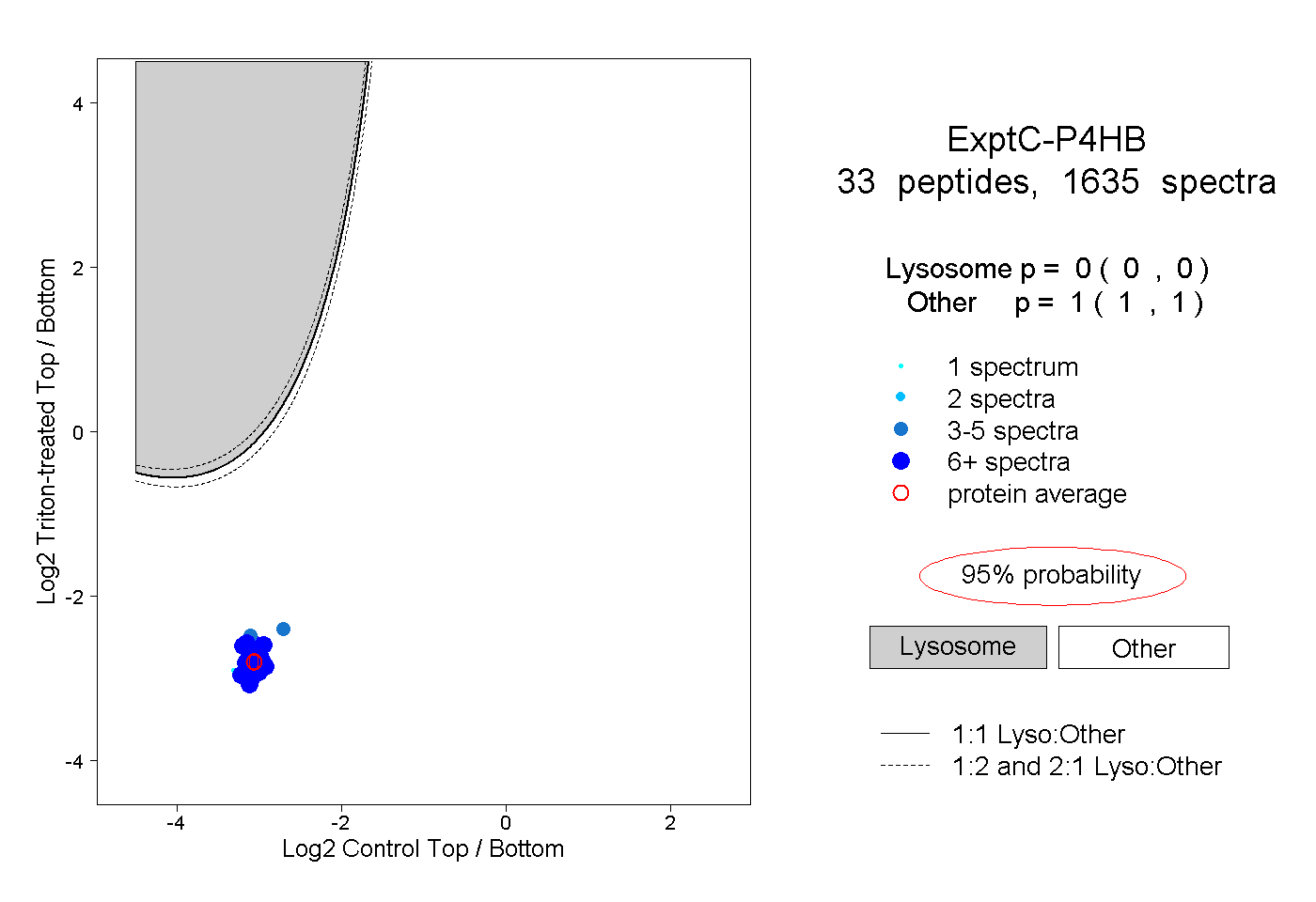 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
159 spectra |
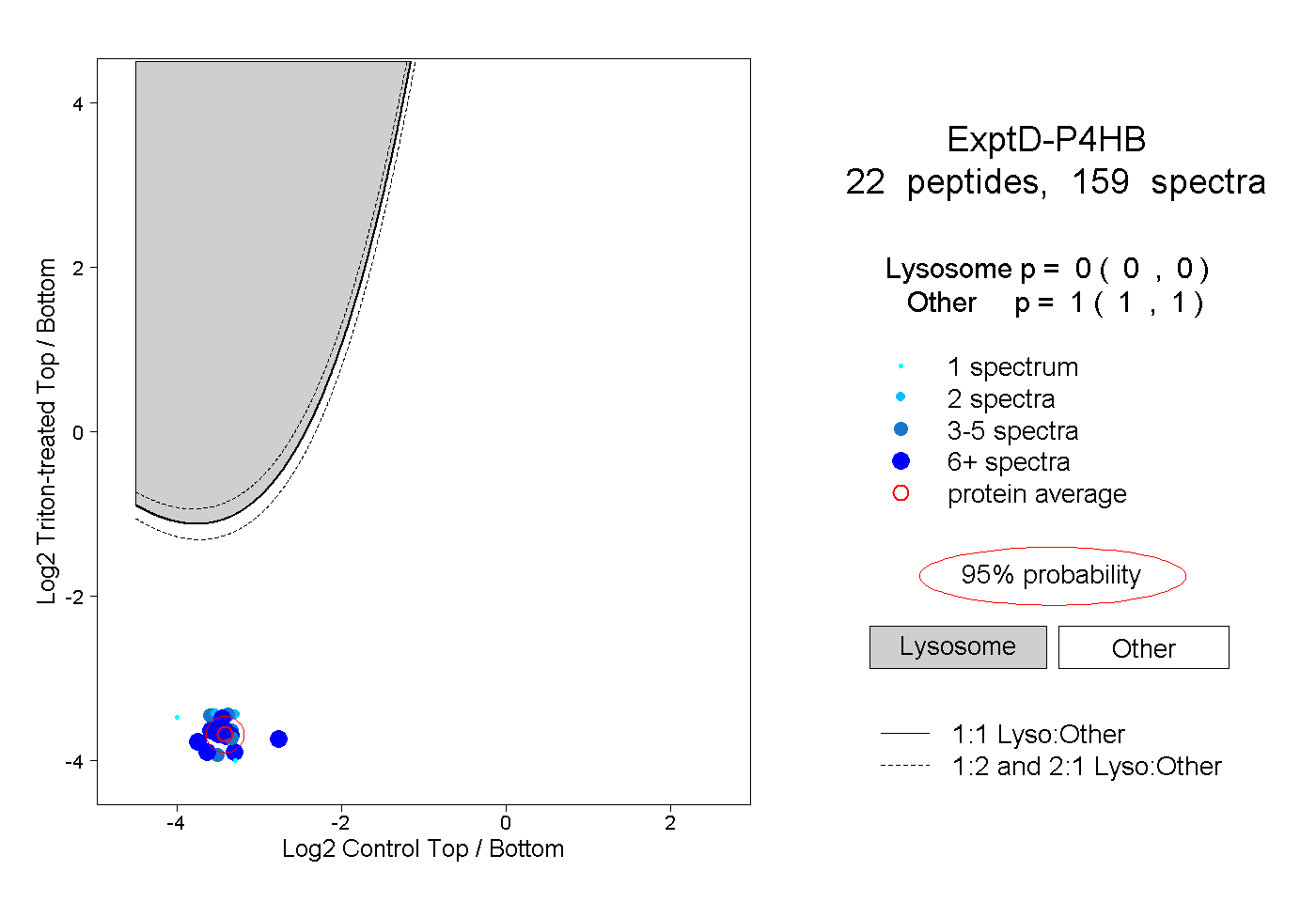 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |