peptides
spectra
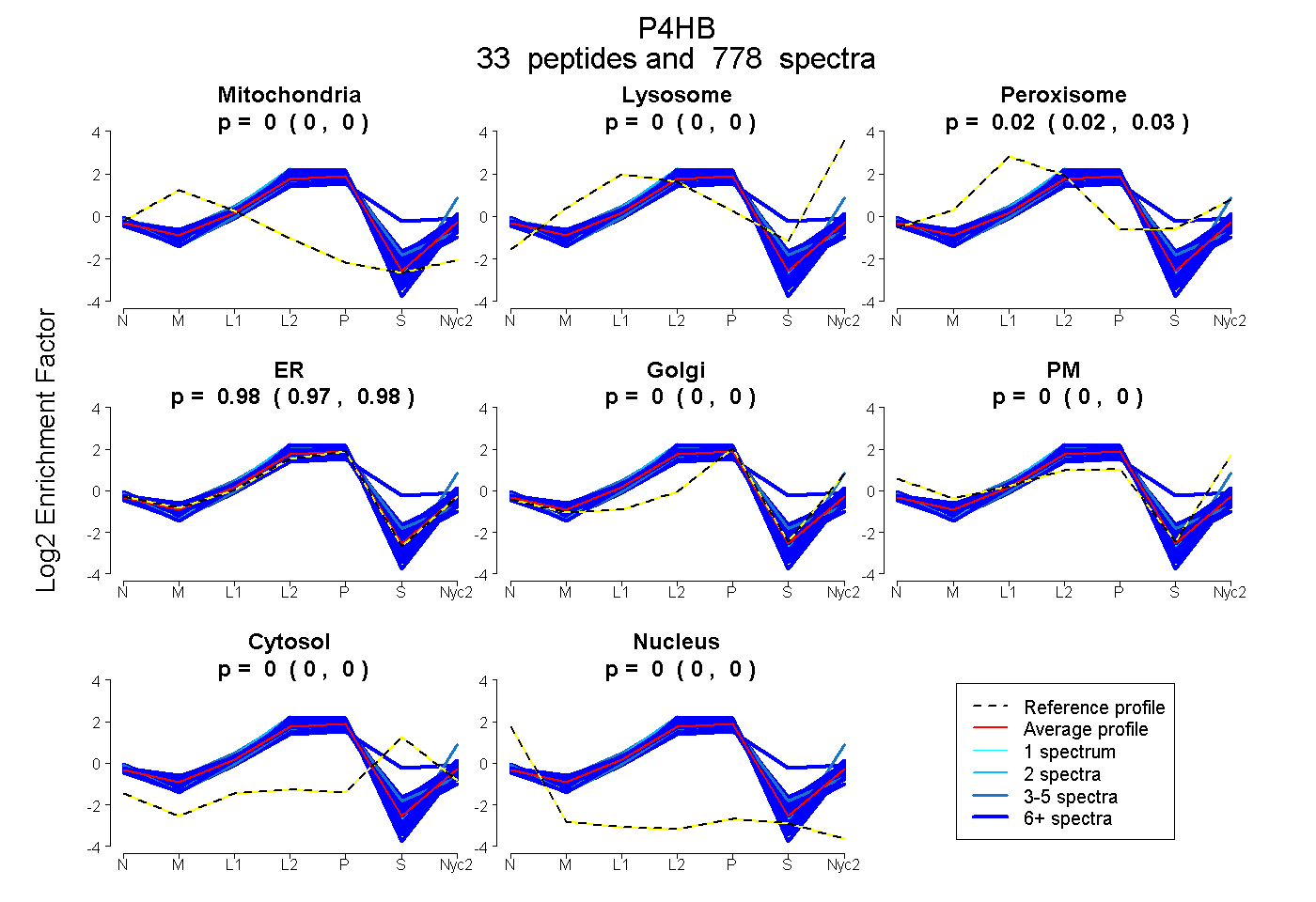
0.000 | 0.000
0.000 | 0.000
0.024 | 0.025
0.975 | 0.976
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
778 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.024 | 0.025 |
0.975 0.975 | 0.976 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 4 spectra, DHENIVIAK | 0.000 | 0.014 | 0.122 | 0.833 | 0.000 | 0.032 | 0.000 | 0.000 | ||
| 4 spectra, VDATEESDLAQQYGVR | 0.000 | 0.000 | 0.000 | 0.893 | 0.000 | 0.000 | 0.107 | 0.000 | ||
| 34 spectra, LIDFLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 21 spectra, EECPAVR | 0.000 | 0.000 | 0.000 | 0.960 | 0.000 | 0.000 | 0.002 | 0.039 | ||
| 9 spectra, NGDTASPK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 20 spectra, THILLFLPK | 0.000 | 0.072 | 0.045 | 0.884 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 33 spectra, TVIDYNGER | 0.000 | 0.000 | 0.032 | 0.968 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, YKPESDELTAEK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, TLDGFK | 0.000 | 0.008 | 0.000 | 0.992 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 86 spectra, SVSDYDGK | 0.000 | 0.000 | 0.021 | 0.974 | 0.000 | 0.000 | 0.006 | 0.000 | ||
| 5 spectra, DGVVLFK | 0.000 | 0.133 | 0.000 | 0.780 | 0.000 | 0.087 | 0.000 | 0.000 | ||
| 28 spectra, ALAPEYAK | 0.000 | 0.000 | 0.006 | 0.994 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 38 spectra, EYTAGR | 0.000 | 0.026 | 0.000 | 0.954 | 0.000 | 0.020 | 0.000 | 0.000 | ||
| 24 spectra, GYPTIK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 40 spectra, VHSFPTLK | 0.000 | 0.033 | 0.007 | 0.934 | 0.000 | 0.026 | 0.000 | 0.000 | ||
| 19 spectra, QLAPIWDK | 0.000 | 0.000 | 0.052 | 0.948 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, DAGSDSAK | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | 0.000 | 0.028 | 0.000 | ||
| 32 spectra, EADDIVNWLK | 0.000 | 0.000 | 0.118 | 0.799 | 0.000 | 0.000 | 0.083 | 0.000 | ||
| 45 spectra, FFPASADR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, HNQLPLVIEFTEQTAPK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, IFNELK | 0.000 | 0.072 | 0.000 | 0.928 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 19 spectra, ILEFFGLK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 34 spectra, MDSTANEVEAVK | 0.000 | 0.088 | 0.002 | 0.886 | 0.000 | 0.000 | 0.024 | 0.000 | ||
| 33 spectra, ITQFCHHFLEGK | 0.000 | 0.000 | 0.027 | 0.954 | 0.000 | 0.000 | 0.020 | 0.000 | ||
| 12 spectra, ILFIFIDSDHTDNQR | 0.000 | 0.000 | 0.102 | 0.850 | 0.000 | 0.000 | 0.048 | 0.000 | ||
| 9 spectra, IFGGEIK | 0.000 | 0.003 | 0.000 | 0.993 | 0.000 | 0.003 | 0.000 | 0.000 | ||
| 6 spectra, LGETYK | 0.000 | 0.068 | 0.000 | 0.858 | 0.000 | 0.000 | 0.074 | 0.000 | ||
| 62 spectra, LITLEEEMTK | 0.000 | 0.060 | 0.023 | 0.917 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 37 spectra, NFEEVAFDEK | 0.000 | 0.000 | 0.071 | 0.899 | 0.000 | 0.000 | 0.030 | 0.000 | ||
| 16 spectra, LSNFK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 27 spectra, NNFEGEITK | 0.000 | 0.000 | 0.049 | 0.931 | 0.000 | 0.000 | 0.019 | 0.000 | ||
| 35 spectra, AAEGFK | 0.000 | 0.000 | 0.042 | 0.939 | 0.000 | 0.000 | 0.019 | 0.000 | ||
| 7 spectra, AEGSEIR | 0.000 | 0.032 | 0.103 | 0.587 | 0.000 | 0.000 | 0.278 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
361 spectra |
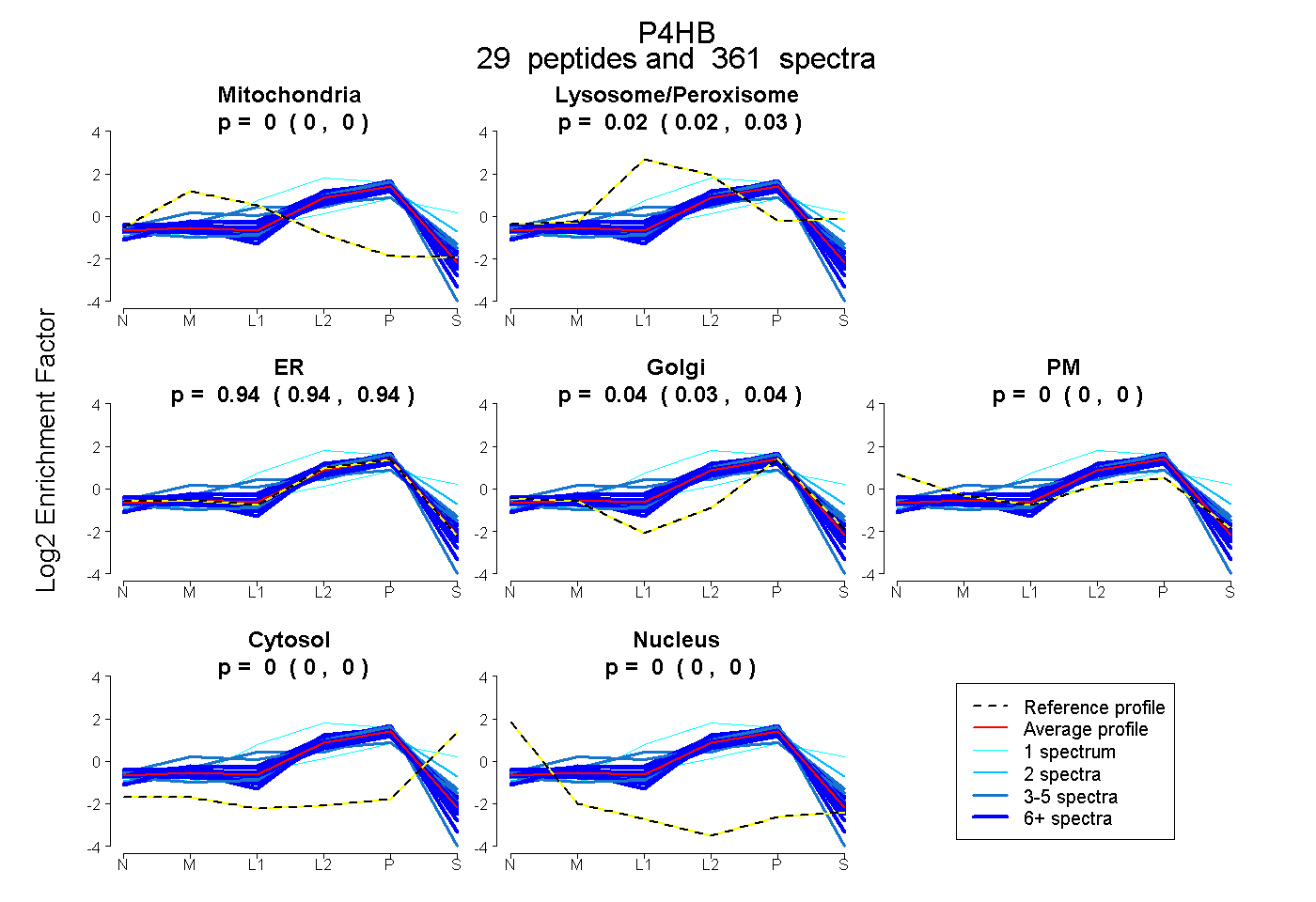 |
0.001 0.000 | 0.002 |
0.024 0.021 | 0.026 |
0.940 0.936 | 0.944 |
0.035 0.032 | 0.038 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1635 spectra |
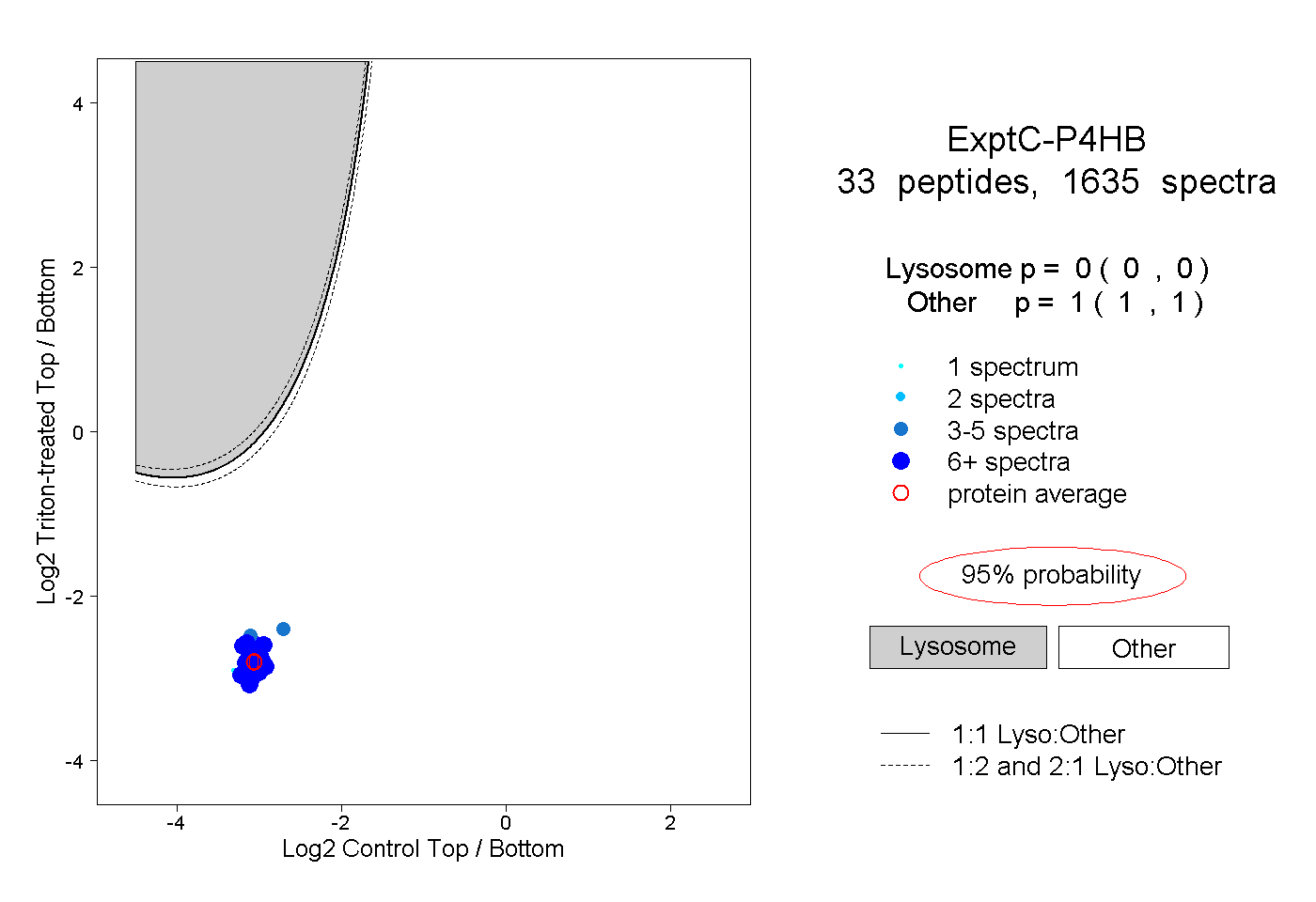 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
159 spectra |
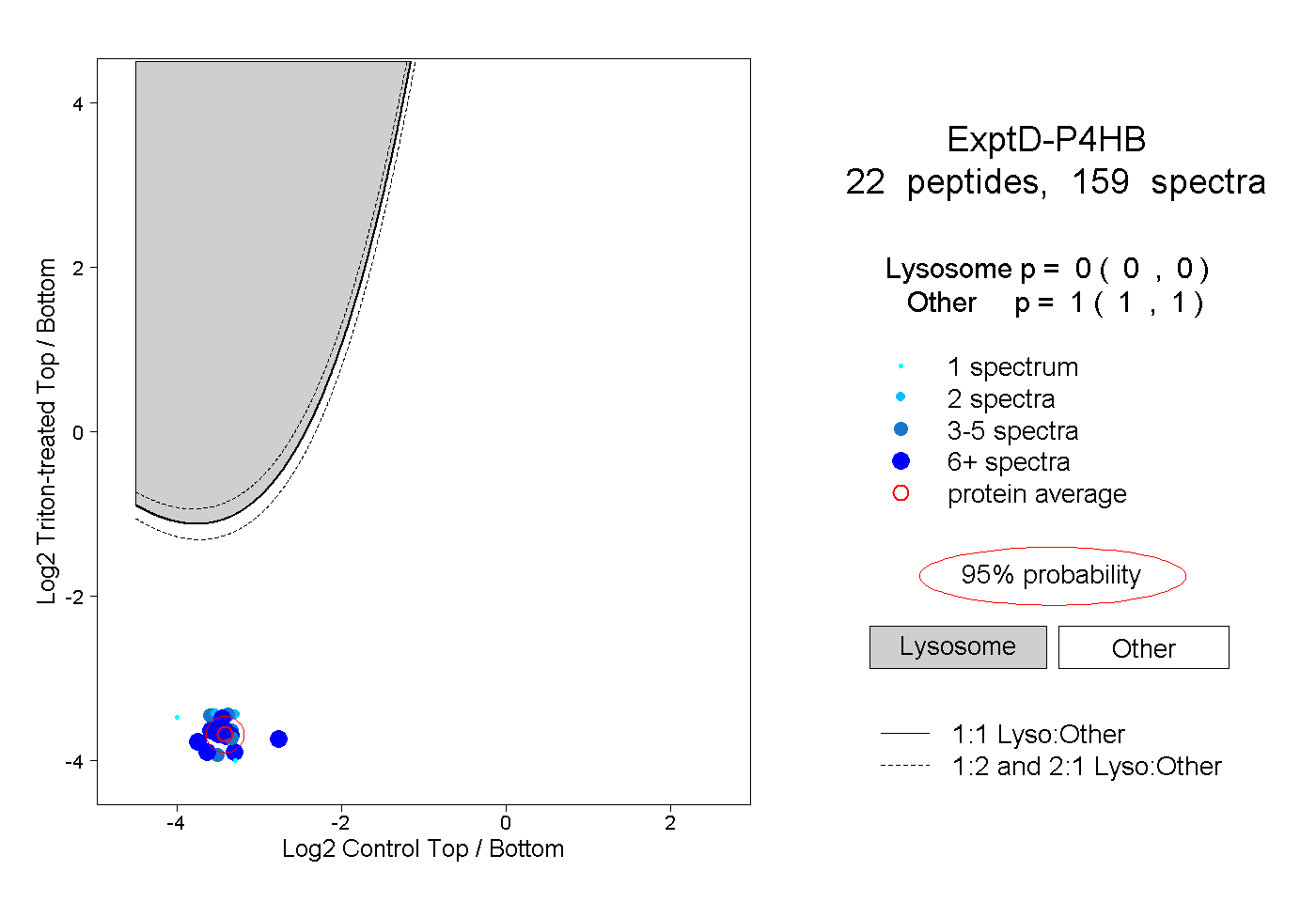 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |