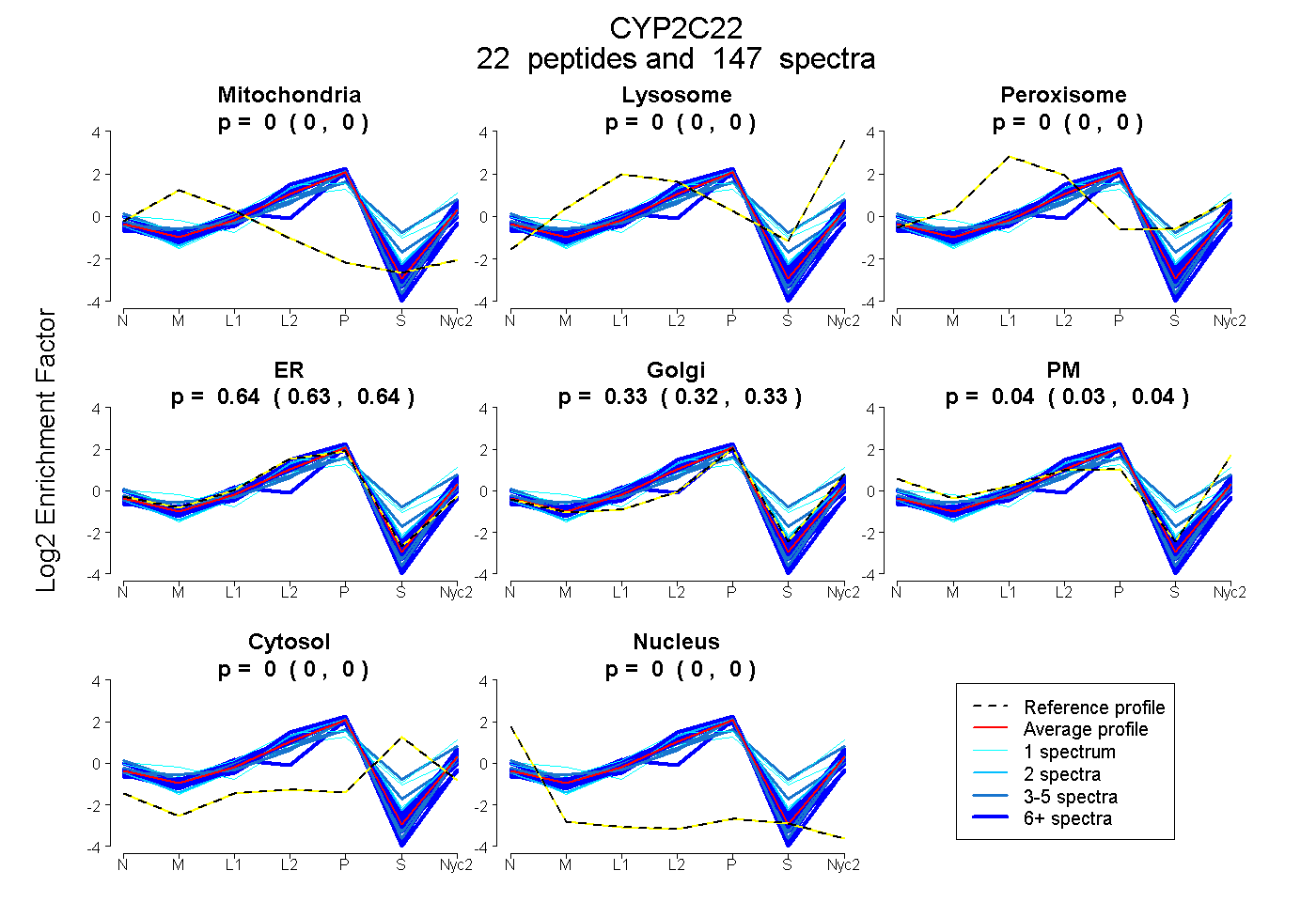
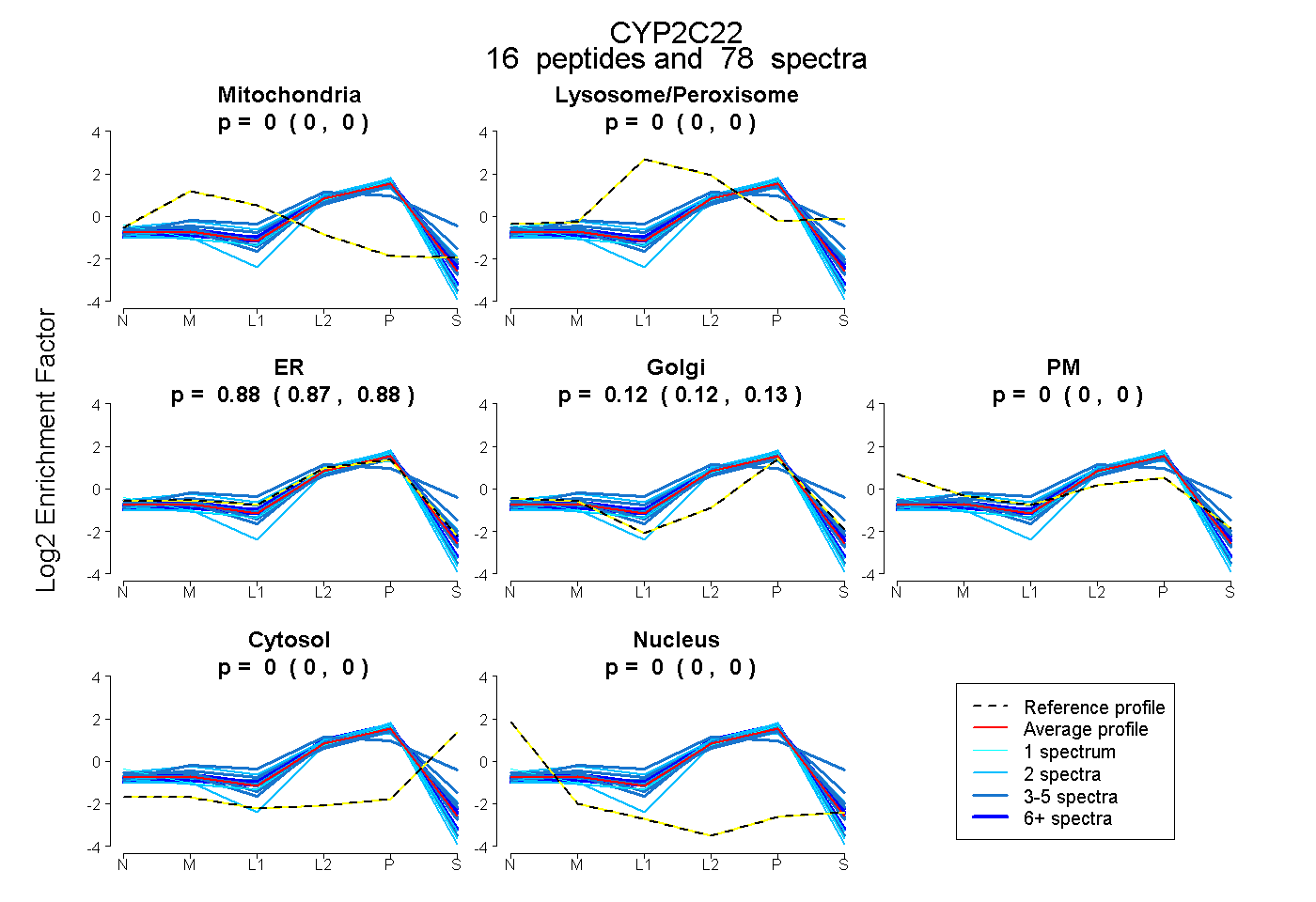
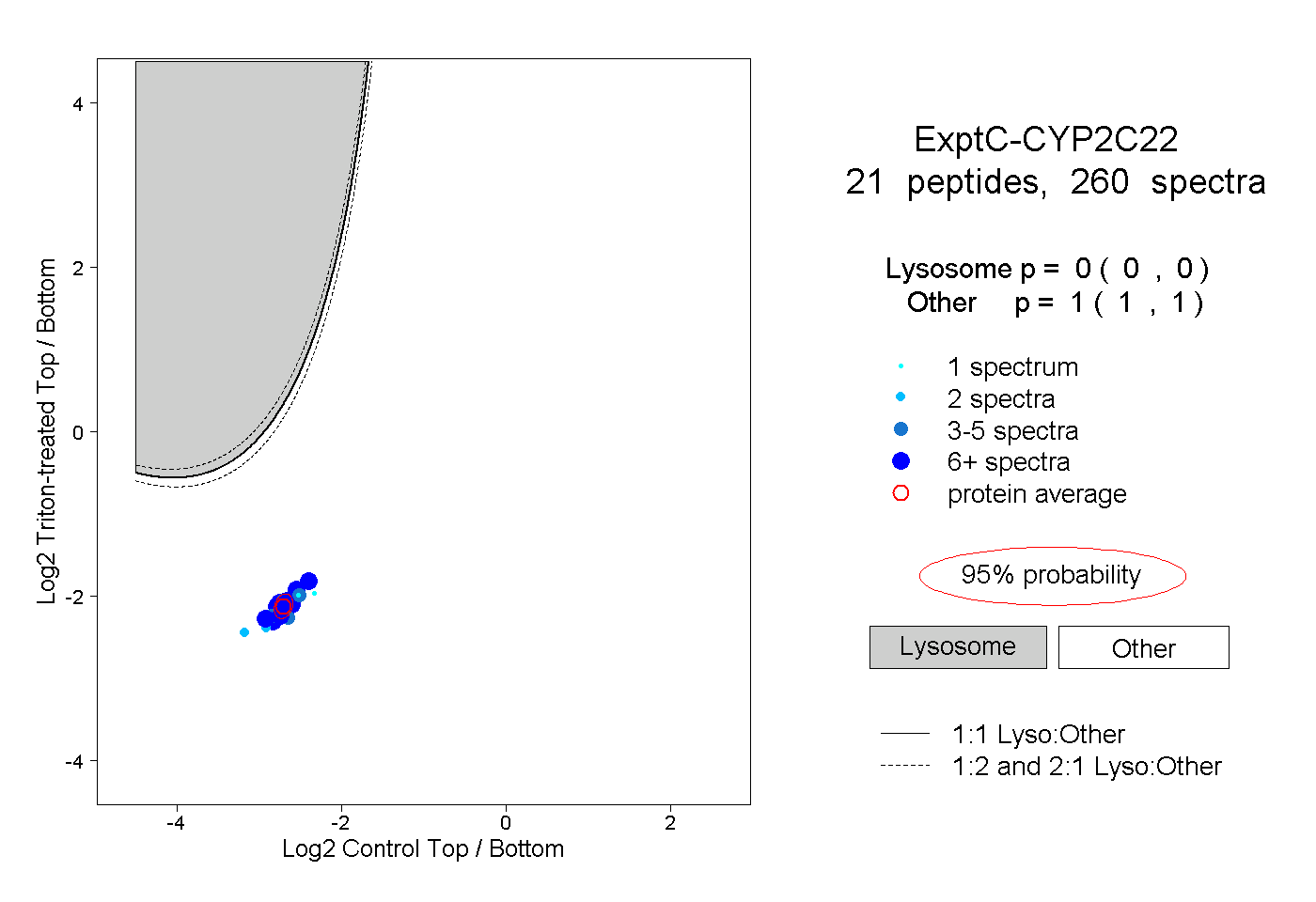
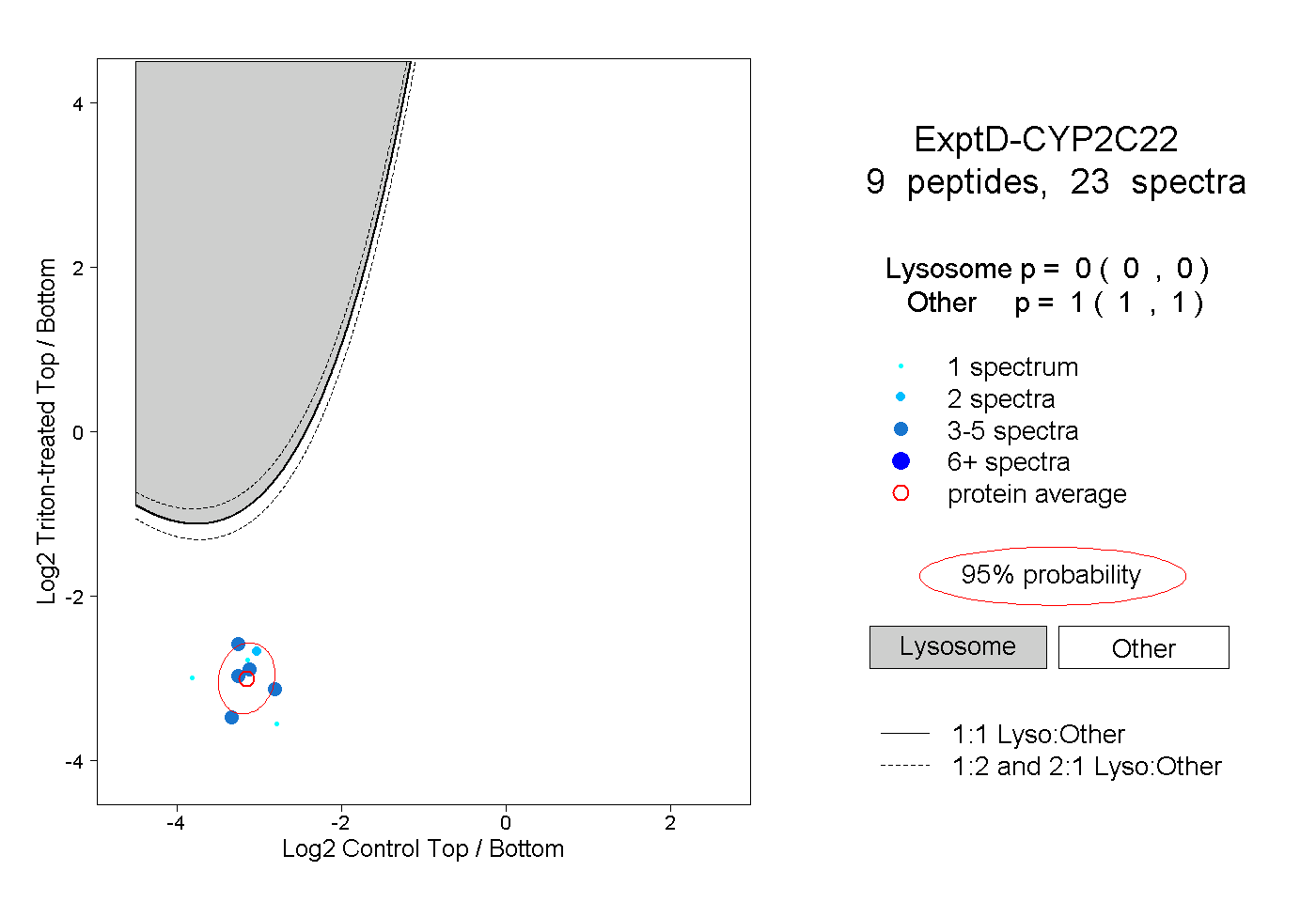
| 23 spectra, FILMEINR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, FDYSDEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SMCMLAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SDYFMAFSAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NHMPYTDAVLHEIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, FIENFHTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, YPEVTAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, RPCMQDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, FDPGHFLDEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, DVTEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, IQEELTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, IQEEVVYLLEALR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LPPGPTPLPIFGNILQVGVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, MHSSMLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 30 spectra, YIDFVPIPLPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, SMGMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, ACIGEGLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VSQGLGIVFSNGEIWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, FSLMVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GEEFSDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, TTQDVEFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |