peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.186 | 0.192
0.000 | 0.000
0.257 | 0.260
0.000 | 0.000
0.549 | 0.555
0.000 | 0.000
peptides
spectra
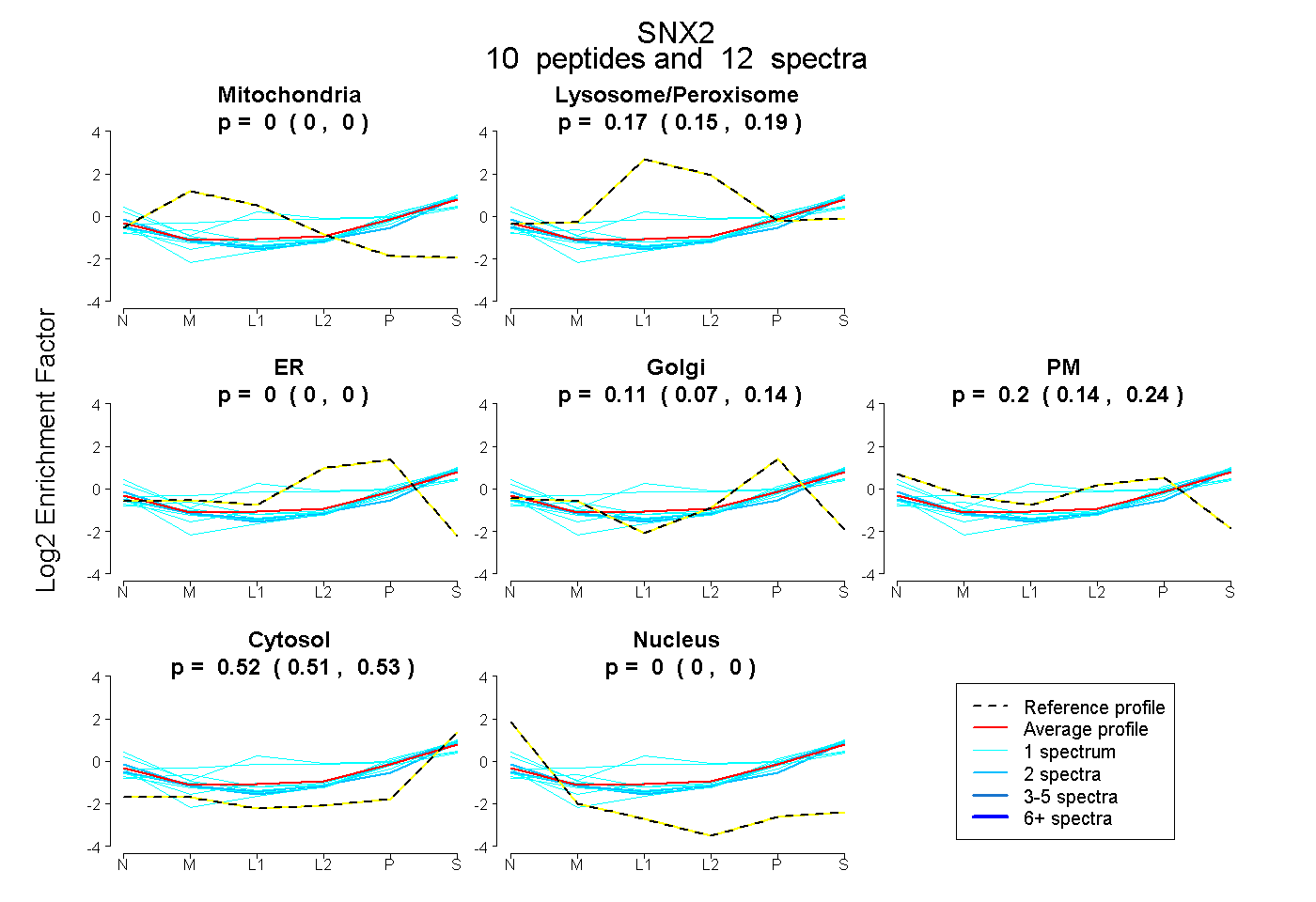
0.000 | 0.000
0.146 | 0.191
0.000 | 0.000
0.074 | 0.143
0.144 | 0.241
0.510 | 0.531
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
94 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.189 0.186 | 0.192 |
0.000 0.000 | 0.000 |
0.259 0.257 | 0.260 |
0.000 0.000 | 0.000 |
0.552 0.549 | 0.555 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
12 spectra |
 |
0.000 0.000 | 0.000 |
0.170 0.146 | 0.191 |
0.000 0.000 | 0.000 |
0.111 0.074 | 0.143 |
0.197 0.144 | 0.241 |
0.522 0.510 | 0.531 |
0.000 0.000 | 0.000 |
| 1 spectrum, YLESLVQTQQQLIK | 0.000 | 0.174 | 0.000 | 0.120 | 0.114 | 0.592 | 0.000 | |||
| 1 spectrum, QFLESSELPR | 0.000 | 0.016 | 0.000 | 0.000 | 0.514 | 0.453 | 0.016 | |||
| 1 spectrum, YWEAFLPEAK | 0.000 | 0.398 | 0.000 | 0.151 | 0.115 | 0.336 | 0.000 | |||
| 2 spectra, FSDFLGLHSK | 0.000 | 0.071 | 0.000 | 0.000 | 0.333 | 0.596 | 0.000 | |||
| 1 spectrum, AVNTQALSGAGILR | 0.000 | 0.093 | 0.000 | 0.221 | 0.085 | 0.601 | 0.000 | |||
| 1 spectrum, SISAPVIFDR | 0.000 | 0.145 | 0.000 | 0.305 | 0.000 | 0.549 | 0.000 | |||
| 1 spectrum, AADAVNK | 0.000 | 0.205 | 0.000 | 0.188 | 0.014 | 0.593 | 0.000 | |||
| 2 spectra, ELSANTAAFAK | 0.000 | 0.112 | 0.000 | 0.212 | 0.103 | 0.572 | 0.000 | |||
| 1 spectrum, ALSQLAEVEEK | 0.000 | 0.209 | 0.000 | 0.266 | 0.000 | 0.525 | 0.000 | |||
| 1 spectrum, GVFDHR | 0.000 | 0.387 | 0.000 | 0.000 | 0.306 | 0.306 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
112 spectra |
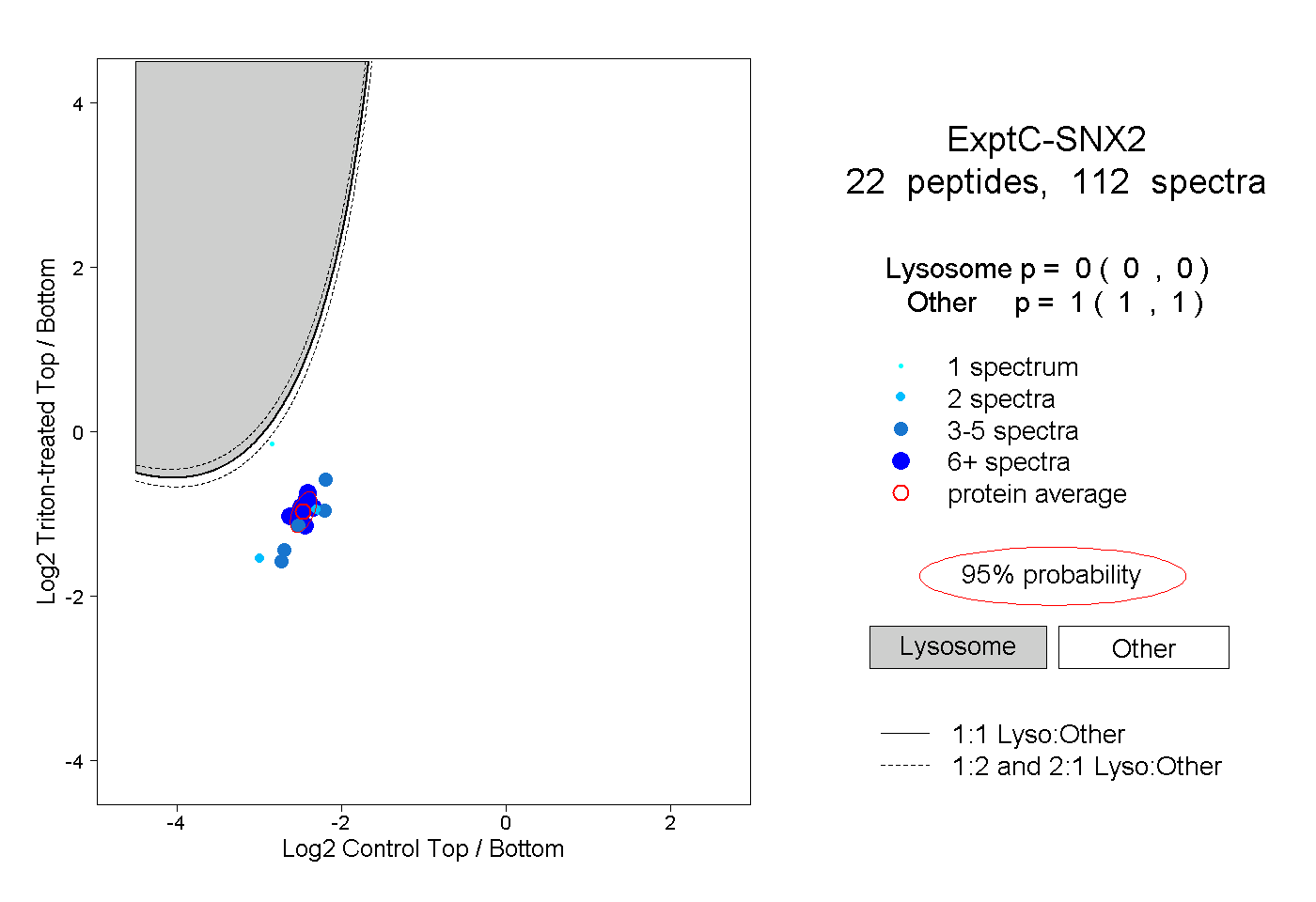 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
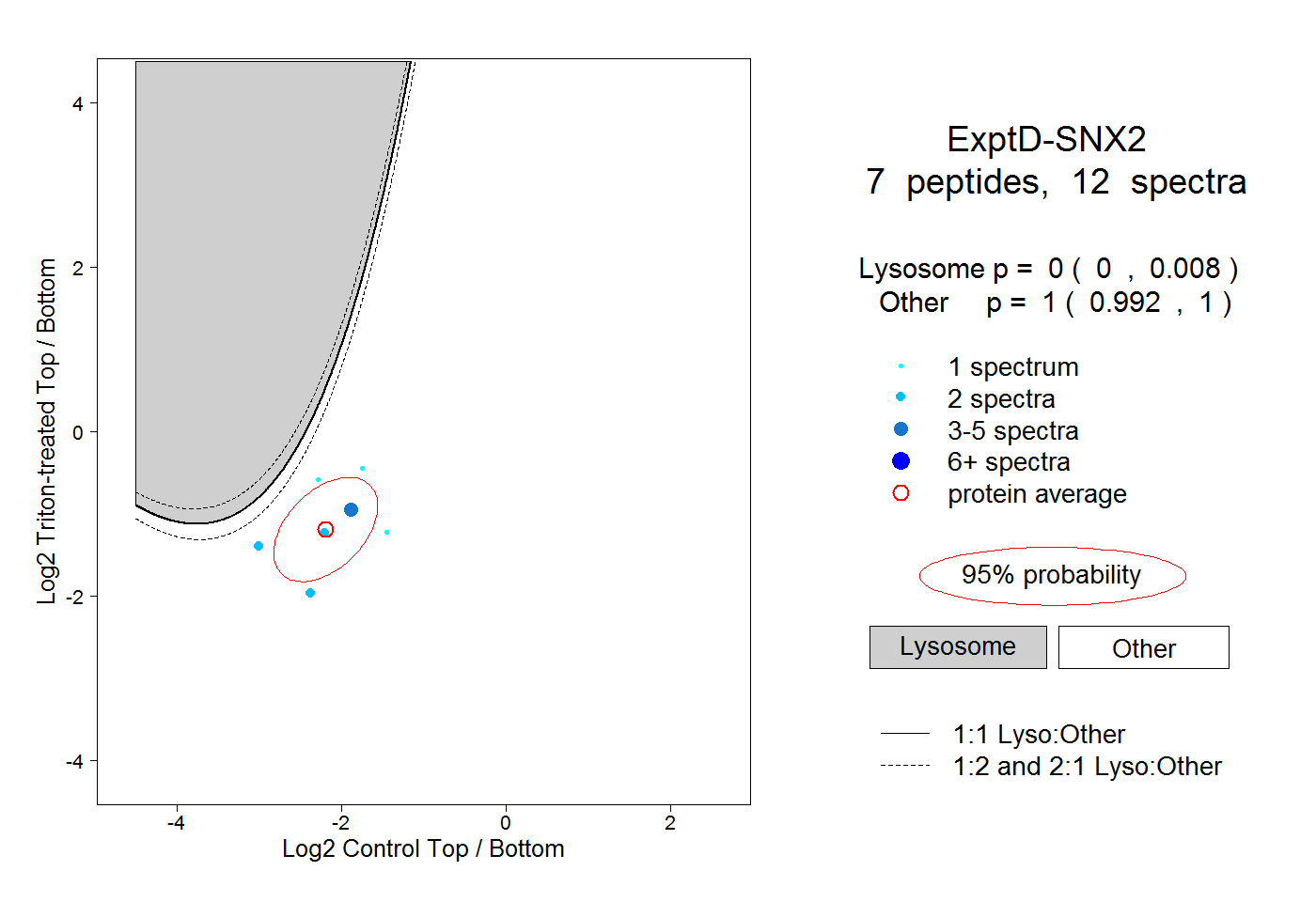 |
0.000 0.000 | 0.008 |
1.000 0.992 | 1.000 |