peptides
spectra
0.264 | 0.272
0.000 | 0.000
0.631 | 0.640
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.094 | 0.097
0.000 | 0.000
peptides
spectra
0.000 | 0.000
0.802 | 0.807
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.192 | 0.197
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
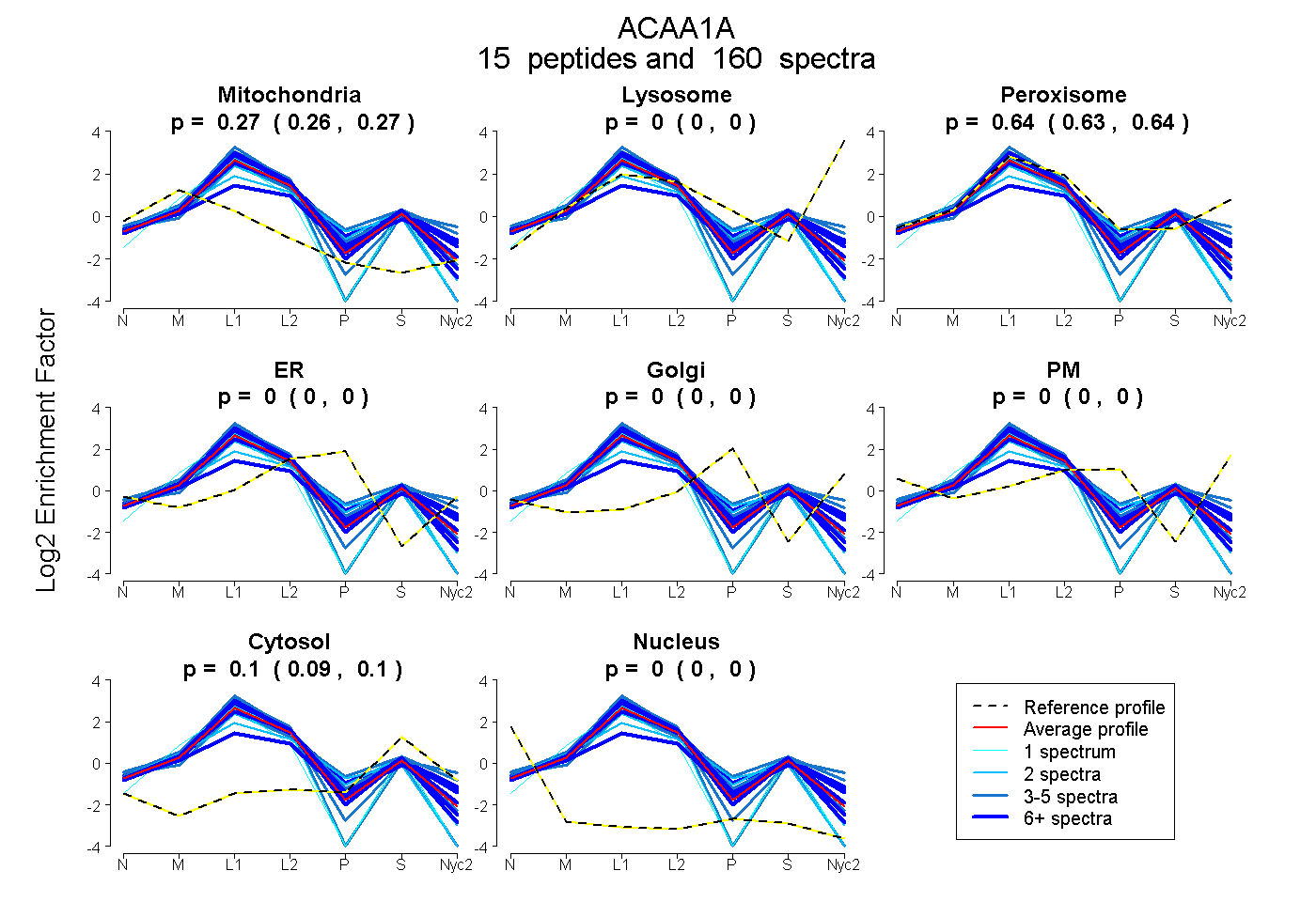
| Expt A |
peptides |
160 spectra |
 |
0.268 0.264 | 0.272 |
0.000 0.000 | 0.000 |
0.636 0.631 | 0.640 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.096 0.094 | 0.097 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
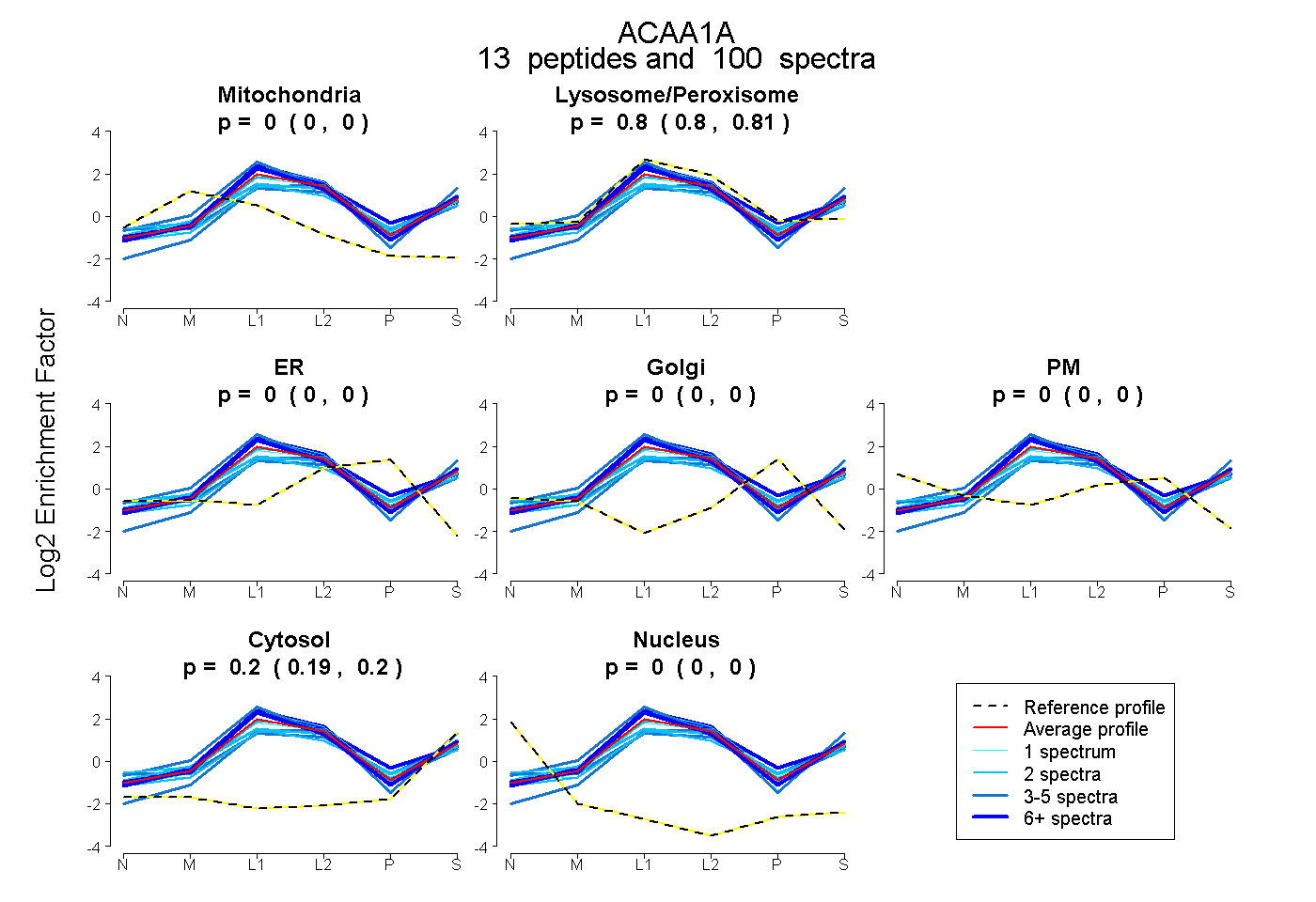
| Expt B |
peptides |
100 spectra |
 |
0.000 0.000 | 0.000 |
0.805 0.802 | 0.807 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.195 0.192 | 0.197 |
0.000 0.000 | 0.000 |
| 2 spectra, TITVSQDEGVRPSTTMEGLAK | 0.000 | 0.733 | 0.000 | 0.000 | 0.000 | 0.267 | 0.000 | |||
| 1 spectrum, ILESDK | 0.000 | 0.870 | 0.000 | 0.000 | 0.000 | 0.130 | 0.000 | |||
| 3 spectra, AEIVPVTTTVLDDK | 0.000 | 0.741 | 0.000 | 0.000 | 0.000 | 0.259 | 0.000 | |||
| 2 spectra, QDAFALASQQK | 0.000 | 0.762 | 0.000 | 0.000 | 0.000 | 0.238 | 0.000 | |||
| 15 spectra, QVVTLLNELK | 0.000 | 0.830 | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | |||
| 3 spectra, LKPAFK | 0.027 | 0.878 | 0.000 | 0.000 | 0.000 | 0.095 | 0.000 | |||
| 3 spectra, LKPECLGDISVGNVLEPGAGAVMAR | 0.000 | 0.679 | 0.000 | 0.000 | 0.000 | 0.321 | 0.000 | |||
| 2 spectra, QCSSGLQAVANIAGGIR | 0.000 | 0.773 | 0.000 | 0.000 | 0.000 | 0.227 | 0.000 | |||
| 27 spectra, VNPLGGAIALGHPLGCTGAR | 0.000 | 0.821 | 0.000 | 0.000 | 0.000 | 0.179 | 0.000 | |||
| 7 spectra, AEELGLPILGVLR | 0.000 | 0.864 | 0.000 | 0.000 | 0.000 | 0.136 | 0.000 | |||
| 1 spectrum, DCLIPMGITSENVAER | 0.000 | 0.781 | 0.000 | 0.000 | 0.000 | 0.219 | 0.000 | |||
| 2 spectra, DGGSTTAGNSSQVSDGAAAVLLAR | 0.000 | 0.800 | 0.000 | 0.000 | 0.000 | 0.200 | 0.000 | |||
| 32 spectra, GNPGNISSR | 0.000 | 0.859 | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1305 spectra |
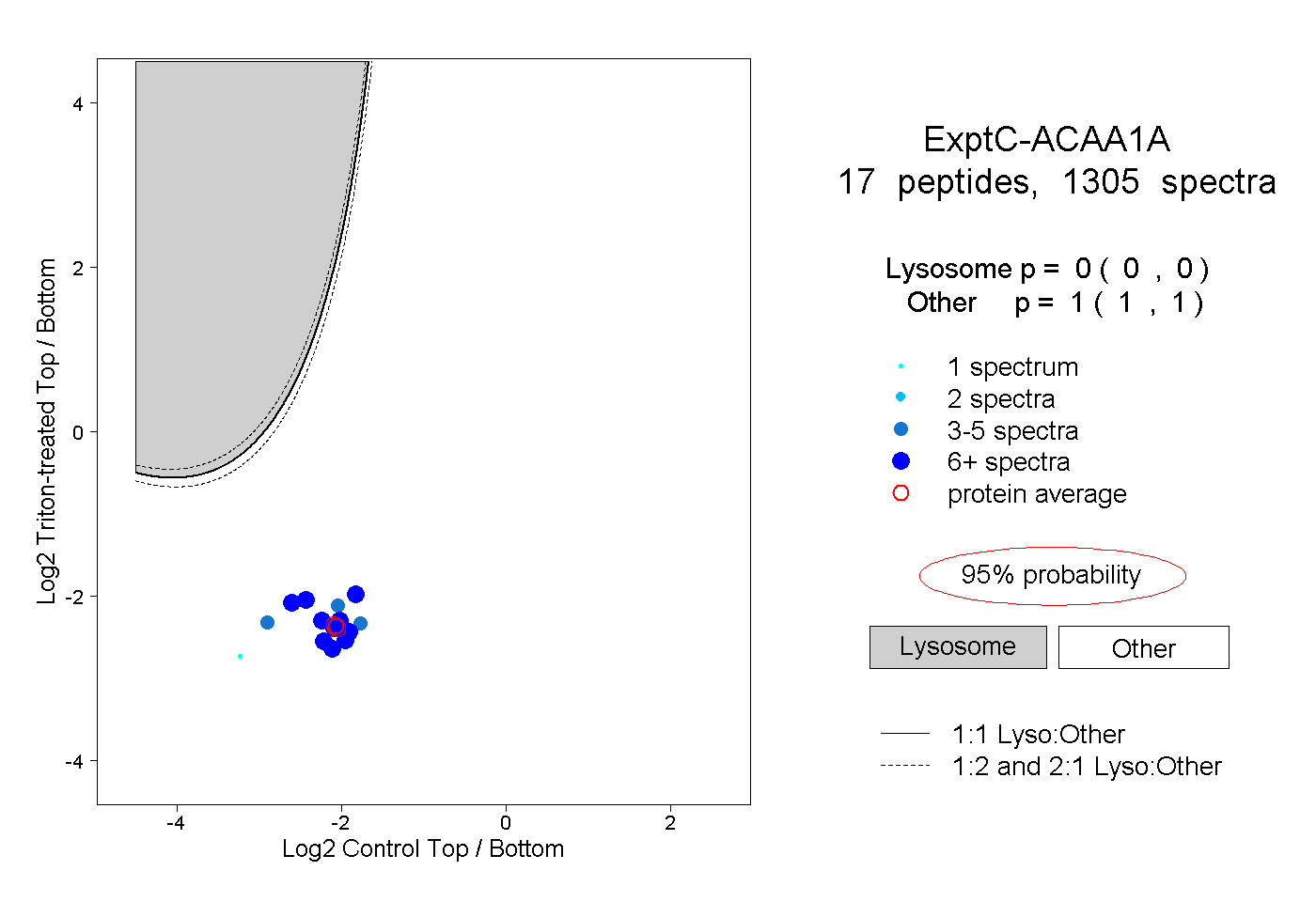 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
33 spectra |
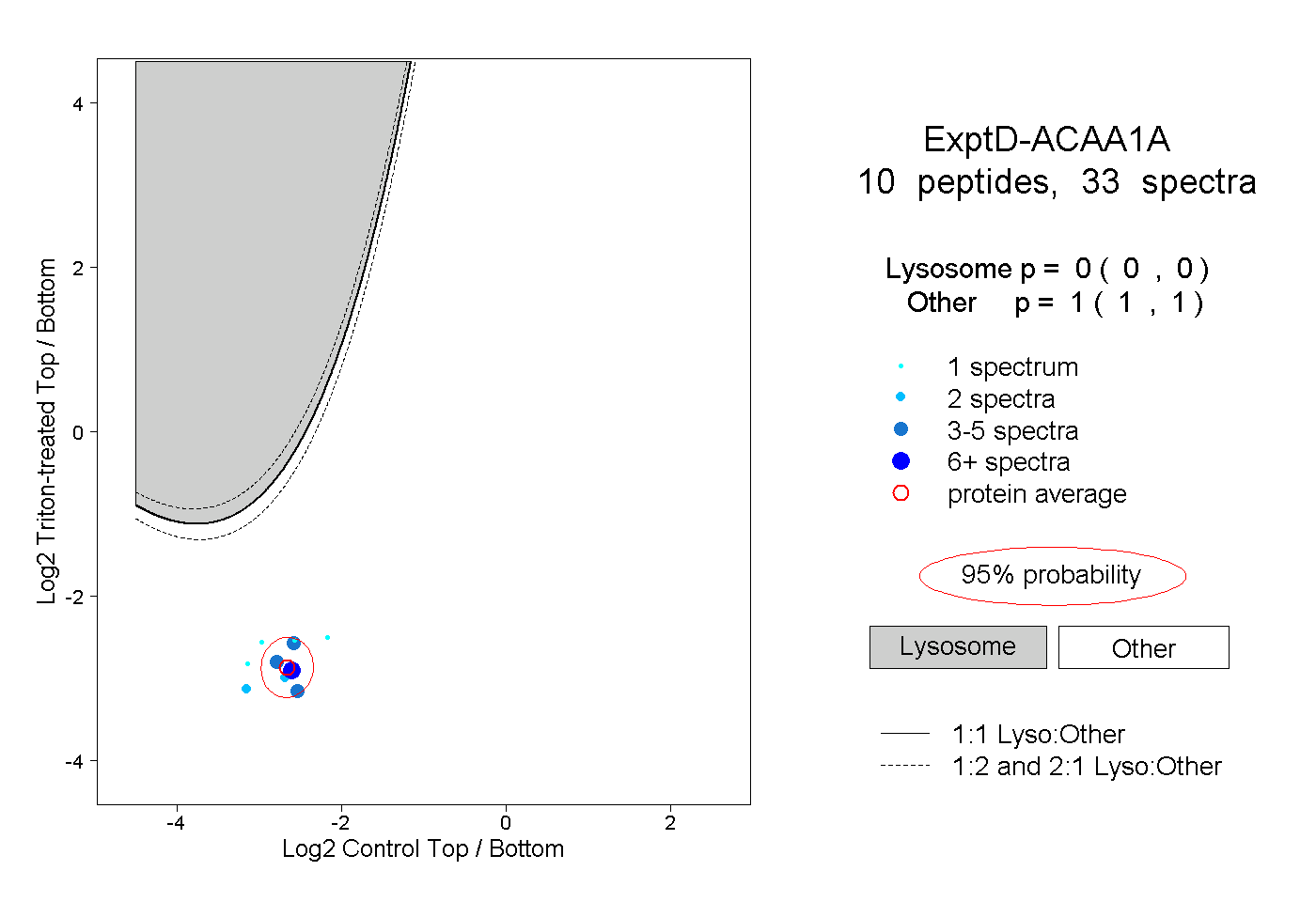 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |