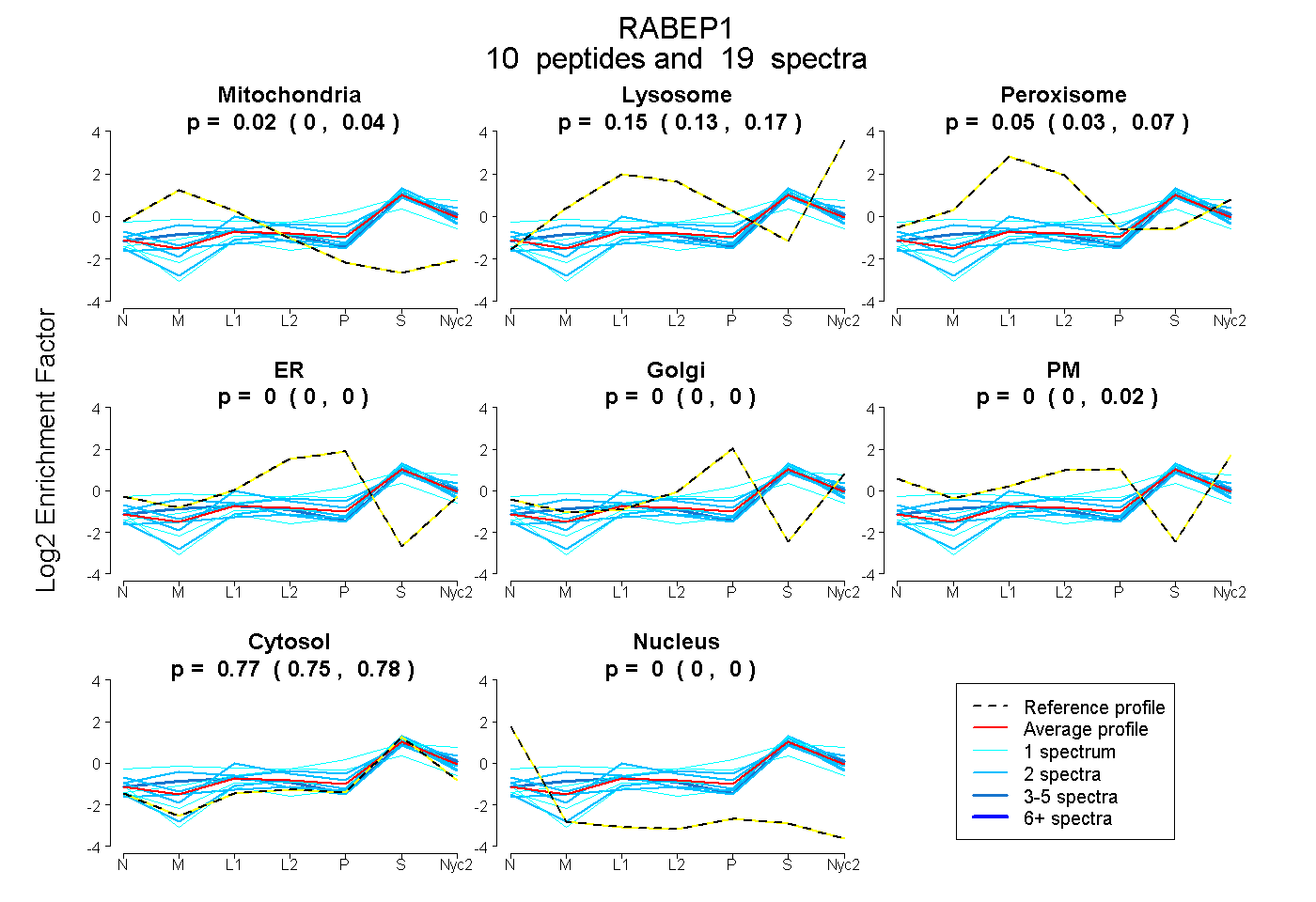
peptides
spectra
0.004 | 0.039
0.128 | 0.166
0.031 | 0.071
0.000 | 0.000
0.000 | 0.000
0.000 | 0.020
0.753 | 0.782
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
19 spectra |
 |
0.025 0.004 | 0.039 |
0.152 0.128 | 0.166 |
0.053 0.031 | 0.071 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.020 |
0.769 0.753 | 0.782 |
0.000 0.000 | 0.000 |
| 2 spectra, QNAVLQAAQDDLGHLR | 0.000 | 0.000 | 0.282 | 0.000 | 0.000 | 0.000 | 0.718 | 0.000 | ||
| 2 spectra, SVLQEDAEK | 0.214 | 0.155 | 0.000 | 0.000 | 0.000 | 0.000 | 0.631 | 0.000 | ||
| 2 spectra, ATVEQLMFEEK | 0.040 | 0.100 | 0.000 | 0.000 | 0.000 | 0.000 | 0.861 | 0.000 | ||
| 1 spectrum, AQSTDSLGTSSSLQSK | 0.169 | 0.000 | 0.258 | 0.000 | 0.134 | 0.016 | 0.422 | 0.000 | ||
| 2 spectra, QLQGIQIQEAETR | 0.000 | 0.137 | 0.052 | 0.000 | 0.000 | 0.149 | 0.661 | 0.000 | ||
| 1 spectrum, MEIVLTSEQLR | 0.000 | 0.140 | 0.000 | 0.000 | 0.000 | 0.000 | 0.860 | 0.000 | ||
| 1 spectrum, AQASEVLLEELQQSFSQAK | 0.000 | 0.010 | 0.000 | 0.000 | 0.000 | 0.009 | 0.981 | 0.000 | ||
| 1 spectrum, IQMLLR | 0.000 | 0.303 | 0.000 | 0.000 | 0.106 | 0.000 | 0.592 | 0.000 | ||
| 5 spectra, AQQQLEQEFNQK | 0.120 | 0.188 | 0.000 | 0.000 | 0.000 | 0.000 | 0.693 | 0.000 | ||
| 2 spectra, ANDQFLESQR | 0.000 | 0.106 | 0.000 | 0.000 | 0.000 | 0.000 | 0.894 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
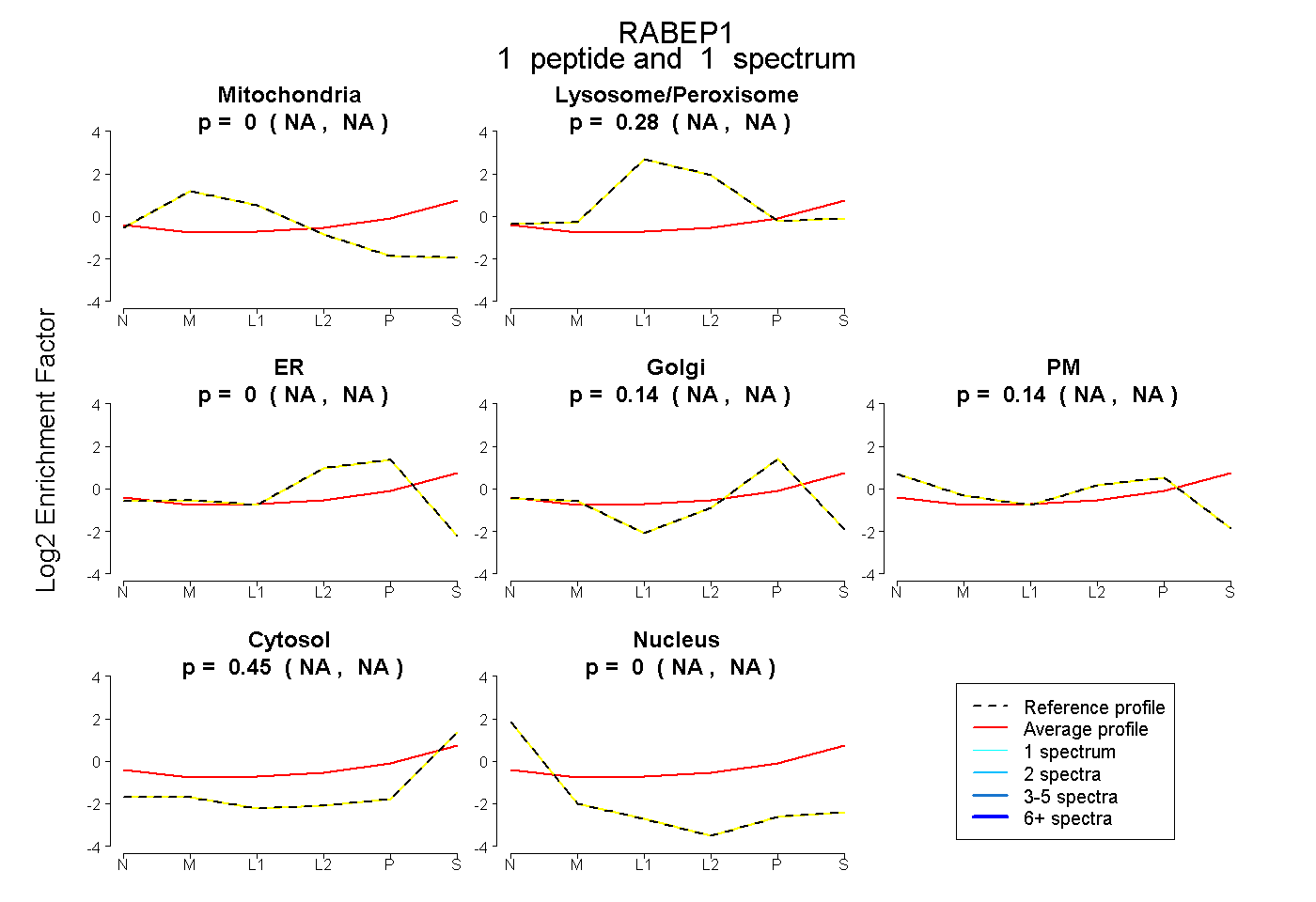 |
0.000 NA | NA |
0.282 NA | NA |
0.000 NA | NA |
0.138 NA | NA |
0.135 NA | NA |
0.445 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
17 spectra |
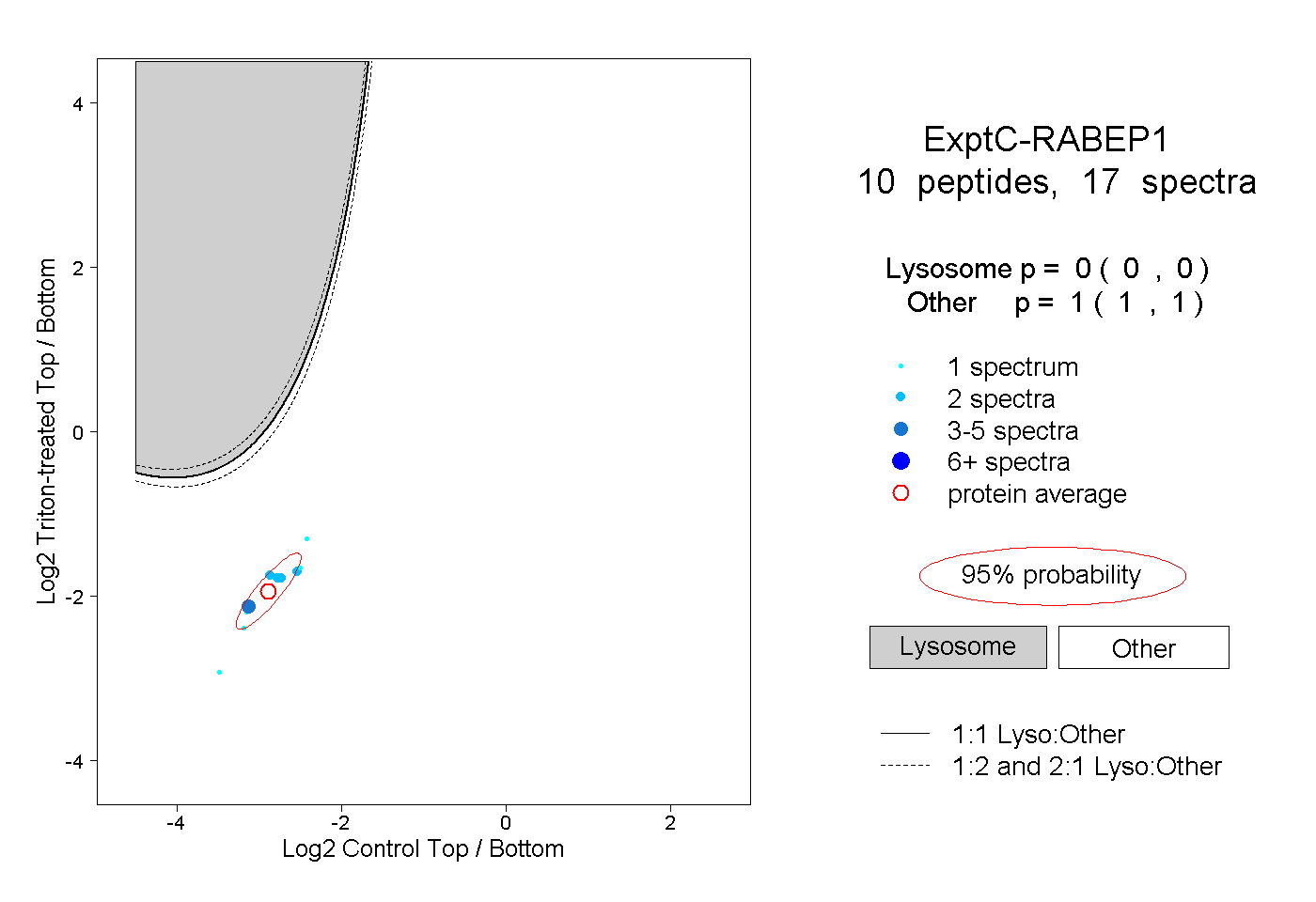 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |