peptides
spectra
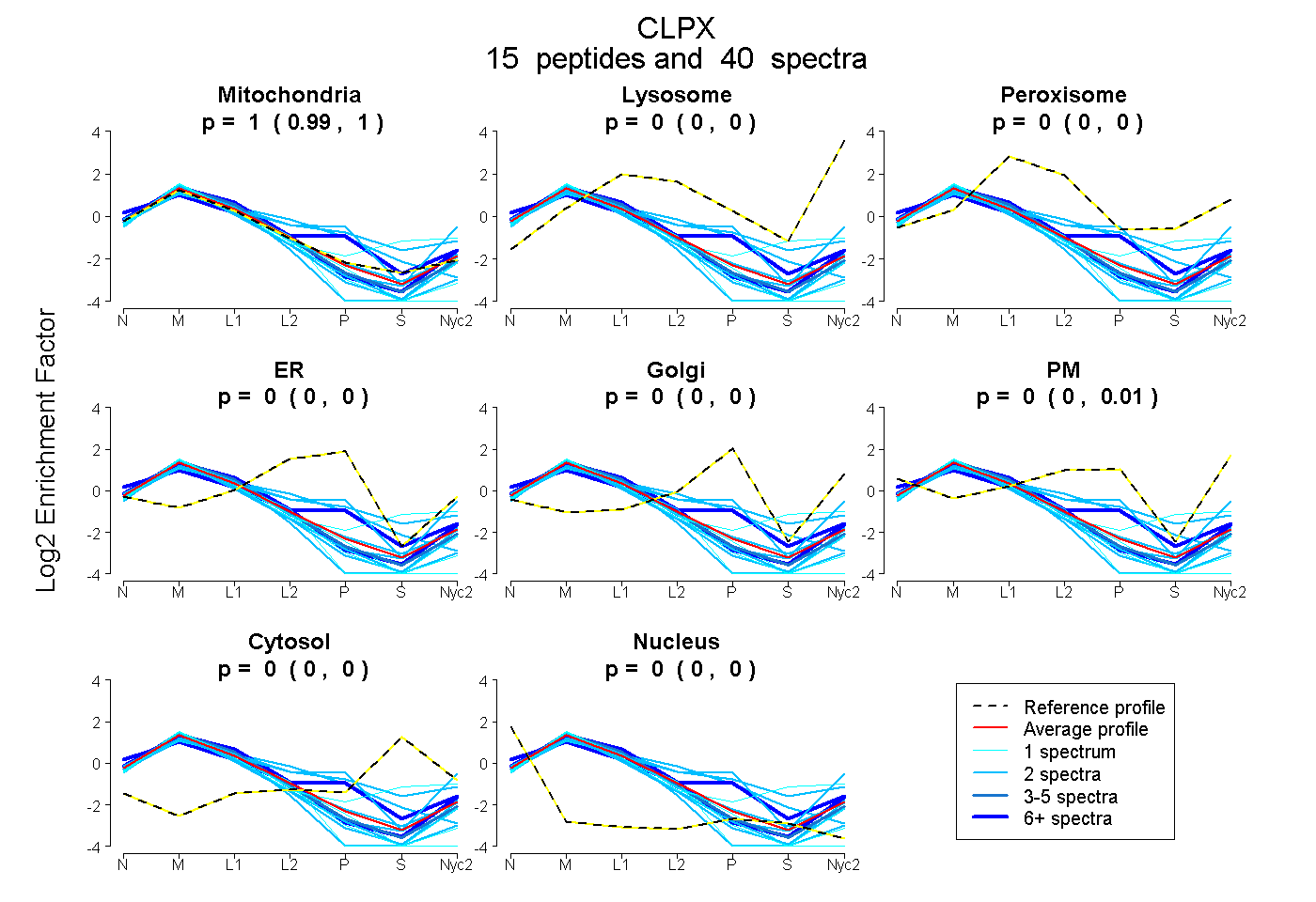
0.986 | 1.000
0.000 | 0.003
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.012
0.000 | 0.000
0.000 | 0.000
peptides
spectra
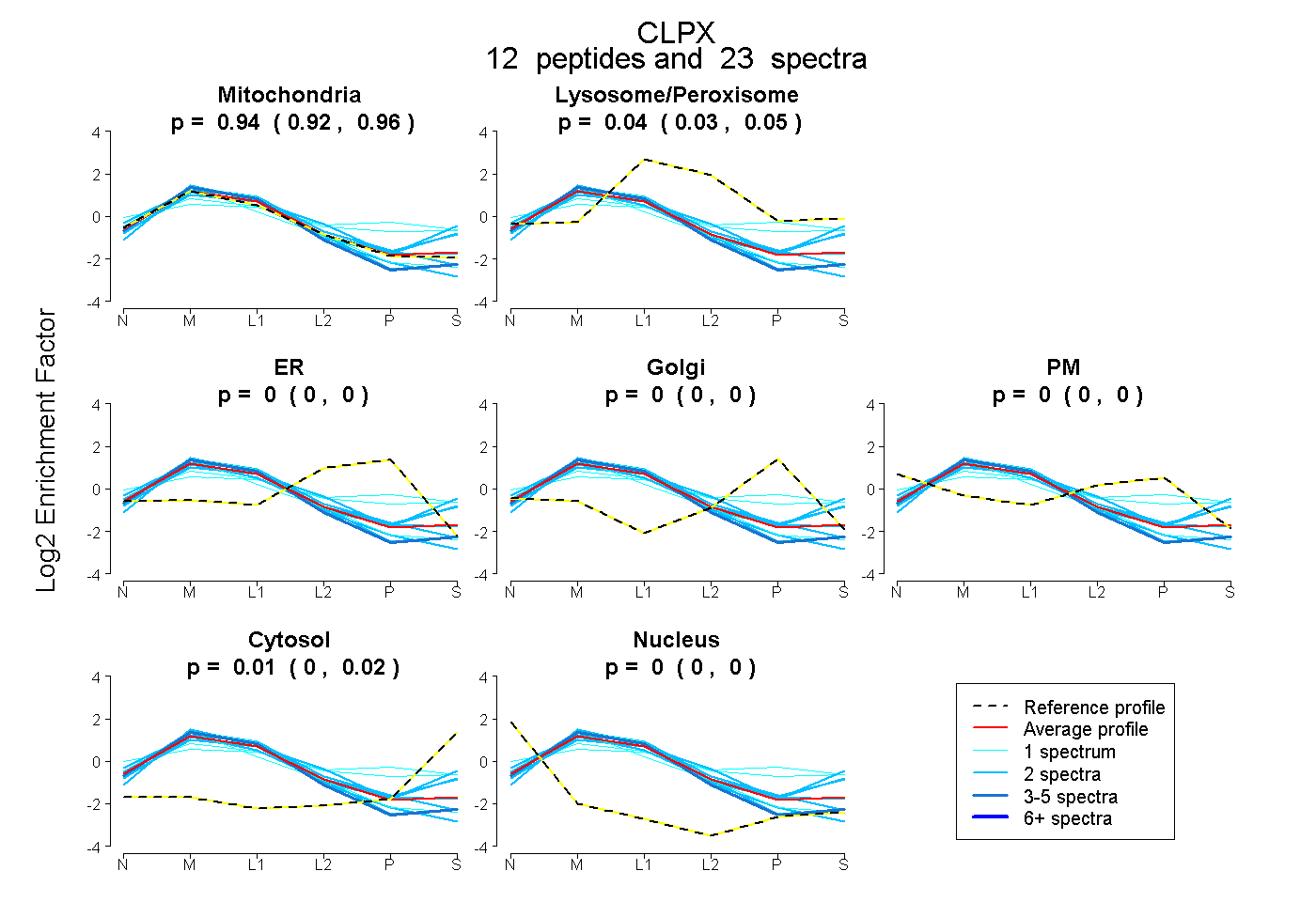
0.923 | 0.962
0.030 | 0.051
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.002 | 0.024
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
40 spectra |
 |
0.997 0.986 | 1.000 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.003 0.000 | 0.012 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
23 spectra |
 |
0.945 0.923 | 0.962 |
0.042 0.030 | 0.051 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.014 0.002 | 0.024 |
0.000 0.000 | 0.000 |
| 2 spectra, IGSVPGIHQLR | 0.737 | 0.153 | 0.000 | 0.000 | 0.000 | 0.109 | 0.000 | |||
| 1 spectrum, SVTEGSSK | 0.977 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.023 | |||
| 2 spectra, QQAEVEK | 0.949 | 0.034 | 0.008 | 0.000 | 0.010 | 0.000 | 0.000 | |||
| 2 spectra, LPVVVPLHSLDEK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CGDLCTHVETFVSSTR | 0.504 | 0.246 | 0.000 | 0.099 | 0.044 | 0.107 | 0.000 | |||
| 1 spectrum, TLLAQTLAK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CELNVTEDALK | 0.347 | 0.267 | 0.000 | 0.116 | 0.174 | 0.096 | 0.000 | |||
| 2 spectra, AAAAADLANR | 0.763 | 0.102 | 0.000 | 0.000 | 0.000 | 0.134 | 0.000 | |||
| 2 spectra, LLQDANYNVEK | 0.621 | 0.225 | 0.000 | 0.000 | 0.000 | 0.153 | 0.000 | |||
| 2 spectra, QTSLTPR | 0.950 | 0.020 | 0.000 | 0.014 | 0.000 | 0.016 | 0.000 | |||
| 2 spectra, IYNNIPANLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, TLVQILTEPR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
198 spectra |
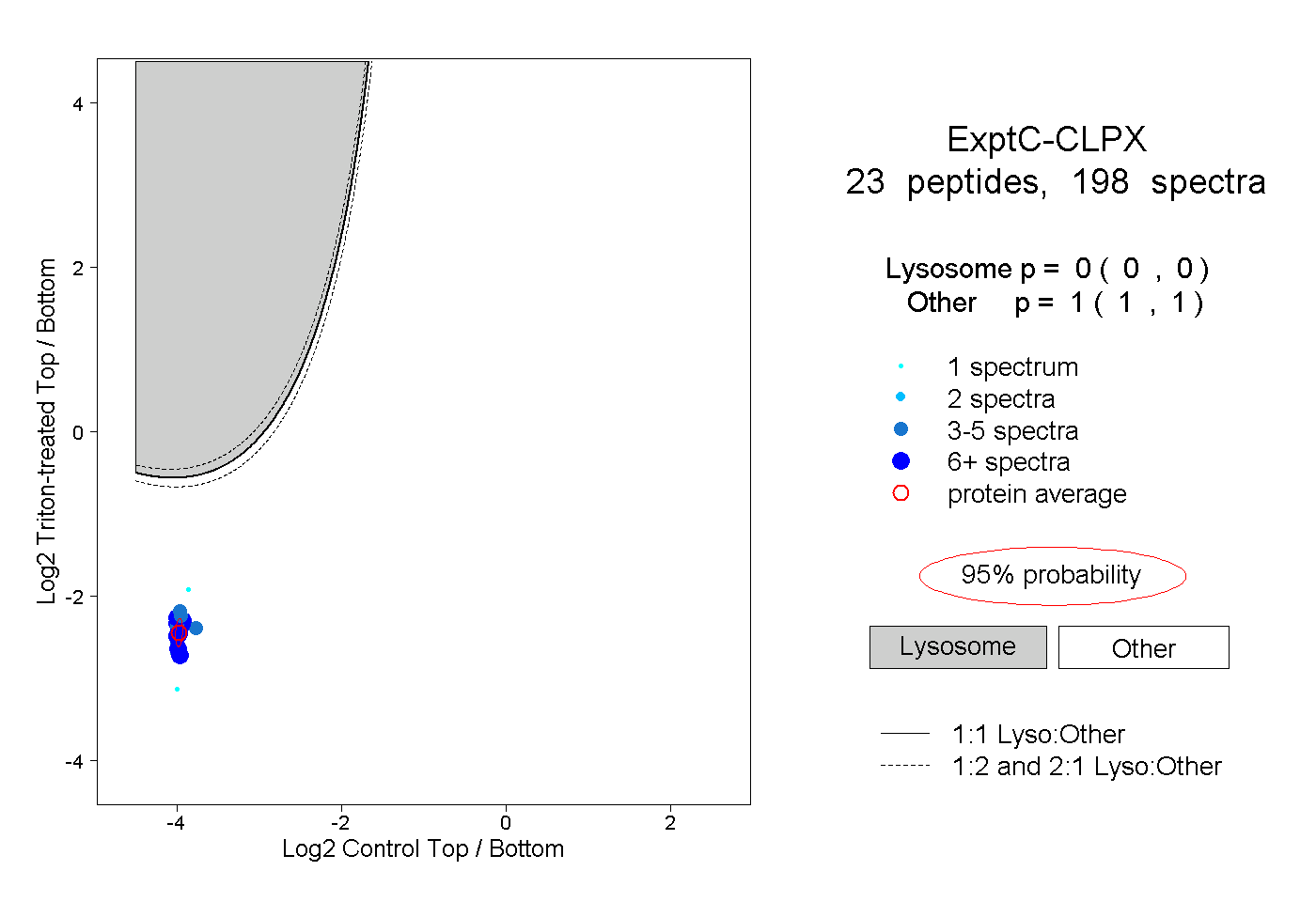 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |