peptides
spectra
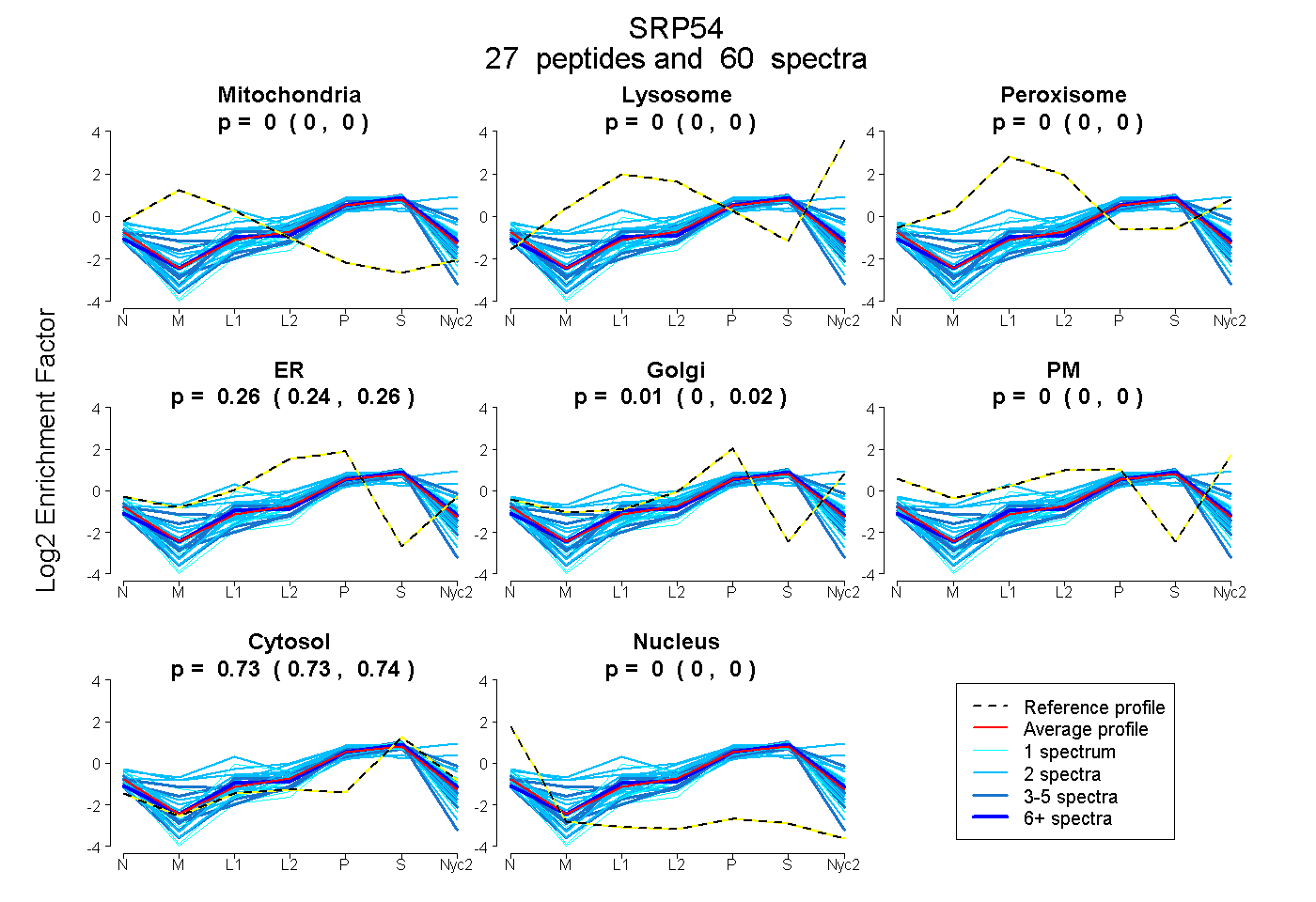
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.242 | 0.265
0.000 | 0.024
0.000 | 0.000
0.730 | 0.737
0.000 | 0.000
peptides
spectra
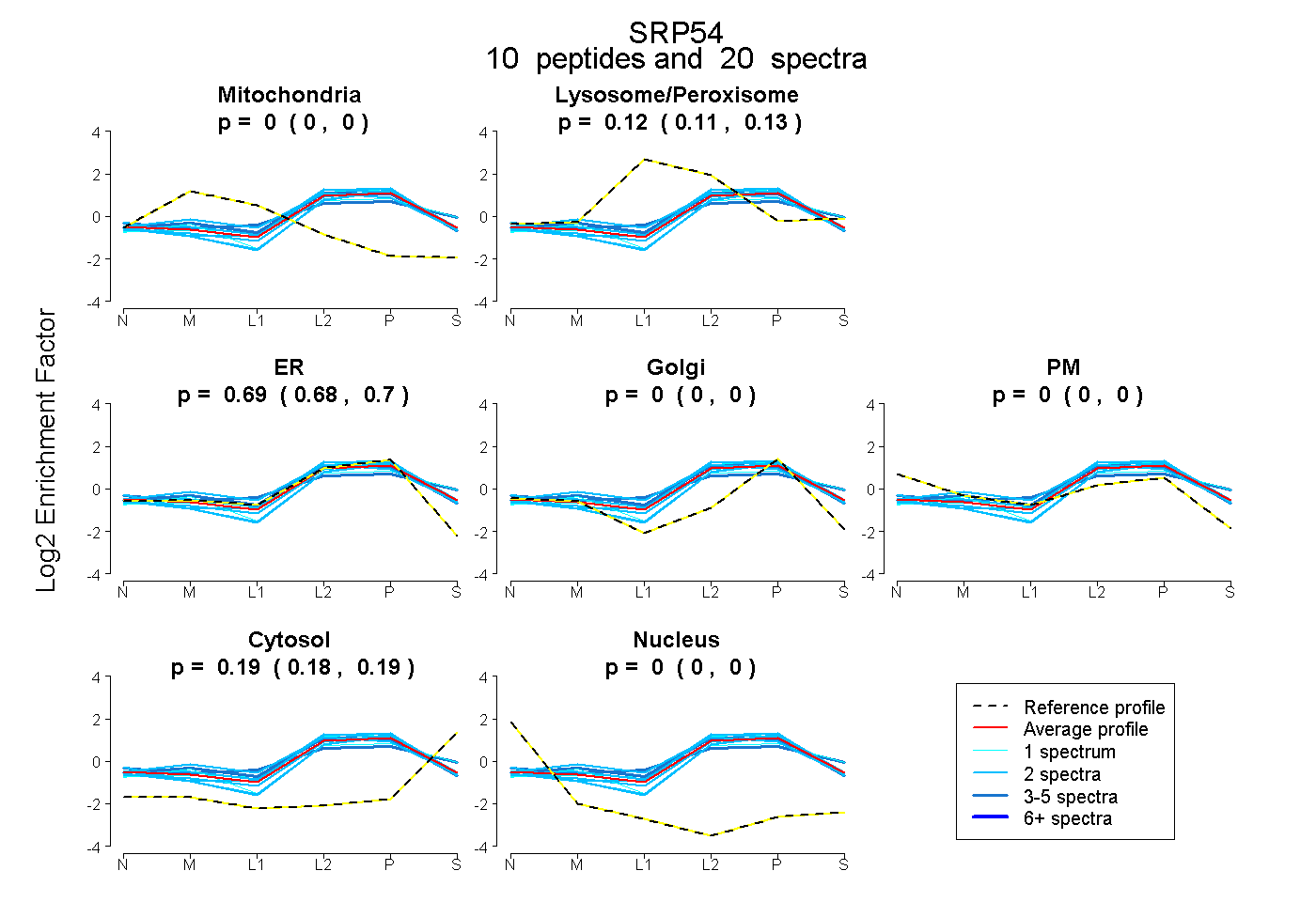
0.000 | 0.000
0.112 | 0.134
0.680 | 0.700
0.000 | 0.000
0.000 | 0.000
0.179 | 0.191
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
60 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.255 0.242 | 0.265 |
0.011 0.000 | 0.024 |
0.000 0.000 | 0.000 |
0.733 0.730 | 0.737 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.123 0.112 | 0.134 |
0.691 0.680 | 0.700 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.186 0.179 | 0.191 |
0.000 0.000 | 0.000 |
| 2 spectra, TCLICADTFR | 0.000 | 0.245 | 0.579 | 0.057 | 0.000 | 0.119 | 0.000 | |||
| 2 spectra, VLADLGR | 0.000 | 0.113 | 0.746 | 0.000 | 0.000 | 0.141 | 0.000 | |||
| 2 spectra, TQPFISK | 0.000 | 0.000 | 0.732 | 0.018 | 0.034 | 0.216 | 0.000 | |||
| 2 spectra, ITSALR | 0.000 | 0.153 | 0.723 | 0.000 | 0.000 | 0.124 | 0.000 | |||
| 3 spectra, HGQFTLR | 0.000 | 0.396 | 0.107 | 0.345 | 0.000 | 0.153 | 0.000 | |||
| 2 spectra, LDGHAK | 0.000 | 0.074 | 0.728 | 0.000 | 0.000 | 0.198 | 0.000 | |||
| 3 spectra, LAYFYQR | 0.000 | 0.171 | 0.689 | 0.000 | 0.000 | 0.141 | 0.000 | |||
| 1 spectrum, AGAFDQLK | 0.000 | 0.150 | 0.720 | 0.000 | 0.000 | 0.130 | 0.000 | |||
| 2 spectra, SPIIFIGTGEHIDDFEPFK | 0.000 | 0.000 | 0.770 | 0.001 | 0.000 | 0.229 | 0.000 | |||
| 1 spectrum, SAIDLEEMASGLNK | 0.000 | 0.070 | 0.630 | 0.000 | 0.000 | 0.300 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
27 spectra |
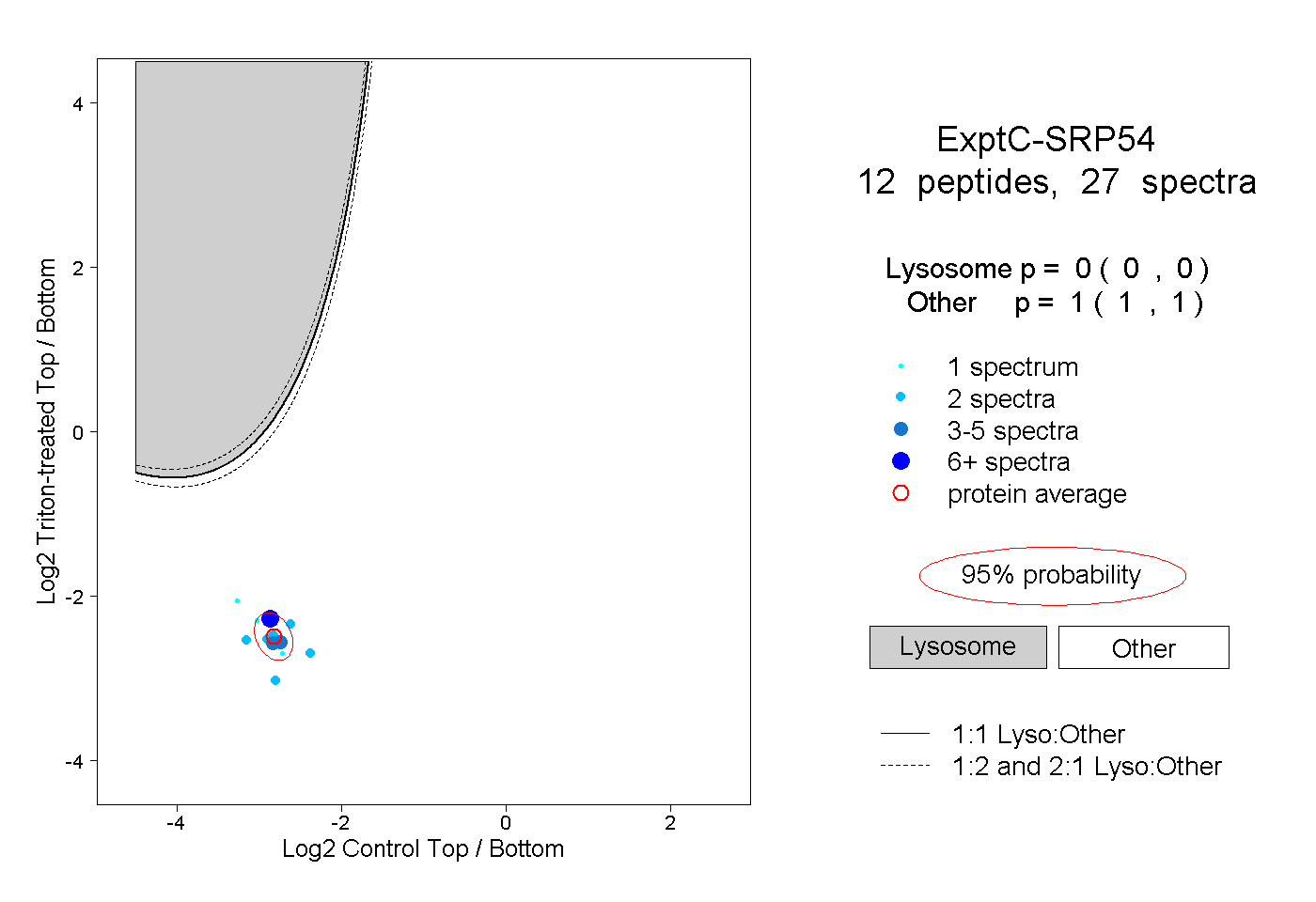 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
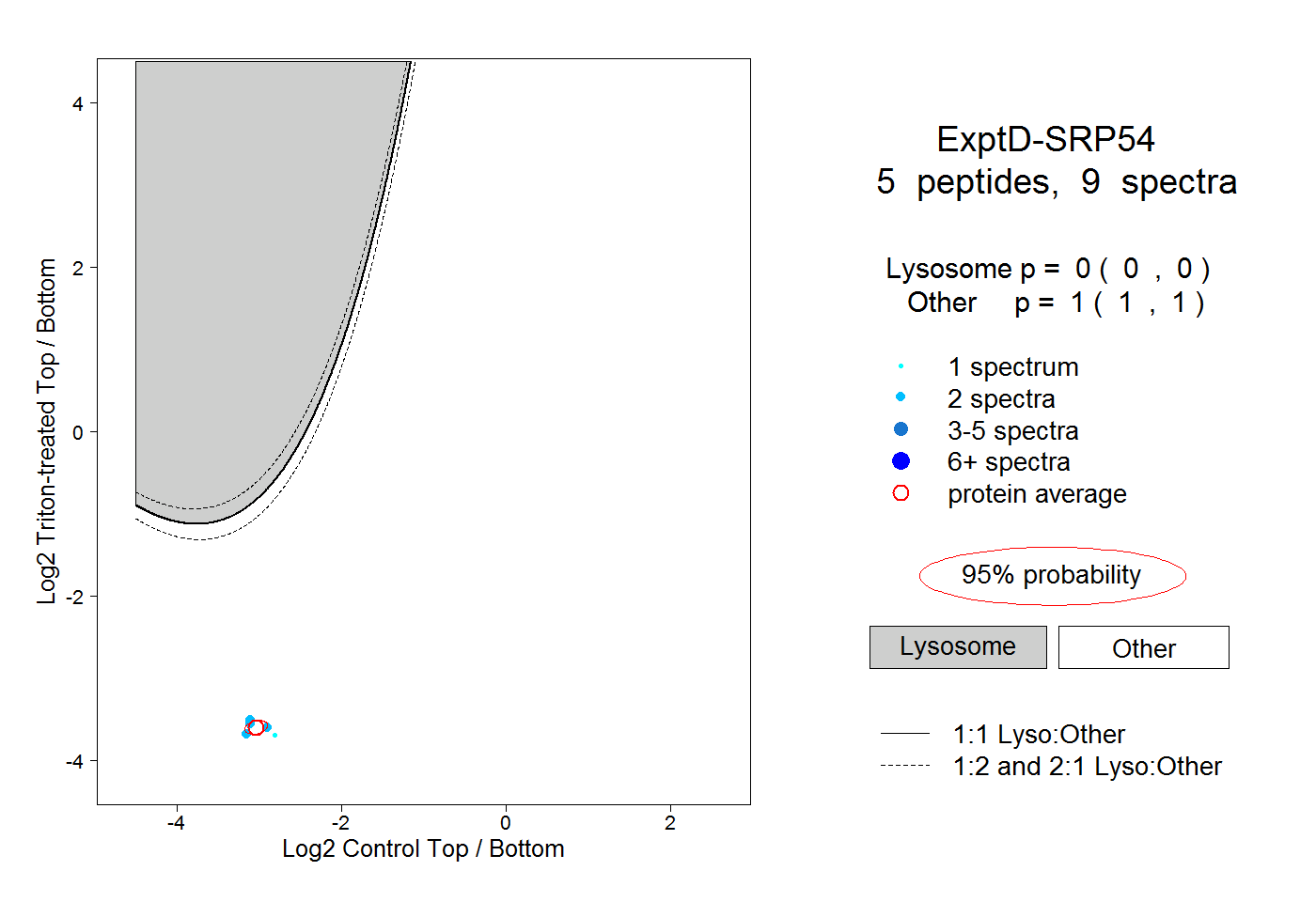 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |