peptides
spectra
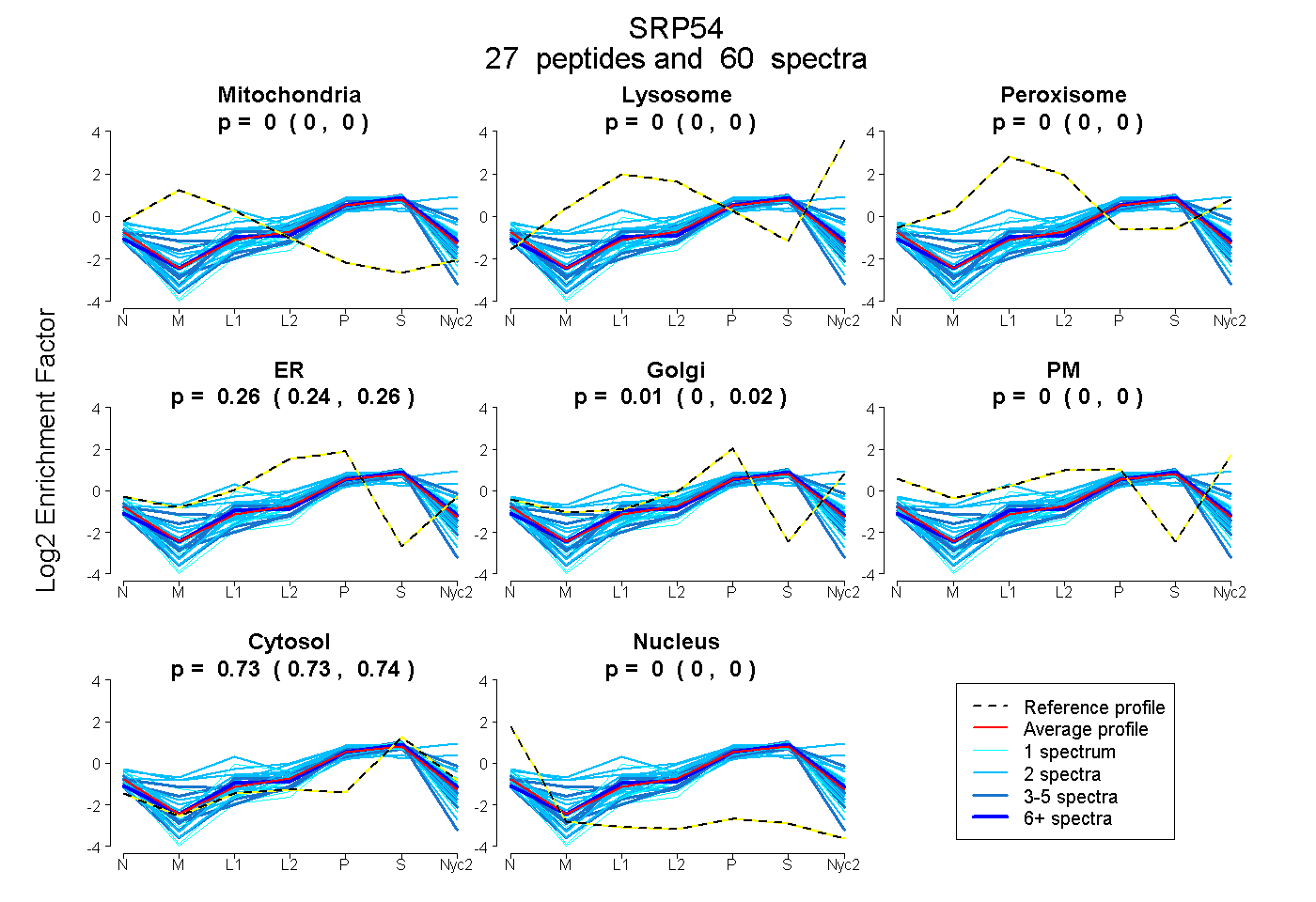
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.242 | 0.265
0.000 | 0.024
0.000 | 0.000
0.730 | 0.737
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
60 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.255 0.242 | 0.265 |
0.011 0.000 | 0.024 |
0.000 0.000 | 0.000 |
0.733 0.730 | 0.737 |
0.000 0.000 | 0.000 |
| 2 spectra, TCLICADTFR | 0.000 | 0.000 | 0.000 | 0.259 | 0.000 | 0.000 | 0.716 | 0.025 | ||
| 1 spectrum, SLSNATIINEEVLNAMLK | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | 0.000 | 0.758 | 0.076 | ||
| 2 spectra, VLADLGR | 0.000 | 0.000 | 0.000 | 0.195 | 0.060 | 0.000 | 0.745 | 0.000 | ||
| 2 spectra, QNVIMFVGLQGSGK | 0.000 | 0.000 | 0.000 | 0.227 | 0.000 | 0.000 | 0.732 | 0.040 | ||
| 1 spectrum, GGDMSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.253 | 0.000 | 0.747 | 0.000 | ||
| 3 spectra, TTTCSK | 0.000 | 0.000 | 0.000 | 0.122 | 0.000 | 0.000 | 0.697 | 0.181 | ||
| 3 spectra, TQPFISK | 0.000 | 0.000 | 0.000 | 0.000 | 0.328 | 0.000 | 0.672 | 0.000 | ||
| 3 spectra, GNEQESMAR | 0.000 | 0.000 | 0.000 | 0.106 | 0.000 | 0.000 | 0.827 | 0.067 | ||
| 2 spectra, HGQFTLR | 0.000 | 0.000 | 0.000 | 0.048 | 0.286 | 0.000 | 0.665 | 0.000 | ||
| 2 spectra, LNQQMAK | 0.000 | 0.004 | 0.222 | 0.000 | 0.348 | 0.065 | 0.361 | 0.000 | ||
| 7 spectra, VLHHMGGMAGLQSMMR | 0.000 | 0.000 | 0.000 | 0.197 | 0.057 | 0.000 | 0.746 | 0.000 | ||
| 2 spectra, AGAFDQLK | 0.000 | 0.000 | 0.000 | 0.266 | 0.000 | 0.000 | 0.734 | 0.000 | ||
| 4 spectra, SAIDLEEMASGLNK | 0.000 | 0.000 | 0.000 | 0.245 | 0.000 | 0.000 | 0.753 | 0.002 | ||
| 2 spectra, VDVASVIVTK | 0.000 | 0.000 | 0.000 | 0.199 | 0.000 | 0.000 | 0.796 | 0.005 | ||
| 2 spectra, DVQELLTQYTK | 0.028 | 0.000 | 0.319 | 0.000 | 0.226 | 0.000 | 0.427 | 0.000 | ||
| 3 spectra, MIQHAVFK | 0.022 | 0.000 | 0.000 | 0.325 | 0.000 | 0.000 | 0.653 | 0.000 | ||
| 1 spectrum, LDDNEALIEK | 0.001 | 0.000 | 0.000 | 0.273 | 0.000 | 0.000 | 0.631 | 0.096 | ||
| 2 spectra, DMYEQFQNIMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.244 | 0.000 | 0.730 | 0.026 | ||
| 2 spectra, FAQMVK | 0.000 | 0.000 | 0.000 | 0.070 | 0.241 | 0.000 | 0.689 | 0.000 | ||
| 2 spectra, GGGALSAVAATK | 0.000 | 0.000 | 0.000 | 0.082 | 0.151 | 0.000 | 0.767 | 0.000 | ||
| 2 spectra, GSGVSTR | 0.000 | 0.101 | 0.000 | 0.000 | 0.254 | 0.116 | 0.529 | 0.000 | ||
| 2 spectra, NVSQSQMAK | 0.000 | 0.000 | 0.000 | 0.293 | 0.019 | 0.000 | 0.688 | 0.000 | ||
| 2 spectra, LVDPGVK | 0.038 | 0.000 | 0.130 | 0.203 | 0.049 | 0.000 | 0.579 | 0.000 | ||
| 1 spectrum, LLGMGDIEGLIDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 | 0.799 | 0.060 | ||
| 3 spectra, LAYFYQR | 0.011 | 0.000 | 0.000 | 0.264 | 0.000 | 0.000 | 0.723 | 0.002 | ||
| 1 spectrum, SPIIFIGTGEHIDDFEPFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.804 | 0.133 | ||
| 1 spectrum, QFQQGAAGNMK | 0.000 | 0.000 | 0.007 | 0.358 | 0.000 | 0.000 | 0.635 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
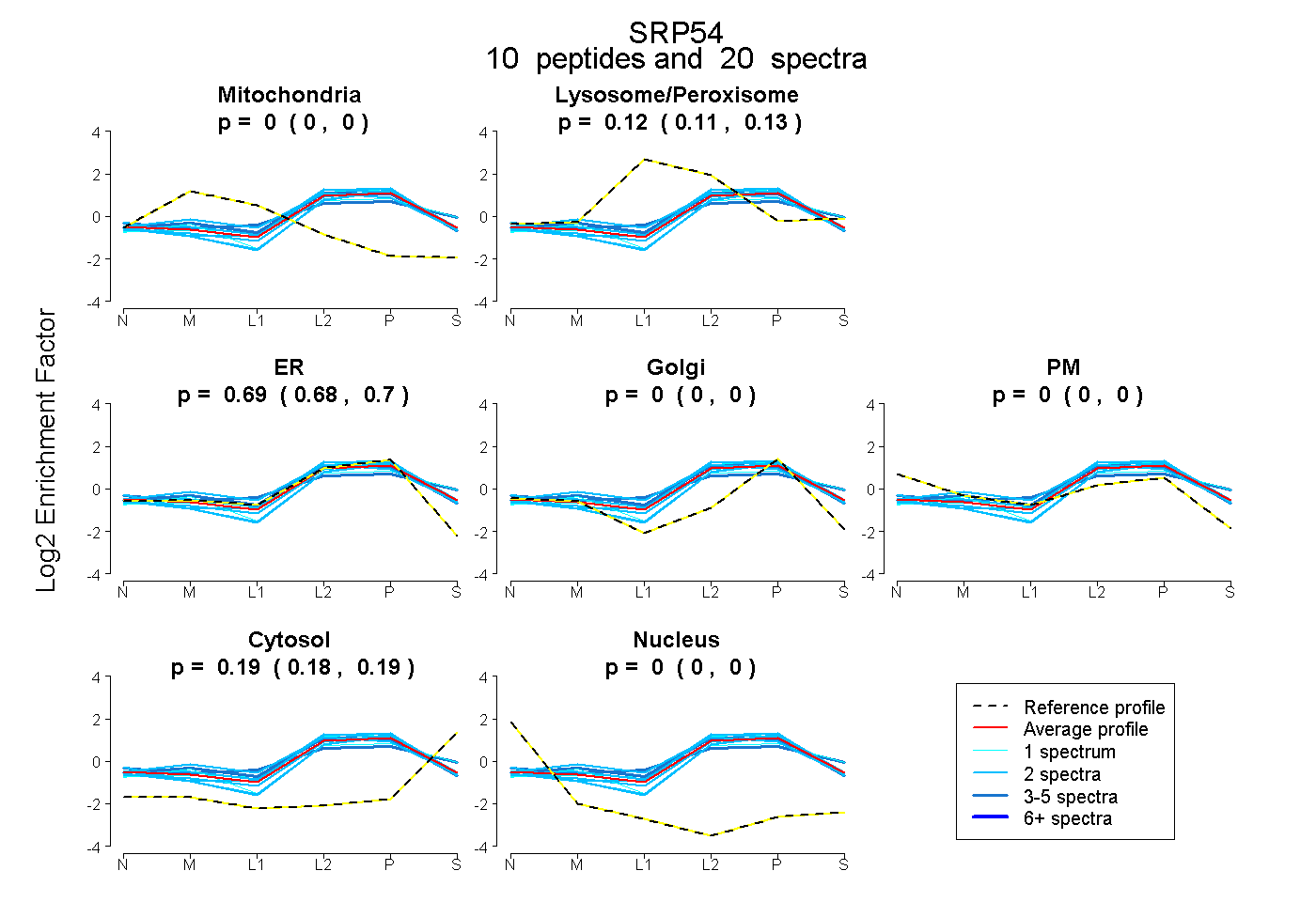 |
0.000 0.000 | 0.000 |
0.123 0.112 | 0.134 |
0.691 0.680 | 0.700 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.186 0.179 | 0.191 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
27 spectra |
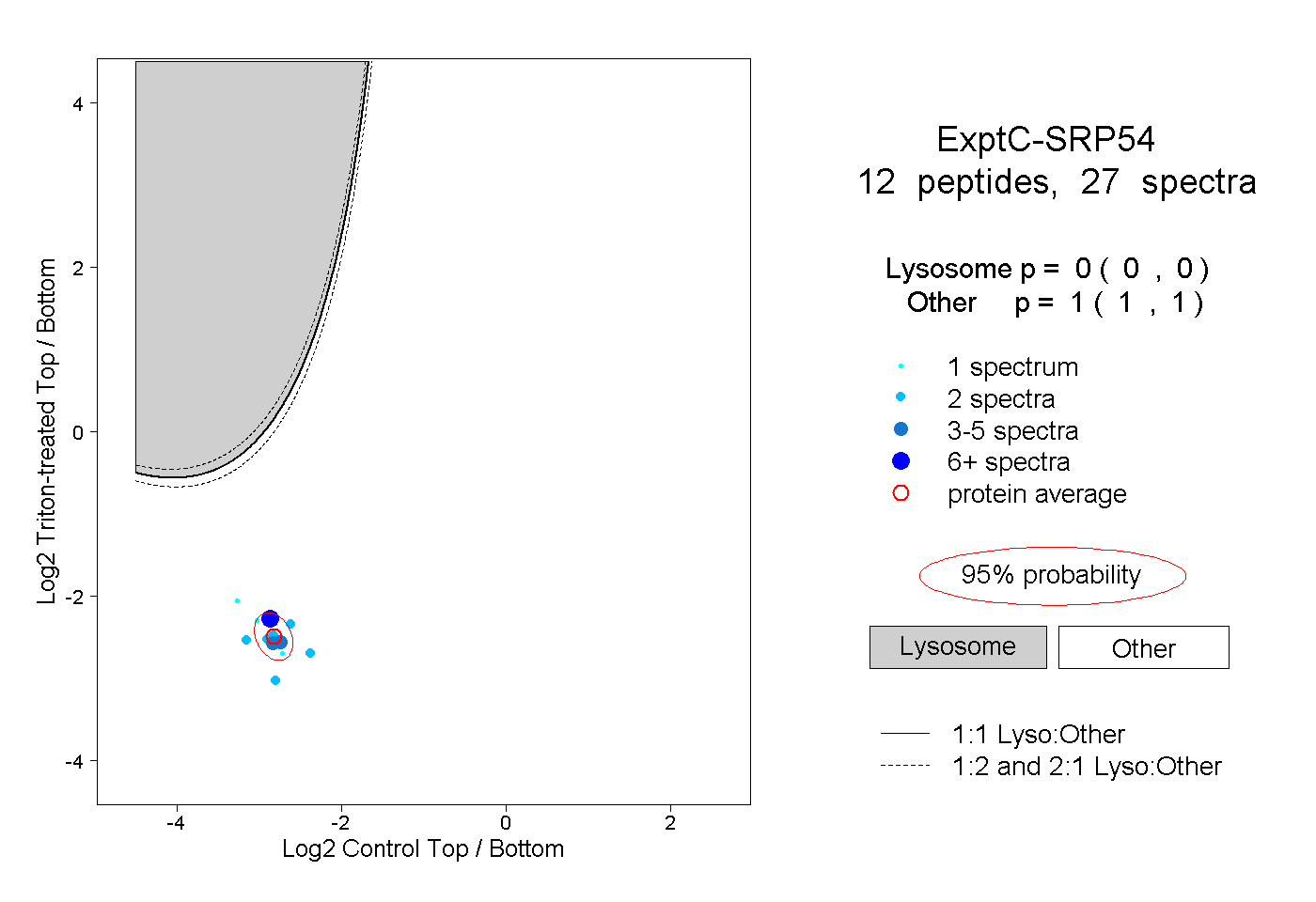 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
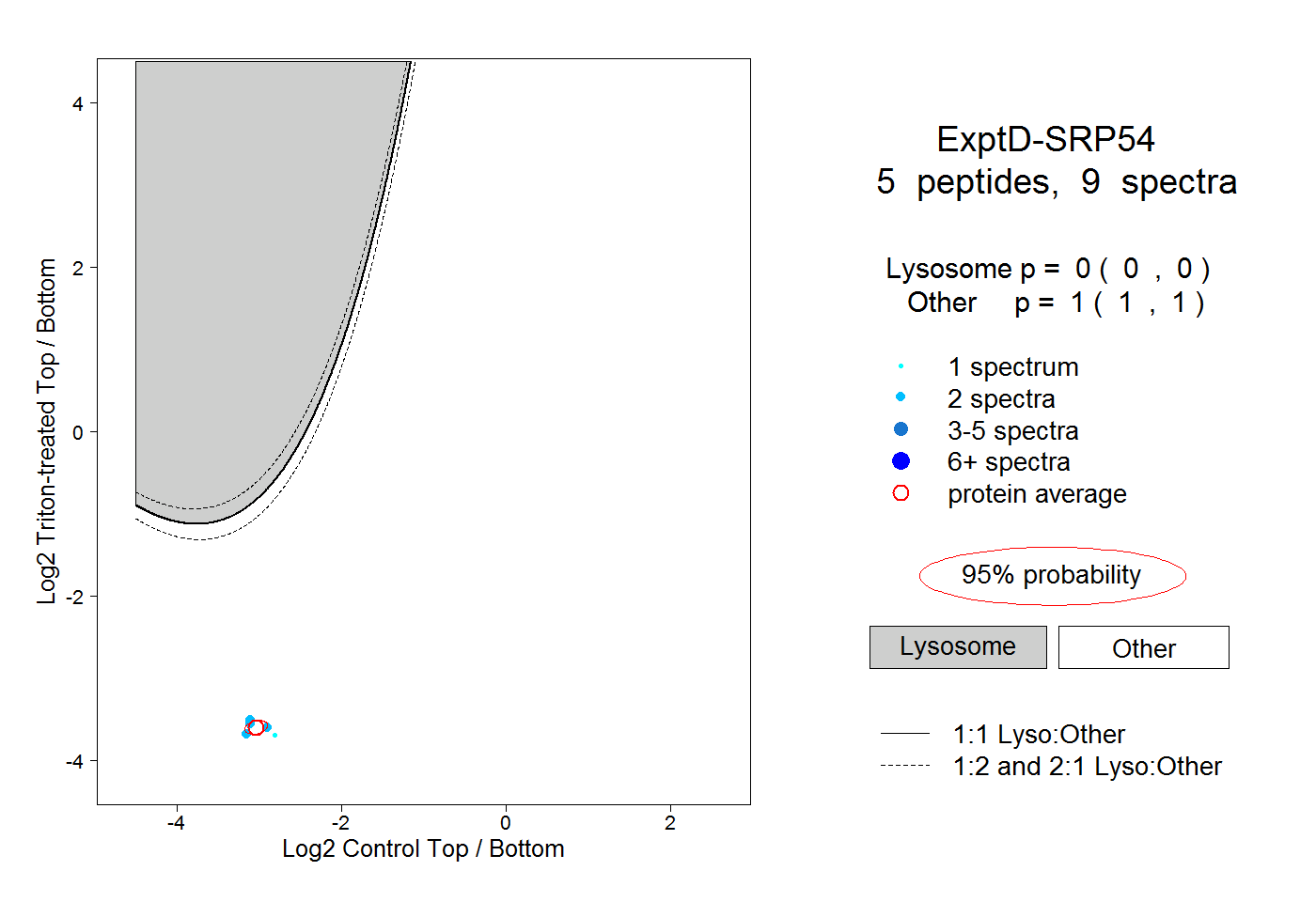 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |