peptides
spectra
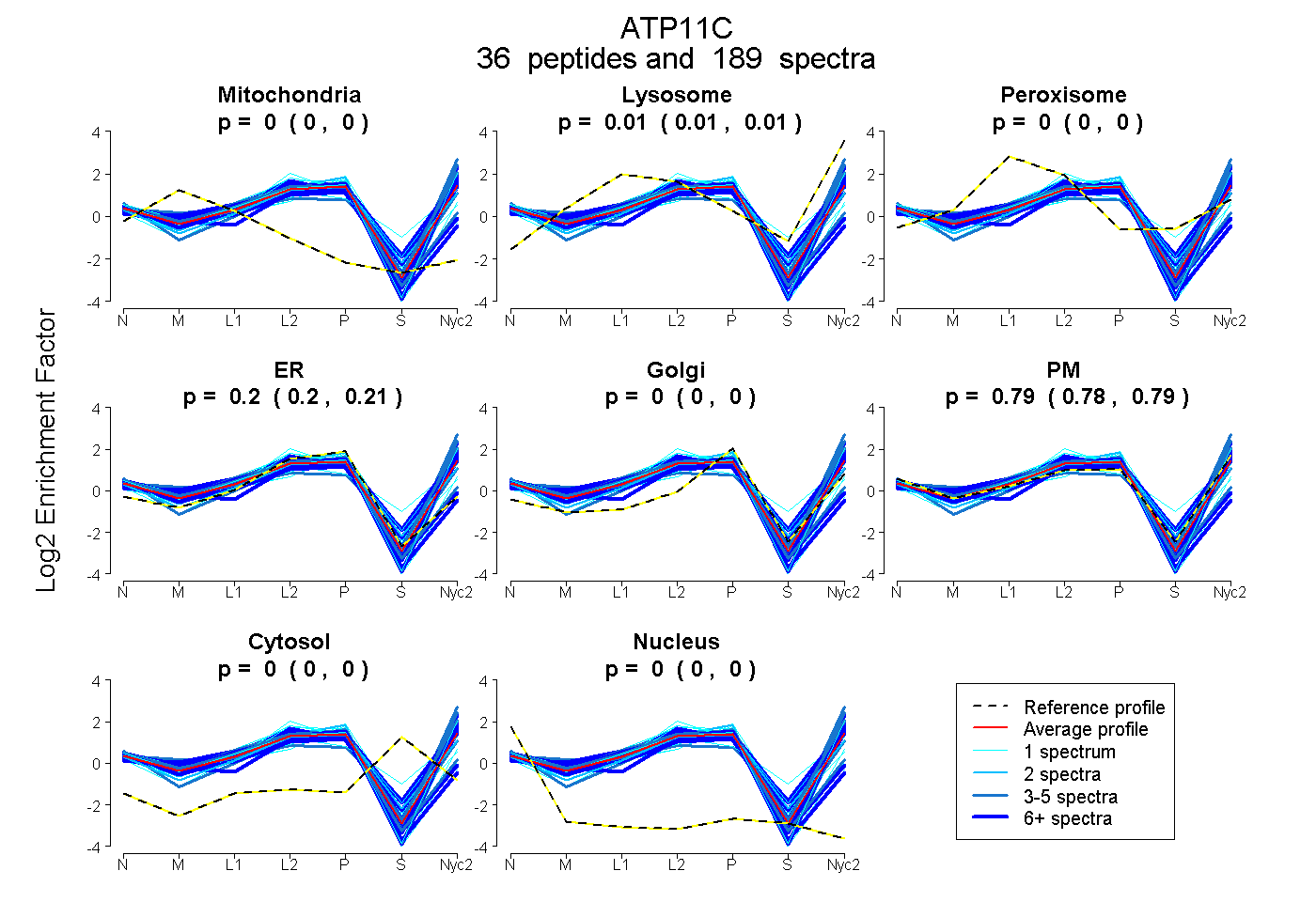
0.000 | 0.000
0.007 | 0.012
0.000 | 0.000
0.199 | 0.210
0.000 | 0.000
0.780 | 0.790
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
189 spectra |
 |
0.000 0.000 | 0.000 |
0.010 0.007 | 0.012 |
0.000 0.000 | 0.000 |
0.205 0.199 | 0.210 |
0.000 0.000 | 0.000 |
0.785 0.780 | 0.790 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, LLLAHGHLYYVR | 0.000 | 0.166 | 0.000 | 0.000 | 0.219 | 0.616 | 0.000 | 0.000 | ||
| 2 spectra, INVQLIEAK | 0.000 | 0.000 | 0.000 | 0.285 | 0.000 | 0.715 | 0.000 | 0.000 | ||
| 7 spectra, TLCVAFK | 0.130 | 0.000 | 0.000 | 0.640 | 0.000 | 0.231 | 0.000 | 0.000 | ||
| 39 spectra, EIPPDDFER | 0.000 | 0.000 | 0.000 | 0.220 | 0.000 | 0.780 | 0.000 | 0.000 | ||
| 4 spectra, VWVLTGDK | 0.000 | 0.101 | 0.000 | 0.050 | 0.000 | 0.849 | 0.000 | 0.000 | ||
| 1 spectrum, CTAVLCCR | 0.119 | 0.000 | 0.000 | 0.743 | 0.000 | 0.138 | 0.000 | 0.000 | ||
| 7 spectra, EIEEYELLHTLNFDSVR | 0.000 | 0.049 | 0.000 | 0.154 | 0.000 | 0.797 | 0.000 | 0.000 | ||
| 3 spectra, TQGGDILLFCK | 0.080 | 0.000 | 0.000 | 0.573 | 0.000 | 0.348 | 0.000 | 0.000 | ||
| 3 spectra, NPNLELPMLLSYK | 0.000 | 0.000 | 0.000 | 0.325 | 0.076 | 0.593 | 0.000 | 0.006 | ||
| 4 spectra, QGYEDWLR | 0.000 | 0.075 | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | 0.000 | ||
| 10 spectra, LHELLIEYR | 0.000 | 0.038 | 0.000 | 0.146 | 0.000 | 0.816 | 0.000 | 0.000 | ||
| 4 spectra, LQDQAAETIEALHAAGLK | 0.000 | 0.008 | 0.000 | 0.119 | 0.000 | 0.873 | 0.000 | 0.000 | ||
| 2 spectra, VHSHEIDLTK | 0.000 | 0.011 | 0.000 | 0.325 | 0.000 | 0.625 | 0.038 | 0.000 | ||
| 6 spectra, ISIYSNSIEAVAR | 0.000 | 0.016 | 0.000 | 0.028 | 0.000 | 0.957 | 0.000 | 0.000 | ||
| 6 spectra, STVYIIENAK | 0.000 | 0.052 | 0.000 | 0.099 | 0.038 | 0.812 | 0.000 | 0.000 | ||
| 4 spectra, SLGPENLLLK | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | 0.937 | 0.000 | 0.000 | ||
| 13 spectra, NAMDGYR | 0.000 | 0.152 | 0.000 | 0.174 | 0.073 | 0.601 | 0.000 | 0.000 | ||
| 8 spectra, NSDYSVPK | 0.000 | 0.130 | 0.000 | 0.016 | 0.097 | 0.718 | 0.038 | 0.000 | ||
| 4 spectra, GADSSIFPR | 0.000 | 0.000 | 0.000 | 0.141 | 0.000 | 0.859 | 0.000 | 0.000 | ||
| 1 spectrum, LFQTNTELLELTTK | 0.000 | 0.005 | 0.000 | 0.013 | 0.000 | 0.982 | 0.000 | 0.000 | ||
| 1 spectrum, THYAVR | 0.000 | 0.027 | 0.000 | 0.214 | 0.000 | 0.759 | 0.000 | 0.000 | ||
| 1 spectrum, YTLWNFLPK | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | 0.954 | 0.000 | 0.000 | ||
| 1 spectrum, MALQDR | 0.000 | 0.000 | 0.246 | 0.000 | 0.000 | 0.654 | 0.100 | 0.000 | ||
| 10 spectra, TIEESER | 0.000 | 0.000 | 0.000 | 0.178 | 0.000 | 0.822 | 0.000 | 0.000 | ||
| 6 spectra, MSVIVR | 0.000 | 0.050 | 0.000 | 0.141 | 0.000 | 0.808 | 0.000 | 0.000 | ||
| 2 spectra, LLHEFPK | 0.000 | 0.064 | 0.000 | 0.096 | 0.087 | 0.753 | 0.000 | 0.000 | ||
| 3 spectra, MALNYQGK | 0.000 | 0.087 | 0.000 | 0.000 | 0.000 | 0.913 | 0.000 | 0.000 | ||
| 4 spectra, ADNEVNK | 0.067 | 0.080 | 0.056 | 0.000 | 0.002 | 0.764 | 0.032 | 0.000 | ||
| 13 spectra, TVFVGNHPISGTEAYIAQR | 0.000 | 0.092 | 0.023 | 0.070 | 0.000 | 0.815 | 0.000 | 0.000 | ||
| 1 spectrum, IYGVAVYTGMETK | 0.000 | 0.173 | 0.000 | 0.031 | 0.000 | 0.796 | 0.000 | 0.000 | ||
| 6 spectra, STCYACR | 0.065 | 0.000 | 0.000 | 0.760 | 0.000 | 0.115 | 0.000 | 0.060 | ||
| 1 spectrum, TGTLTENSMEFIECCIDGHK | 0.000 | 0.065 | 0.000 | 0.222 | 0.000 | 0.712 | 0.000 | 0.000 | ||
| 1 spectrum, AAIECEQPQPDLYK | 0.000 | 0.000 | 0.056 | 0.364 | 0.374 | 0.204 | 0.000 | 0.002 | ||
| 1 spectrum, DTIELCTAESIDNLR | 0.000 | 0.000 | 0.000 | 0.577 | 0.000 | 0.423 | 0.000 | 0.000 | ||
| 1 spectrum, AAVCTTLK | 0.051 | 0.000 | 0.000 | 0.610 | 0.141 | 0.184 | 0.000 | 0.015 | ||
| 8 spectra, NLFEQFR | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.918 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
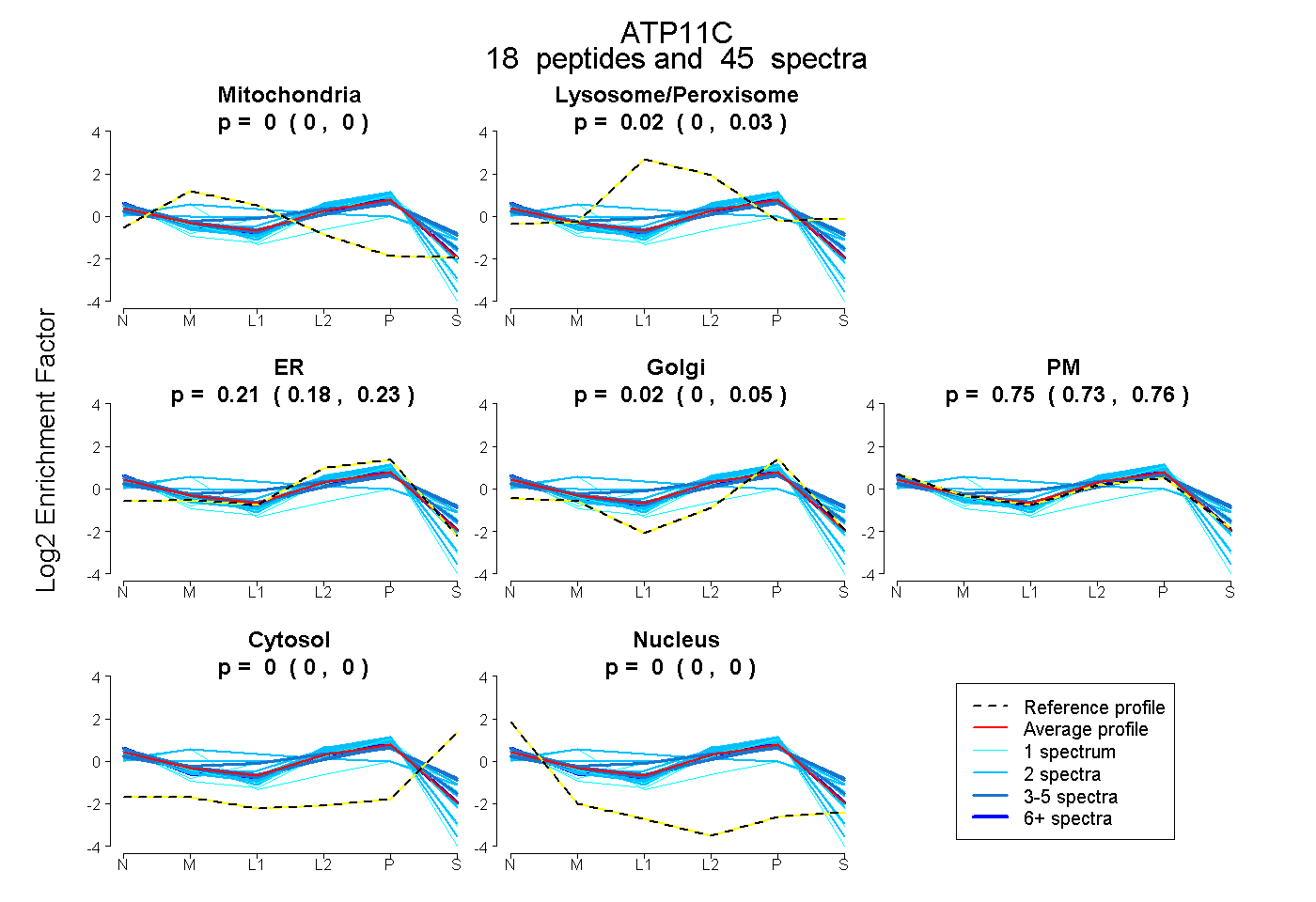 |
0.000 0.000 | 0.004 |
0.017 0.000 | 0.029 |
0.208 0.180 | 0.232 |
0.025 0.000 | 0.045 |
0.750 0.733 | 0.762 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
303 spectra |
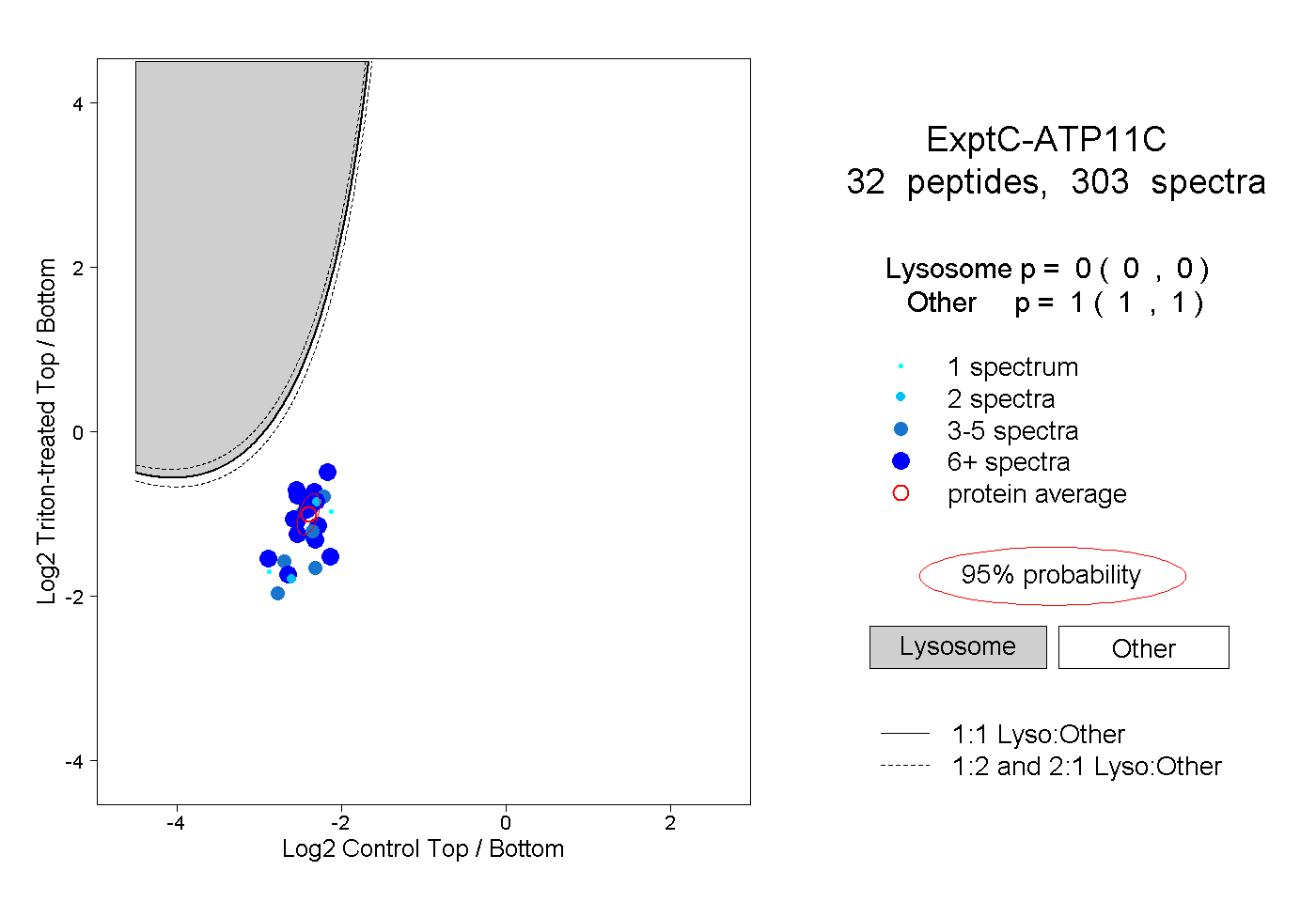 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
55 spectra |
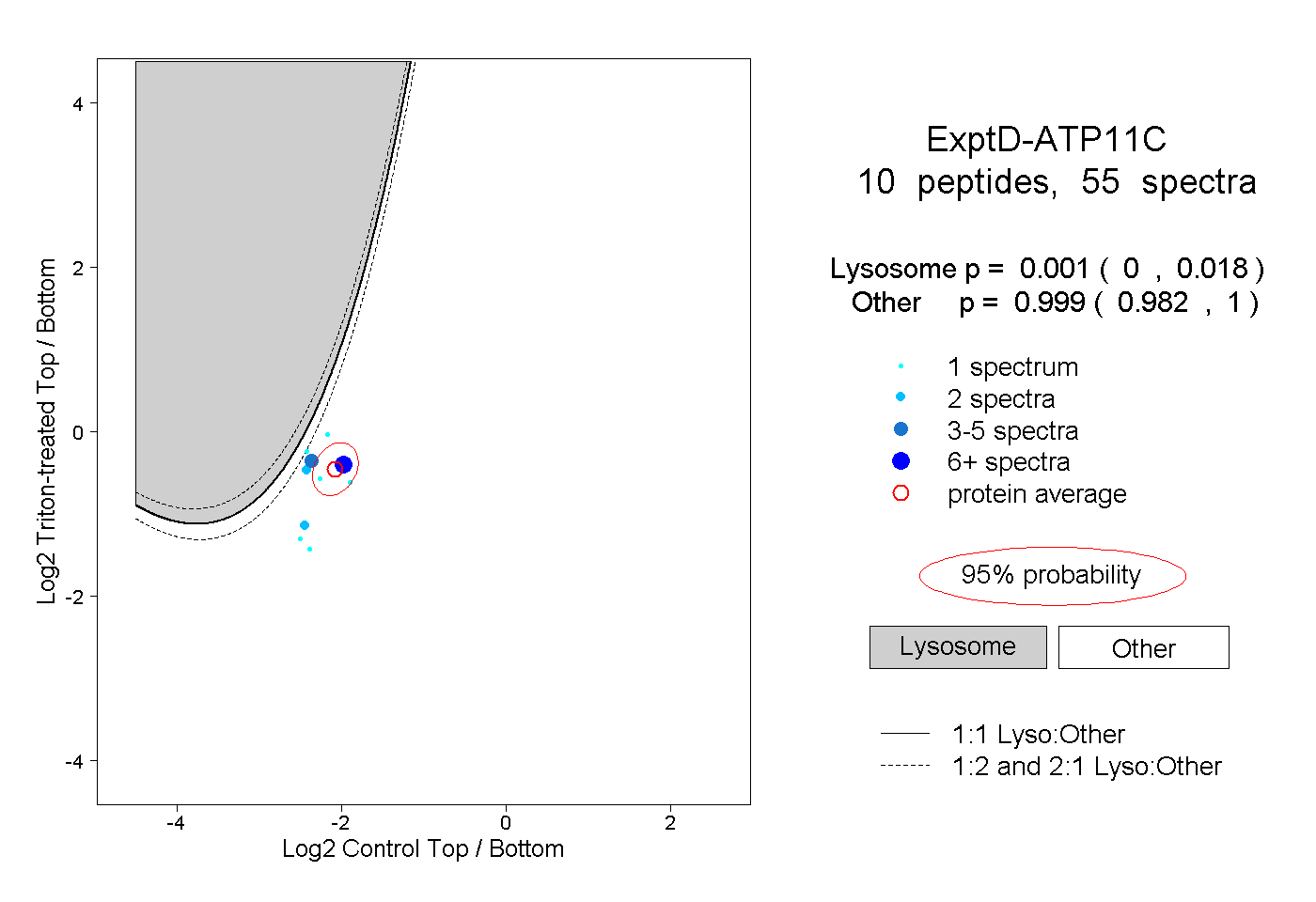 |
0.001 0.000 | 0.018 |
0.999 0.982 | 1.000 |