peptides
spectra
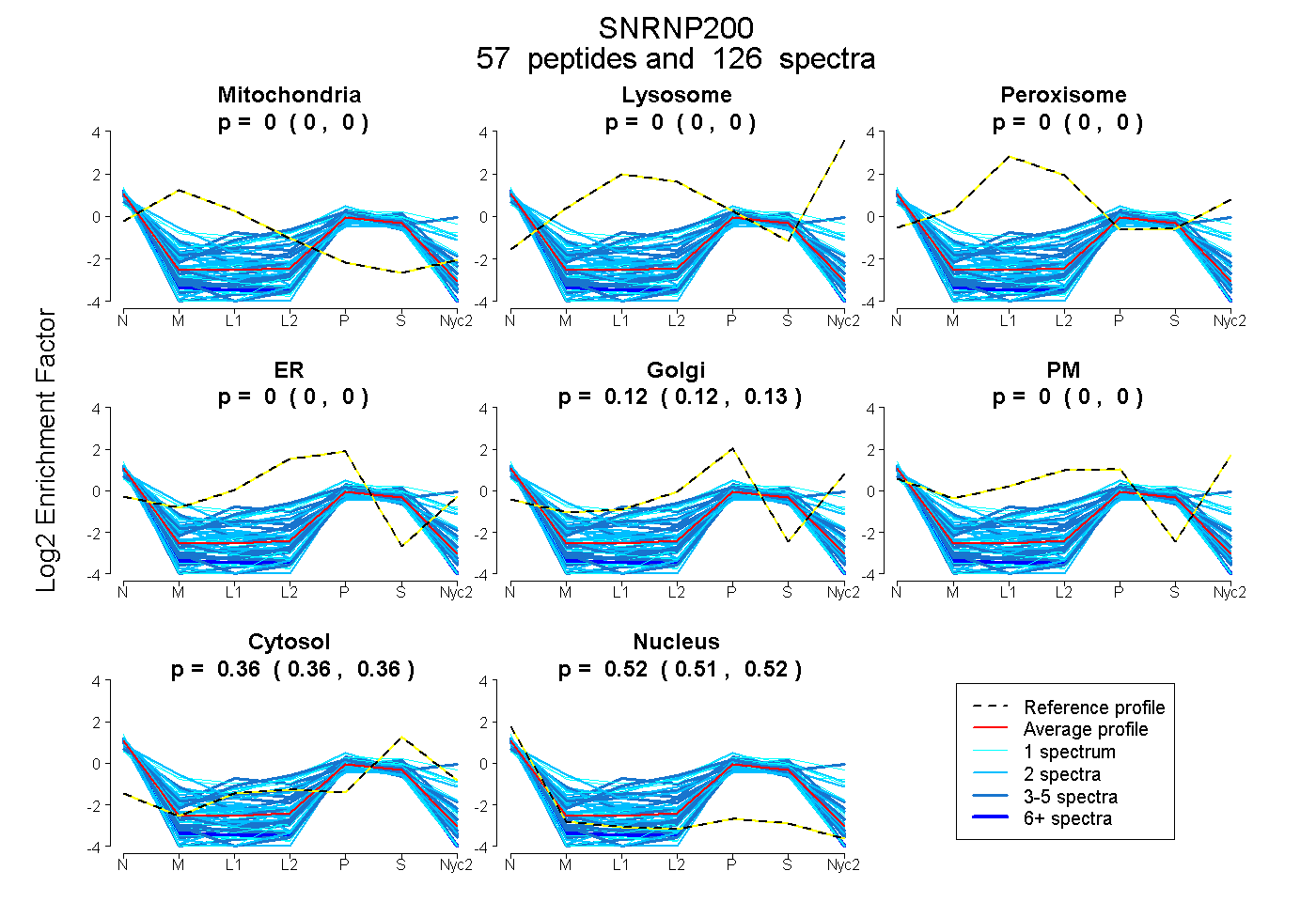
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.122 | 0.126
0.000 | 0.000
0.358 | 0.361
0.514 | 0.518
peptides
spectra
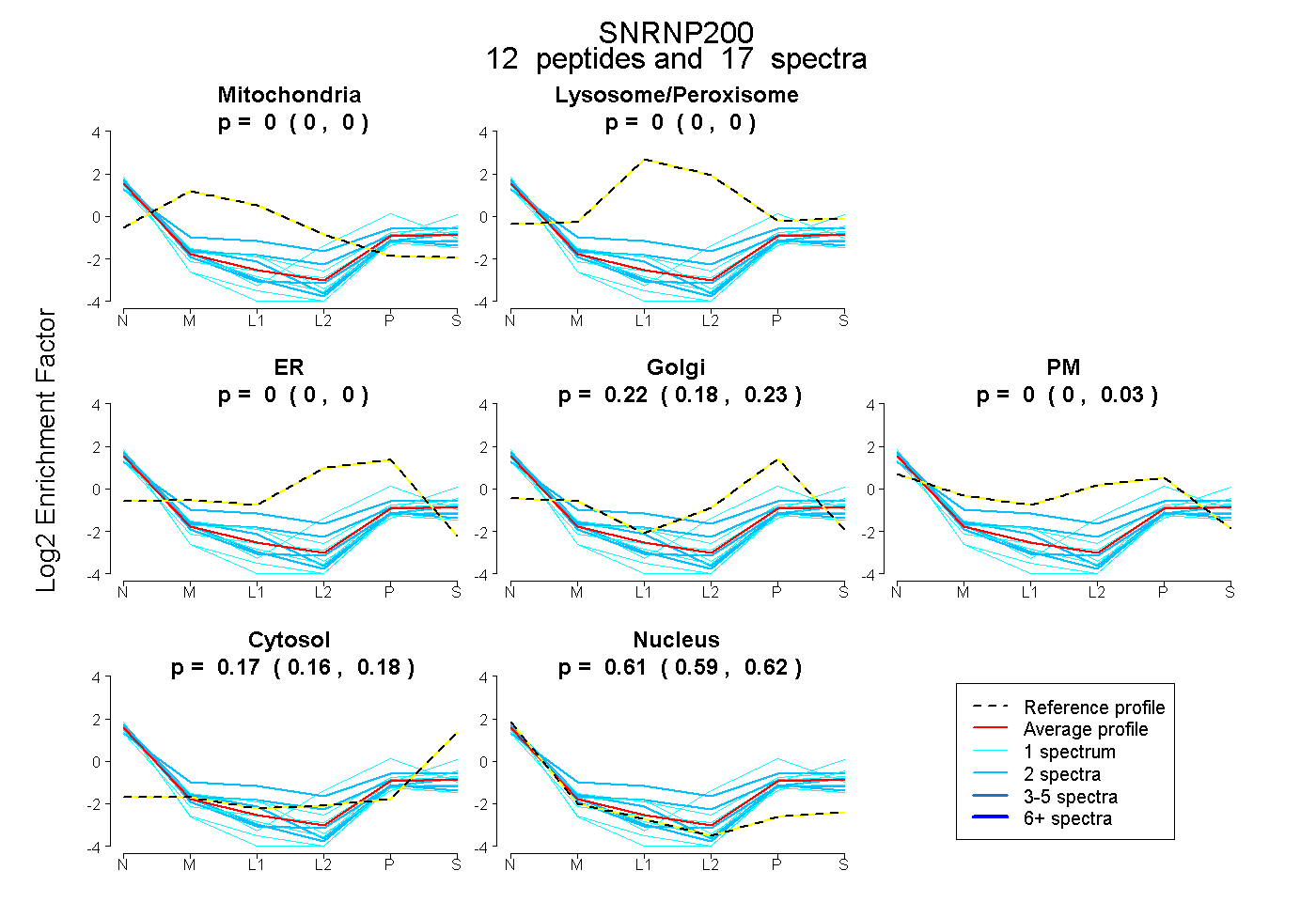
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.182 | 0.225
0.000 | 0.034
0.161 | 0.182
0.594 | 0.622
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
126 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.125 0.122 | 0.126 |
0.000 0.000 | 0.000 |
0.360 0.358 | 0.361 |
0.516 0.514 | 0.518 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.217 0.182 | 0.225 |
0.000 0.000 | 0.034 |
0.172 0.161 | 0.182 |
0.611 0.594 | 0.622 |
| 1 spectrum, GDPLLDQR | 0.000 | 0.000 | 0.000 | 0.010 | 0.286 | 0.242 | 0.461 | |||
| 1 spectrum, TLVEDLFADK | 0.000 | 0.000 | 0.000 | 0.107 | 0.014 | 0.378 | 0.500 | |||
| 2 spectra, NQVLVFVHSR | 0.000 | 0.110 | 0.000 | 0.000 | 0.381 | 0.170 | 0.339 | |||
| 1 spectrum, DILCGAADEVLAVLK | 0.000 | 0.000 | 0.000 | 0.536 | 0.018 | 0.080 | 0.366 | |||
| 1 spectrum, YVHLFPK | 0.000 | 0.056 | 0.000 | 0.000 | 0.037 | 0.264 | 0.643 | |||
| 2 spectra, EGSASTEVLR | 0.000 | 0.002 | 0.000 | 0.195 | 0.000 | 0.078 | 0.725 | |||
| 2 spectra, TGNFQVTELGR | 0.000 | 0.000 | 0.000 | 0.178 | 0.000 | 0.113 | 0.709 | |||
| 2 spectra, KPVIVFVPSR | 0.000 | 0.005 | 0.000 | 0.000 | 0.328 | 0.176 | 0.491 | |||
| 1 spectrum, DTLGLFLR | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.142 | 0.815 | |||
| 1 spectrum, IIYIAPMR | 0.000 | 0.000 | 0.000 | 0.156 | 0.000 | 0.192 | 0.651 | |||
| 1 spectrum, ADEVLEILK | 0.000 | 0.000 | 0.000 | 0.052 | 0.000 | 0.074 | 0.874 | |||
| 2 spectra, EEGWWVVIGDAK | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.192 | 0.703 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7 spectra |
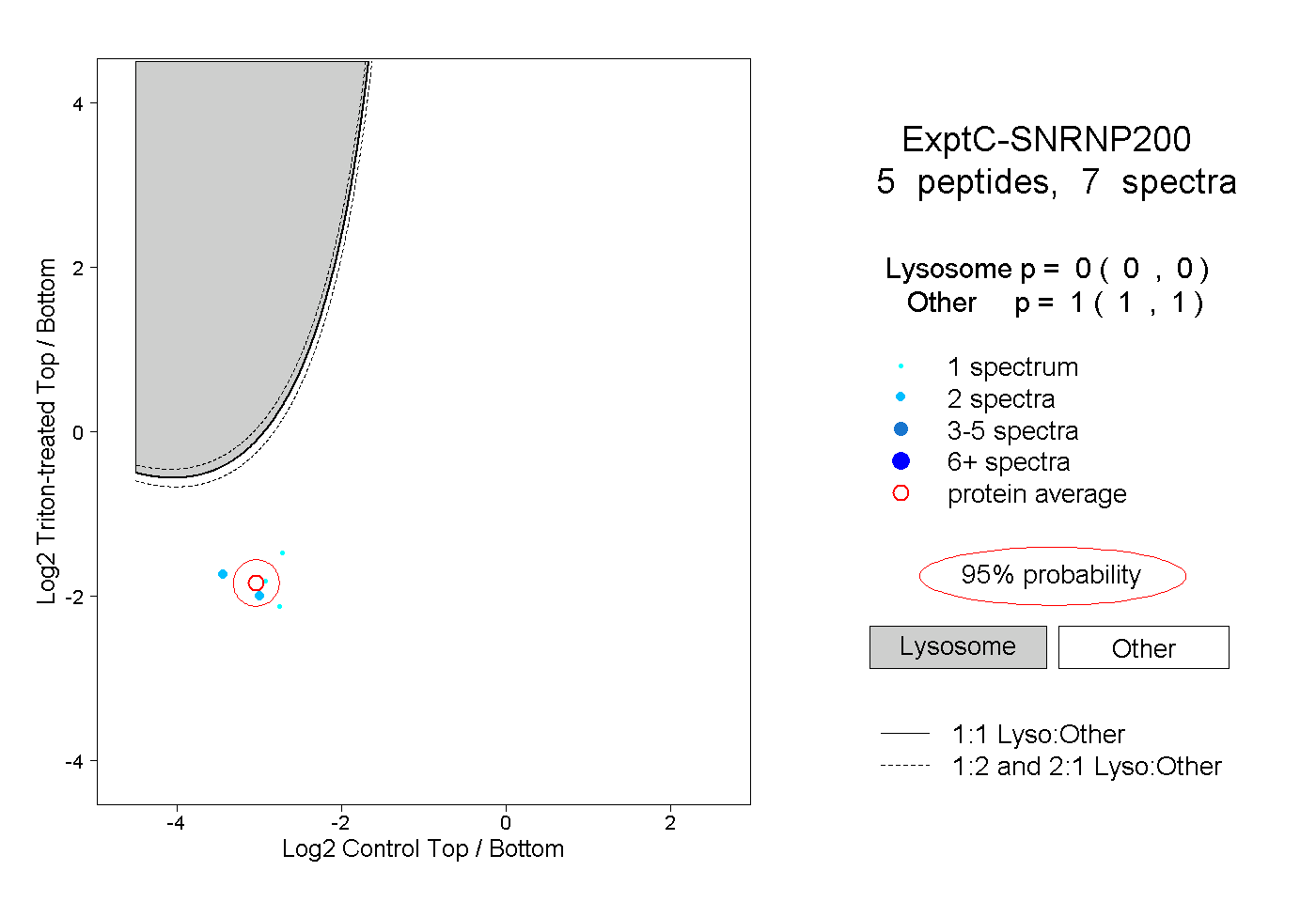 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
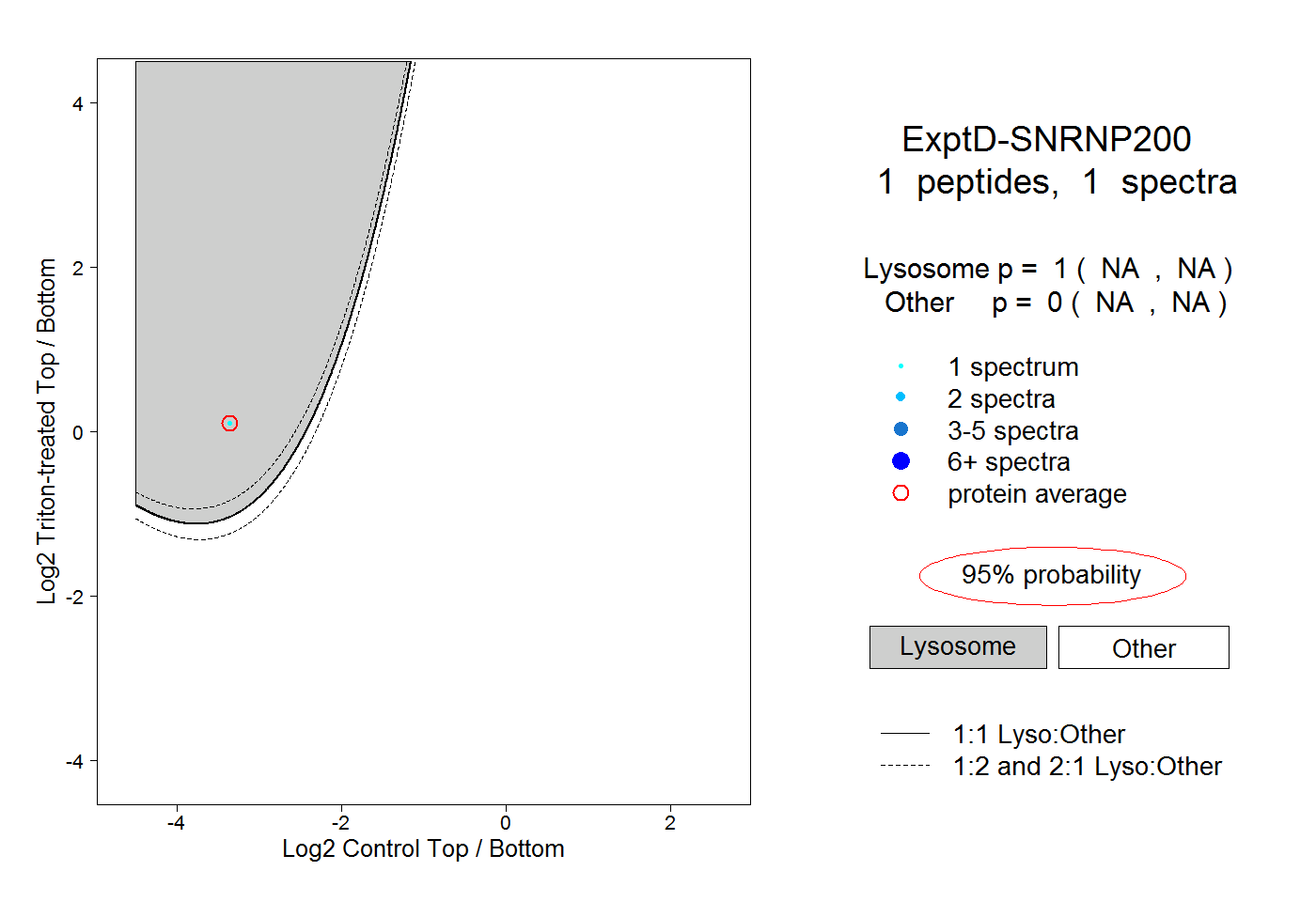 |
1.000 NA | NA |
0.000 NA | NA |