peptides
spectra
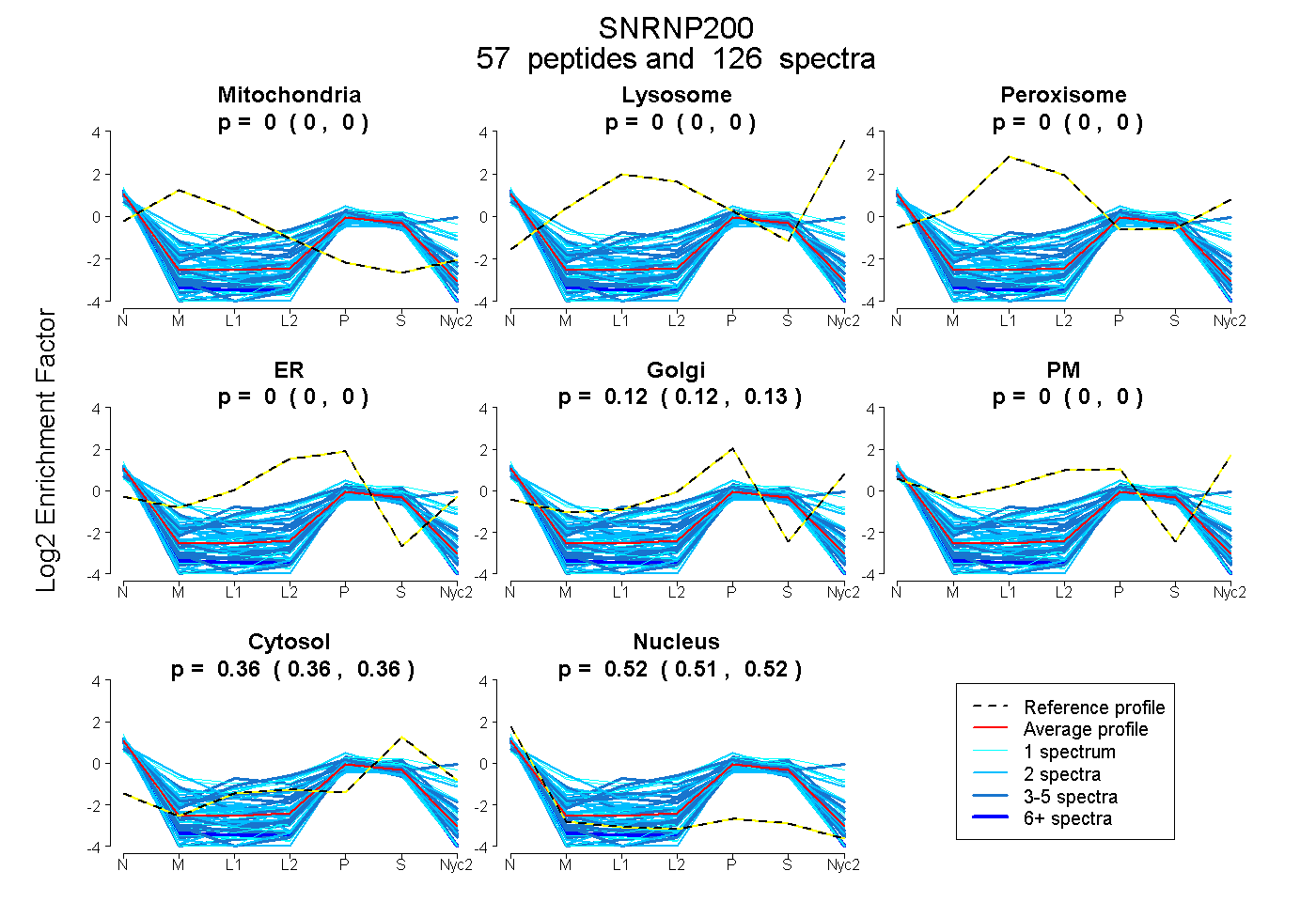
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.122 | 0.126
0.000 | 0.000
0.358 | 0.361
0.514 | 0.518
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
126 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.125 0.122 | 0.126 |
0.000 0.000 | 0.000 |
0.360 0.358 | 0.361 |
0.516 0.514 | 0.518 |
| 2 spectra, FLHCTEK | 0.000 | 0.000 | 0.000 | 0.221 | 0.118 | 0.104 | 0.367 | 0.190 | ||
| 2 spectra, SGGPVVVLVQLER | 0.074 | 0.000 | 0.000 | 0.074 | 0.000 | 0.000 | 0.300 | 0.552 | ||
| 2 spectra, DLIPYLEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.323 | 0.677 | ||
| 2 spectra, AGRPQYDTK | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | 0.000 | 0.382 | 0.547 | ||
| 4 spectra, WDIITR | 0.000 | 0.000 | 0.000 | 0.000 | 0.033 | 0.000 | 0.368 | 0.599 | ||
| 2 spectra, NFPFER | 0.000 | 0.000 | 0.000 | 0.094 | 0.000 | 0.000 | 0.289 | 0.617 | ||
| 3 spectra, HINMDGTINVDDFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | 0.362 | 0.566 | ||
| 2 spectra, AIFEIVLNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.290 | 0.710 | ||
| 4 spectra, DTLGLFLR | 0.000 | 0.000 | 0.000 | 0.309 | 0.000 | 0.000 | 0.289 | 0.402 | ||
| 2 spectra, NSAFESLYQDK | 0.000 | 0.000 | 0.000 | 0.180 | 0.014 | 0.000 | 0.337 | 0.469 | ||
| 1 spectrum, MTQNPNYYNLQGISHR | 0.120 | 0.000 | 0.000 | 0.080 | 0.073 | 0.221 | 0.425 | 0.082 | ||
| 7 spectra, IIYIAPMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.316 | 0.684 | ||
| 1 spectrum, IVALSSSLSNAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.271 | 0.729 | ||
| 1 spectrum, GWAQLTDK | 0.000 | 0.000 | 0.000 | 0.001 | 0.006 | 0.000 | 0.484 | 0.509 | ||
| 3 spectra, GTQVYSPEK | 0.000 | 0.000 | 0.123 | 0.224 | 0.000 | 0.000 | 0.308 | 0.344 | ||
| 1 spectrum, FSVDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.099 | 0.000 | 0.422 | 0.478 | ||
| 3 spectra, ANSNLVLQADR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.310 | 0.690 | ||
| 3 spectra, TKPQMQEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.174 | 0.000 | 0.338 | 0.488 | ||
| 3 spectra, VVLLTGETSTDLK | 0.000 | 0.000 | 0.000 | 0.155 | 0.063 | 0.000 | 0.390 | 0.392 | ||
| 2 spectra, TLVEDLFADK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.352 | 0.648 | ||
| 2 spectra, TLNLCK | 0.000 | 0.000 | 0.000 | 0.189 | 0.000 | 0.000 | 0.309 | 0.502 | ||
| 1 spectrum, NALLQLTDSQIADVAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.282 | 0.718 | ||
| 4 spectra, EGSASTEVLR | 0.000 | 0.000 | 0.000 | 0.047 | 0.000 | 0.000 | 0.375 | 0.578 | ||
| 3 spectra, TNVALMCMLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.307 | 0.586 | ||
| 1 spectrum, FQIMNEIVYEK | 0.049 | 0.000 | 0.027 | 0.000 | 0.241 | 0.000 | 0.355 | 0.328 | ||
| 2 spectra, TYTQLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | 0.275 | 0.559 | ||
| 3 spectra, MEADPELSK | 0.036 | 0.000 | 0.000 | 0.058 | 0.128 | 0.000 | 0.450 | 0.329 | ||
| 2 spectra, GPVLEALVAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.418 | 0.582 | ||
| 2 spectra, YAQAGFEGFK | 0.000 | 0.000 | 0.000 | 0.070 | 0.000 | 0.000 | 0.347 | 0.583 | ||
| 1 spectrum, VPIPVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.011 | 0.000 | 0.319 | 0.669 | ||
| 1 spectrum, DEPTGEVLSLVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.051 | 0.000 | 0.367 | 0.582 | ||
| 2 spectra, FNDPHVK | 0.000 | 0.000 | 0.000 | 0.035 | 0.026 | 0.000 | 0.289 | 0.650 | ||
| 2 spectra, GDPLLDQR | 0.000 | 0.000 | 0.000 | 0.100 | 0.012 | 0.000 | 0.373 | 0.515 | ||
| 4 spectra, DIDAFWLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.313 | 0.687 | ||
| 2 spectra, HHEDNLLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.473 | 0.221 | ||
| 2 spectra, HLILPEK | 0.000 | 0.000 | 0.000 | 0.325 | 0.000 | 0.000 | 0.379 | 0.296 | ||
| 4 spectra, LIVLDEIHLLHDDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.334 | 0.666 | ||
| 1 spectrum, ESIEEPSAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.273 | 0.727 | ||
| 2 spectra, YVHLFPK | 0.183 | 0.000 | 0.000 | 0.172 | 0.072 | 0.000 | 0.275 | 0.297 | ||
| 1 spectrum, SNSLISIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.208 | 0.000 | 0.354 | 0.437 | ||
| 1 spectrum, DLLPYGFAIHHAGMTR | 0.043 | 0.000 | 0.000 | 0.073 | 0.000 | 0.389 | 0.302 | 0.192 | ||
| 2 spectra, LYDLNHNEIGELIR | 0.000 | 0.000 | 0.000 | 0.075 | 0.014 | 0.000 | 0.283 | 0.628 | ||
| 5 spectra, KPVIVFVPSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.320 | 0.680 | ||
| 2 spectra, MLLQNSEGR | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.000 | 0.319 | 0.573 | ||
| 2 spectra, ADEVLEILK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.285 | 0.715 | ||
| 2 spectra, EEGWWVVIGDAK | 0.000 | 0.000 | 0.000 | 0.048 | 0.041 | 0.000 | 0.459 | 0.452 | ||
| 1 spectrum, EIDLLLGQTDDTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.285 | 0.715 | ||
| 2 spectra, YISSQIERPIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.247 | 0.000 | 0.326 | 0.428 | ||
| 3 spectra, YHVLVNLGK | 0.000 | 0.000 | 0.000 | 0.382 | 0.000 | 0.000 | 0.345 | 0.273 | ||
| 1 spectrum, VFSLSSEFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.167 | 0.216 | 0.514 | 0.103 | ||
| 3 spectra, NIEMTQEDVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.239 | 0.188 | 0.372 | 0.201 | ||
| 1 spectrum, NQVLVFVHSR | 0.000 | 0.000 | 0.000 | 0.215 | 0.125 | 0.077 | 0.441 | 0.142 | ||
| 3 spectra, WDILSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | 0.351 | 0.599 | ||
| 1 spectrum, WLSCETQLPVSFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.033 | 0.000 | 0.274 | 0.693 | ||
| 1 spectrum, SLQYEYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.142 | 0.000 | 0.405 | 0.453 | ||
| 2 spectra, TGNFQVTELGR | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.263 | 0.598 | ||
| 2 spectra, TICAEFAILR | 0.000 | 0.000 | 0.000 | 0.039 | 0.013 | 0.000 | 0.326 | 0.622 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
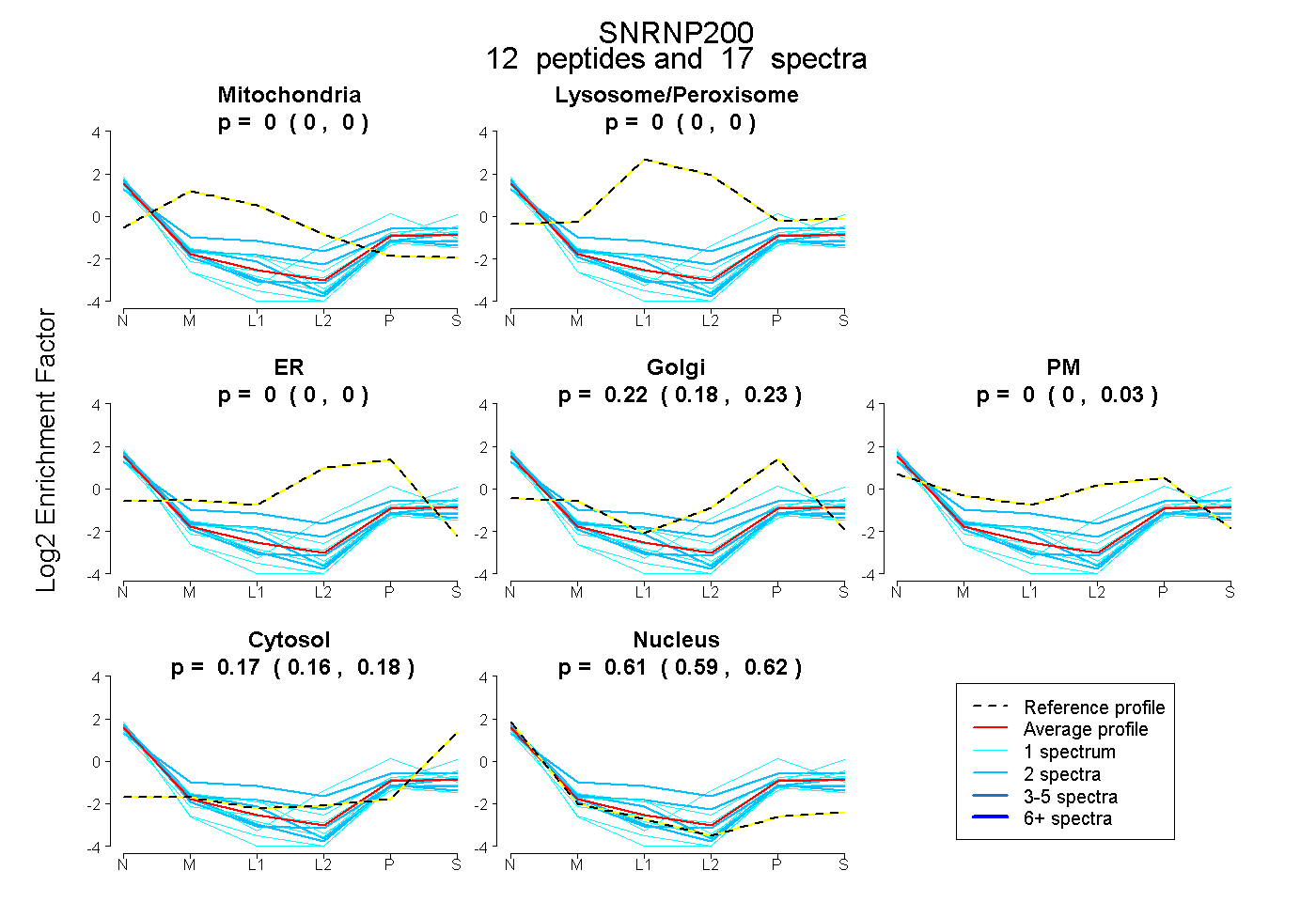 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.217 0.182 | 0.225 |
0.000 0.000 | 0.034 |
0.172 0.161 | 0.182 |
0.611 0.594 | 0.622 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7 spectra |
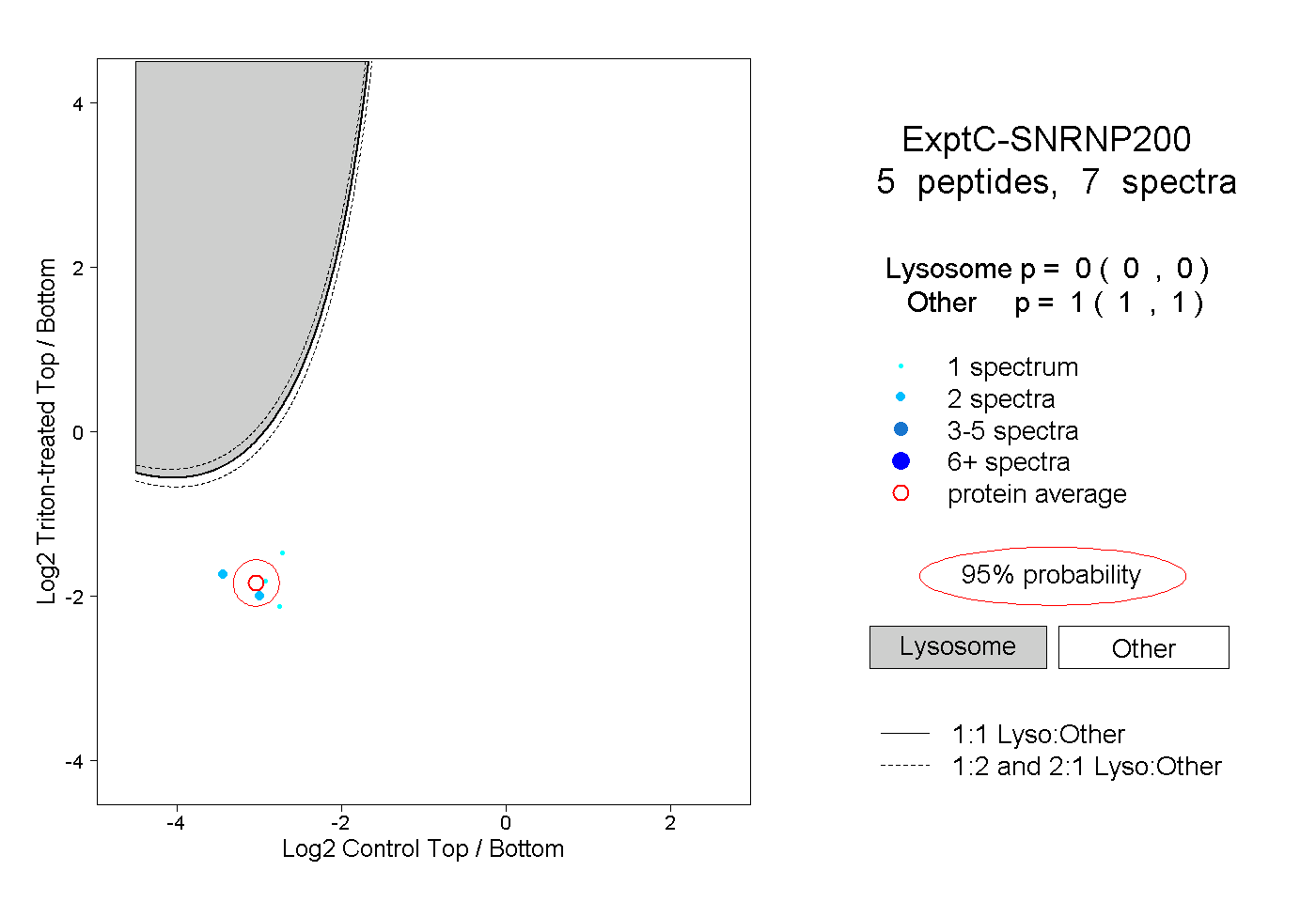 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
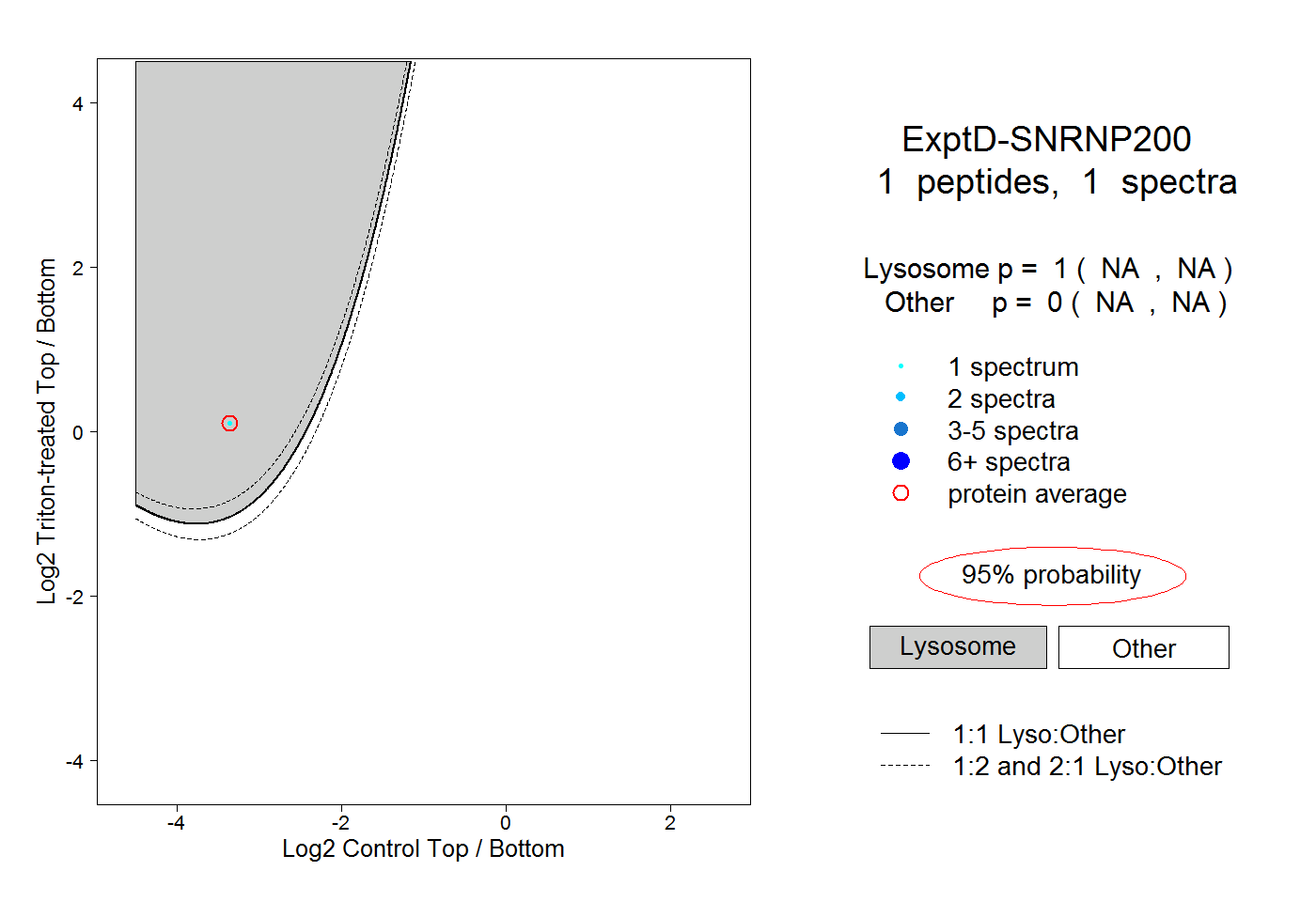 |
1.000 NA | NA |
0.000 NA | NA |