peptides
spectra
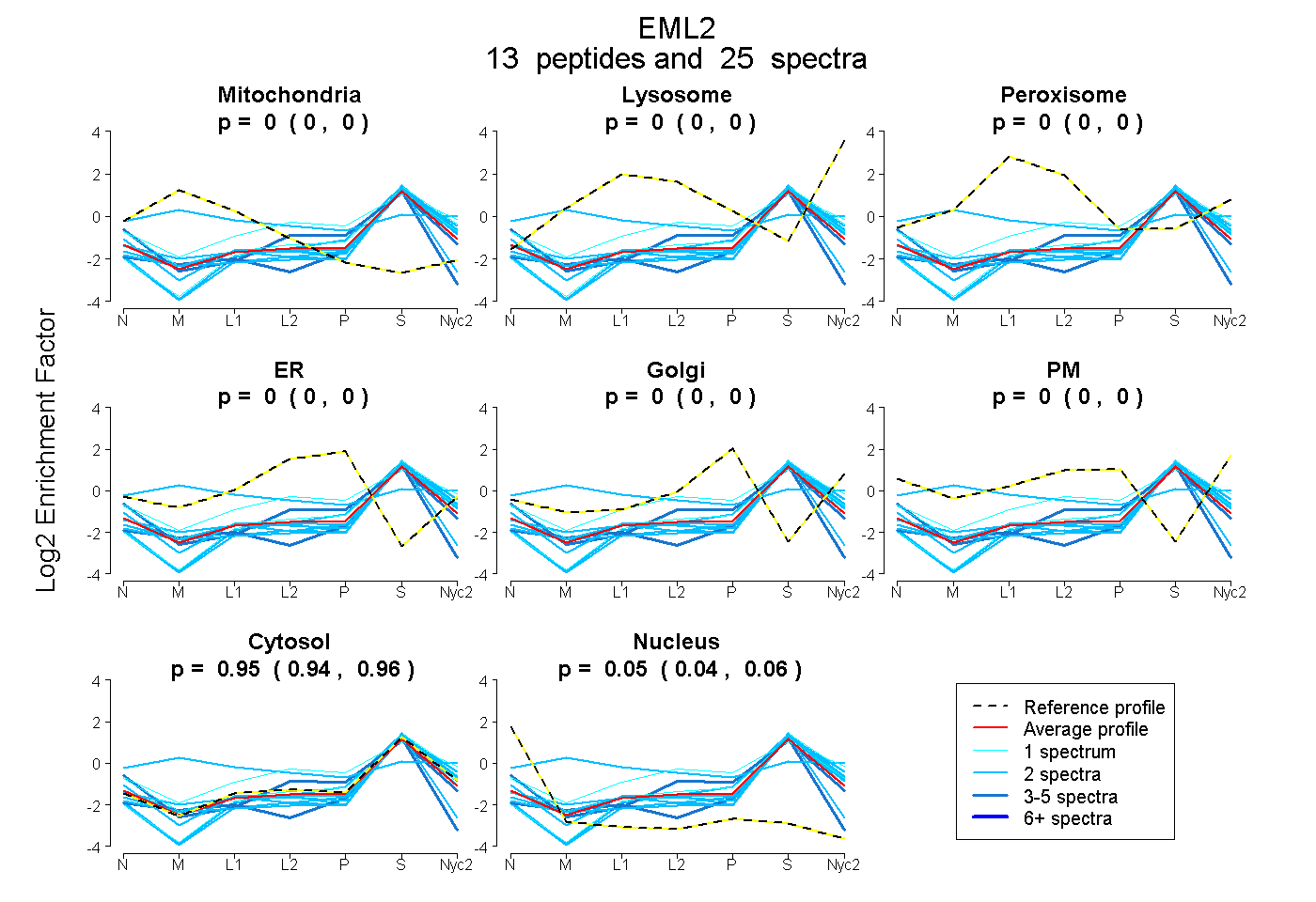
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.937 | 0.957
0.040 | 0.060
peptides
spectra
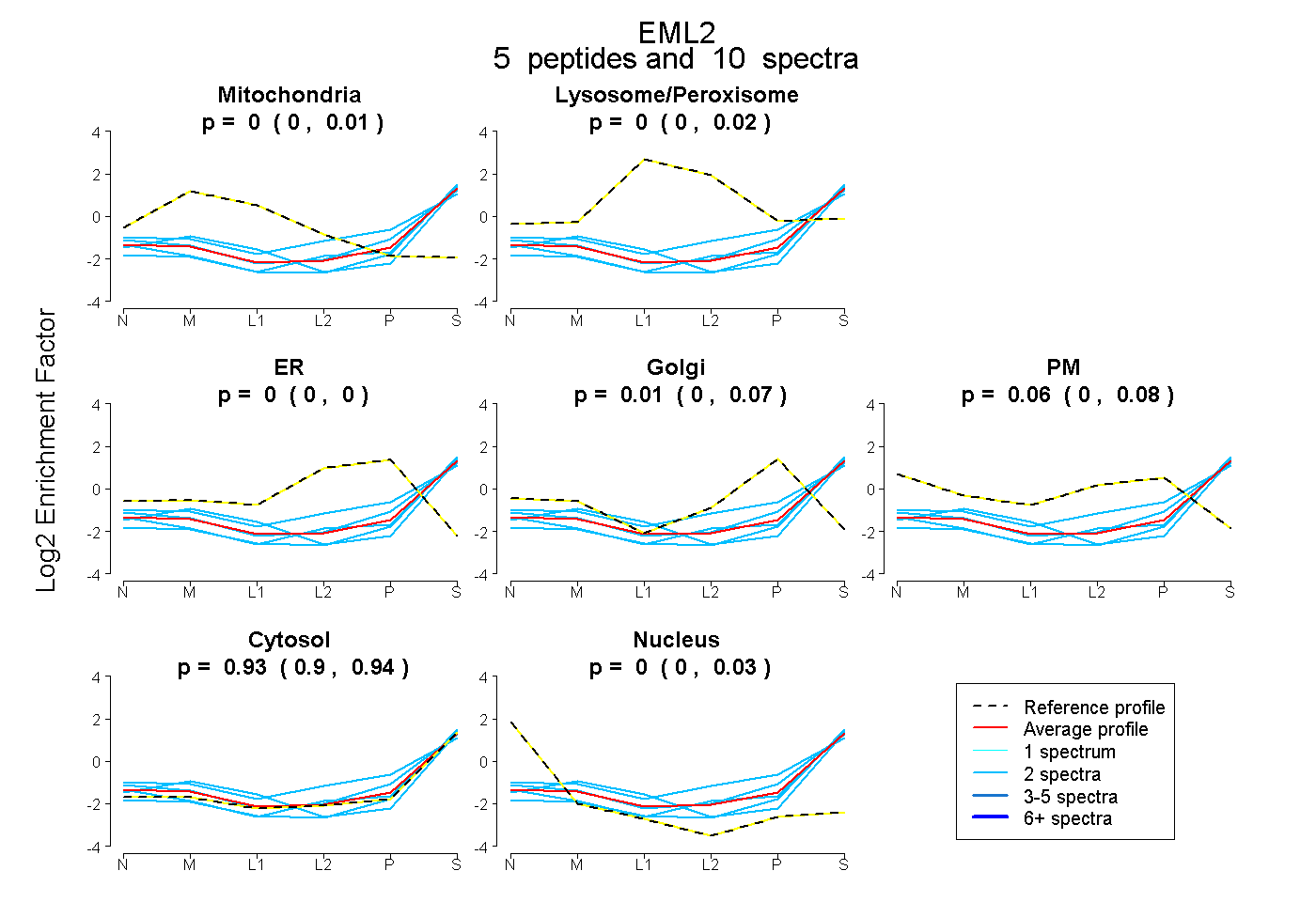
0.000 | 0.012
0.000 | 0.019
0.000 | 0.000
0.000 | 0.069
0.000 | 0.077
0.900 | 0.937
0.000 | 0.027
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.948 0.937 | 0.957 |
0.052 0.040 | 0.060 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
 |
0.000 0.000 | 0.012 |
0.000 0.000 | 0.019 |
0.000 0.000 | 0.000 |
0.009 0.000 | 0.069 |
0.062 0.000 | 0.077 |
0.927 0.900 | 0.937 |
0.003 0.000 | 0.027 |
| 2 spectra, DGTLVSGGGR | 0.000 | 0.000 | 0.000 | 0.117 | 0.033 | 0.850 | 0.000 | |||
| 2 spectra, SELPSSR | 0.000 | 0.125 | 0.000 | 0.181 | 0.020 | 0.674 | 0.000 | |||
| 2 spectra, GDTLYVGTTR | 0.000 | 0.000 | 0.000 | 0.007 | 0.000 | 0.964 | 0.029 | |||
| 2 spectra, QITSADTVR | 0.123 | 0.000 | 0.000 | 0.000 | 0.000 | 0.877 | 0.000 | |||
| 2 spectra, ITQEVLGAHDGGVFALCALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.996 | 0.004 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
27 spectra |
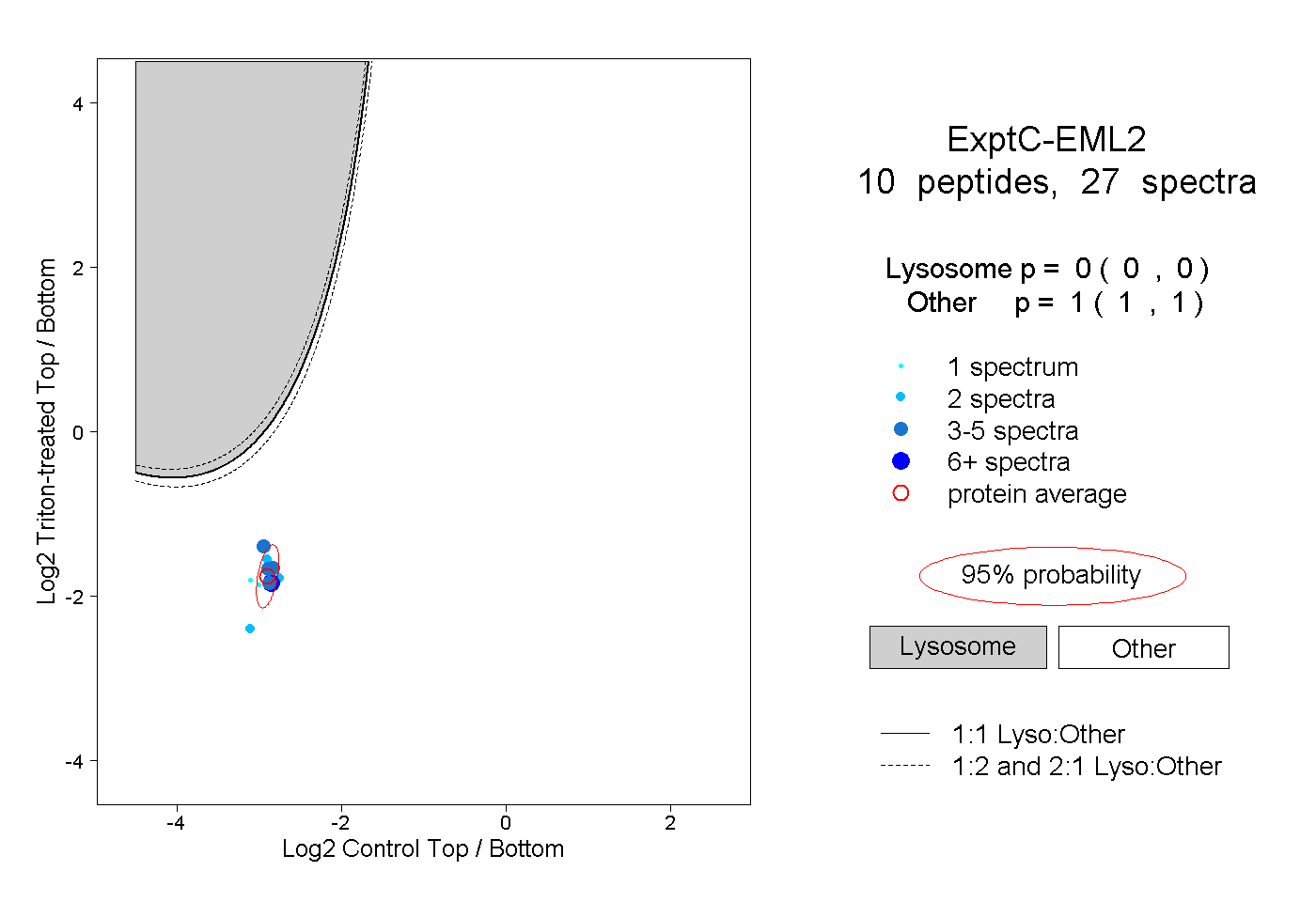 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
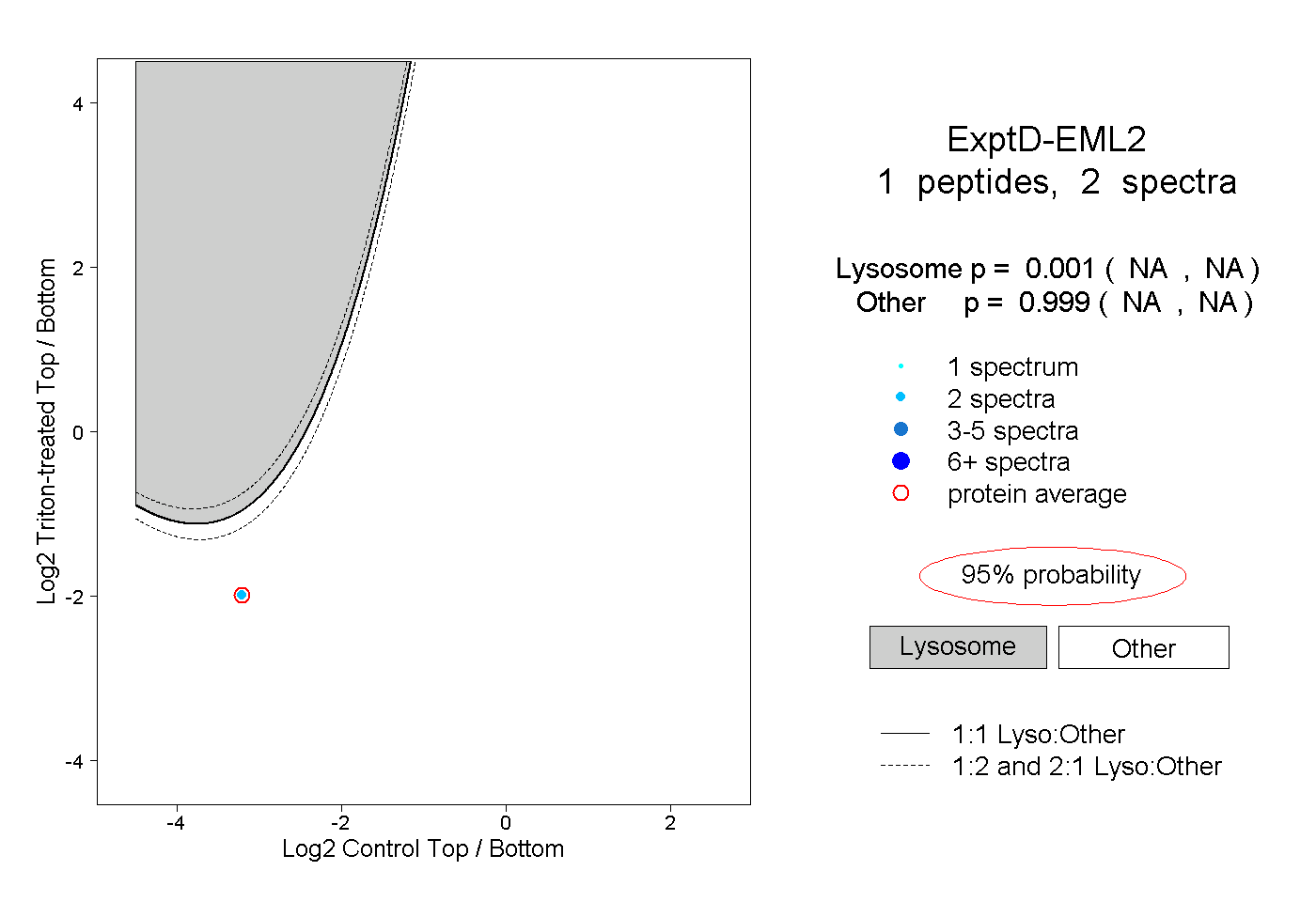 |
0.001 NA | NA |
0.999 NA | NA |